peptides
spectra
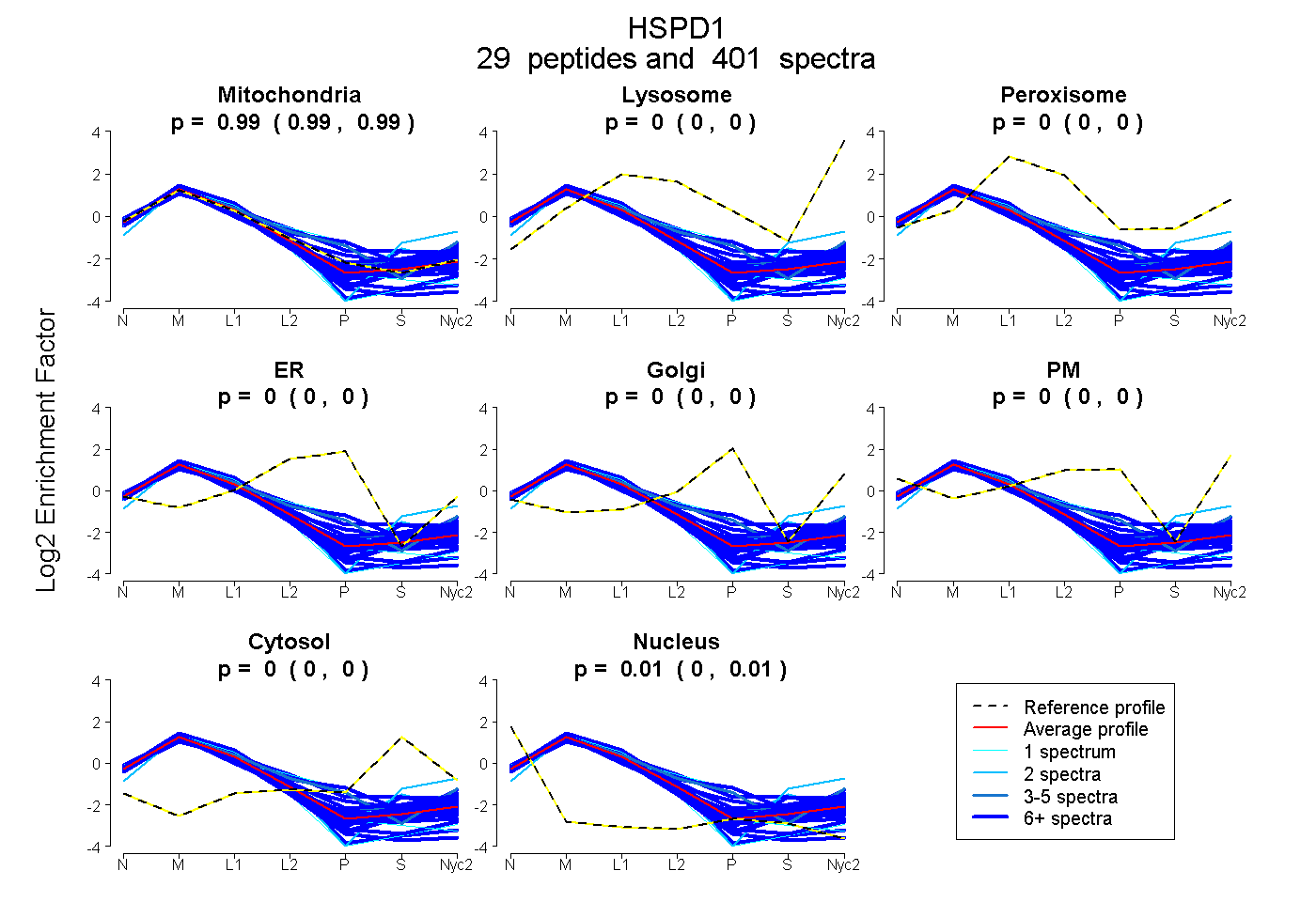
0.990 | 0.992
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.002 | 0.005
0.004 | 0.006
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
401 spectra |
 |
0.991 0.990 | 0.992 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.004 0.002 | 0.005 |
0.005 0.004 | 0.006 |
| 10 spectra, VGEVIVTK | 0.867 | 0.041 | 0.016 | 0.000 | 0.000 | 0.000 | 0.076 | 0.000 | ||
| 24 spectra, TLNDELEIIEGMK | 0.969 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.031 | ||
| 8 spectra, IGIEIIK | 0.930 | 0.058 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.012 | ||
| 1 spectrum, DMAIATGGAVFGEEGLNLNLEDVQAHDLGK | 0.957 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.043 | ||
| 5 spectra, TVIIEQSWGSPK | 0.809 | 0.047 | 0.000 | 0.004 | 0.030 | 0.110 | 0.000 | 0.000 | ||
| 11 spectra, CEFQDAYVLLSEK | 0.942 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.058 | ||
| 10 spectra, LSDGVAVLK | 0.972 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.028 | ||
| 13 spectra, IPAMTIAK | 0.973 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.027 | ||
| 9 spectra, ISSVQSIVPALEIANAHR | 0.772 | 0.004 | 0.069 | 0.000 | 0.155 | 0.000 | 0.000 | 0.000 | ||
| 29 spectra, APGFGDNR | 0.884 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.116 | 0.000 | ||
| 11 spectra, DGVTVAK | 0.976 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.024 | ||
| 13 spectra, DIGNIISDAMK | 0.745 | 0.000 | 0.145 | 0.008 | 0.000 | 0.000 | 0.102 | 0.000 | ||
| 39 spectra, GANPVEIR | 0.964 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.036 | ||
| 1 spectrum, IQEITEQLDITTSEYEK | 0.807 | 0.000 | 0.027 | 0.146 | 0.000 | 0.000 | 0.020 | 0.000 | ||
| 1 spectrum, KPLVIIAEDVDGEALSTLVLNR | 0.965 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.035 | ||
| 6 spectra, AAVEEGIVLGGGCALLR | 0.940 | 0.000 | 0.006 | 0.000 | 0.000 | 0.000 | 0.053 | 0.000 | ||
| 15 spectra, GYISPYFINTSK | 0.991 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.009 | ||
| 19 spectra, VGLQVVAVK | 0.976 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.024 | 0.000 | ||
| 12 spectra, GIIDPTK | 0.994 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.006 | ||
| 2 spectra, DPGMGAMGGMGGGVGGGMF | 0.798 | 0.072 | 0.000 | 0.000 | 0.000 | 0.000 | 0.129 | 0.000 | ||
| 10 spectra, NAGVEGSLIVEK | 0.947 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.053 | 0.000 | ||
| 11 spectra, ALMLQGVDLLADAVAVTMGPK | 0.974 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.026 | ||
| 5 spectra, GVITVK | 0.874 | 0.060 | 0.023 | 0.000 | 0.000 | 0.000 | 0.043 | 0.000 | ||
| 15 spectra, GVMLAVDAVIAELK | 0.973 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.027 | ||
| 2 spectra, CIPALDSLKPANEDQK | 0.888 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.112 | 0.000 | ||
| 27 spectra, DDAMLLK | 0.972 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.028 | ||
| 59 spectra, VTDALNATR | 0.920 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.080 | 0.000 | ||
| 13 spectra, VGGTSDVEVNEK | 0.967 | 0.007 | 0.000 | 0.000 | 0.000 | 0.000 | 0.025 | 0.000 | ||
| 20 spectra, FGADAR | 0.911 | 0.000 | 0.009 | 0.000 | 0.000 | 0.000 | 0.080 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
221 spectra |
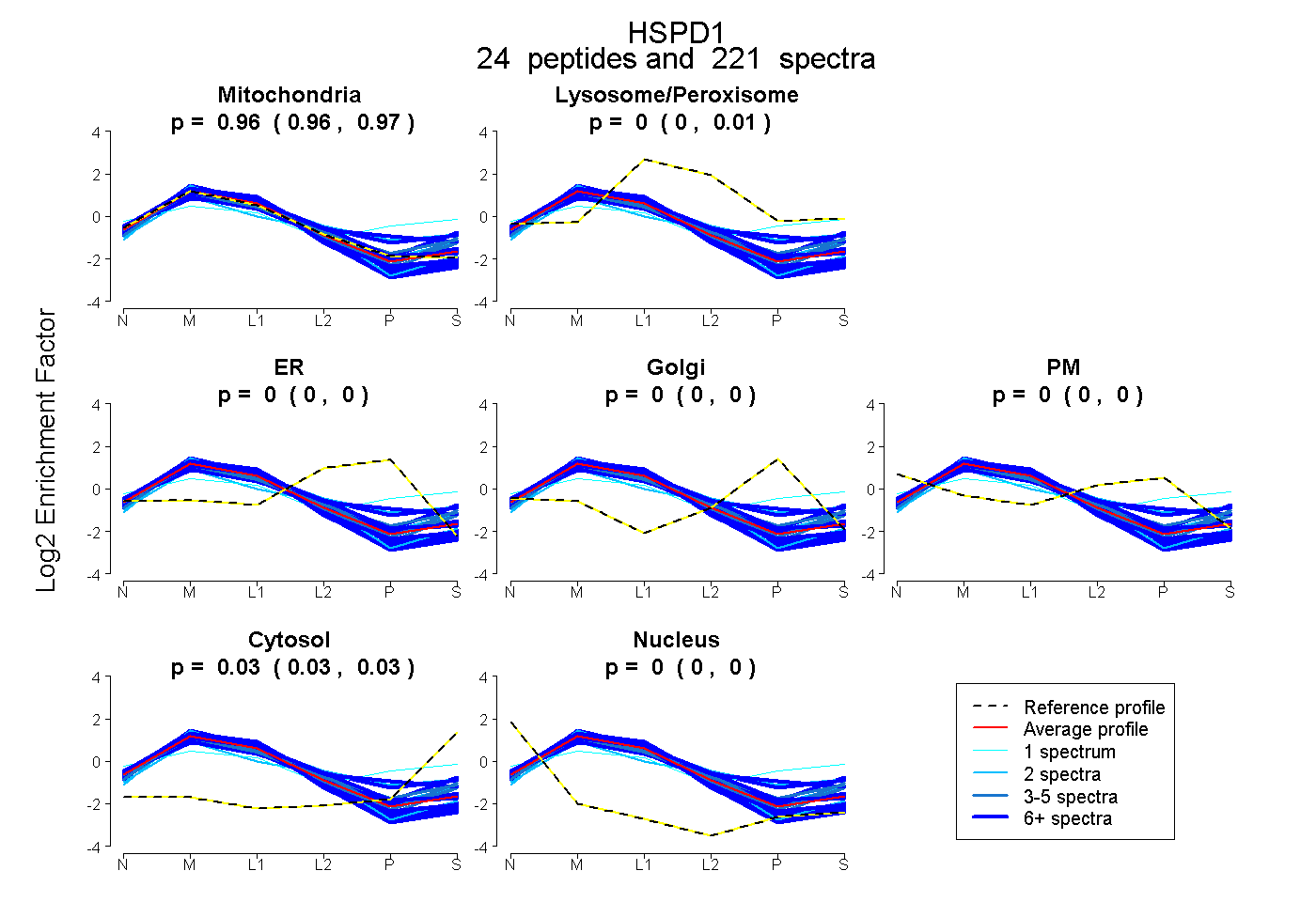 |
0.963 0.960 | 0.966 |
0.005 0.003 | 0.006 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.032 0.030 | 0.033 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1779 spectra |
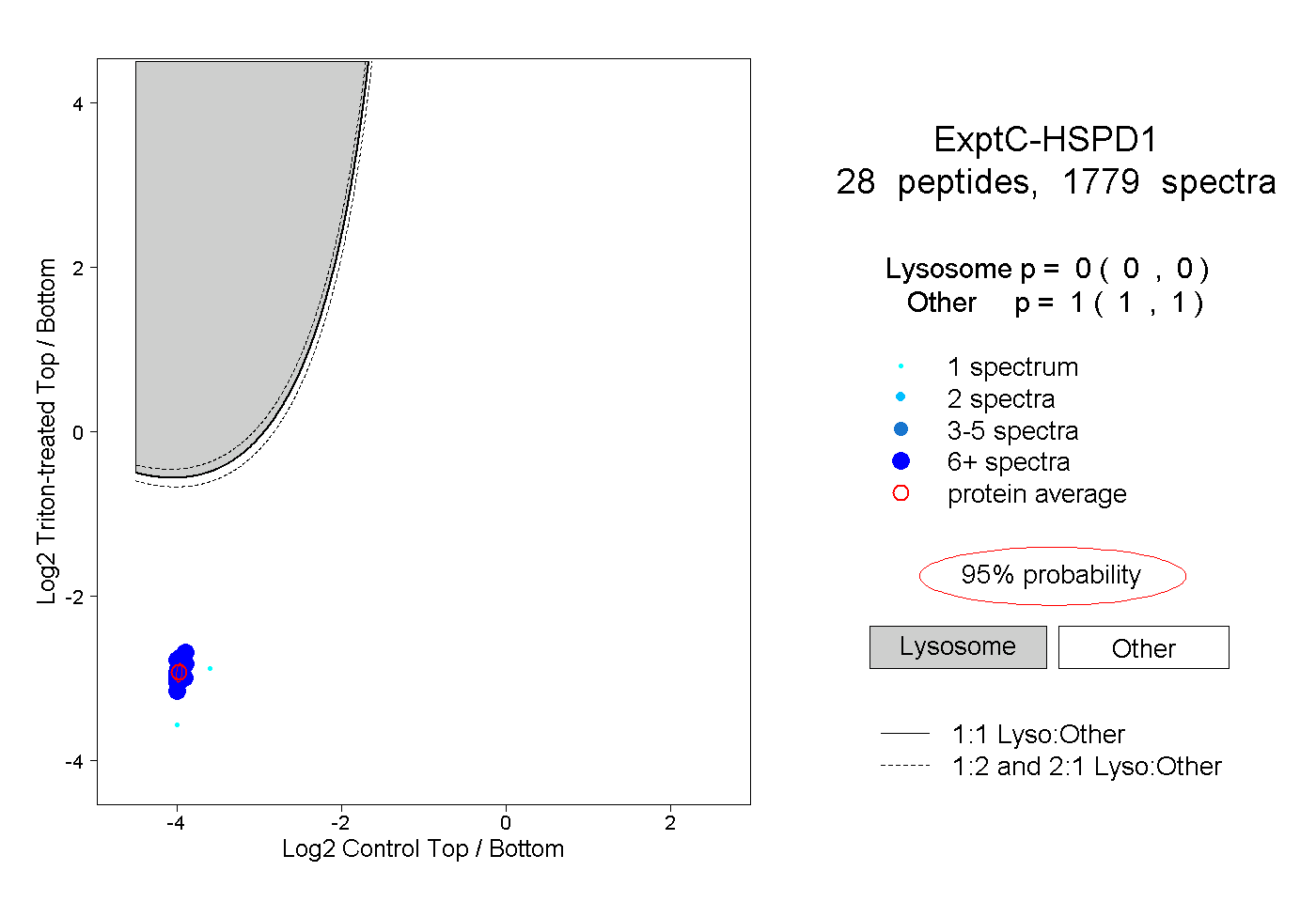 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
121 spectra |
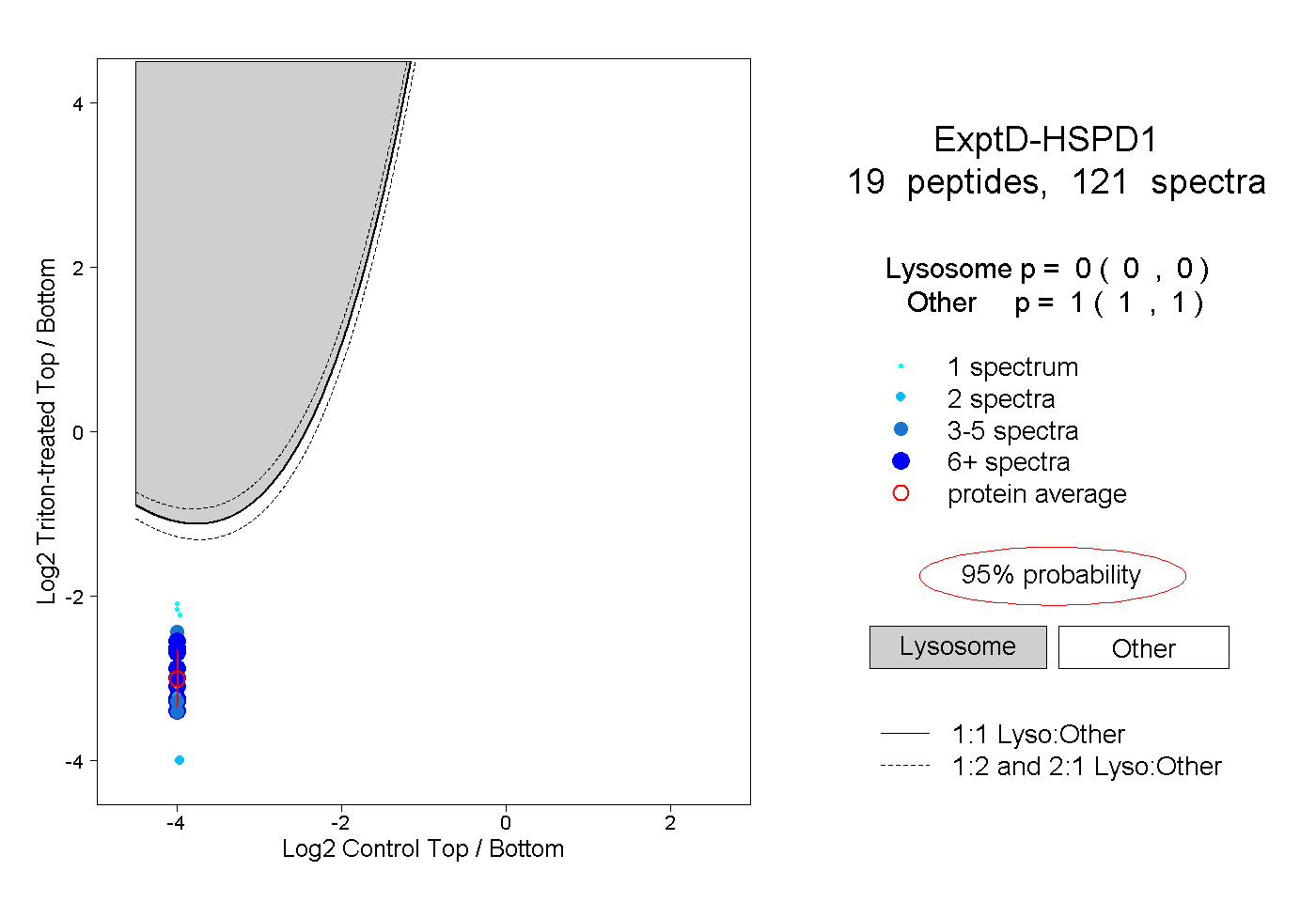 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |