peptides
spectra
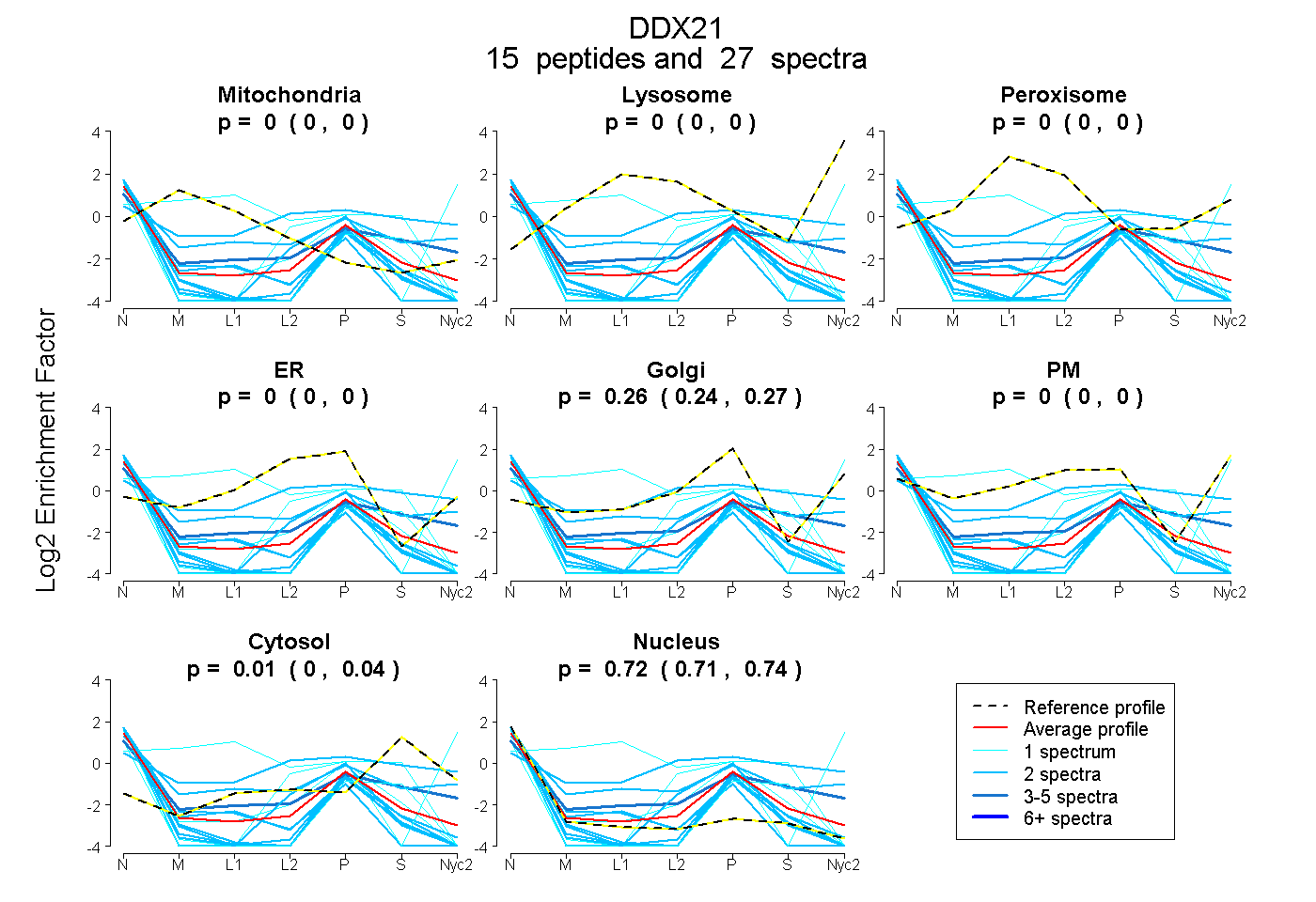
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.240 | 0.274
0.000 | 0.000
0.000 | 0.035
0.707 | 0.740
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
27 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.261 0.240 | 0.274 |
0.000 0.000 | 0.000 |
0.015 0.000 | 0.035 |
0.724 0.707 | 0.740 |
| 1 spectrum, STYEQVDLIGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.144 | 0.856 | ||
| 2 spectra, SGIDILVGTPGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.037 | 0.000 | 0.000 | 0.963 | ||
| 4 spectra, GVNFLFPIQAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.252 | 0.028 | 0.263 | 0.457 | ||
| 1 spectrum, DFSDITK | 0.000 | 0.000 | 0.000 | 0.234 | 0.000 | 0.000 | 0.026 | 0.741 | ||
| 2 spectra, EGAFSNFPISEETVK | 0.000 | 0.000 | 0.000 | 0.126 | 0.000 | 0.000 | 0.000 | 0.874 | ||
| 2 spectra, AAVIGDVIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.053 | 0.000 | 0.000 | 0.947 | ||
| 2 spectra, TFSFAIPLIEK | 0.000 | 0.000 | 0.000 | 0.214 | 0.000 | 0.000 | 0.000 | 0.786 | ||
| 2 spectra, GQRPGGGNK | 0.000 | 0.000 | 0.000 | 0.000 | 0.038 | 0.000 | 0.000 | 0.962 | ||
| 1 spectrum, NGNFGVLVATNVAAR | 0.272 | 0.043 | 0.000 | 0.000 | 0.000 | 0.685 | 0.000 | 0.000 | ||
| 2 spectra, GPSEDDVGPPK | 0.000 | 0.000 | 0.025 | 0.186 | 0.000 | 0.311 | 0.427 | 0.052 | ||
| 1 spectrum, DVESYIHR | 0.000 | 0.000 | 0.000 | 0.084 | 0.000 | 0.000 | 0.392 | 0.524 | ||
| 2 spectra, IGVPSATEIIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.179 | 0.000 | 0.000 | 0.821 | ||
| 1 spectrum, AAITVEHLAIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.029 | 0.000 | 0.000 | 0.971 | ||
| 2 spectra, QDAQSLHGDIPQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.089 | 0.358 | 0.198 | 0.355 | ||
| 2 spectra, APQVLVLAPTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.047 | 0.000 | 0.000 | 0.953 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
6 spectra |
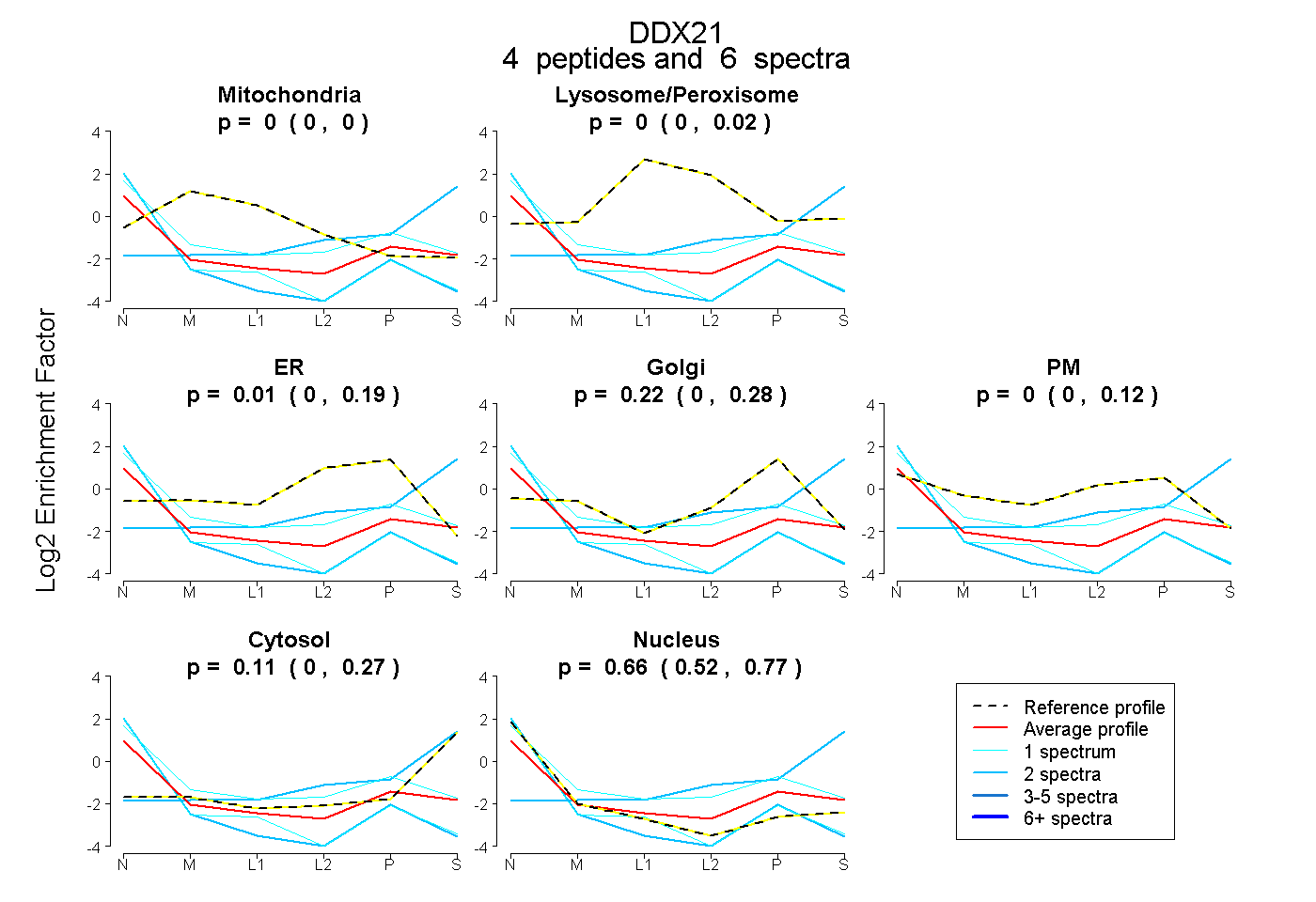 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.022 |
0.012 0.000 | 0.191 |
0.217 0.000 | 0.275 |
0.000 0.000 | 0.123 |
0.112 0.000 | 0.270 |
0.659 0.521 | 0.768 |