peptides
spectra
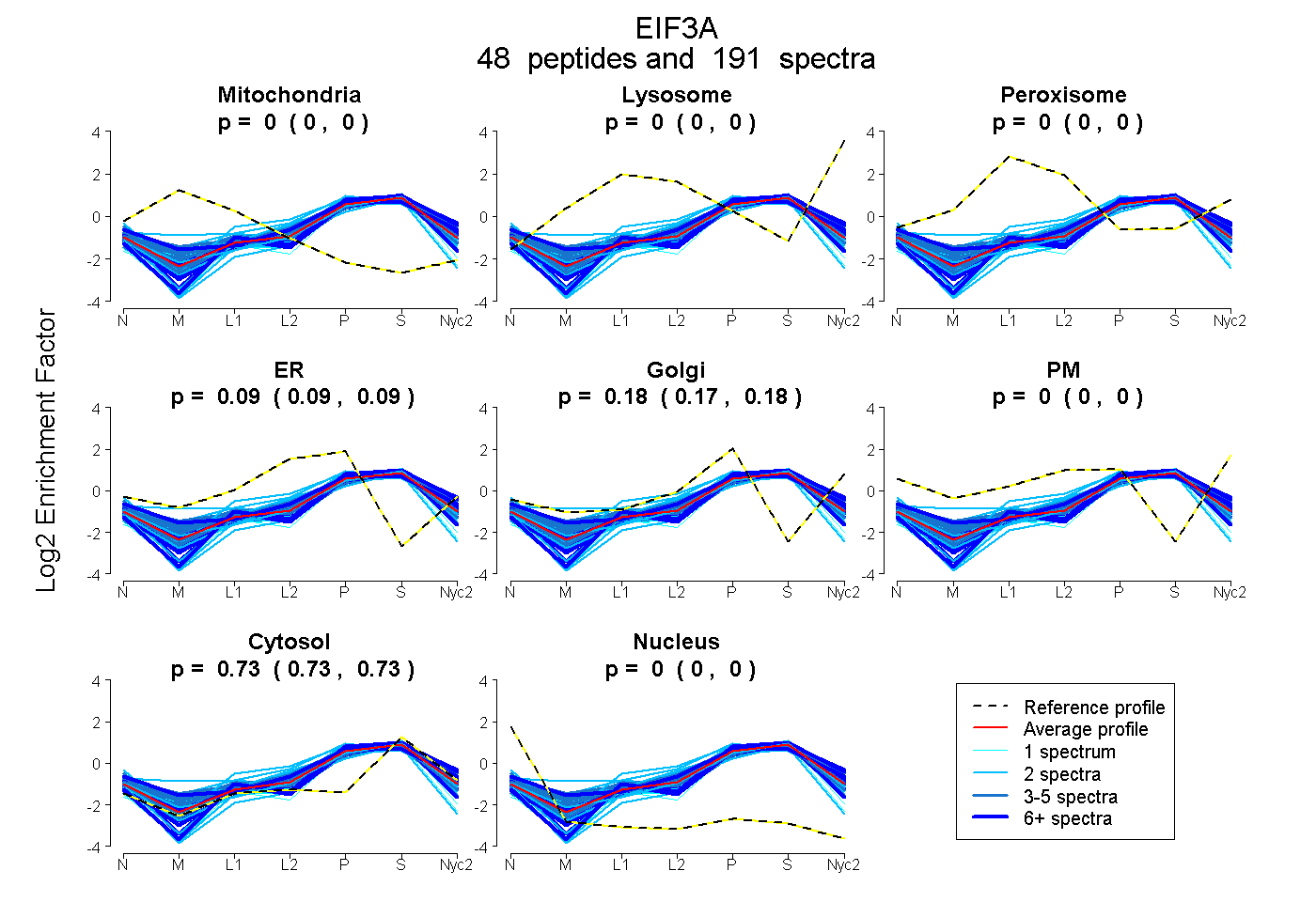
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.089 | 0.095
0.175 | 0.181
0.000 | 0.000
0.729 | 0.731
0.000 | 0.000
peptides
spectra
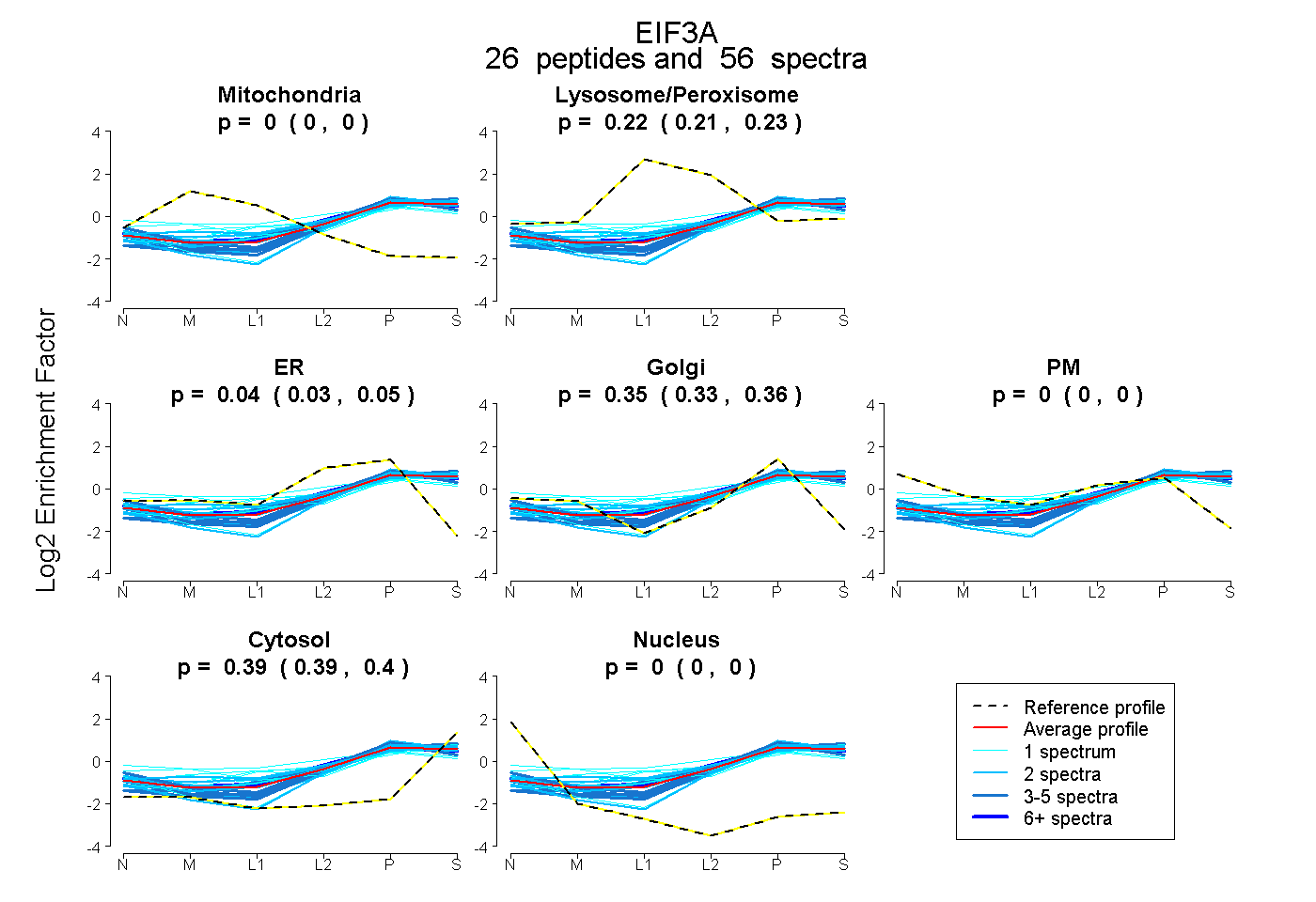
0.000 | 0.000
0.213 | 0.227
0.027 | 0.054
0.333 | 0.355
0.000 | 0.000
0.388 | 0.397
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
191 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.092 0.089 | 0.095 |
0.178 0.175 | 0.181 |
0.000 0.000 | 0.000 |
0.730 0.729 | 0.731 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
56 spectra |
 |
0.000 0.000 | 0.000 |
0.220 0.213 | 0.227 |
0.041 0.027 | 0.054 |
0.345 0.333 | 0.355 |
0.000 0.000 | 0.000 |
0.393 0.388 | 0.397 |
0.000 0.000 | 0.000 |
| 2 spectra, QVEQLEK | 0.000 | 0.293 | 0.000 | 0.377 | 0.000 | 0.330 | 0.000 | |||
| 1 spectrum, SAYEEQR | 0.000 | 0.000 | 0.246 | 0.281 | 0.000 | 0.473 | 0.000 | |||
| 1 spectrum, ITTMQLER | 0.000 | 0.357 | 0.000 | 0.225 | 0.000 | 0.418 | 0.000 | |||
| 1 spectrum, FCLQYTR | 0.000 | 0.317 | 0.000 | 0.275 | 0.000 | 0.408 | 0.000 | |||
| 4 spectra, LEEIPLIK | 0.000 | 0.083 | 0.286 | 0.190 | 0.000 | 0.442 | 0.000 | |||
| 2 spectra, FLWESYR | 0.000 | 0.140 | 0.084 | 0.321 | 0.000 | 0.454 | 0.000 | |||
| 5 spectra, IGLINDMVR | 0.000 | 0.027 | 0.411 | 0.000 | 0.000 | 0.562 | 0.000 | |||
| 1 spectrum, QPALDVLYDVMK | 0.000 | 0.356 | 0.000 | 0.287 | 0.000 | 0.357 | 0.000 | |||
| 2 spectra, VSTVFWK | 0.000 | 0.318 | 0.000 | 0.350 | 0.000 | 0.332 | 0.000 | |||
| 1 spectrum, LYHLSR | 0.000 | 0.407 | 0.000 | 0.365 | 0.000 | 0.228 | 0.000 | |||
| 3 spectra, LLLTPWVK | 0.000 | 0.248 | 0.052 | 0.320 | 0.000 | 0.380 | 0.000 | |||
| 1 spectrum, NLTQDEMQR | 0.000 | 0.236 | 0.065 | 0.254 | 0.000 | 0.446 | 0.000 | |||
| 6 spectra, FNVLQYVVPEVK | 0.000 | 0.246 | 0.070 | 0.326 | 0.000 | 0.359 | 0.000 | |||
| 1 spectrum, AVEDIHGLFSLSK | 0.000 | 0.189 | 0.147 | 0.255 | 0.000 | 0.409 | 0.000 | |||
| 2 spectra, NICQQVNIK | 0.000 | 0.259 | 0.000 | 0.334 | 0.000 | 0.407 | 0.000 | |||
| 4 spectra, LLDMDGIIVEK | 0.000 | 0.000 | 0.423 | 0.000 | 0.000 | 0.577 | 0.000 | |||
| 2 spectra, AIVDAAR | 0.000 | 0.236 | 0.000 | 0.406 | 0.000 | 0.358 | 0.000 | |||
| 1 spectrum, QCLDLLR | 0.000 | 0.217 | 0.000 | 0.313 | 0.176 | 0.294 | 0.000 | |||
| 2 spectra, ILQEHEQIK | 0.000 | 0.259 | 0.000 | 0.320 | 0.000 | 0.420 | 0.000 | |||
| 2 spectra, VLNWVR | 0.000 | 0.192 | 0.139 | 0.248 | 0.000 | 0.421 | 0.000 | |||
| 2 spectra, GLDDDRPPR | 0.000 | 0.054 | 0.239 | 0.241 | 0.000 | 0.466 | 0.000 | |||
| 1 spectrum, LGGDDEER | 0.000 | 0.224 | 0.117 | 0.236 | 0.000 | 0.424 | 0.000 | |||
| 2 spectra, TLSFGSDLNYATR | 0.000 | 0.000 | 0.245 | 0.238 | 0.000 | 0.517 | 0.000 | |||
| 4 spectra, SLEDVVR | 0.000 | 0.178 | 0.067 | 0.432 | 0.000 | 0.322 | 0.000 | |||
| 2 spectra, LESLNIQR | 0.000 | 0.222 | 0.066 | 0.314 | 0.000 | 0.398 | 0.000 | |||
| 1 spectrum, LGEDPLSR | 0.000 | 0.264 | 0.000 | 0.435 | 0.000 | 0.300 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
108 spectra |
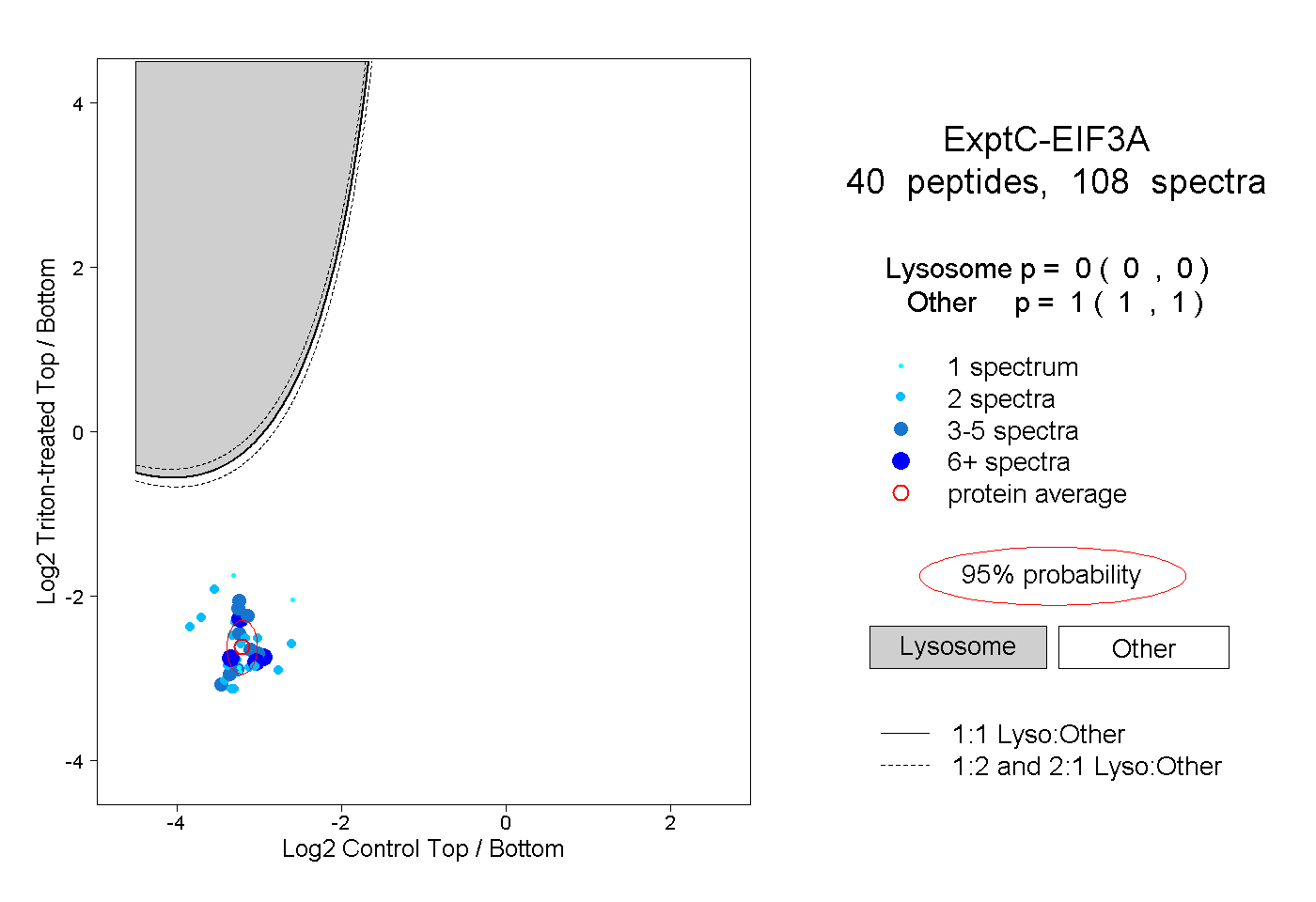 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
23 spectra |
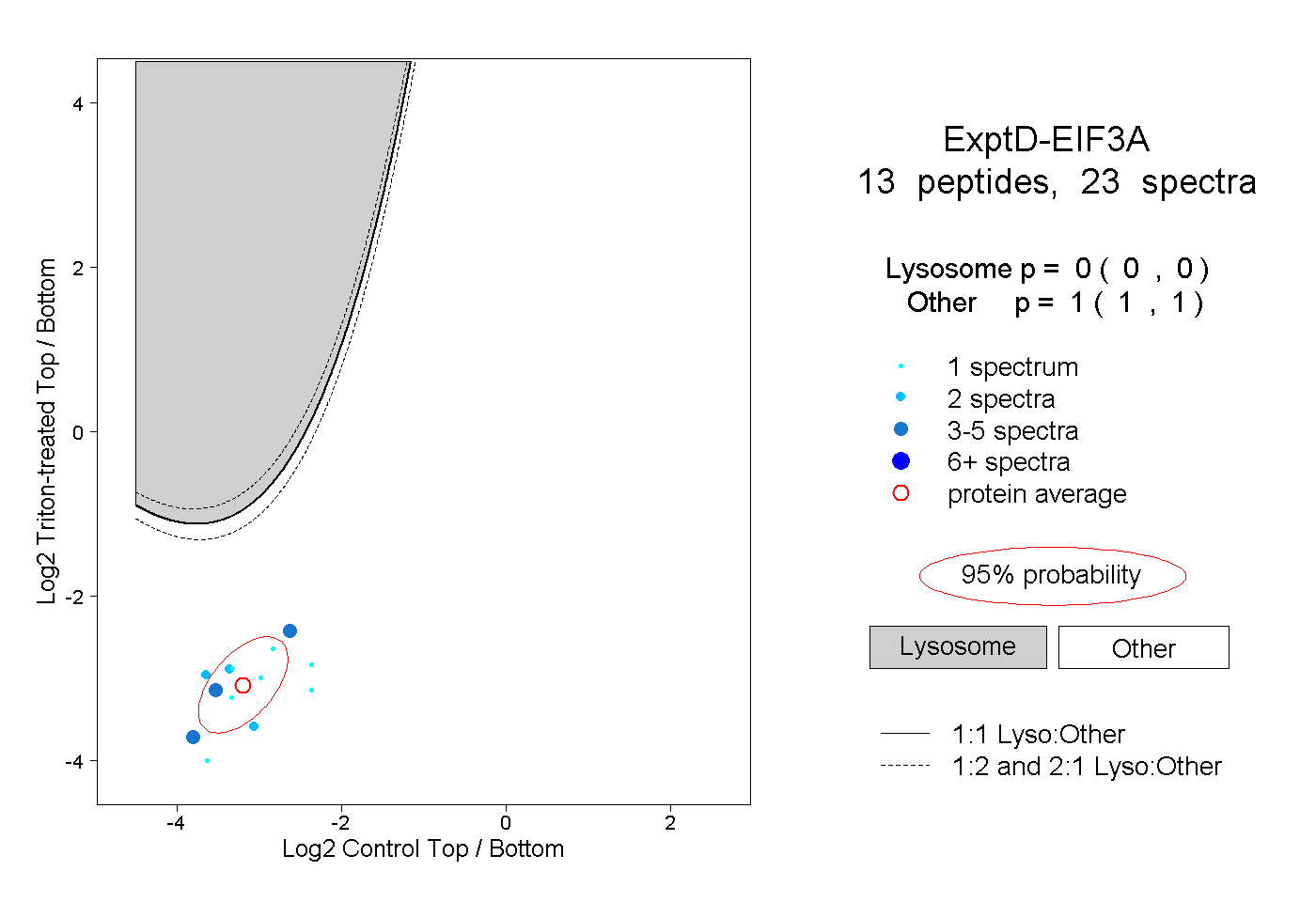 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |