peptides
spectra
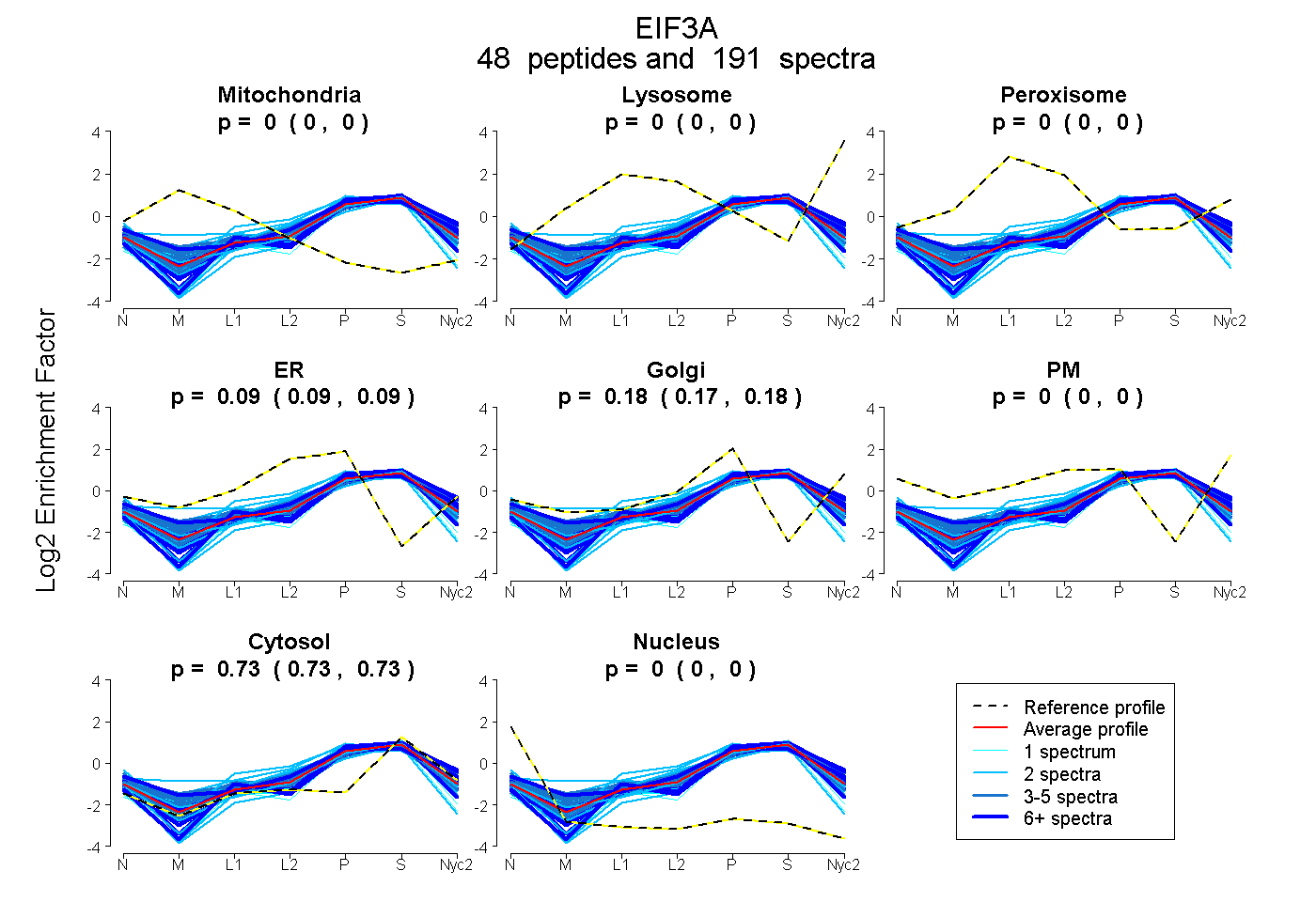
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.089 | 0.095
0.175 | 0.181
0.000 | 0.000
0.729 | 0.731
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
191 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.092 0.089 | 0.095 |
0.178 0.175 | 0.181 |
0.000 0.000 | 0.000 |
0.730 0.729 | 0.731 |
0.000 0.000 | 0.000 |
| 5 spectra, QVEQLEK | 0.000 | 0.000 | 0.000 | 0.157 | 0.114 | 0.000 | 0.729 | 0.000 | ||
| 5 spectra, SAYEEQR | 0.000 | 0.000 | 0.000 | 0.051 | 0.214 | 0.000 | 0.735 | 0.000 | ||
| 1 spectrum, DDERPHR | 0.000 | 0.000 | 0.000 | 0.011 | 0.132 | 0.000 | 0.838 | 0.020 | ||
| 3 spectra, EDAPIGPHLQSMPSEQIR | 0.000 | 0.000 | 0.000 | 0.123 | 0.174 | 0.000 | 0.703 | 0.000 | ||
| 28 spectra, MHLSQIQR | 0.000 | 0.000 | 0.000 | 0.078 | 0.104 | 0.000 | 0.818 | 0.000 | ||
| 2 spectra, IHEPIMLK | 0.000 | 0.000 | 0.000 | 0.235 | 0.017 | 0.000 | 0.749 | 0.000 | ||
| 4 spectra, ANEFLEVGK | 0.000 | 0.000 | 0.000 | 0.069 | 0.162 | 0.000 | 0.768 | 0.000 | ||
| 3 spectra, IDYFER | 0.000 | 0.000 | 0.000 | 0.102 | 0.129 | 0.000 | 0.769 | 0.000 | ||
| 2 spectra, VSTVFWK | 0.000 | 0.000 | 0.000 | 0.050 | 0.203 | 0.000 | 0.746 | 0.000 | ||
| 5 spectra, LLLTPWVK | 0.000 | 0.000 | 0.000 | 0.287 | 0.000 | 0.000 | 0.713 | 0.000 | ||
| 7 spectra, NLTQDEMQR | 0.000 | 0.000 | 0.000 | 0.102 | 0.190 | 0.000 | 0.707 | 0.000 | ||
| 1 spectrum, LVQLDSAISMELWQEAFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.336 | 0.000 | 0.664 | 0.000 | ||
| 4 spectra, FNVLQYVVPEVK | 0.000 | 0.000 | 0.000 | 0.114 | 0.209 | 0.000 | 0.677 | 0.000 | ||
| 4 spectra, DLFVMR | 0.000 | 0.000 | 0.000 | 0.062 | 0.118 | 0.000 | 0.820 | 0.000 | ||
| 2 spectra, NICQQVNIK | 0.000 | 0.000 | 0.000 | 0.390 | 0.000 | 0.000 | 0.610 | 0.000 | ||
| 7 spectra, LLDMDGIIVEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.240 | 0.000 | 0.760 | 0.000 | ||
| 1 spectrum, DMDLWEQQEEER | 0.000 | 0.000 | 0.000 | 0.000 | 0.141 | 0.000 | 0.859 | 0.000 | ||
| 4 spectra, AEEQMLK | 0.000 | 0.000 | 0.000 | 0.122 | 0.241 | 0.000 | 0.637 | 0.000 | ||
| 4 spectra, LTSLVPFVDAFQLER | 0.000 | 0.000 | 0.005 | 0.162 | 0.213 | 0.000 | 0.621 | 0.000 | ||
| 4 spectra, GTDDDRPSWR | 0.000 | 0.000 | 0.000 | 0.130 | 0.210 | 0.000 | 0.660 | 0.000 | ||
| 2 spectra, GLDDER | 0.000 | 0.000 | 0.000 | 0.007 | 0.199 | 0.000 | 0.795 | 0.000 | ||
| 4 spectra, EGLYQYK | 0.000 | 0.000 | 0.000 | 0.000 | 0.239 | 0.000 | 0.761 | 0.000 | ||
| 3 spectra, PAYFQRPENALK | 0.000 | 0.000 | 0.000 | 0.082 | 0.295 | 0.000 | 0.624 | 0.000 | ||
| 5 spectra, GLDDDRPPR | 0.000 | 0.000 | 0.000 | 0.158 | 0.105 | 0.000 | 0.737 | 0.000 | ||
| 2 spectra, LGGDDEER | 0.000 | 0.000 | 0.000 | 0.000 | 0.195 | 0.000 | 0.805 | 0.000 | ||
| 4 spectra, GPAEESSSWR | 0.000 | 0.000 | 0.000 | 0.093 | 0.140 | 0.000 | 0.728 | 0.040 | ||
| 6 spectra, VPPPTLSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.238 | 0.000 | 0.762 | 0.000 | ||
| 2 spectra, LCDNLR | 0.000 | 0.000 | 0.000 | 0.291 | 0.000 | 0.000 | 0.649 | 0.061 | ||
| 2 spectra, DSEGTWR | 0.089 | 0.000 | 0.014 | 0.113 | 0.193 | 0.000 | 0.592 | 0.000 | ||
| 1 spectrum, FCLQYTR | 0.000 | 0.000 | 0.000 | 0.218 | 0.000 | 0.000 | 0.716 | 0.066 | ||
| 2 spectra, HTDDDRPPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.112 | 0.000 | 0.839 | 0.049 | ||
| 6 spectra, FLWESYR | 0.000 | 0.000 | 0.000 | 0.089 | 0.141 | 0.000 | 0.770 | 0.000 | ||
| 2 spectra, LEEIPLIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.252 | 0.000 | 0.748 | 0.000 | ||
| 2 spectra, IGDDDR | 0.000 | 0.000 | 0.000 | 0.180 | 0.000 | 0.000 | 0.820 | 0.000 | ||
| 6 spectra, IGLINDMVR | 0.000 | 0.000 | 0.000 | 0.019 | 0.248 | 0.000 | 0.733 | 0.000 | ||
| 3 spectra, QPALDVLYDVMK | 0.000 | 0.000 | 0.000 | 0.096 | 0.186 | 0.000 | 0.717 | 0.000 | ||
| 7 spectra, ESRPPEER | 0.000 | 0.000 | 0.000 | 0.137 | 0.120 | 0.000 | 0.743 | 0.000 | ||
| 2 spectra, DEGGWR | 0.000 | 0.000 | 0.000 | 0.113 | 0.182 | 0.000 | 0.705 | 0.000 | ||
| 2 spectra, NADDDRPPR | 0.000 | 0.000 | 0.000 | 0.102 | 0.119 | 0.000 | 0.779 | 0.000 | ||
| 4 spectra, AIVDAAR | 0.000 | 0.000 | 0.000 | 0.071 | 0.187 | 0.000 | 0.742 | 0.000 | ||
| 4 spectra, NQLTAMSSVLAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.292 | 0.000 | 0.708 | 0.000 | ||
| 6 spectra, EEASSWR | 0.000 | 0.000 | 0.000 | 0.000 | 0.275 | 0.000 | 0.725 | 0.000 | ||
| 2 spectra, LYHDIAQQAFK | 0.000 | 0.000 | 0.000 | 0.266 | 0.000 | 0.000 | 0.734 | 0.000 | ||
| 7 spectra, VLNWVR | 0.000 | 0.000 | 0.000 | 0.095 | 0.285 | 0.000 | 0.620 | 0.000 | ||
| 1 spectrum, QTIEER | 0.000 | 0.000 | 0.000 | 0.000 | 0.208 | 0.000 | 0.792 | 0.000 | ||
| 4 spectra, TLSFGSDLNYATR | 0.000 | 0.000 | 0.000 | 0.083 | 0.196 | 0.000 | 0.721 | 0.000 | ||
| 2 spectra, LESLNIQR | 0.000 | 0.000 | 0.000 | 0.059 | 0.328 | 0.000 | 0.613 | 0.000 | ||
| 2 spectra, LGEDPLSR | 0.000 | 0.000 | 0.000 | 0.391 | 0.000 | 0.000 | 0.609 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
56 spectra |
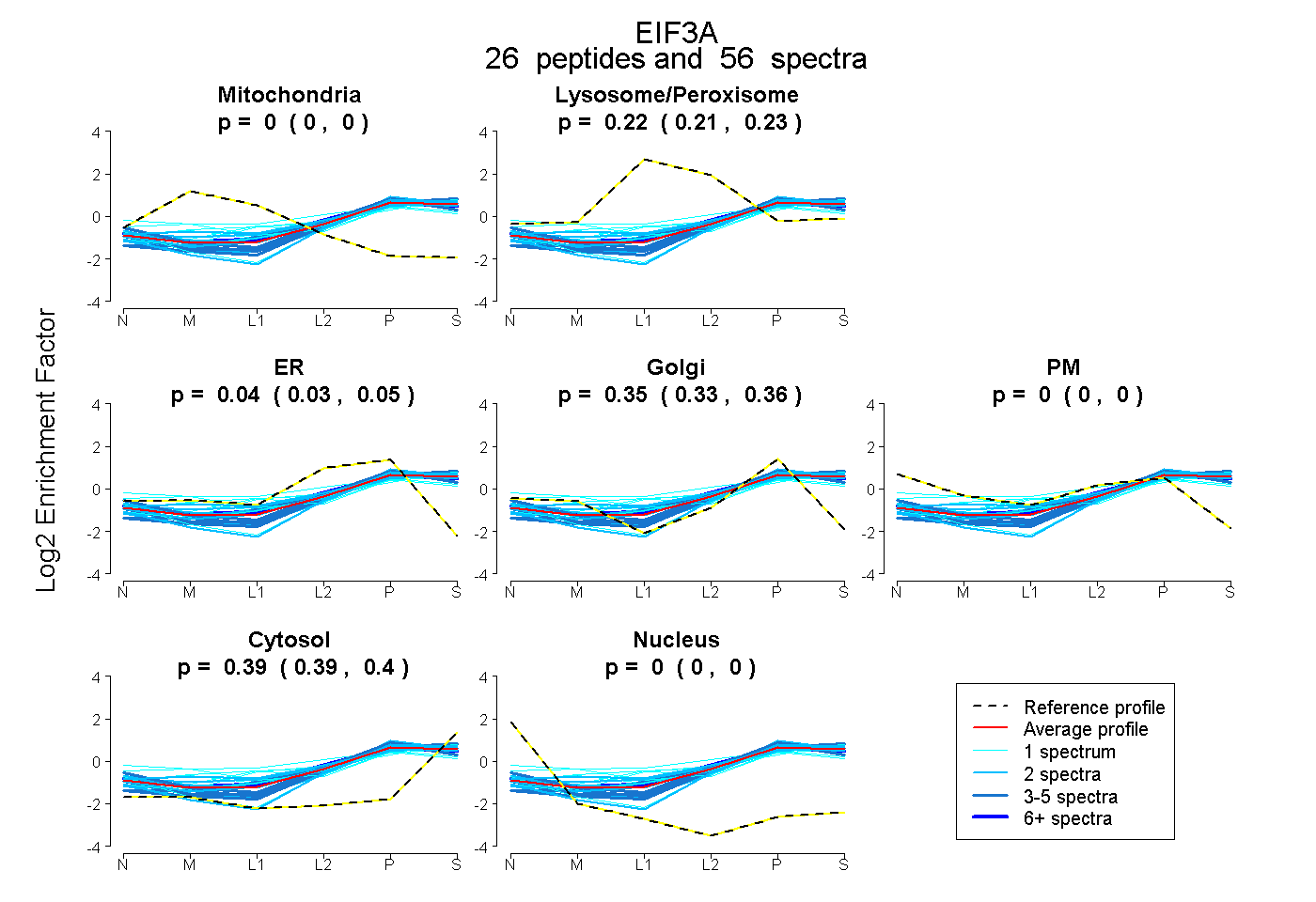 |
0.000 0.000 | 0.000 |
0.220 0.213 | 0.227 |
0.041 0.027 | 0.054 |
0.345 0.333 | 0.355 |
0.000 0.000 | 0.000 |
0.393 0.388 | 0.397 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
108 spectra |
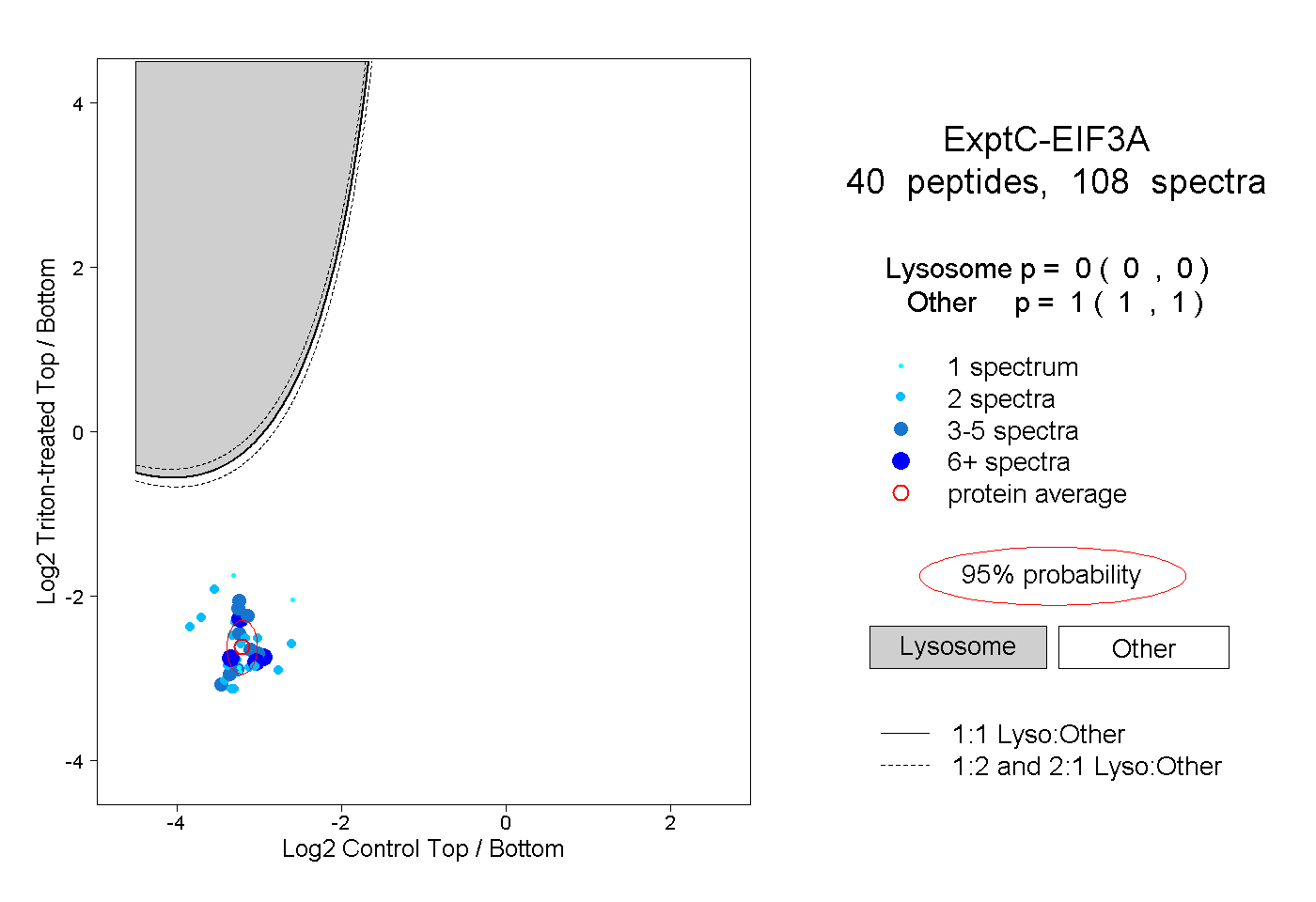 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
23 spectra |
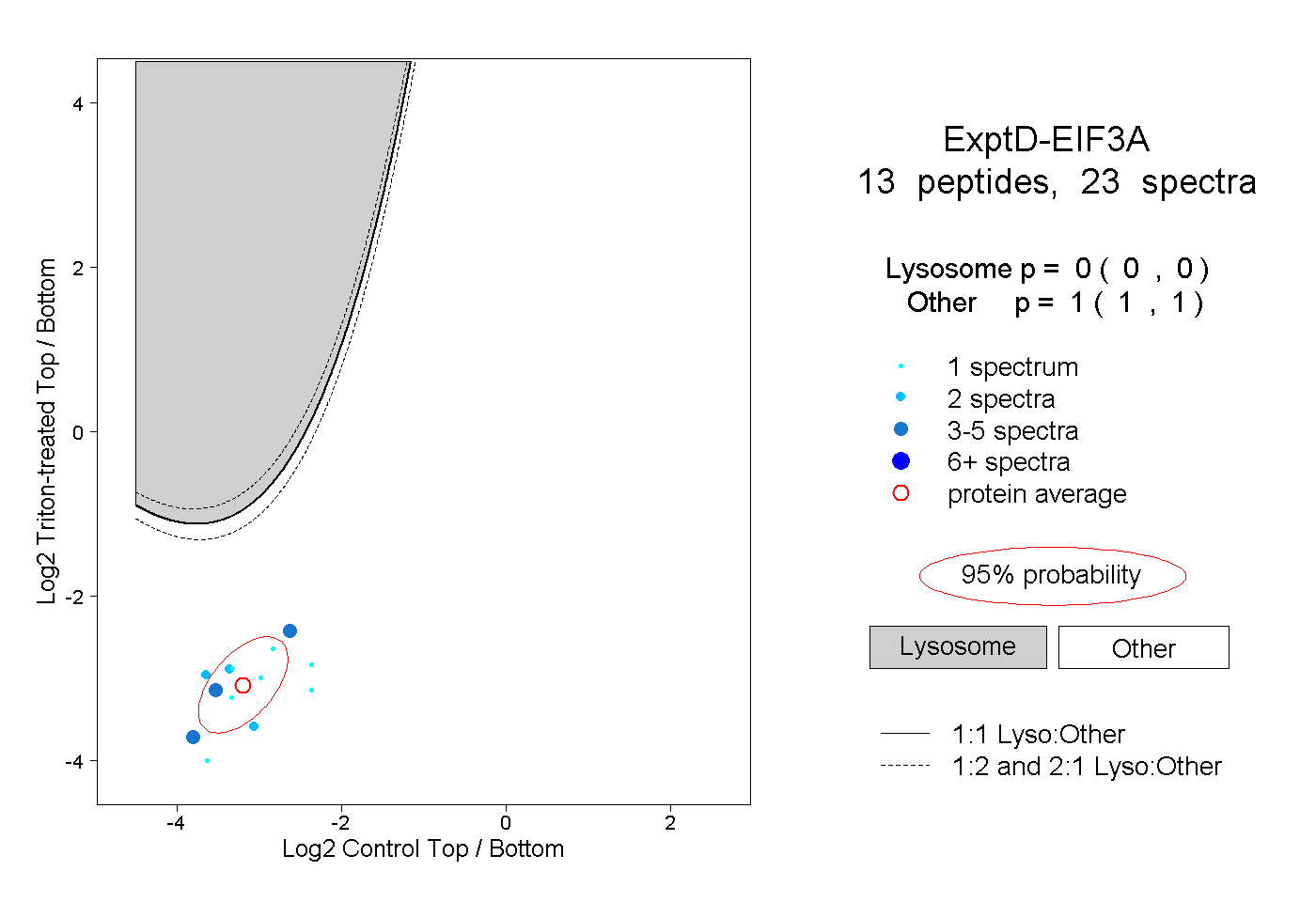 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |