peptides
spectra
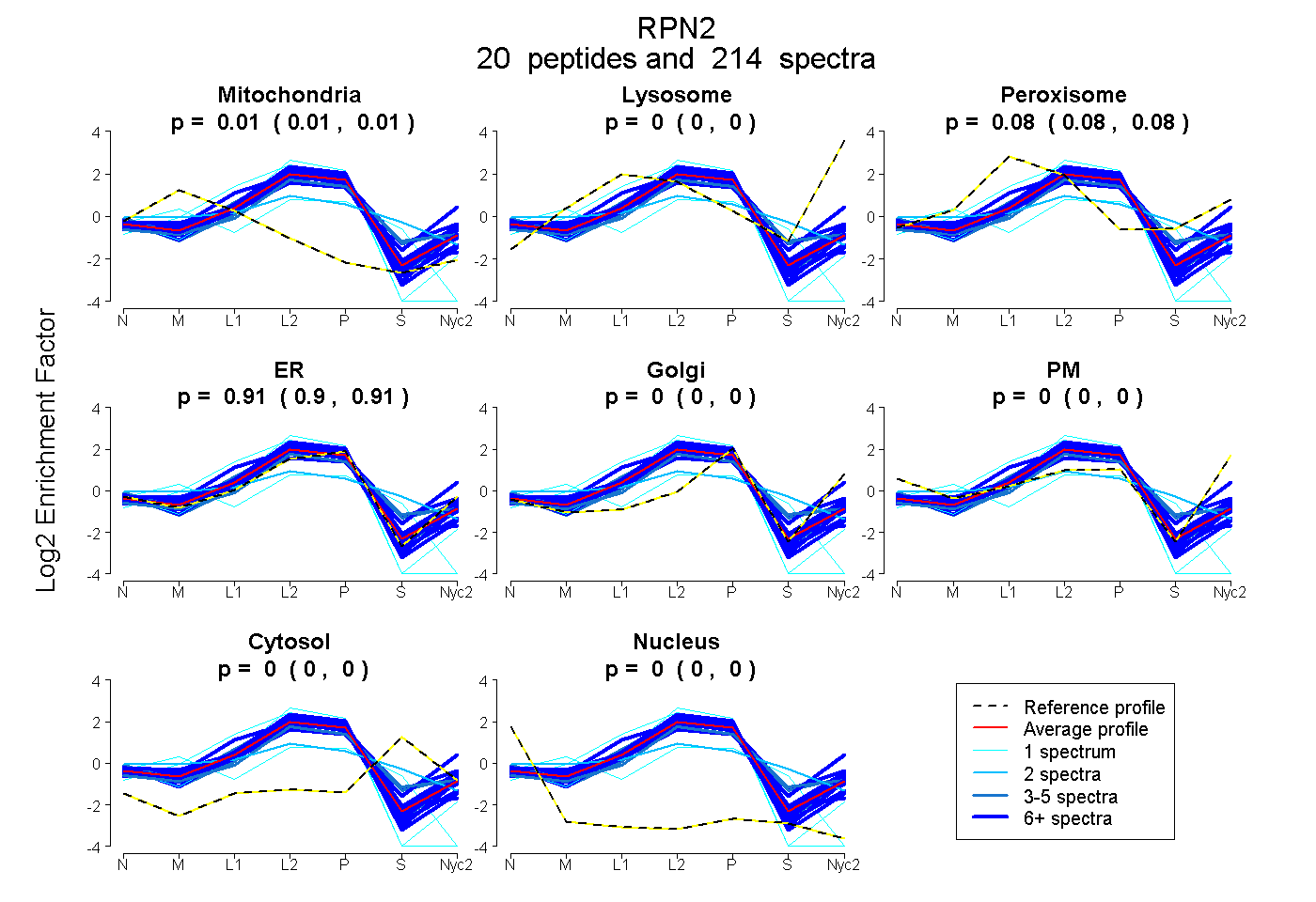
0.009 | 0.012
0.000 | 0.000
0.079 | 0.085
0.905 | 0.909
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
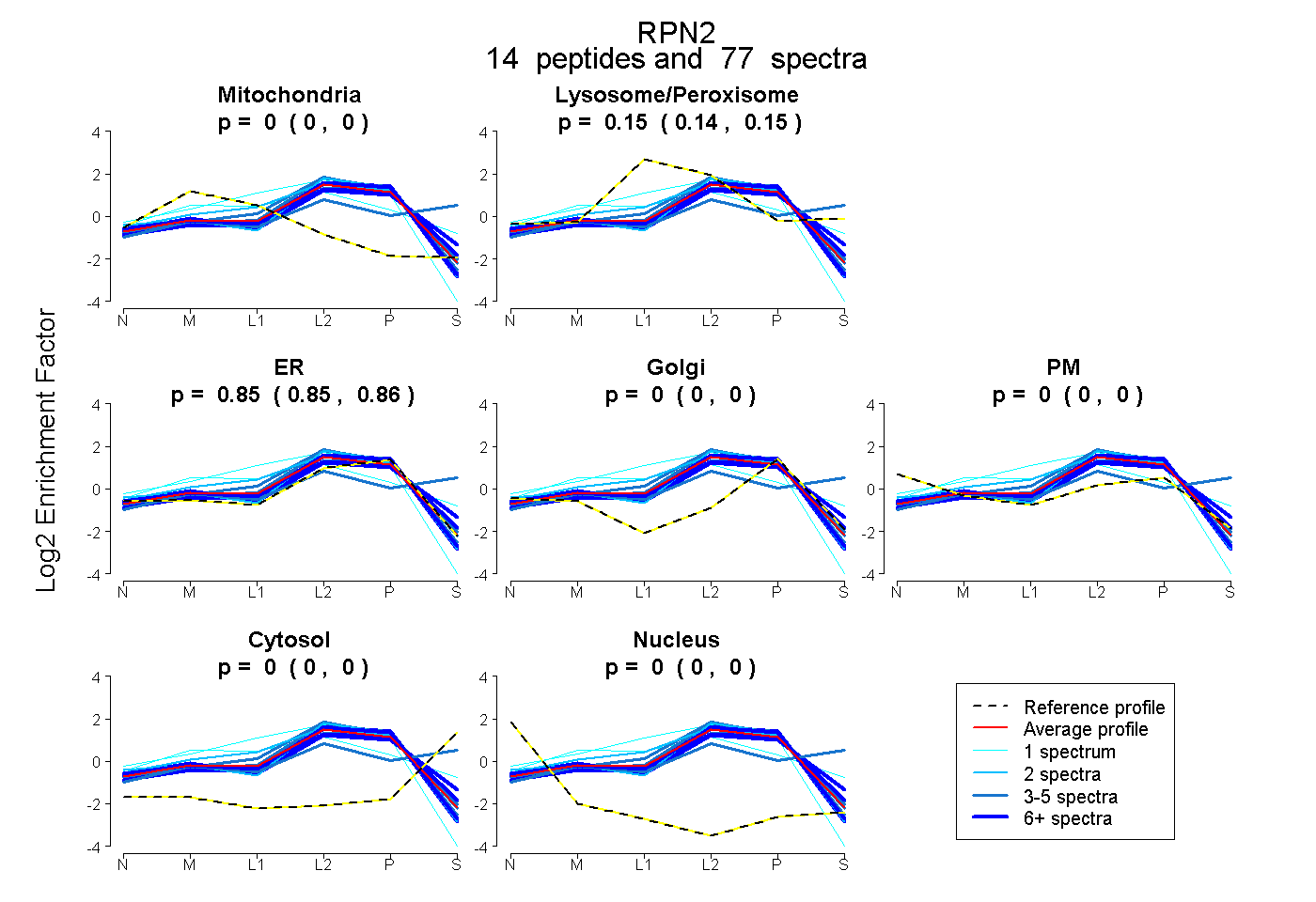
0.000 | 0.000
0.138 | 0.152
0.847 | 0.861
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
214 spectra |
 |
0.011 0.009 | 0.012 |
0.000 0.000 | 0.000 |
0.082 0.079 | 0.085 |
0.907 0.905 | 0.909 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
77 spectra |
 |
0.000 0.000 | 0.000 |
0.145 0.138 | 0.152 |
0.855 0.847 | 0.861 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 13 spectra, FELDTSER | 0.000 | 0.044 | 0.956 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EETVLATVQALHTASHLSQQADLR | 0.150 | 0.447 | 0.259 | 0.143 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, NPILWNVADVVIK | 0.000 | 0.239 | 0.761 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 13 spectra, QEIQHLFR | 0.000 | 0.124 | 0.864 | 0.000 | 0.000 | 0.012 | 0.000 | |||
| 1 spectrum, ACAFIK | 0.097 | 0.166 | 0.737 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, NIVEEIEDLVAR | 0.000 | 0.080 | 0.920 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, LPSGYYDFSVR | 0.004 | 0.102 | 0.894 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VTYPAK | 0.007 | 0.203 | 0.790 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, TGQEVVFVAEPDNK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, YHVPVVVVPEGSASDTQEQAILR | 0.000 | 0.361 | 0.291 | 0.000 | 0.000 | 0.348 | 0.000 | |||
| 8 spectra, MPFSLVGDVFELNFK | 0.000 | 0.006 | 0.994 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, LQVSSVLSQPLAQAAVK | 0.000 | 0.153 | 0.788 | 0.000 | 0.000 | 0.059 | 0.000 | |||
| 4 spectra, MLAQQAVK | 0.000 | 0.146 | 0.854 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, YIANTVELR | 0.000 | 0.051 | 0.949 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
417 spectra |
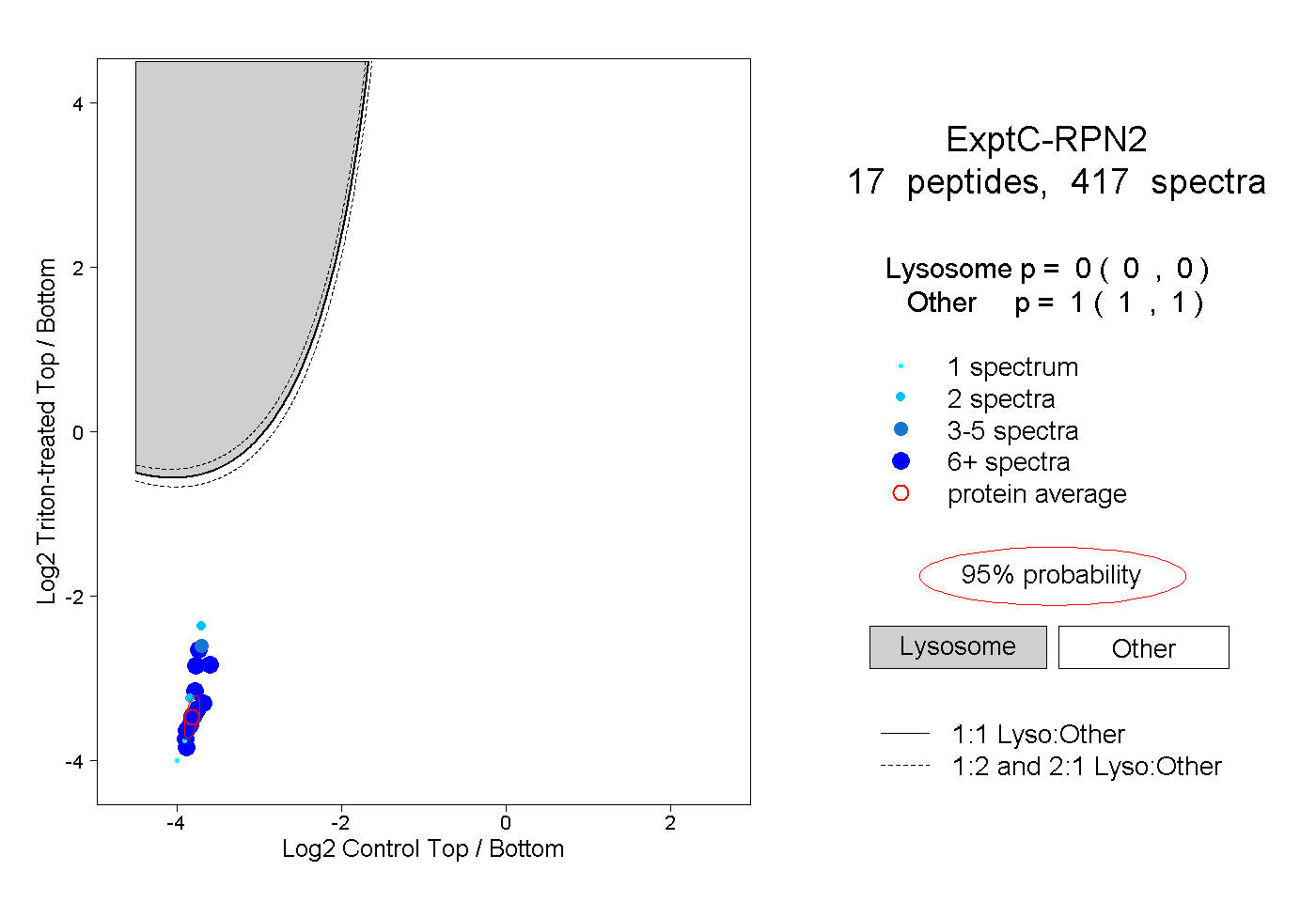 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
45 spectra |
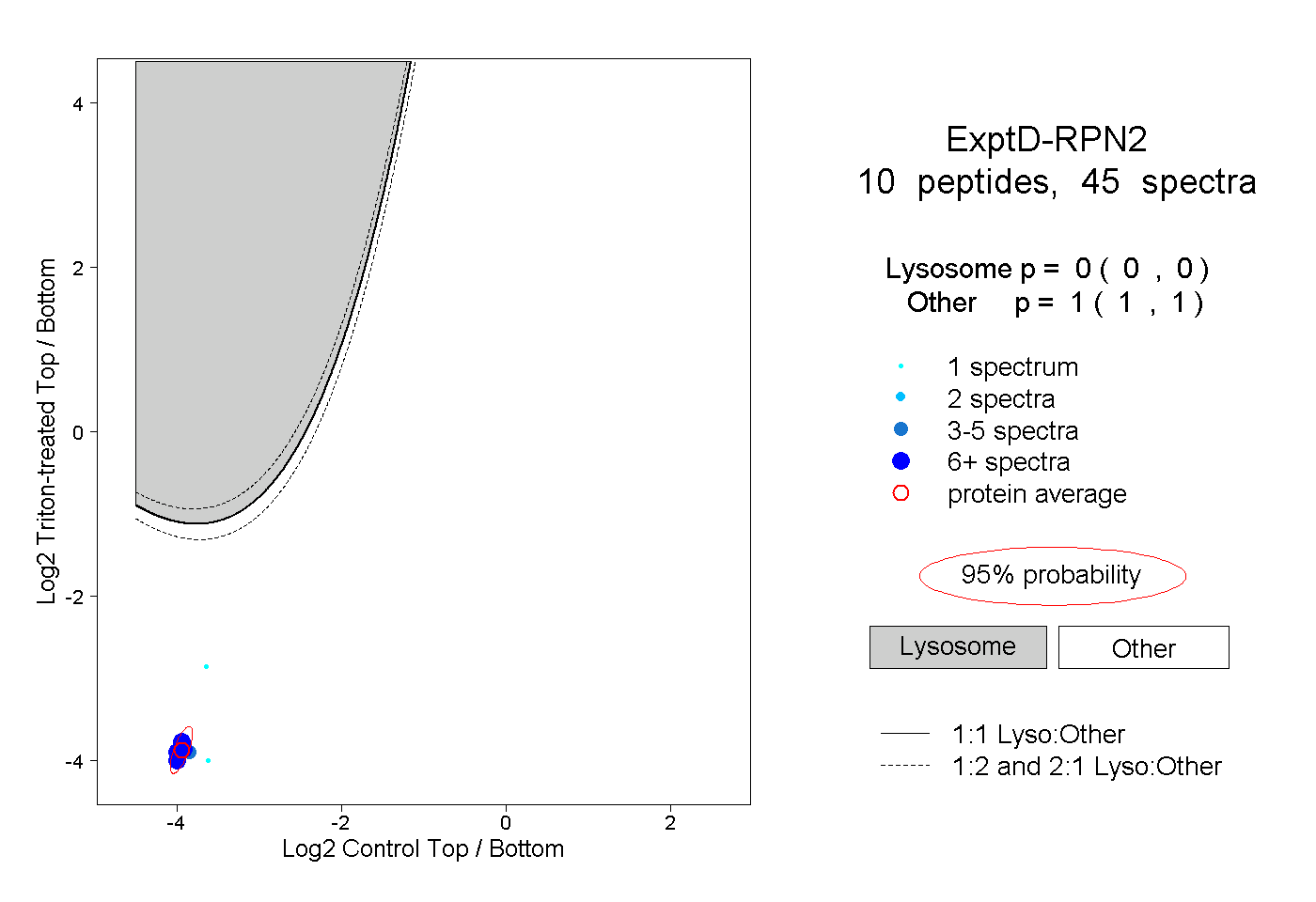 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |