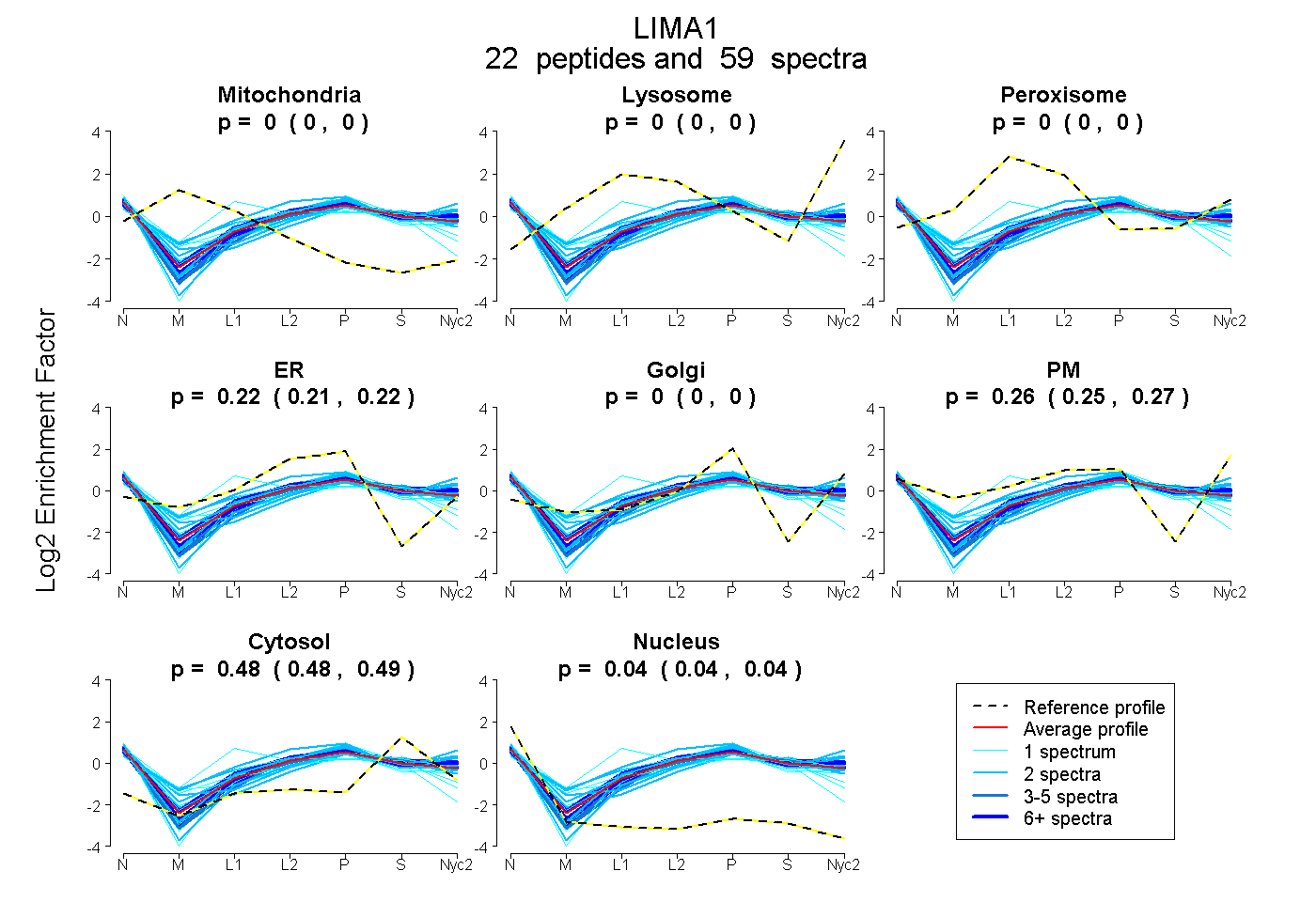
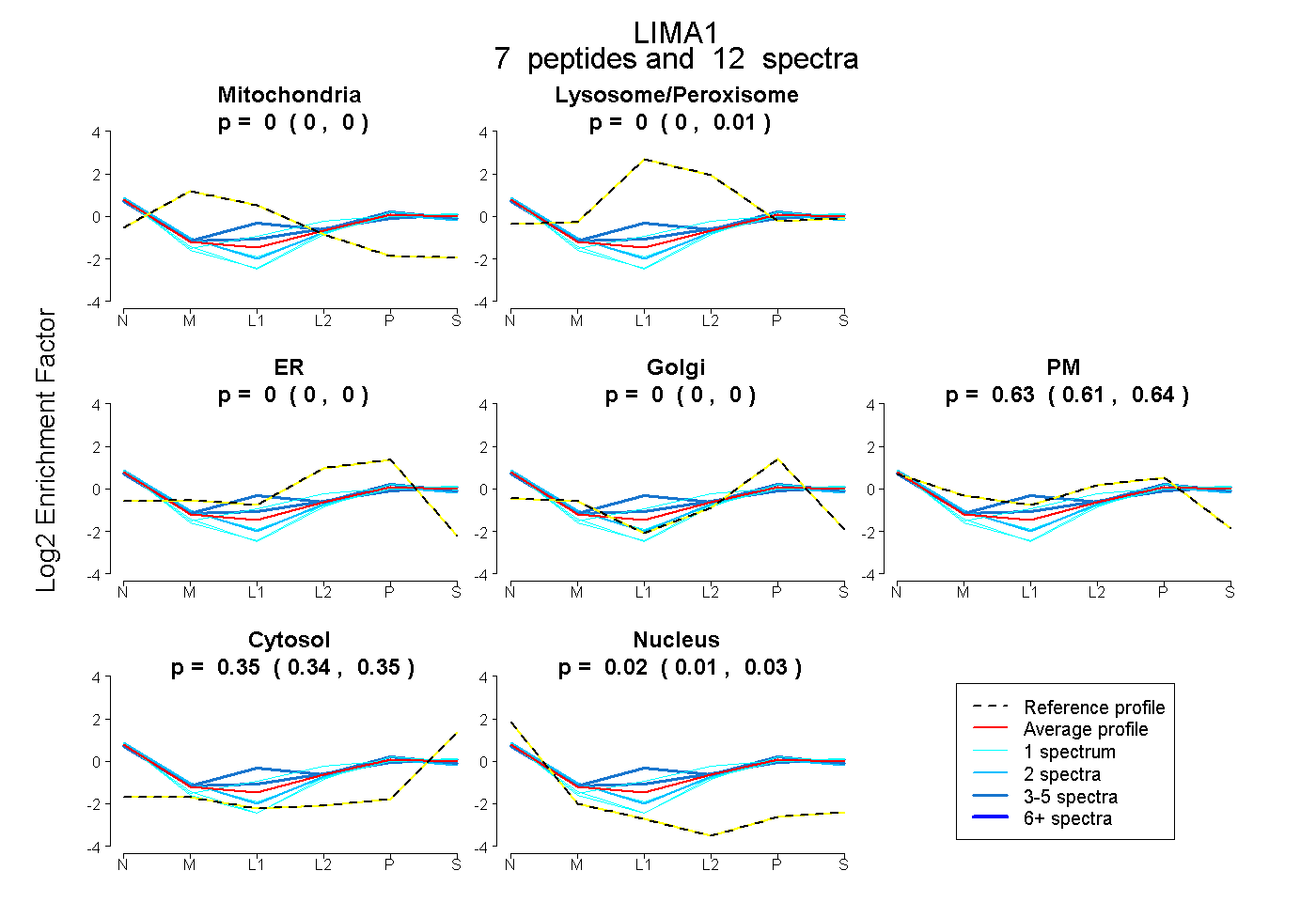
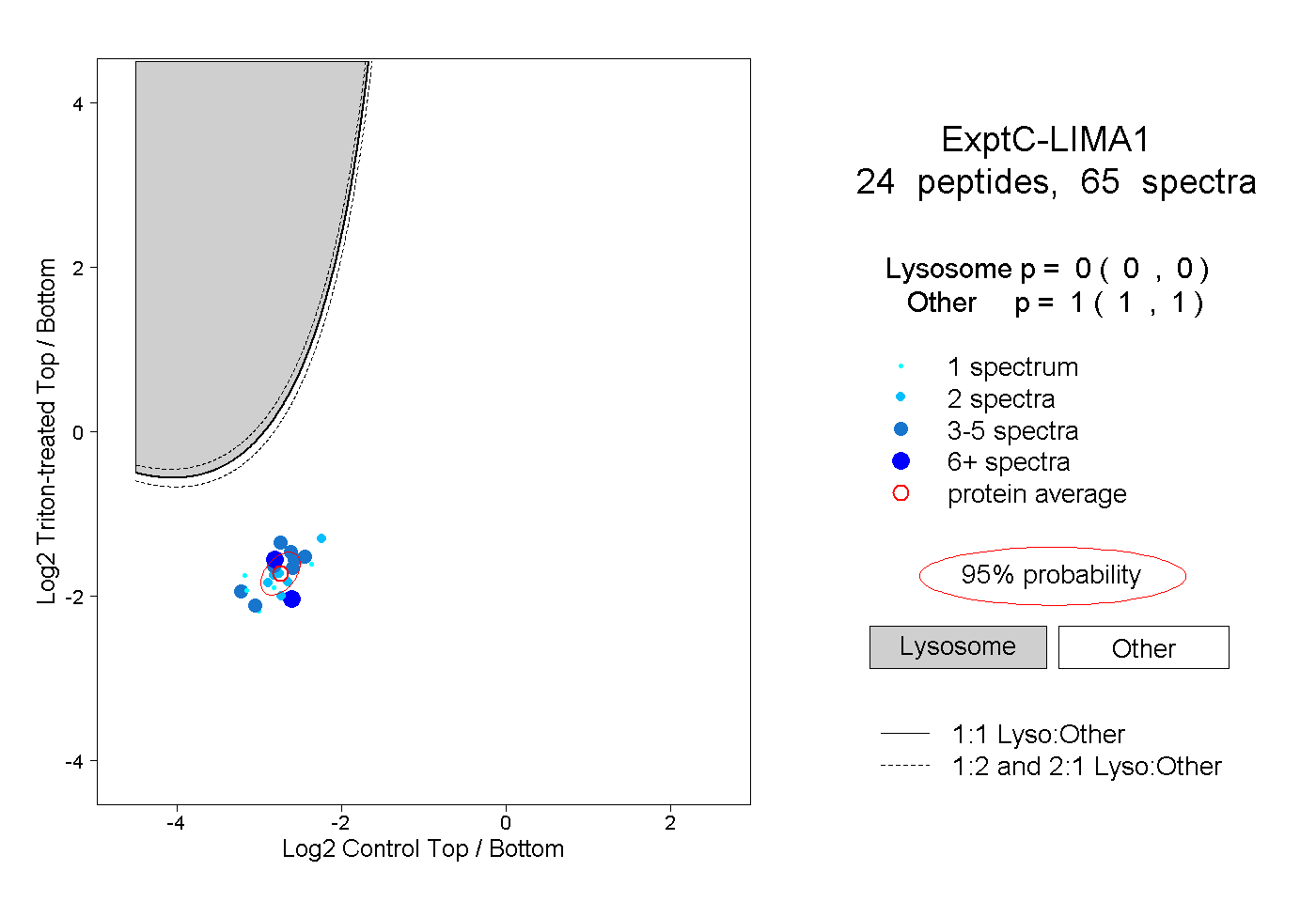
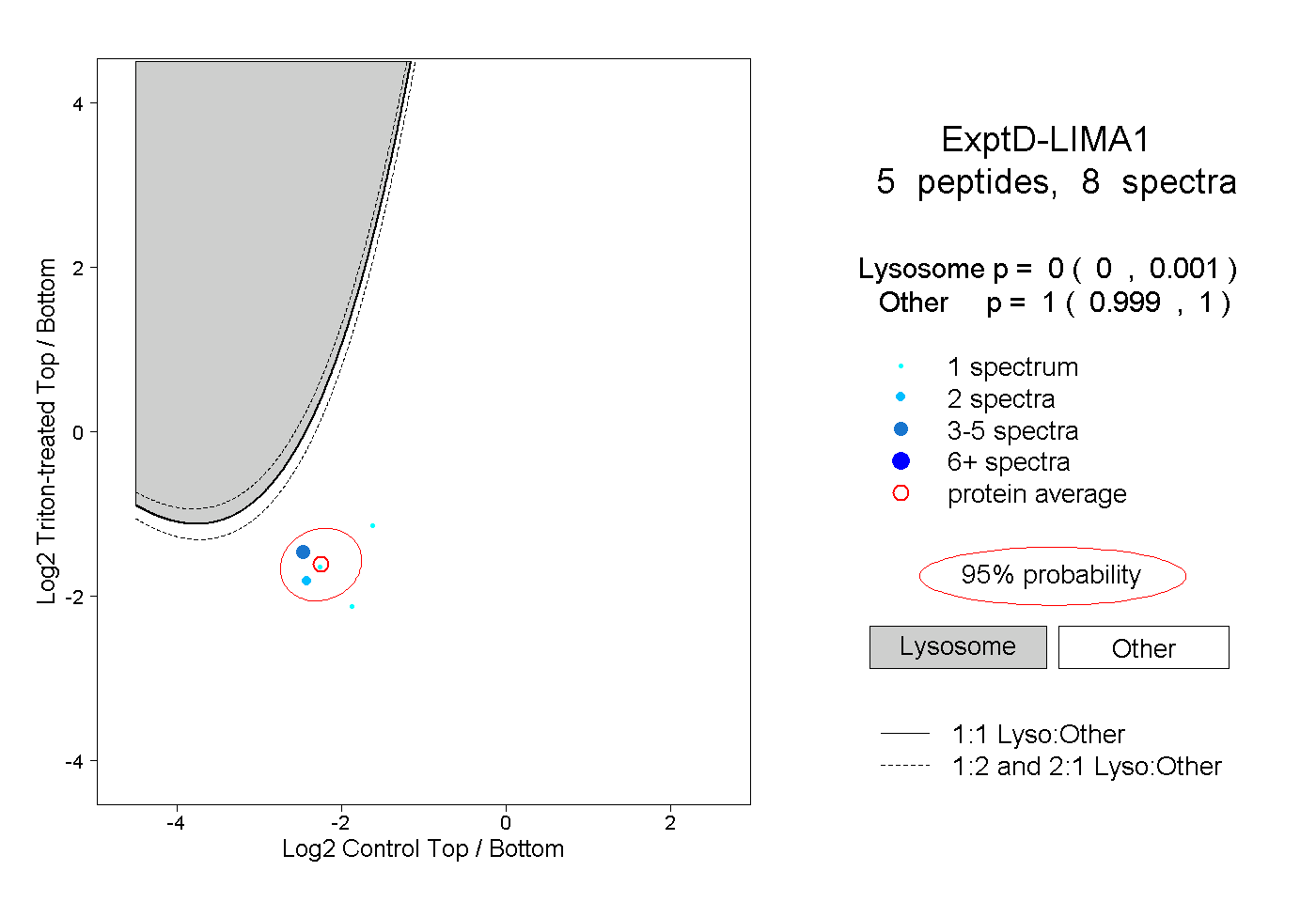
| 4 spectra, SPKPLSPSLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, GNYDEGFGHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, NLELPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VGVLAASMEAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SEAQQPIYTKPLSPDAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, YNVPLNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NNTESLPQHFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ELSVEEQIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, TSSLPESSPSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SEDSHDFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, ESCVECQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, YQAAVSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, SSTIVEIFSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TVYPMER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SQDVGFWEGEVVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GEHSQNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LLANQQVFHISCFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, QSSPASYASELKPSESK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, HEAEKPEMSENTETSGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SRPFTVAASFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FGSRPEAVTQCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, AAEEANMER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LSLGTYASLHGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ELSLVNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |