peptides
spectra
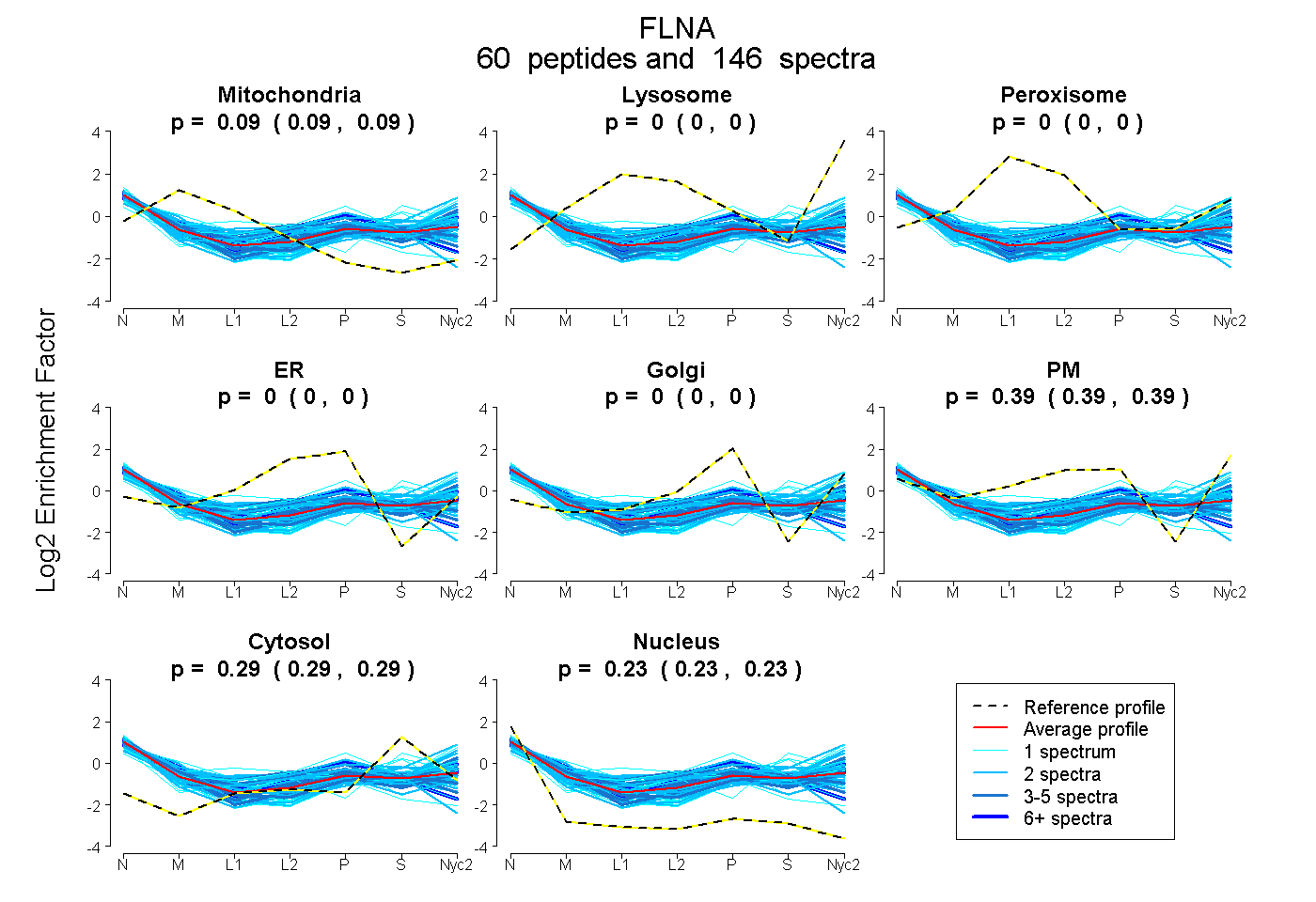
0.085 | 0.089
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.387 | 0.391
0.291 | 0.294
0.230 | 0.232
peptides
spectra
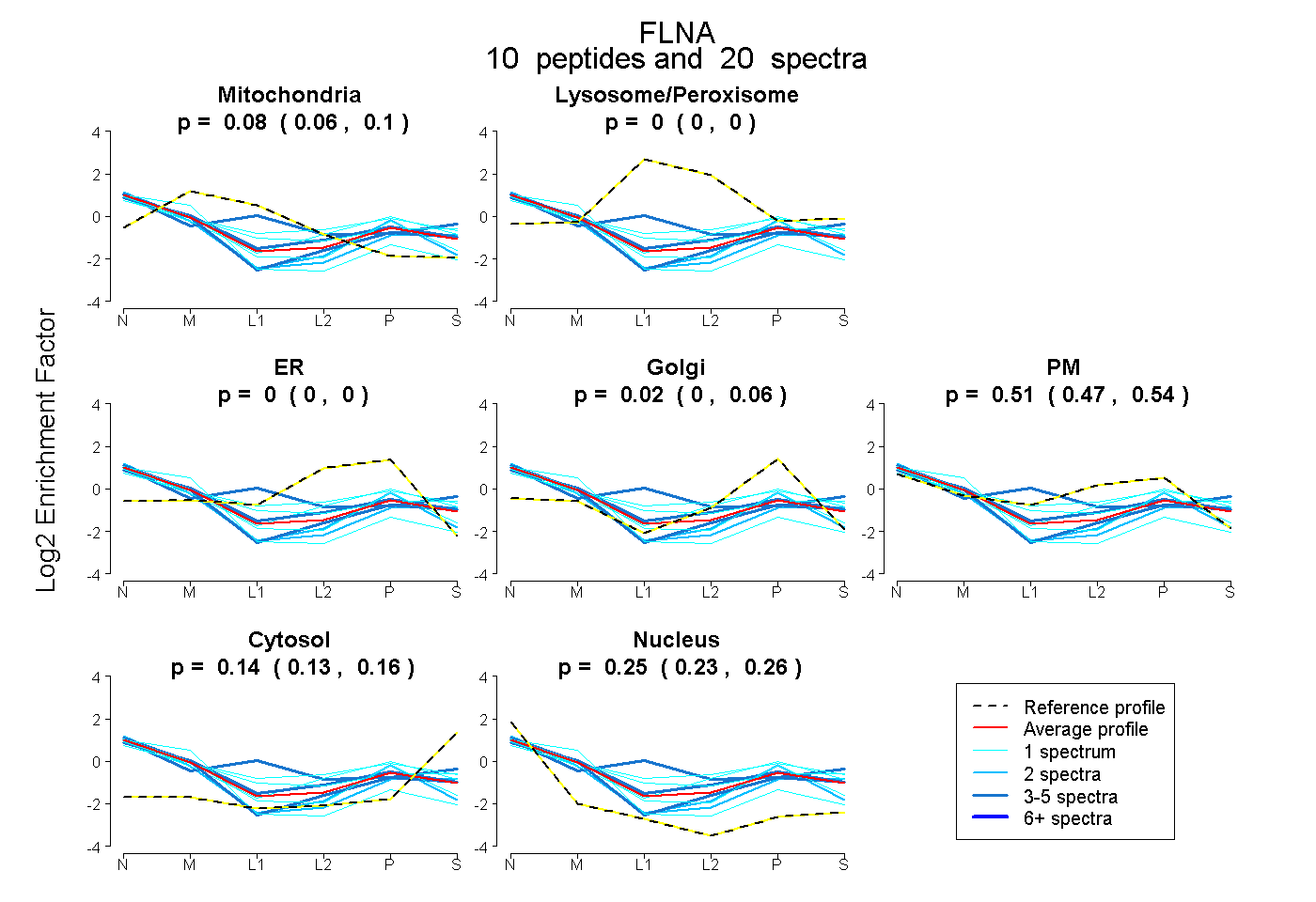
0.056 | 0.096
0.000 | 0.000
0.000 | 0.000
0.000 | 0.056
0.466 | 0.537
0.128 | 0.159
0.231 | 0.258
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
146 spectra |
 |
0.087 0.085 | 0.089 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.389 0.387 | 0.391 |
0.293 0.291 | 0.294 |
0.231 0.230 | 0.232 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
20 spectra |
 |
0.078 0.056 | 0.096 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.023 0.000 | 0.056 |
0.509 0.466 | 0.537 |
0.144 0.128 | 0.159 |
0.246 0.231 | 0.258 |
| 1 spectrum, YVICVR | 0.128 | 0.000 | 0.000 | 0.371 | 0.173 | 0.000 | 0.328 | |||
| 2 spectra, AEFTVETR | 0.015 | 0.000 | 0.000 | 0.150 | 0.249 | 0.181 | 0.405 | |||
| 2 spectra, FTVETR | 0.046 | 0.000 | 0.000 | 0.436 | 0.154 | 0.000 | 0.365 | |||
| 5 spectra, AFGPGLQGGNAGSPAR | 0.000 | 0.418 | 0.000 | 0.000 | 0.167 | 0.100 | 0.315 | |||
| 3 spectra, GTVEPQLEAR | 0.007 | 0.000 | 0.000 | 0.132 | 0.367 | 0.163 | 0.331 | |||
| 1 spectrum, IANLQTDLSDGLR | 0.257 | 0.000 | 0.000 | 0.248 | 0.000 | 0.000 | 0.495 | |||
| 1 spectrum, EAGAGGLAIAVEGPSK | 0.000 | 0.000 | 0.000 | 0.057 | 0.648 | 0.184 | 0.112 | |||
| 1 spectrum, ENGVYLIDVK | 0.047 | 0.069 | 0.000 | 0.000 | 0.648 | 0.185 | 0.051 | |||
| 3 spectra, ETGEHLVHVK | 0.093 | 0.000 | 0.000 | 0.000 | 0.575 | 0.161 | 0.171 | |||
| 1 spectrum, FNEEHIPDSPFVVPVASPSGDAR | 0.109 | 0.052 | 0.000 | 0.000 | 0.483 | 0.198 | 0.159 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
108 spectra |
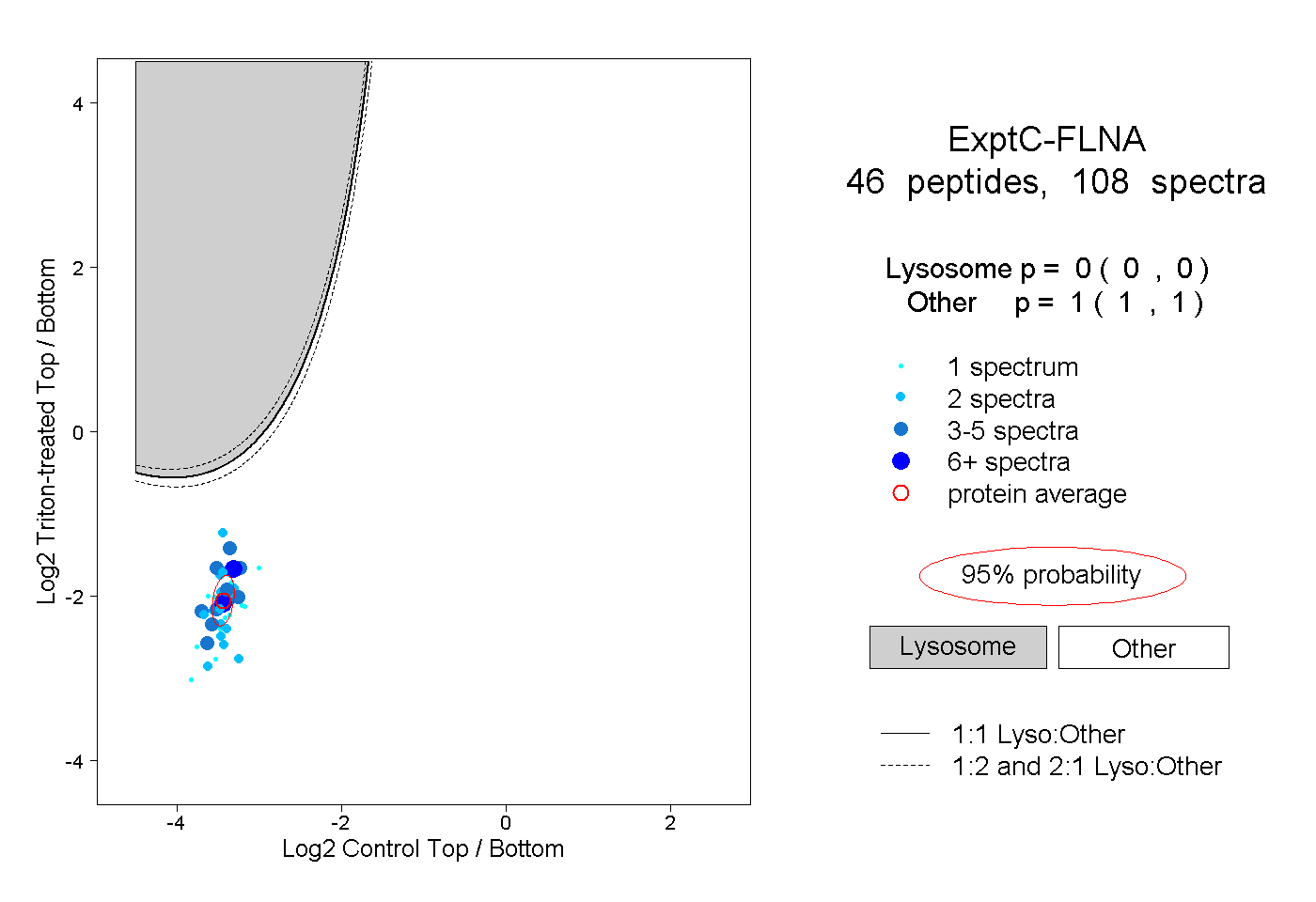 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
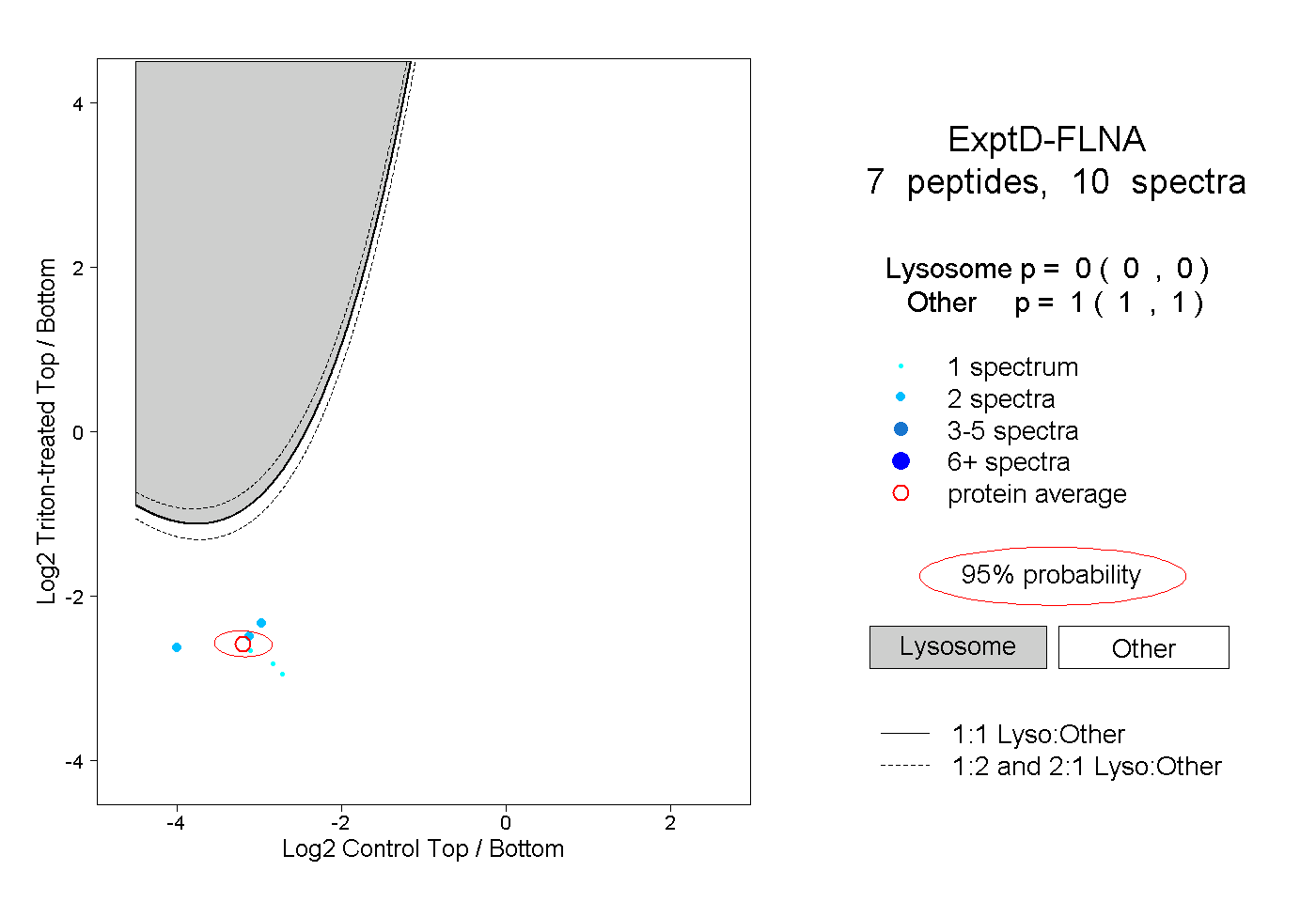 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |