peptides
spectra
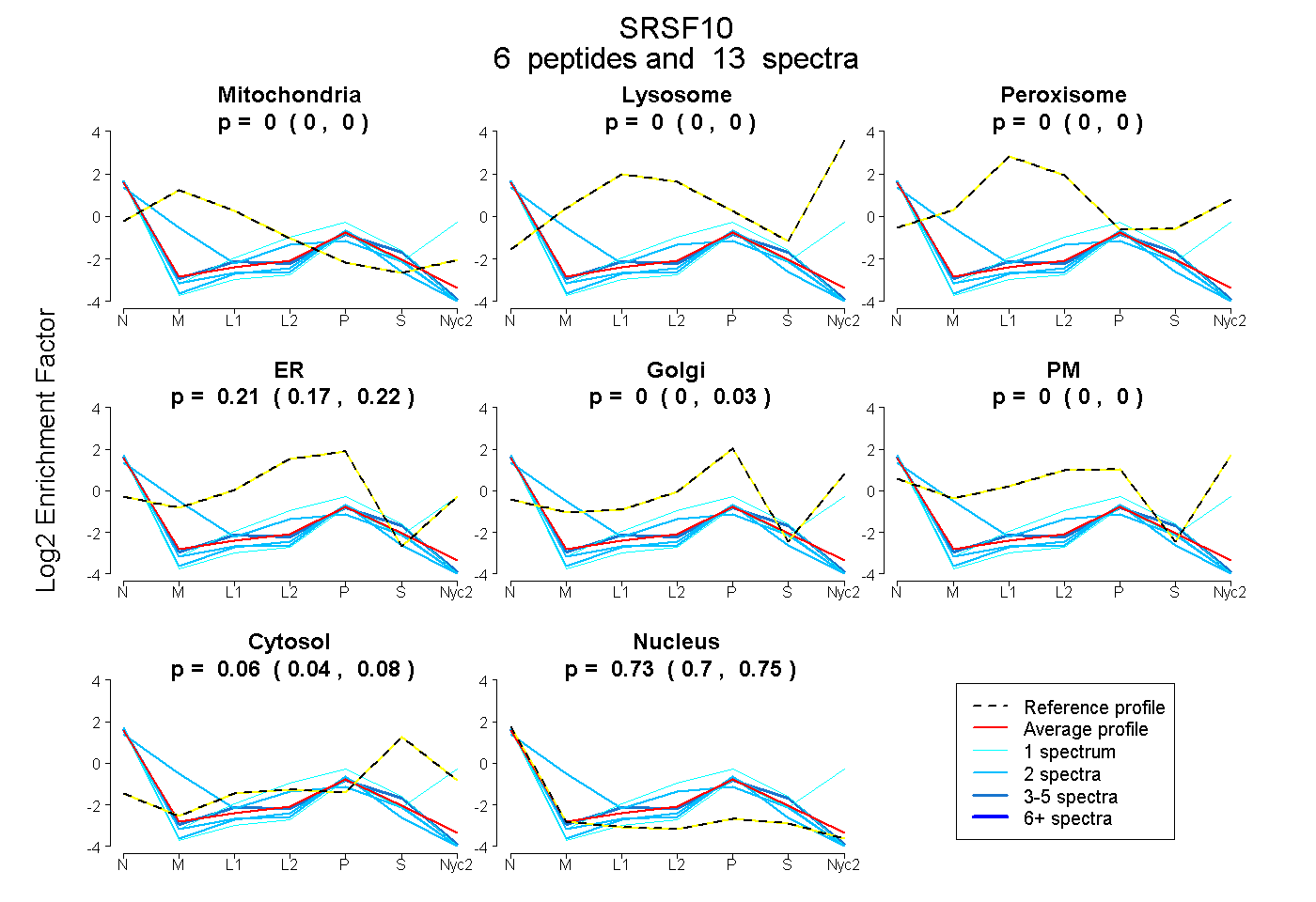
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.167 | 0.224
0.000 | 0.029
0.000 | 0.000
0.039 | 0.080
0.704 | 0.751
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
13 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.208 0.167 | 0.224 |
0.000 0.000 | 0.029 |
0.000 0.000 | 0.000 |
0.062 0.039 | 0.080 |
0.731 0.704 | 0.751 |
| 2 spectra, YLRPPNTSLFVR | 0.000 | 0.000 | 0.000 | 0.156 | 0.000 | 0.000 | 0.000 | 0.844 | ||
| 1 spectrum, QIEIQFAQGDR | 0.000 | 0.000 | 0.000 | 0.283 | 0.000 | 0.000 | 0.078 | 0.639 | ||
| 2 spectra, GFAYVQFEDVR | 0.281 | 0.000 | 0.000 | 0.154 | 0.000 | 0.000 | 0.000 | 0.565 | ||
| 5 spectra, DAEDALHNLDR | 0.000 | 0.000 | 0.000 | 0.155 | 0.000 | 0.000 | 0.108 | 0.736 | ||
| 1 spectrum, NVYSSSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.320 | 0.000 | 0.093 | 0.587 | ||
| 2 spectra, NVADDTR | 0.000 | 0.000 | 0.000 | 0.127 | 0.000 | 0.000 | 0.050 | 0.822 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
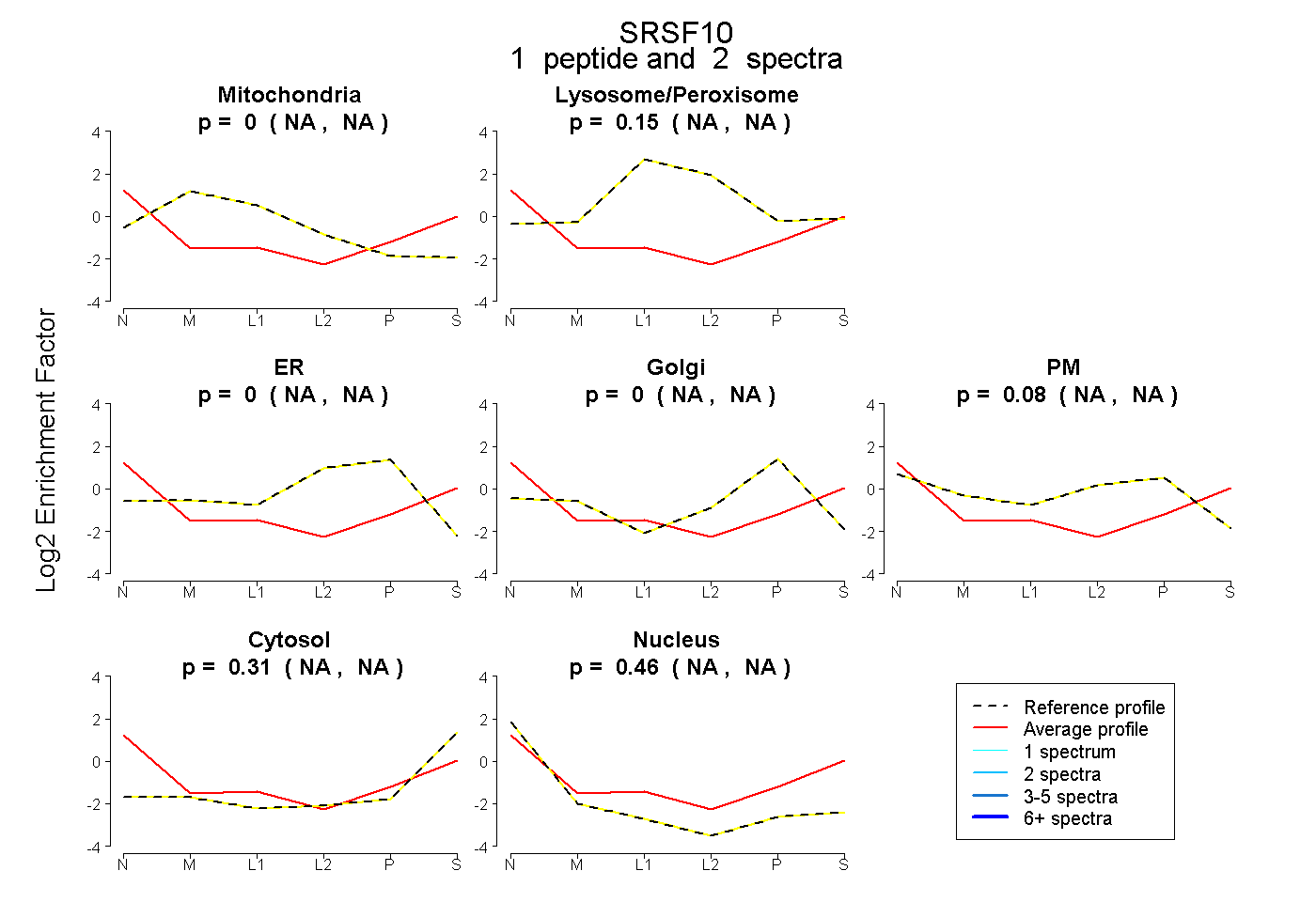 |
0.000 NA | NA |
0.153 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.081 NA | NA |
0.311 NA | NA |
0.455 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
3 spectra |
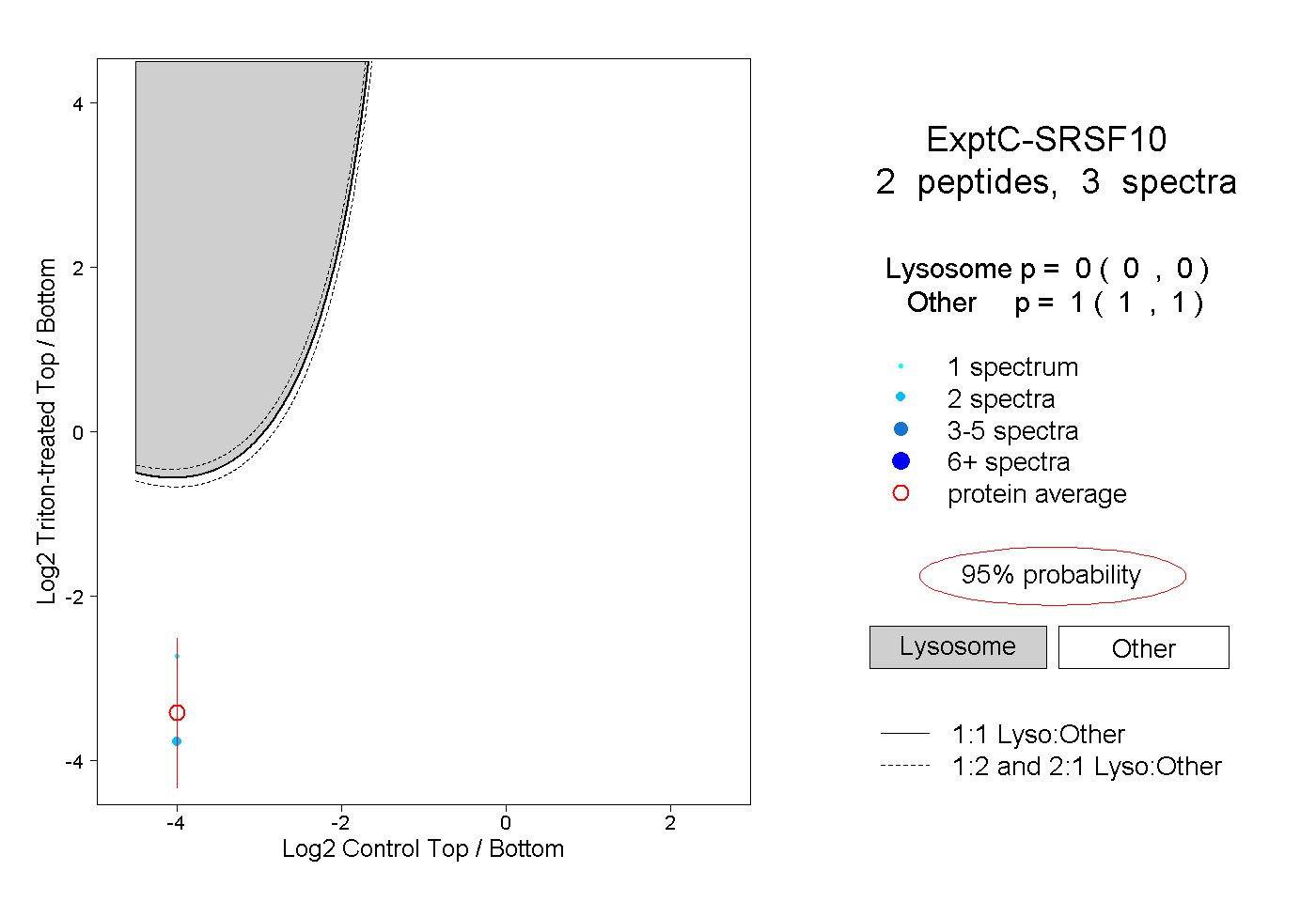 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |