peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.378 | 0.385
0.178 | 0.189
0.000 | 0.000
0.194 | 0.207
0.224 | 0.229
0.004 | 0.008
peptides
spectra
0.000 | 0.000
0.481 | 0.501
0.000 | 0.000
0.000 | 0.000
0.464 | 0.490
0.000 | 0.000
0.024 | 0.035
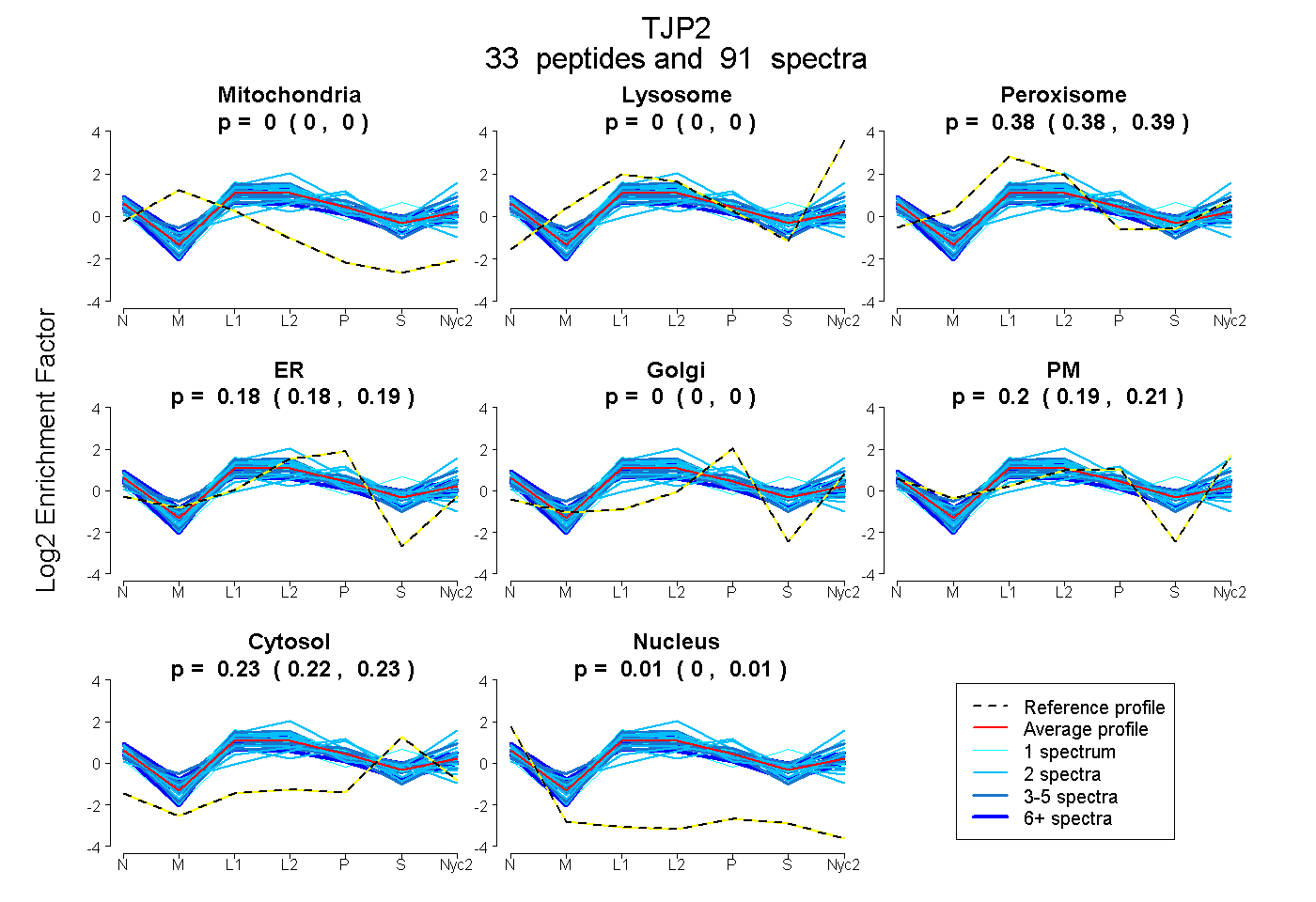
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
91 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.382 0.378 | 0.385 |
0.184 0.178 | 0.189 |
0.000 0.000 | 0.000 |
0.201 0.194 | 0.207 |
0.226 0.224 | 0.229 |
0.006 0.004 | 0.008 |
||
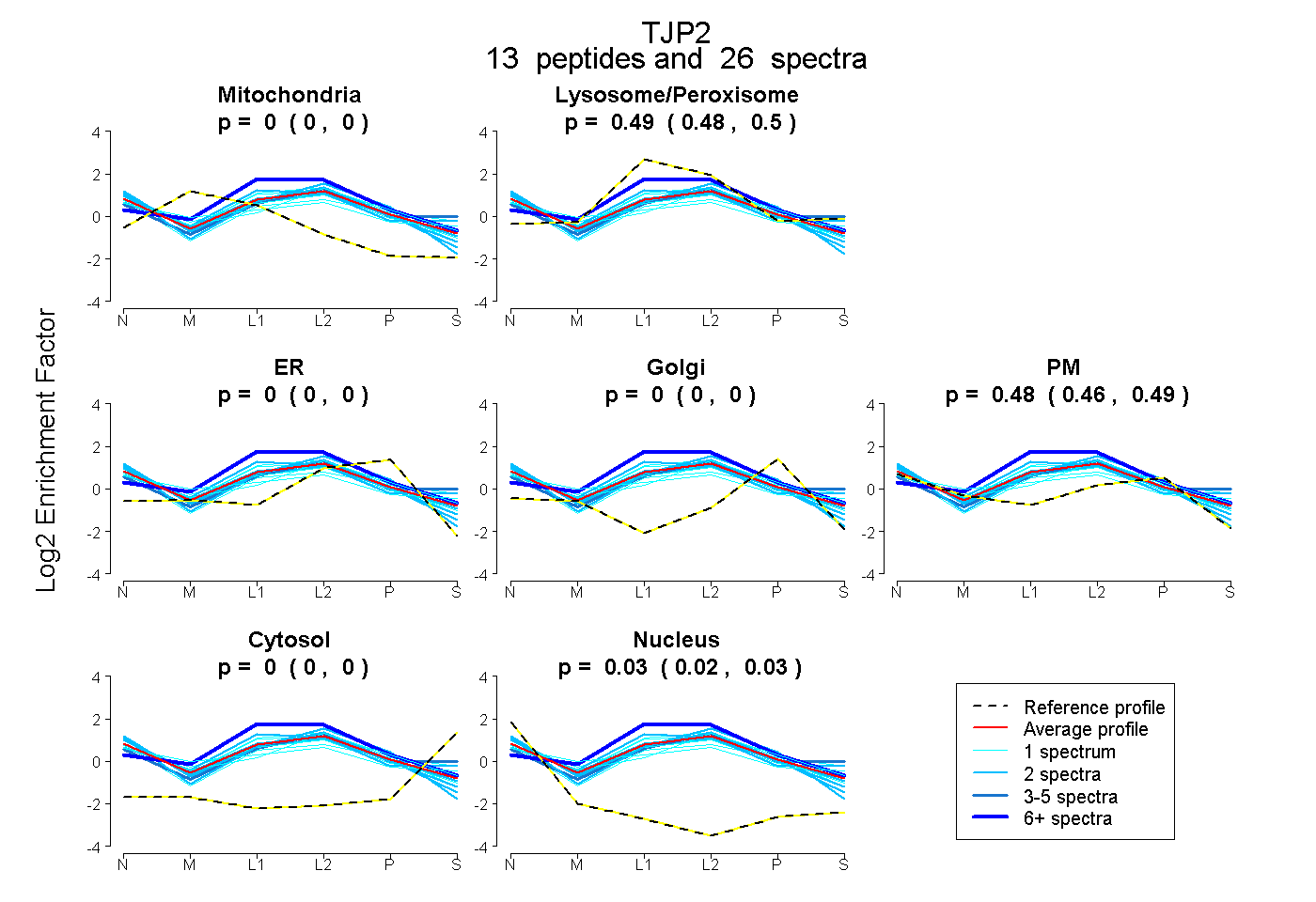
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
26 spectra |
 |
0.000 0.000 | 0.000 |
0.492 0.481 | 0.501 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.478 0.464 | 0.490 |
0.000 0.000 | 0.000 |
0.030 0.024 | 0.035 |
| 1 spectrum, DILACGR | 0.000 | 0.511 | 0.000 | 0.000 | 0.445 | 0.000 | 0.043 | |||
| 1 spectrum, DGNLHEGDIILK | 0.000 | 0.489 | 0.000 | 0.000 | 0.511 | 0.000 | 0.000 | |||
| 2 spectra, ANEEYGLR | 0.000 | 0.402 | 0.000 | 0.000 | 0.545 | 0.000 | 0.053 | |||
| 3 spectra, EDAVLYLLEIPK | 0.000 | 0.527 | 0.000 | 0.000 | 0.368 | 0.105 | 0.000 | |||
| 1 spectrum, GETVTILAQSR | 0.000 | 0.489 | 0.000 | 0.000 | 0.450 | 0.006 | 0.054 | |||
| 2 spectra, GDSFFIR | 0.000 | 0.458 | 0.000 | 0.000 | 0.501 | 0.000 | 0.042 | |||
| 1 spectrum, SSEPVQHEESIR | 0.000 | 0.388 | 0.000 | 0.000 | 0.598 | 0.014 | 0.000 | |||
| 1 spectrum, LGSQIFIK | 0.014 | 0.411 | 0.000 | 0.000 | 0.453 | 0.086 | 0.036 | |||
| 2 spectra, GLDHEDYGR | 0.000 | 0.362 | 0.015 | 0.000 | 0.622 | 0.000 | 0.000 | |||
| 2 spectra, ETPQSLAFTR | 0.000 | 0.452 | 0.000 | 0.000 | 0.533 | 0.000 | 0.015 | |||
| 2 spectra, IGNELEK | 0.000 | 0.674 | 0.000 | 0.000 | 0.224 | 0.012 | 0.090 | |||
| 1 spectrum, DAGSEK | 0.000 | 0.463 | 0.000 | 0.000 | 0.398 | 0.075 | 0.064 | |||
| 7 spectra, LGHWLAVR | 0.000 | 0.716 | 0.007 | 0.000 | 0.278 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
136 spectra |
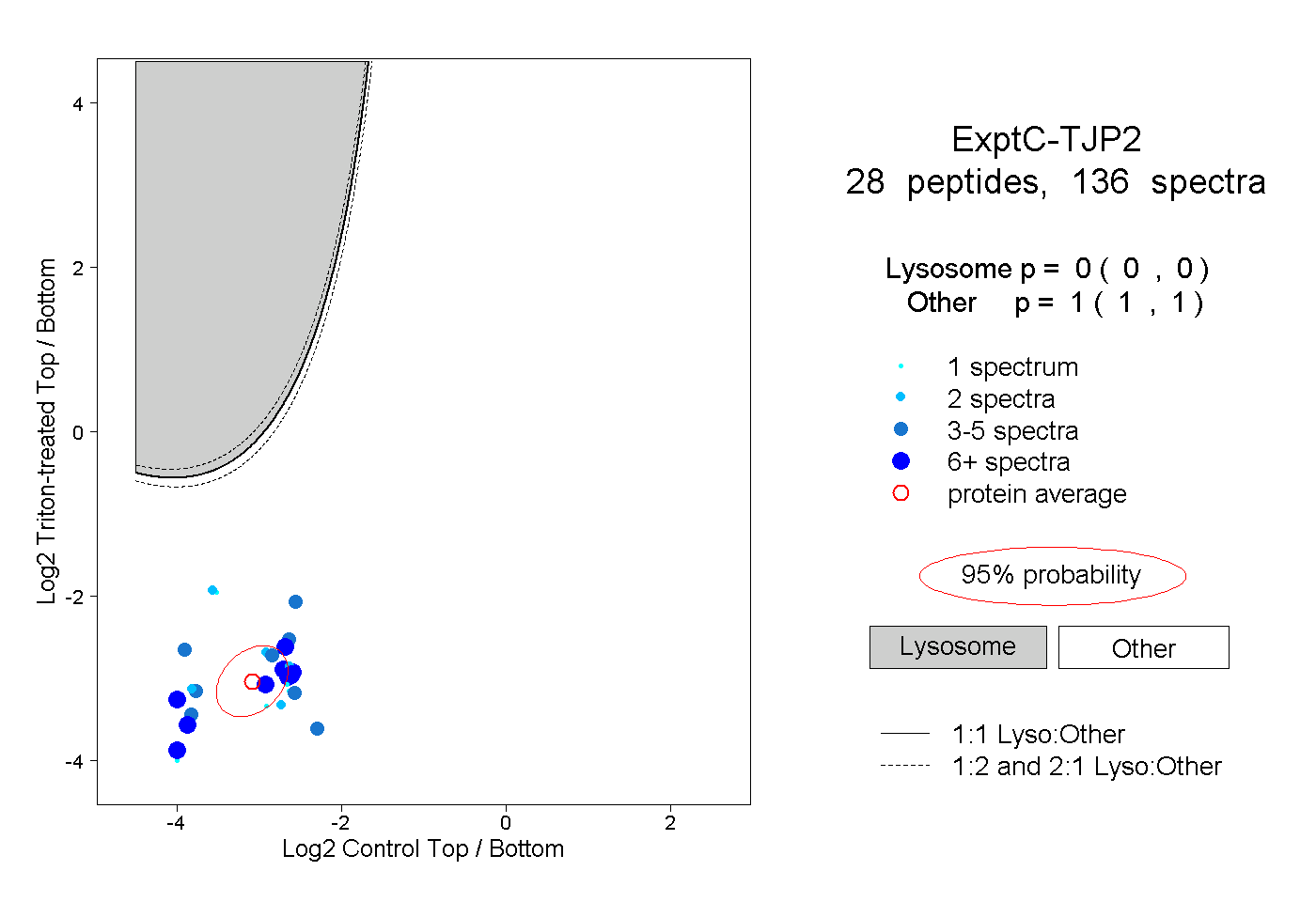 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
26 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |