peptides
spectra
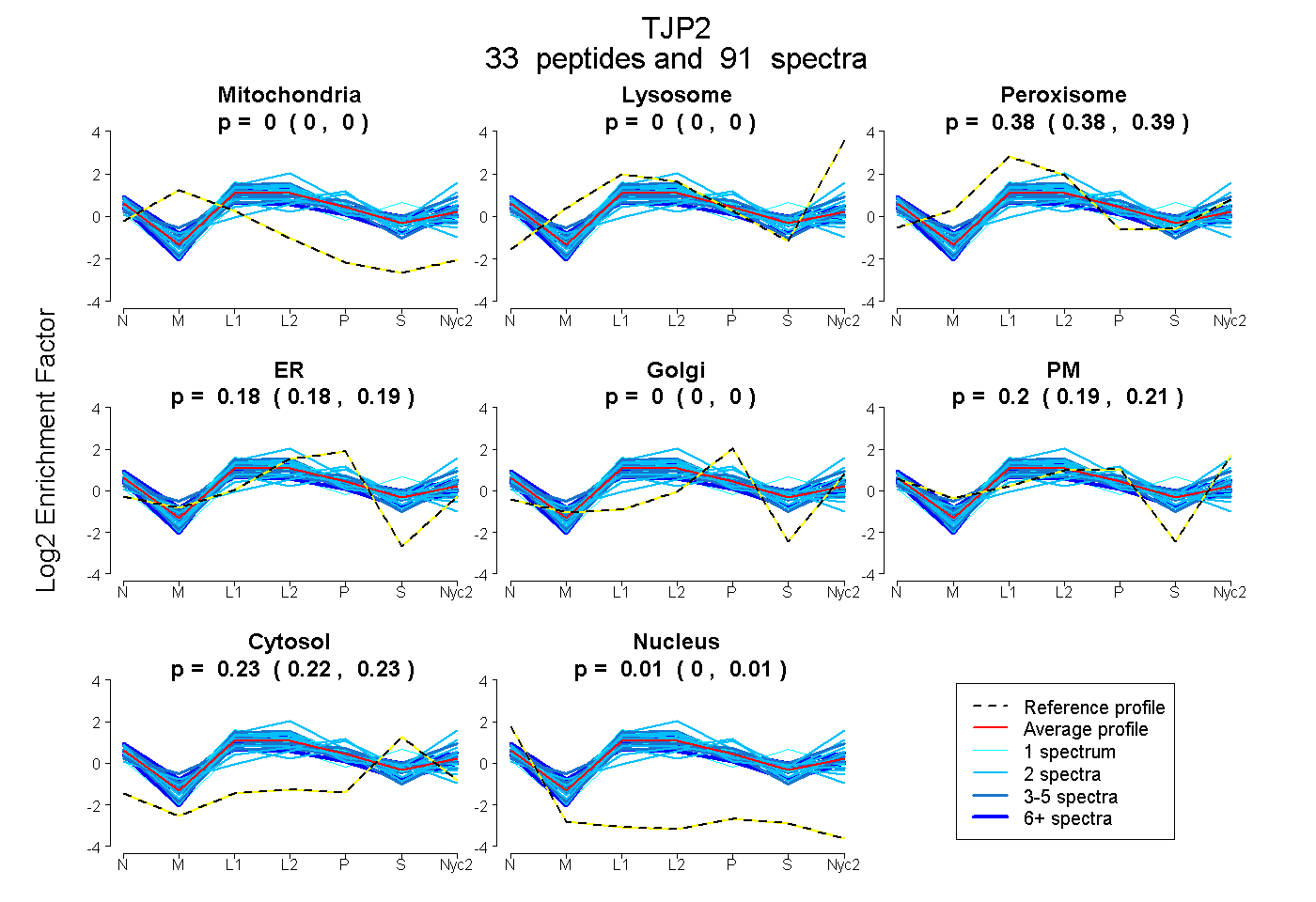
0.000 | 0.000
0.000 | 0.000
0.378 | 0.385
0.178 | 0.189
0.000 | 0.000
0.194 | 0.207
0.224 | 0.229
0.004 | 0.008
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
91 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.382 0.378 | 0.385 |
0.184 0.178 | 0.189 |
0.000 0.000 | 0.000 |
0.201 0.194 | 0.207 |
0.226 0.224 | 0.229 |
0.006 0.004 | 0.008 |
| 3 spectra, DGNLHEGDIILK | 0.000 | 0.000 | 0.383 | 0.092 | 0.000 | 0.328 | 0.190 | 0.008 | ||
| 1 spectrum, LFDQANK | 0.000 | 0.000 | 0.352 | 0.160 | 0.000 | 0.286 | 0.203 | 0.000 | ||
| 4 spectra, GETVTILAQSR | 0.000 | 0.000 | 0.436 | 0.145 | 0.000 | 0.125 | 0.252 | 0.041 | ||
| 2 spectra, SHFECEK | 0.000 | 0.000 | 0.421 | 0.262 | 0.000 | 0.000 | 0.238 | 0.079 | ||
| 6 spectra, GFEMMDEFDGR | 0.000 | 0.000 | 0.426 | 0.153 | 0.000 | 0.164 | 0.257 | 0.000 | ||
| 1 spectrum, ETPQSLAFTR | 0.000 | 0.000 | 0.358 | 0.103 | 0.000 | 0.055 | 0.485 | 0.000 | ||
| 3 spectra, SFSPEER | 0.000 | 0.000 | 0.253 | 0.209 | 0.000 | 0.253 | 0.284 | 0.000 | ||
| 2 spectra, SNLSAMAGSEIPGGSTK | 0.000 | 0.000 | 0.149 | 0.504 | 0.000 | 0.017 | 0.330 | 0.000 | ||
| 2 spectra, AEQMASVQNAQR | 0.000 | 0.000 | 0.490 | 0.335 | 0.000 | 0.000 | 0.117 | 0.058 | ||
| 2 spectra, LGHWLAVR | 0.000 | 0.000 | 0.467 | 0.279 | 0.000 | 0.000 | 0.194 | 0.059 | ||
| 2 spectra, VFLRPSPEDEAIYGPNTK | 0.000 | 0.023 | 0.440 | 0.000 | 0.000 | 0.390 | 0.147 | 0.000 | ||
| 1 spectrum, QIIEQDK | 0.000 | 0.000 | 0.303 | 0.332 | 0.000 | 0.165 | 0.200 | 0.000 | ||
| 3 spectra, RPVVLFGPIADIAMER | 0.000 | 0.000 | 0.398 | 0.239 | 0.000 | 0.072 | 0.262 | 0.029 | ||
| 2 spectra, IAAIVVK | 0.000 | 0.000 | 0.421 | 0.067 | 0.000 | 0.345 | 0.167 | 0.000 | ||
| 2 spectra, SSGVVR | 0.000 | 0.000 | 0.336 | 0.140 | 0.000 | 0.236 | 0.289 | 0.000 | ||
| 2 spectra, SQEESPVPQPR | 0.000 | 0.000 | 0.471 | 0.294 | 0.000 | 0.008 | 0.177 | 0.050 | ||
| 2 spectra, INGTVTENMSLTDAR | 0.000 | 0.000 | 0.458 | 0.297 | 0.000 | 0.190 | 0.054 | 0.000 | ||
| 6 spectra, ANEEYGLR | 0.000 | 0.000 | 0.381 | 0.211 | 0.000 | 0.134 | 0.269 | 0.005 | ||
| 1 spectrum, LTTELPDLFQTAK | 0.000 | 0.000 | 0.463 | 0.018 | 0.000 | 0.365 | 0.153 | 0.000 | ||
| 4 spectra, GDSFFIR | 0.000 | 0.000 | 0.510 | 0.103 | 0.000 | 0.220 | 0.143 | 0.024 | ||
| 4 spectra, LGSQIFIK | 0.000 | 0.000 | 0.353 | 0.130 | 0.000 | 0.354 | 0.079 | 0.084 | ||
| 2 spectra, FPAYEK | 0.000 | 0.000 | 0.424 | 0.326 | 0.000 | 0.000 | 0.215 | 0.035 | ||
| 5 spectra, GLDHEDYGR | 0.000 | 0.000 | 0.427 | 0.208 | 0.000 | 0.122 | 0.223 | 0.020 | ||
| 2 spectra, GYYSQPSR | 0.000 | 0.000 | 0.237 | 0.195 | 0.000 | 0.232 | 0.335 | 0.000 | ||
| 2 spectra, GFGIAVSGGR | 0.000 | 0.000 | 0.391 | 0.130 | 0.000 | 0.329 | 0.139 | 0.012 | ||
| 4 spectra, DILACGR | 0.000 | 0.000 | 0.514 | 0.169 | 0.000 | 0.109 | 0.163 | 0.045 | ||
| 3 spectra, EDAVLYLLEIPK | 0.000 | 0.000 | 0.544 | 0.157 | 0.000 | 0.065 | 0.171 | 0.063 | ||
| 6 spectra, GDSVGLR | 0.000 | 0.000 | 0.384 | 0.040 | 0.000 | 0.325 | 0.106 | 0.144 | ||
| 1 spectrum, KPSPEPR | 0.000 | 0.000 | 0.479 | 0.336 | 0.000 | 0.000 | 0.174 | 0.011 | ||
| 4 spectra, SSEPVQHEESIR | 0.000 | 0.000 | 0.387 | 0.000 | 0.000 | 0.374 | 0.240 | 0.000 | ||
| 2 spectra, MQELQEAQNAR | 0.000 | 0.000 | 0.308 | 0.000 | 0.000 | 0.481 | 0.211 | 0.000 | ||
| 3 spectra, LQLVVLR | 0.000 | 0.000 | 0.445 | 0.163 | 0.000 | 0.214 | 0.173 | 0.005 | ||
| 2 spectra, VNTQDFR | 0.000 | 0.000 | 0.130 | 0.259 | 0.000 | 0.381 | 0.229 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
26 spectra |
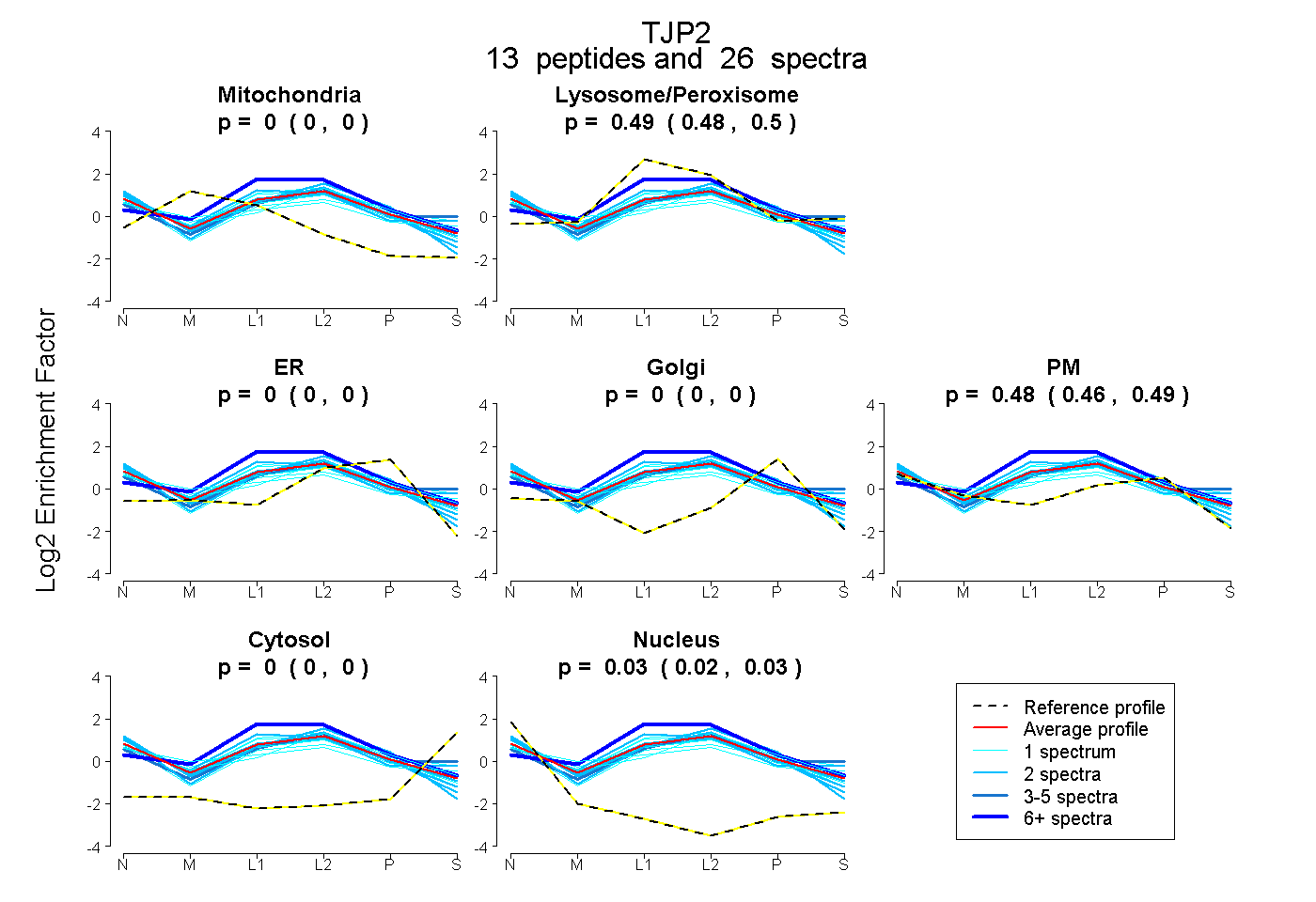 |
0.000 0.000 | 0.000 |
0.492 0.481 | 0.501 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.478 0.464 | 0.490 |
0.000 0.000 | 0.000 |
0.030 0.024 | 0.035 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
136 spectra |
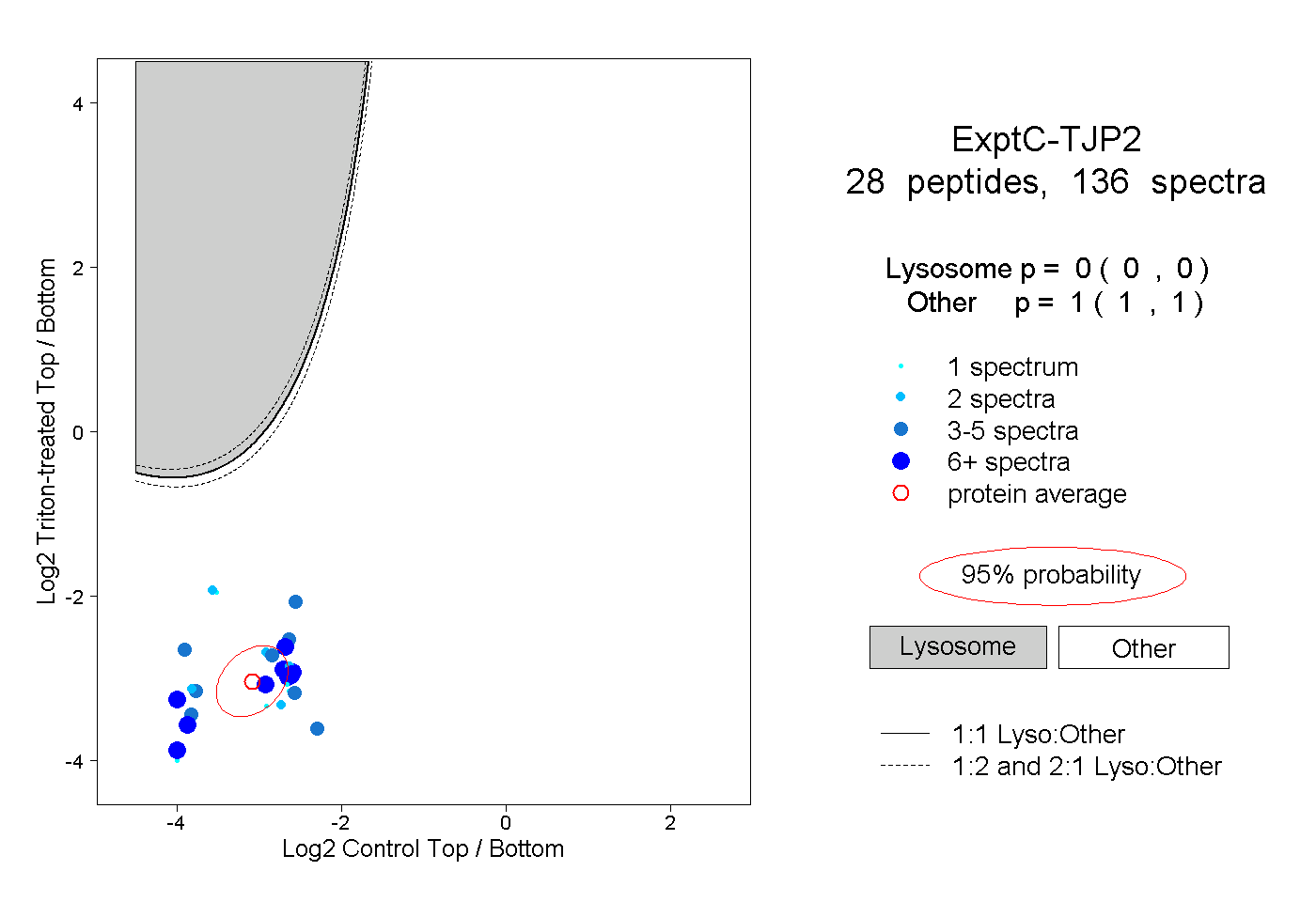 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
26 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |