peptides
spectra
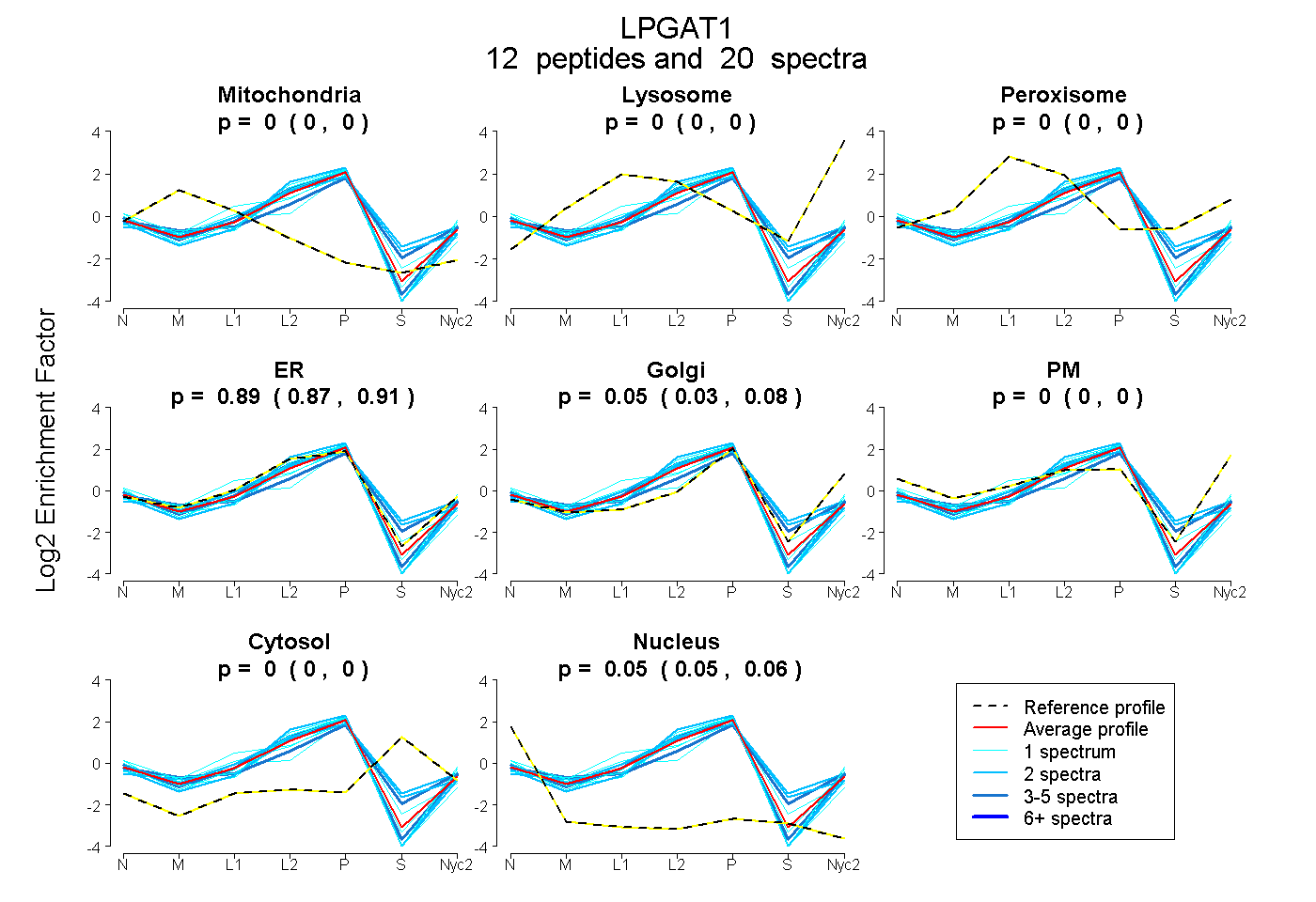
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.866 | 0.910
0.032 | 0.075
0.000 | 0.000
0.000 | 0.000
0.050 | 0.058
peptides
spectra
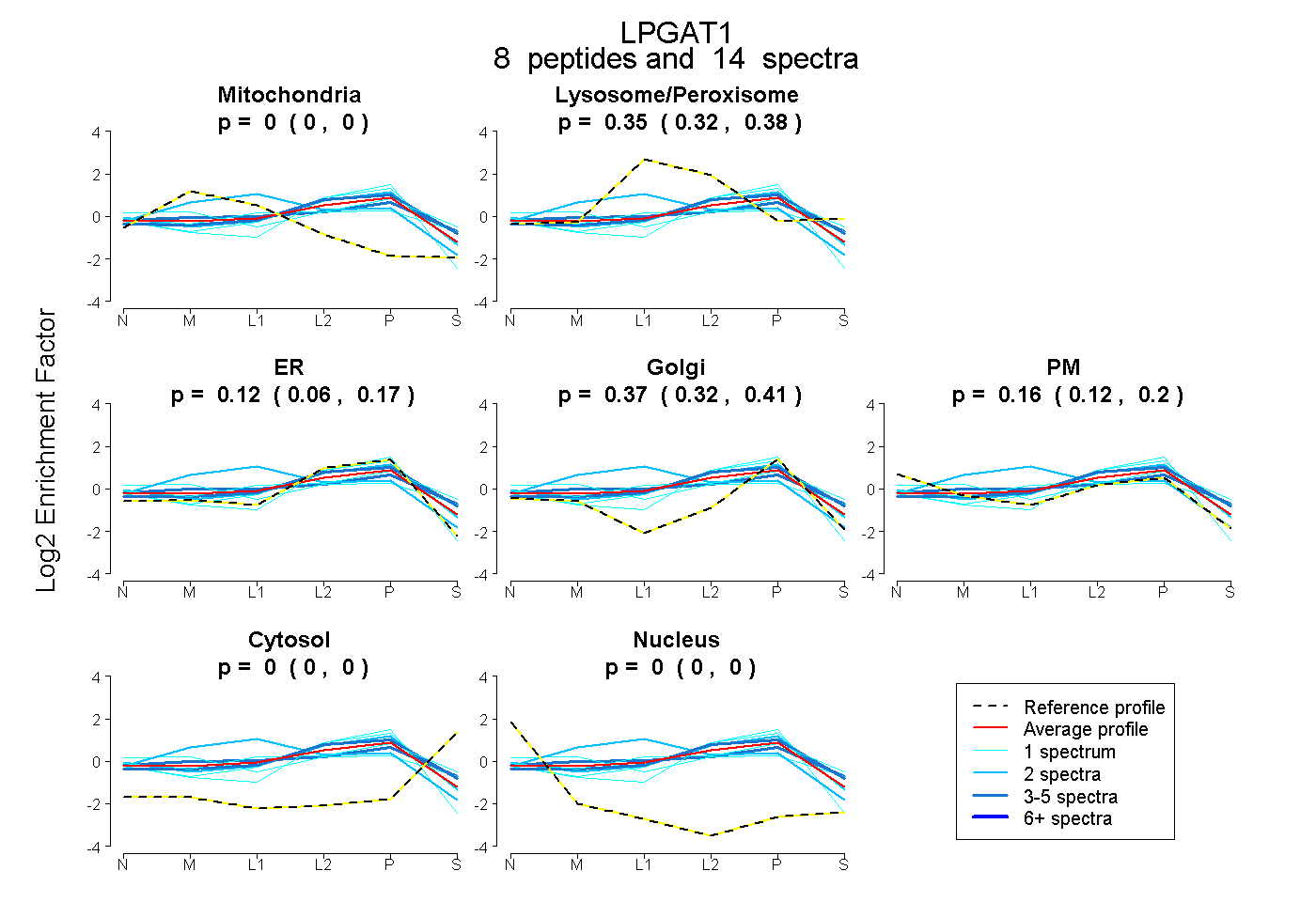
0.000 | 0.000
0.316 | 0.376
0.063 | 0.168
0.316 | 0.413
0.124 | 0.196
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
20 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.891 0.866 | 0.910 |
0.055 0.032 | 0.075 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.054 0.050 | 0.058 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
14 spectra |
 |
0.000 0.000 | 0.000 |
0.347 0.316 | 0.376 |
0.119 0.063 | 0.168 |
0.370 0.316 | 0.413 |
0.163 0.124 | 0.196 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, AVTVEEAPWLGWIVAK | 0.000 | 0.248 | 0.350 | 0.216 | 0.186 | 0.000 | 0.000 | |||
| 1 spectrum, FGATNIILK | 0.000 | 0.000 | 0.932 | 0.036 | 0.008 | 0.000 | 0.023 | |||
| 1 spectrum, TGAFPPPQGQK | 0.000 | 0.458 | 0.000 | 0.458 | 0.042 | 0.043 | 0.000 | |||
| 1 spectrum, HLEHNYR | 0.056 | 0.204 | 0.000 | 0.094 | 0.537 | 0.109 | 0.000 | |||
| 2 spectra, KPTVTHVHYR | 0.344 | 0.262 | 0.331 | 0.000 | 0.063 | 0.000 | 0.000 | |||
| 3 spectra, NNLPFLTHVTLPR | 0.000 | 0.384 | 0.212 | 0.386 | 0.000 | 0.017 | 0.000 | |||
| 1 spectrum, EDLLSHFYK | 0.000 | 0.233 | 0.532 | 0.219 | 0.016 | 0.000 | 0.000 | |||
| 3 spectra, ETSQAFAK | 0.025 | 0.407 | 0.000 | 0.436 | 0.096 | 0.037 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
25 spectra |
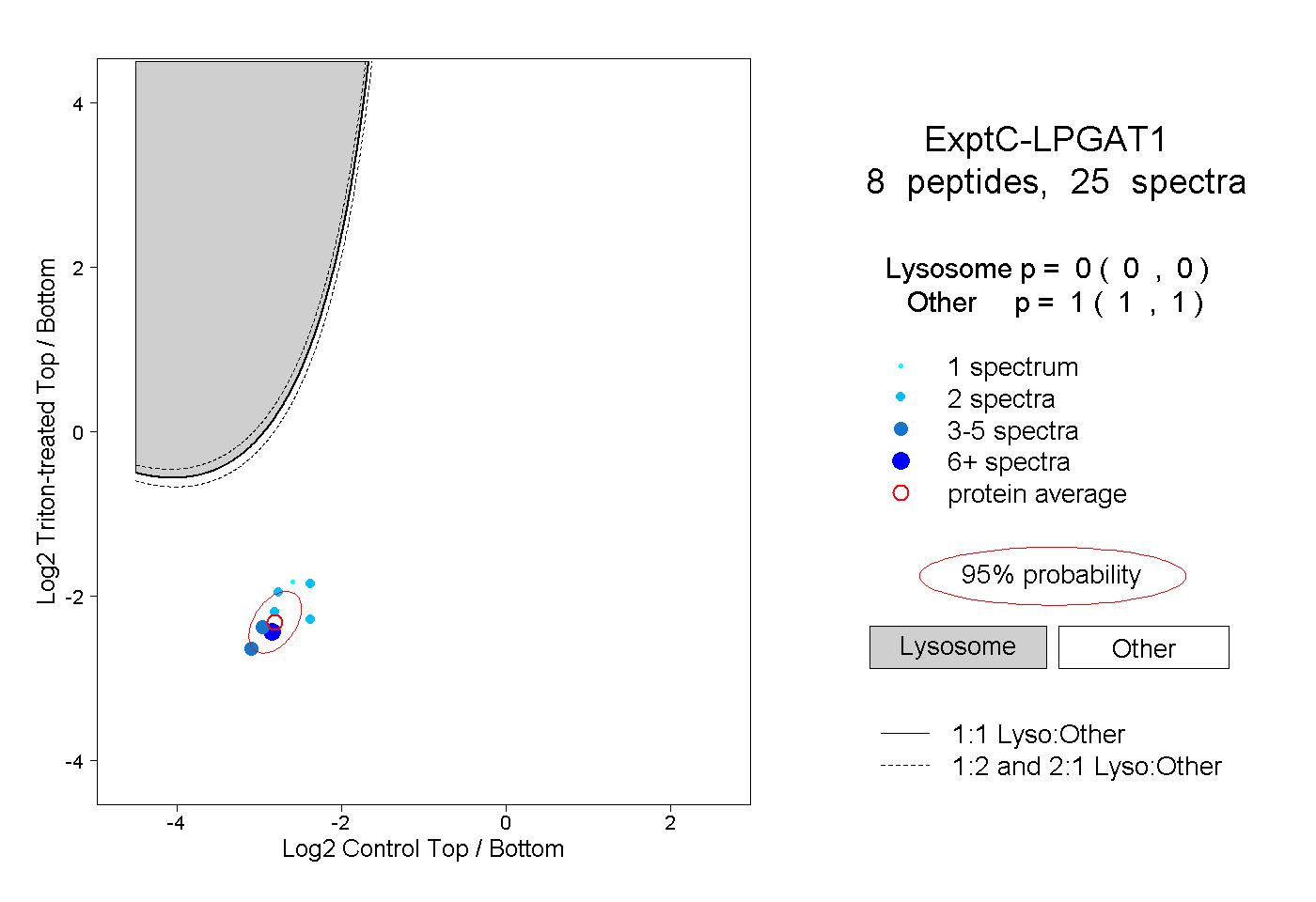 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
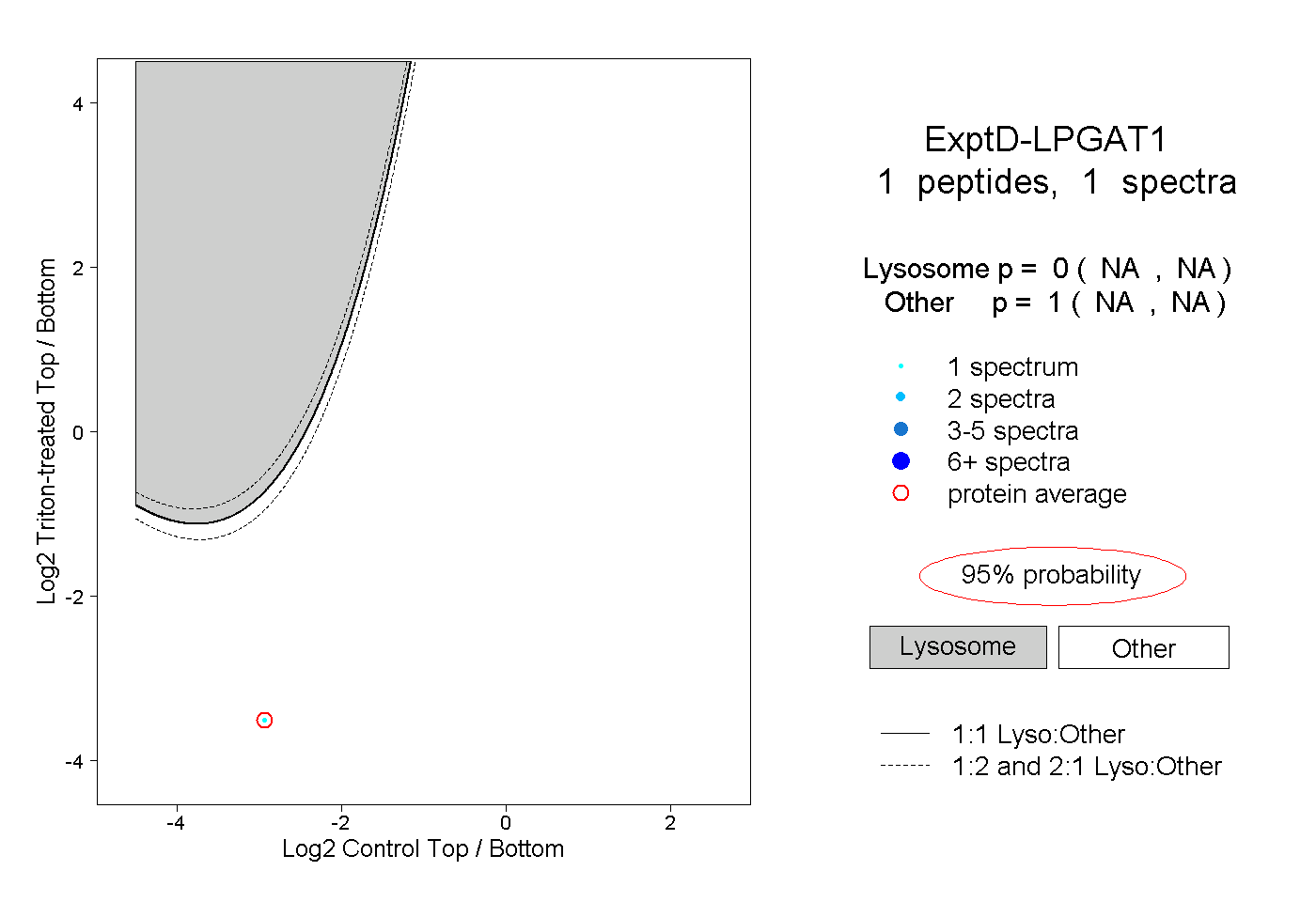 |
0.000 NA | NA |
1.000 NA | NA |