peptides
spectra
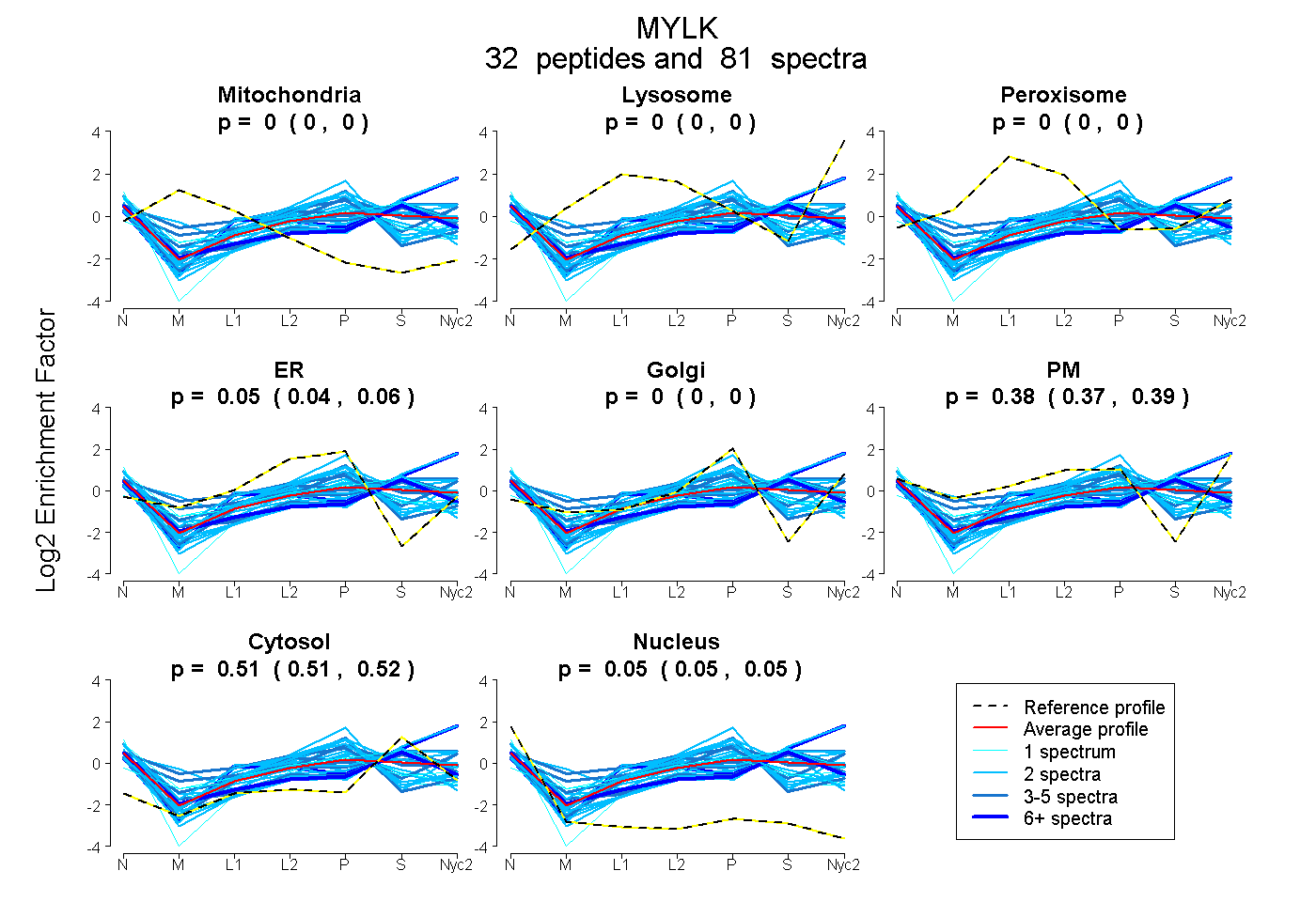
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.040 | 0.060
0.000 | 0.000
0.373 | 0.394
0.508 | 0.517
0.048 | 0.054
peptides
spectra
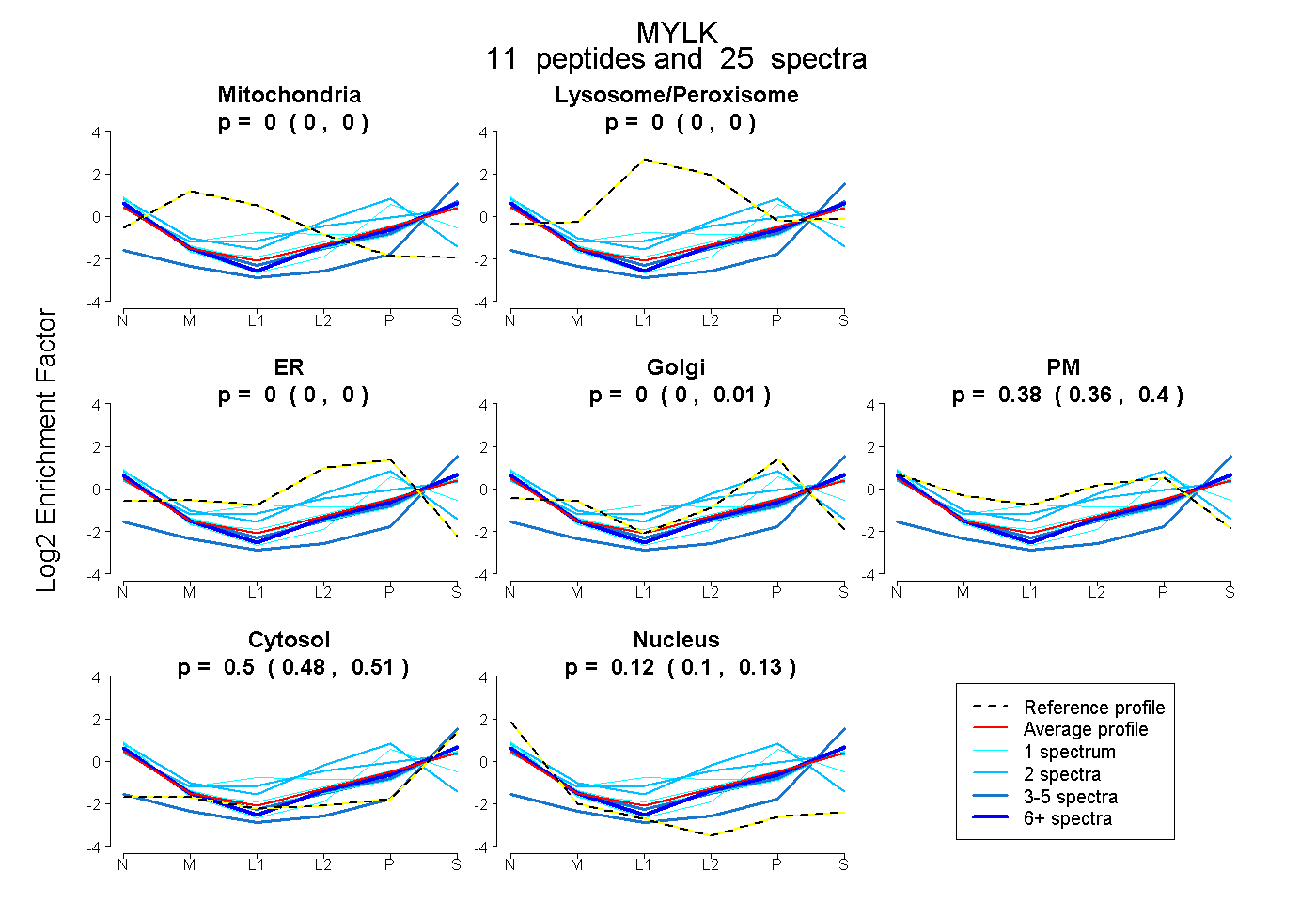
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.010
0.364 | 0.396
0.480 | 0.513
0.101 | 0.133
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
81 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.051 0.040 | 0.060 |
0.000 0.000 | 0.000 |
0.385 0.373 | 0.394 |
0.513 0.508 | 0.517 |
0.052 0.048 | 0.054 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
25 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.010 |
0.384 0.364 | 0.396 |
0.498 0.480 | 0.513 |
0.118 0.101 | 0.133 |
| 6 spectra, VSDVYDIEER | 0.000 | 0.000 | 0.000 | 0.002 | 0.314 | 0.531 | 0.153 | |||
| 5 spectra, IIDFGLAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.962 | 0.038 | |||
| 1 spectrum, DLEVVEGSAAR | 0.000 | 0.283 | 0.000 | 0.000 | 0.141 | 0.432 | 0.144 | |||
| 1 spectrum, QATPPTR | 0.000 | 0.000 | 0.000 | 0.555 | 0.000 | 0.184 | 0.261 | |||
| 4 spectra, LTILAAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.295 | 0.548 | 0.157 | |||
| 1 spectrum, ALPEDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.410 | 0.474 | 0.116 | |||
| 2 spectra, QIQESENIR | 0.000 | 0.089 | 0.000 | 0.000 | 0.509 | 0.402 | 0.000 | |||
| 1 spectrum, LQDVHVAEGEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.333 | 0.466 | 0.201 | |||
| 1 spectrum, LVQCVDAFEEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.310 | 0.526 | 0.165 | |||
| 2 spectra, FLLDGGVR | 0.000 | 0.000 | 0.000 | 0.281 | 0.633 | 0.033 | 0.054 | |||
| 1 spectrum, FGQVFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.338 | 0.529 | 0.132 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
101 spectra |
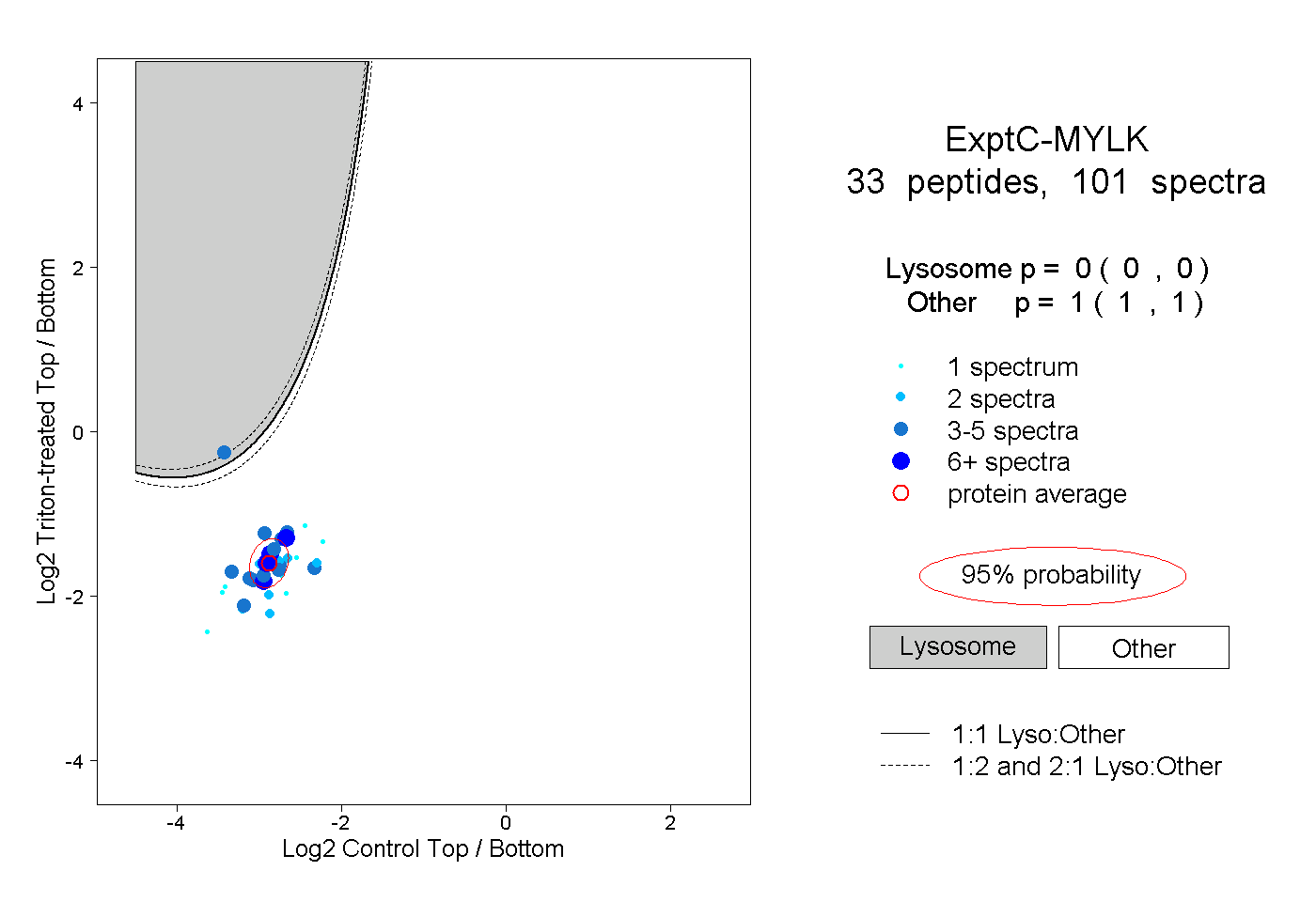 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
18 spectra |
 |
0.000 0.000 | 0.177 |
1.000 0.821 | 1.000 |