peptides
spectra
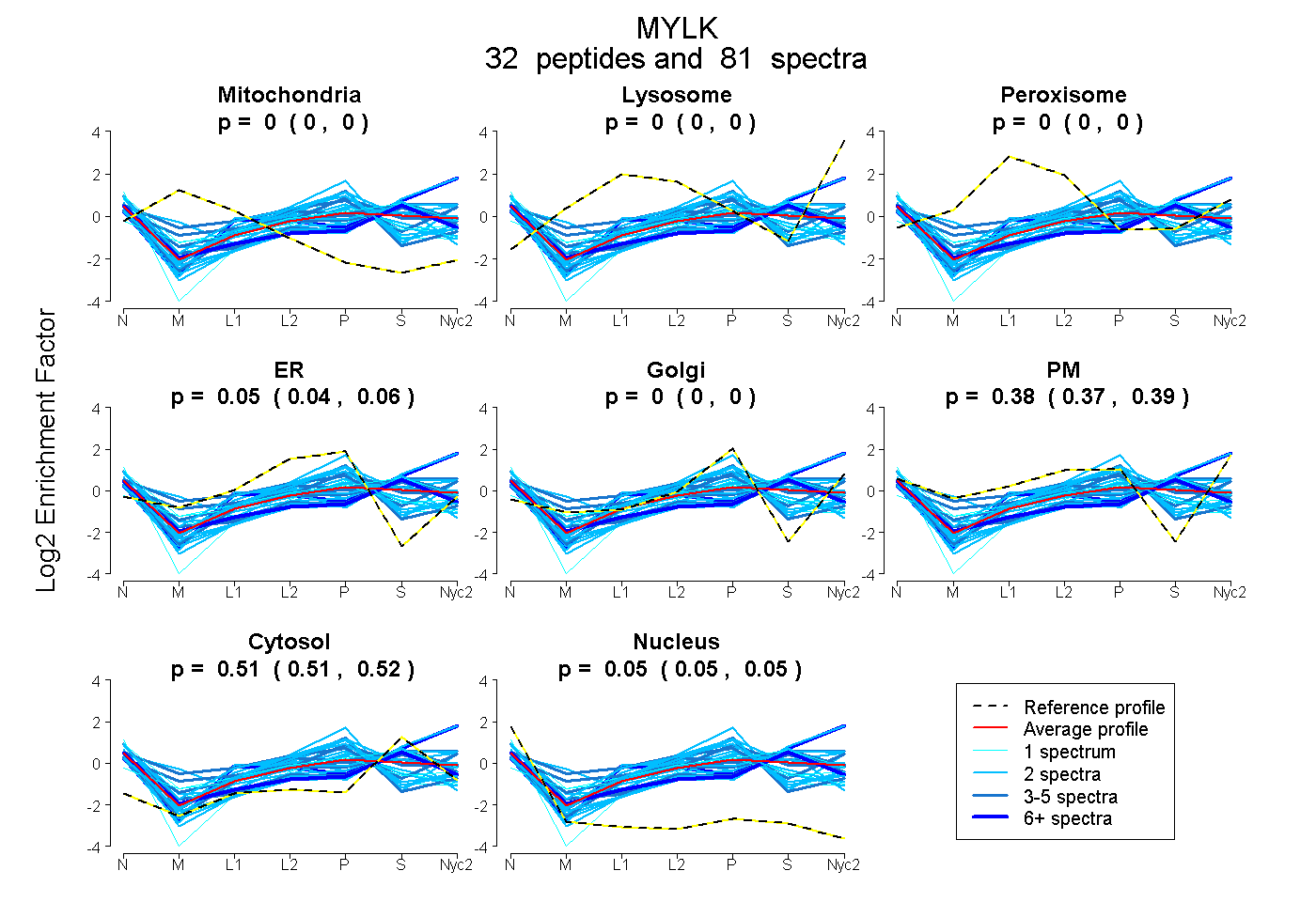
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.040 | 0.060
0.000 | 0.000
0.373 | 0.394
0.508 | 0.517
0.048 | 0.054
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
81 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.051 0.040 | 0.060 |
0.000 0.000 | 0.000 |
0.385 0.373 | 0.394 |
0.513 0.508 | 0.517 |
0.052 0.048 | 0.054 |
| 1 spectrum, GQGWPEEEDGEDVR | 0.000 | 0.000 | 0.000 | 0.223 | 0.144 | 0.000 | 0.399 | 0.235 | ||
| 2 spectra, DDQSIR | 0.000 | 0.211 | 0.000 | 0.000 | 0.000 | 0.249 | 0.541 | 0.000 | ||
| 2 spectra, TSHSVDPSR | 0.000 | 0.000 | 0.021 | 0.432 | 0.000 | 0.200 | 0.250 | 0.098 | ||
| 1 spectrum, ALPEDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.302 | 0.670 | 0.028 | ||
| 4 spectra, GNVPLQPSAR | 0.000 | 0.000 | 0.000 | 0.473 | 0.113 | 0.073 | 0.175 | 0.166 | ||
| 2 spectra, DGTLRPCWPAR | 0.142 | 0.000 | 0.000 | 0.328 | 0.124 | 0.035 | 0.311 | 0.060 | ||
| 3 spectra, FGQVFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.282 | 0.661 | 0.057 | ||
| 1 spectrum, TQAILTVQEPHDGTQPWFISKPR | 0.000 | 0.000 | 0.044 | 0.114 | 0.000 | 0.399 | 0.296 | 0.148 | ||
| 2 spectra, ILDFGLAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.212 | 0.662 | 0.126 | ||
| 2 spectra, AAGIGASGPGEER | 0.000 | 0.000 | 0.000 | 0.228 | 0.384 | 0.192 | 0.195 | 0.000 | ||
| 3 spectra, QIQESENIR | 0.000 | 0.000 | 0.037 | 0.000 | 0.000 | 0.373 | 0.568 | 0.022 | ||
| 6 spectra, DLEVVEGSAAR | 0.000 | 0.203 | 0.000 | 0.000 | 0.000 | 0.226 | 0.571 | 0.000 | ||
| 2 spectra, IIDEDFELTER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.202 | 0.668 | 0.130 | ||
| 4 spectra, QISEGVEYIHK | 0.009 | 0.000 | 0.103 | 0.053 | 0.000 | 0.332 | 0.474 | 0.029 | ||
| 2 spectra, DIPAEQMDFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.102 | 0.419 | 0.479 | 0.000 | ||
| 2 spectra, IEGYPDPEVVWFK | 0.000 | 0.240 | 0.000 | 0.000 | 0.000 | 0.166 | 0.594 | 0.000 | ||
| 4 spectra, LSSMAMISGLSGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.422 | 0.578 | 0.000 | ||
| 4 spectra, TPVPEK | 0.003 | 0.000 | 0.059 | 0.086 | 0.000 | 0.569 | 0.275 | 0.008 | ||
| 2 spectra, YTCEASNGSGAR | 0.000 | 0.000 | 0.000 | 0.495 | 0.025 | 0.119 | 0.243 | 0.118 | ||
| 2 spectra, LDCTQCLQHPWLMK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.365 | 0.635 | 0.000 | ||
| 7 spectra, VSDVYDIEER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.261 | 0.626 | 0.113 | ||
| 2 spectra, GTFSLVIR | 0.000 | 0.000 | 0.000 | 0.317 | 0.150 | 0.187 | 0.212 | 0.134 | ||
| 4 spectra, LTILAAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.290 | 0.610 | 0.100 | ||
| 3 spectra, QATPPTR | 0.000 | 0.000 | 0.000 | 0.084 | 0.260 | 0.173 | 0.456 | 0.028 | ||
| 2 spectra, VQPEVR | 0.000 | 0.000 | 0.000 | 0.257 | 0.145 | 0.162 | 0.436 | 0.000 | ||
| 1 spectrum, VHSPQQVDFR | 0.000 | 0.000 | 0.031 | 0.091 | 0.027 | 0.255 | 0.596 | 0.000 | ||
| 2 spectra, DSVVIEGQDFVLR | 0.000 | 0.000 | 0.000 | 0.200 | 0.031 | 0.211 | 0.378 | 0.179 | ||
| 2 spectra, LVQCVDAFEEK | 0.000 | 0.000 | 0.000 | 0.148 | 0.000 | 0.027 | 0.630 | 0.194 | ||
| 2 spectra, RPESQGSAPVFK | 0.000 | 0.000 | 0.000 | 0.102 | 0.020 | 0.315 | 0.516 | 0.047 | ||
| 1 spectrum, ASGFPGETRPSIWGECPPK | 0.000 | 0.000 | 0.000 | 0.426 | 0.171 | 0.000 | 0.238 | 0.165 | ||
| 2 spectra, STSFNVQDLLPDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.205 | 0.683 | 0.112 | ||
| 2 spectra, TGNAVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.401 | 0.599 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
25 spectra |
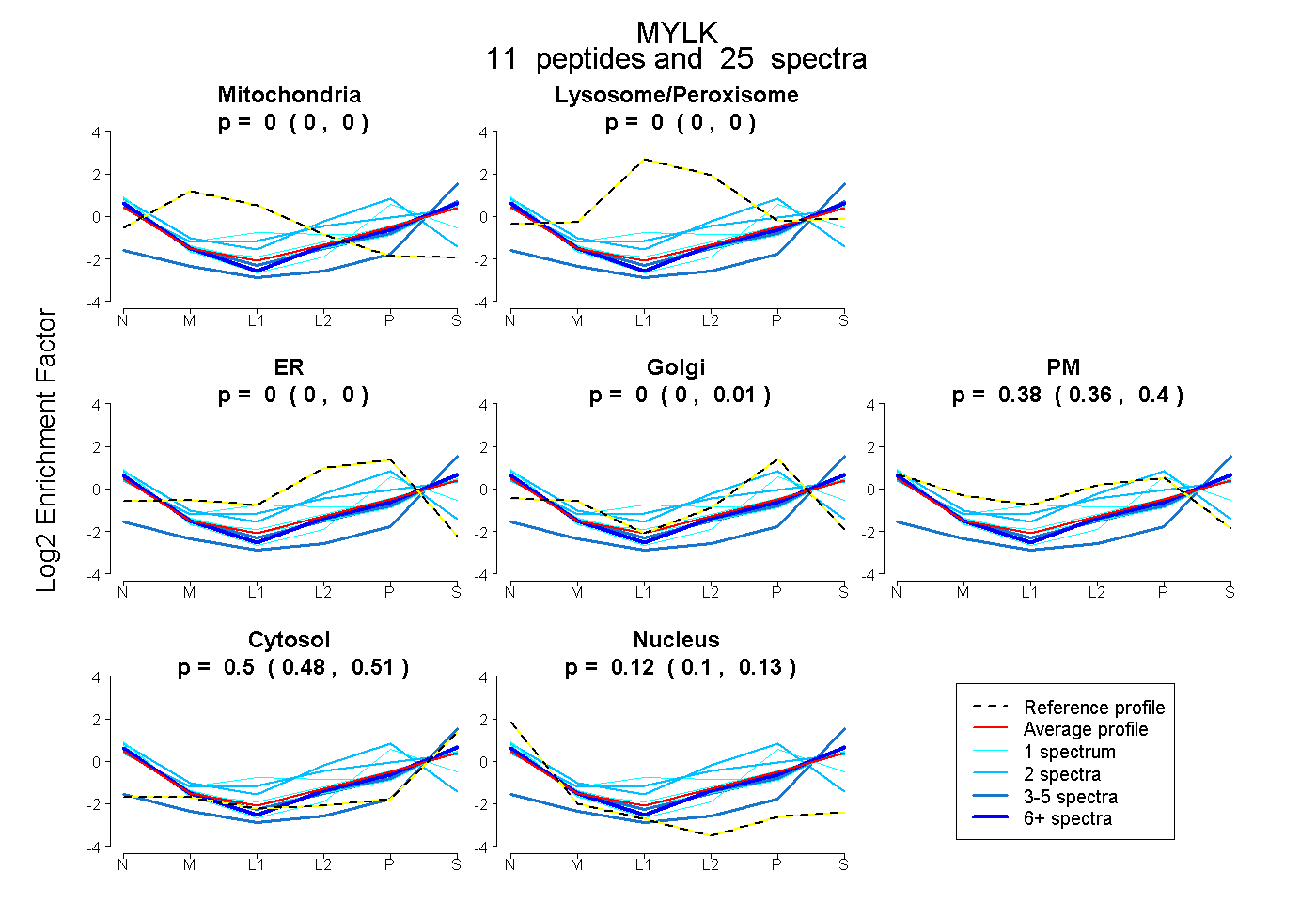 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.010 |
0.384 0.364 | 0.396 |
0.498 0.480 | 0.513 |
0.118 0.101 | 0.133 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
101 spectra |
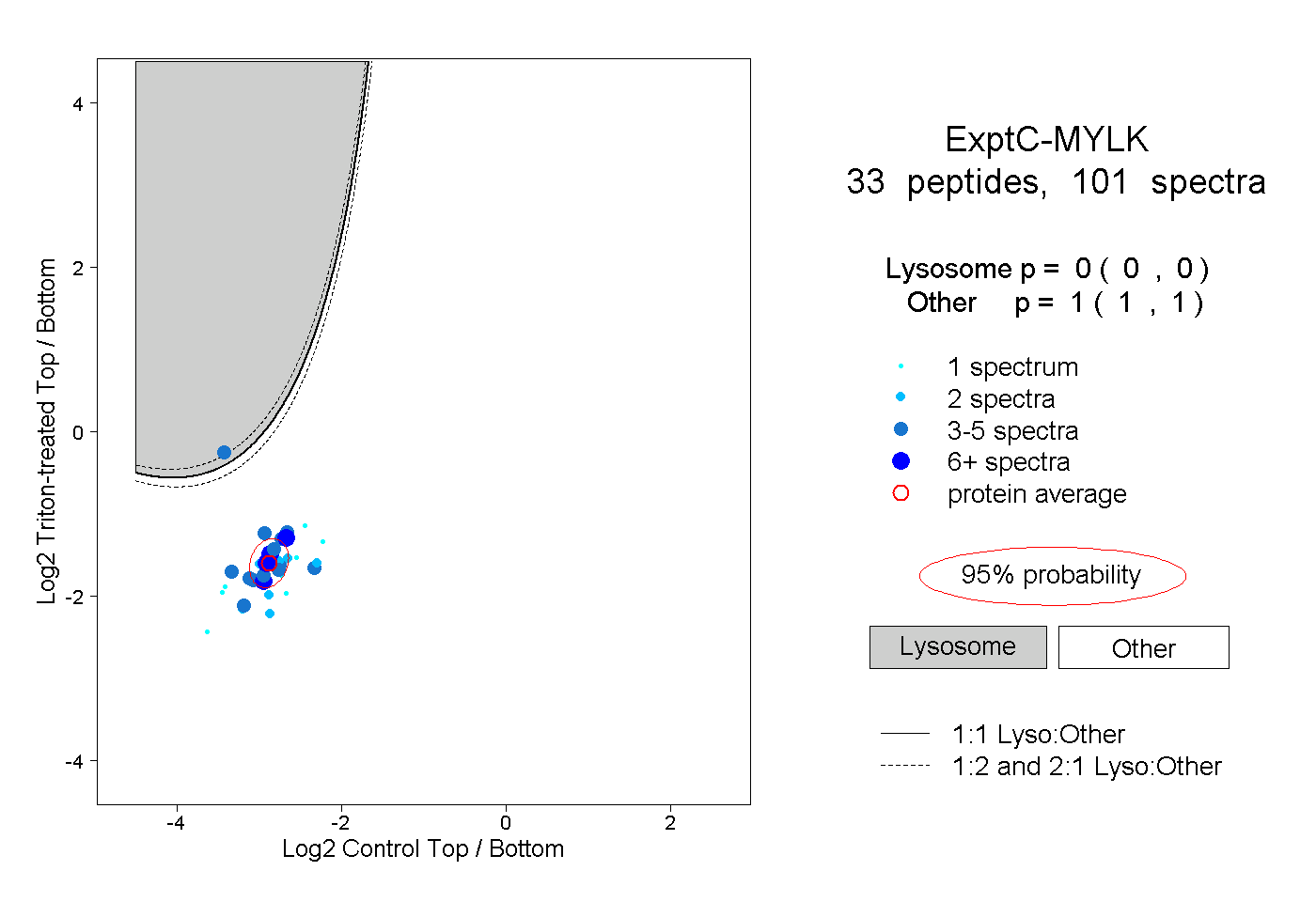 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
18 spectra |
 |
0.000 0.000 | 0.177 |
1.000 0.821 | 1.000 |