peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.428 | 0.437
0.563 | 0.571
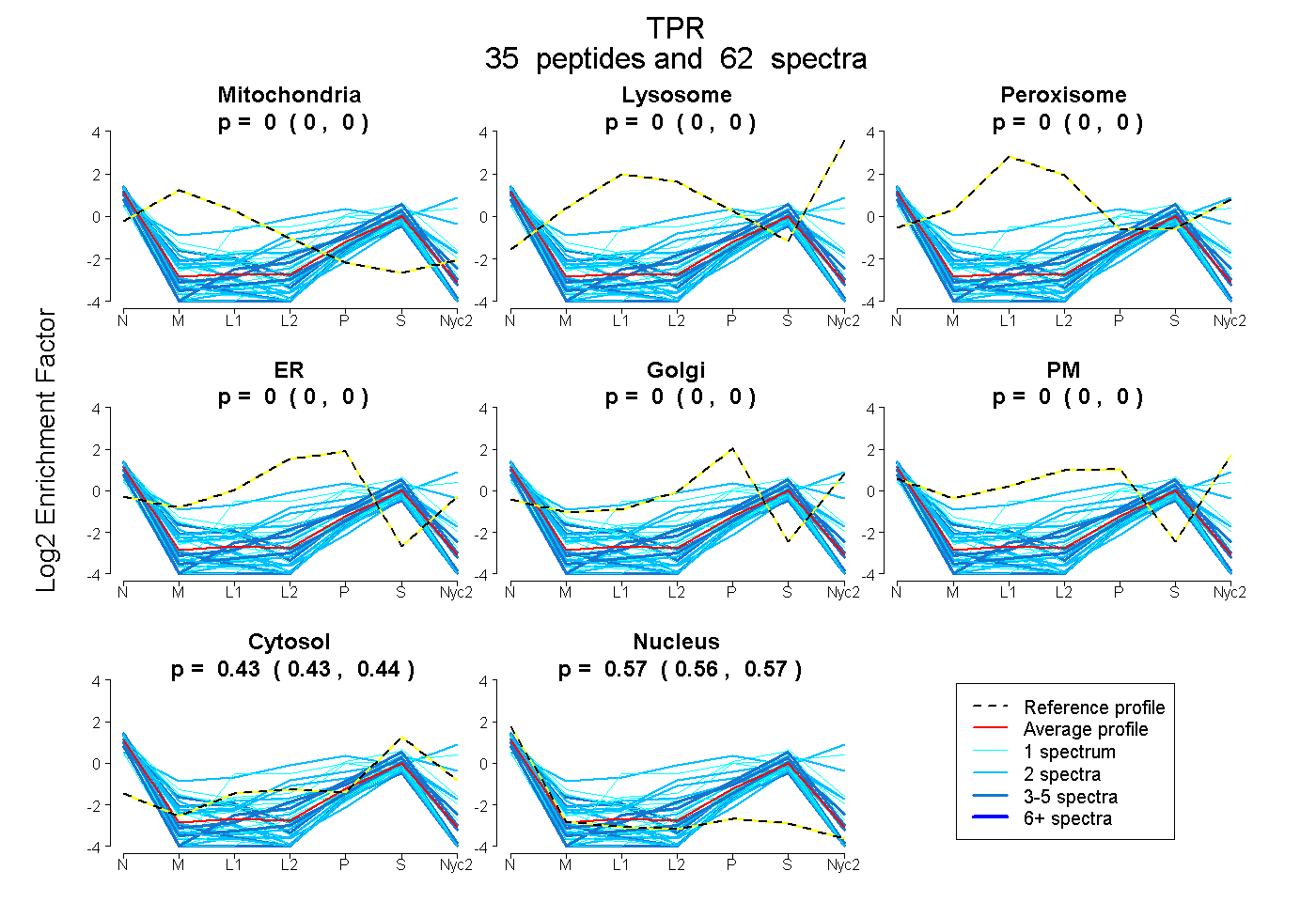
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
62 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.433 0.428 | 0.437 |
0.567 0.563 | 0.571 |
| 1 spectrum, QAEEQVNDLK | 0.034 | 0.000 | 0.000 | 0.000 | 0.055 | 0.051 | 0.451 | 0.410 | ||
| 1 spectrum, EQQASMEEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.334 | 0.666 | ||
| 2 spectra, FEVAQVESLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.286 | 0.714 | ||
| 3 spectra, LENSLTELEQLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.207 | 0.793 | ||
| 1 spectrum, SLQEQTAQLQSELSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.358 | 0.573 | 0.069 | ||
| 1 spectrum, LQNEQLEK | 0.000 | 0.000 | 0.000 | 0.130 | 0.000 | 0.000 | 0.312 | 0.558 | ||
| 2 spectra, LEQNLQQMQAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.588 | 0.412 | 0.000 | ||
| 3 spectra, TTPASGER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.555 | 0.445 | ||
| 3 spectra, ASTALSNEQQAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.227 | 0.773 | ||
| 2 spectra, AVDELHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.246 | 0.754 | ||
| 2 spectra, HVEDLLTK | 0.000 | 0.000 | 0.000 | 0.006 | 0.000 | 0.000 | 0.349 | 0.645 | ||
| 1 spectrum, QVTEEVHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.358 | 0.642 | ||
| 2 spectra, LEEQMNGLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.199 | 0.582 | 0.219 | ||
| 2 spectra, SAADDSEAK | 0.000 | 0.000 | 0.000 | 0.222 | 0.000 | 0.004 | 0.474 | 0.301 | ||
| 1 spectrum, DLSQQIR | 0.061 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.303 | 0.635 | ||
| 1 spectrum, APEQQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.316 | 0.684 | ||
| 1 spectrum, SQEQILEILR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.256 | 0.744 | ||
| 2 spectra, LEHEISHLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.287 | 0.713 | ||
| 3 spectra, VLLMELEEAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.497 | 0.503 | ||
| 1 spectrum, LDELQASDVTVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.391 | 0.609 | ||
| 1 spectrum, LTATTQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.235 | 0.765 | ||
| 1 spectrum, EITSLQER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.315 | 0.685 | ||
| 2 spectra, TSNEHLQK | 0.000 | 0.000 | 0.000 | 0.100 | 0.000 | 0.088 | 0.447 | 0.365 | ||
| 3 spectra, TSASNVEQYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.438 | 0.562 | ||
| 4 spectra, AESQLLECK | 0.009 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.394 | 0.597 | ||
| 3 spectra, AMVTSLEDSLNK | 0.047 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.375 | 0.577 | ||
| 1 spectrum, NIEELQQQNQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.313 | 0.687 | ||
| 2 spectra, IIDIQEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.252 | 0.748 | ||
| 1 spectrum, LQEDTDK | 0.080 | 0.000 | 0.000 | 0.000 | 0.000 | 0.006 | 0.659 | 0.255 | ||
| 1 spectrum, QEQIINTMTQDLR | 0.179 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.384 | 0.437 | ||
| 1 spectrum, IAELQNK | 0.000 | 0.000 | 0.030 | 0.036 | 0.000 | 0.000 | 0.522 | 0.413 | ||
| 2 spectra, FHNELNAHIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.246 | 0.754 | ||
| 2 spectra, LSQSQER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.353 | 0.647 | ||
| 2 spectra, YLDEIVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.210 | 0.790 | ||
| 1 spectrum, GNEILELK | 0.000 | 0.000 | 0.000 | 0.098 | 0.000 | 0.000 | 0.621 | 0.281 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
5 spectra |
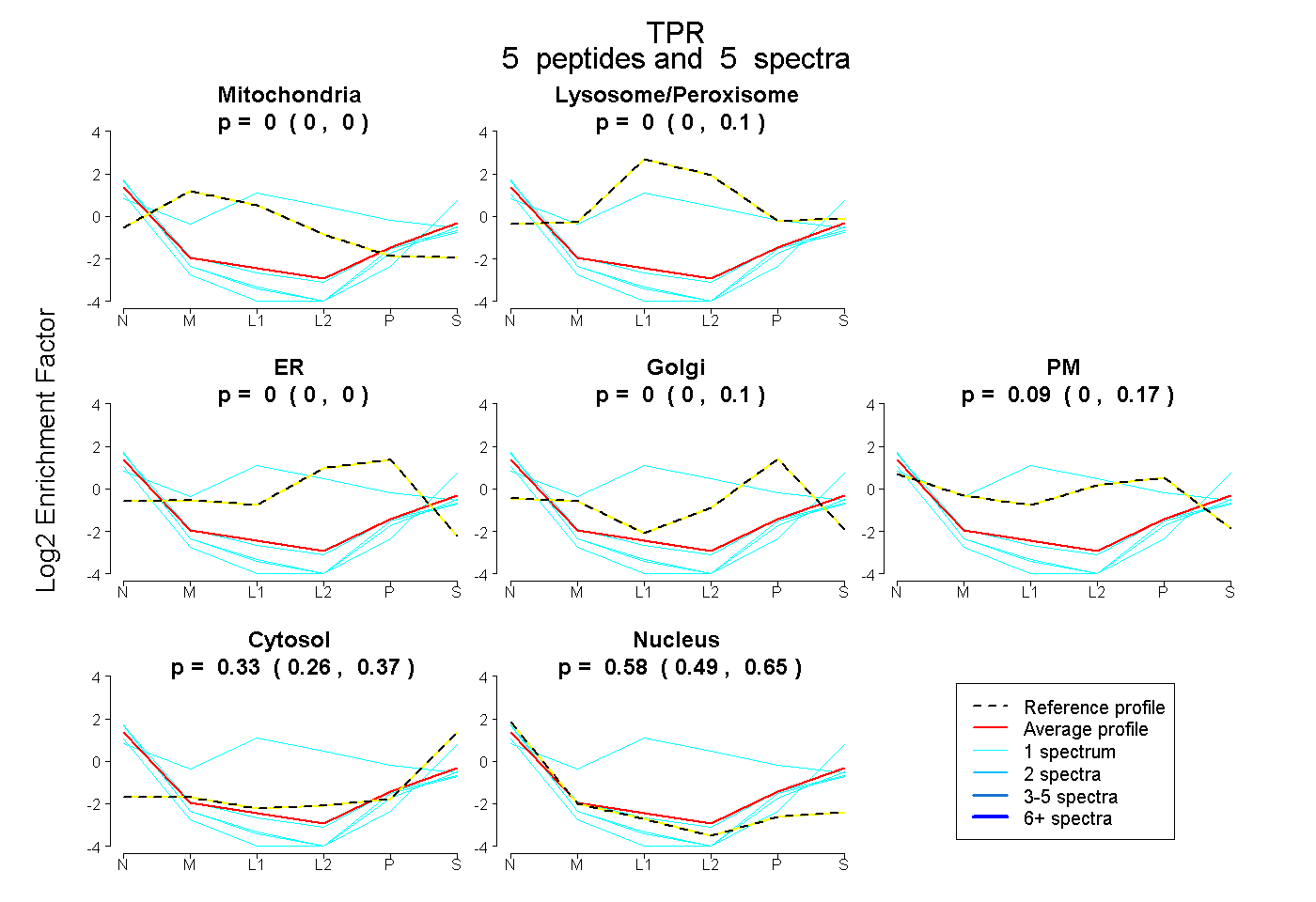 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.097 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.103 |
0.089 0.000 | 0.166 |
0.333 0.255 | 0.367 |
0.578 0.487 | 0.653 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
5 spectra |
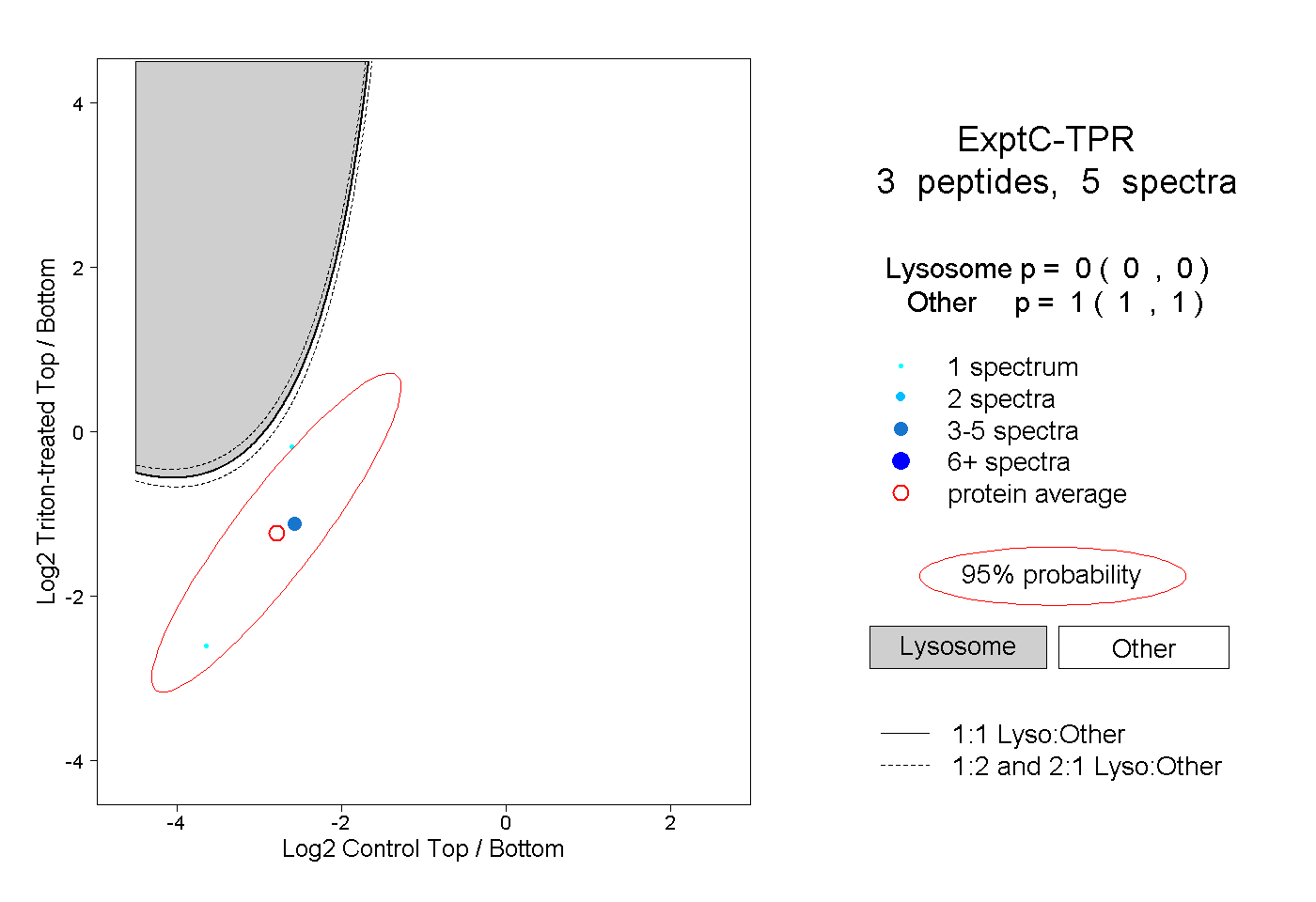 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |