peptides
spectra
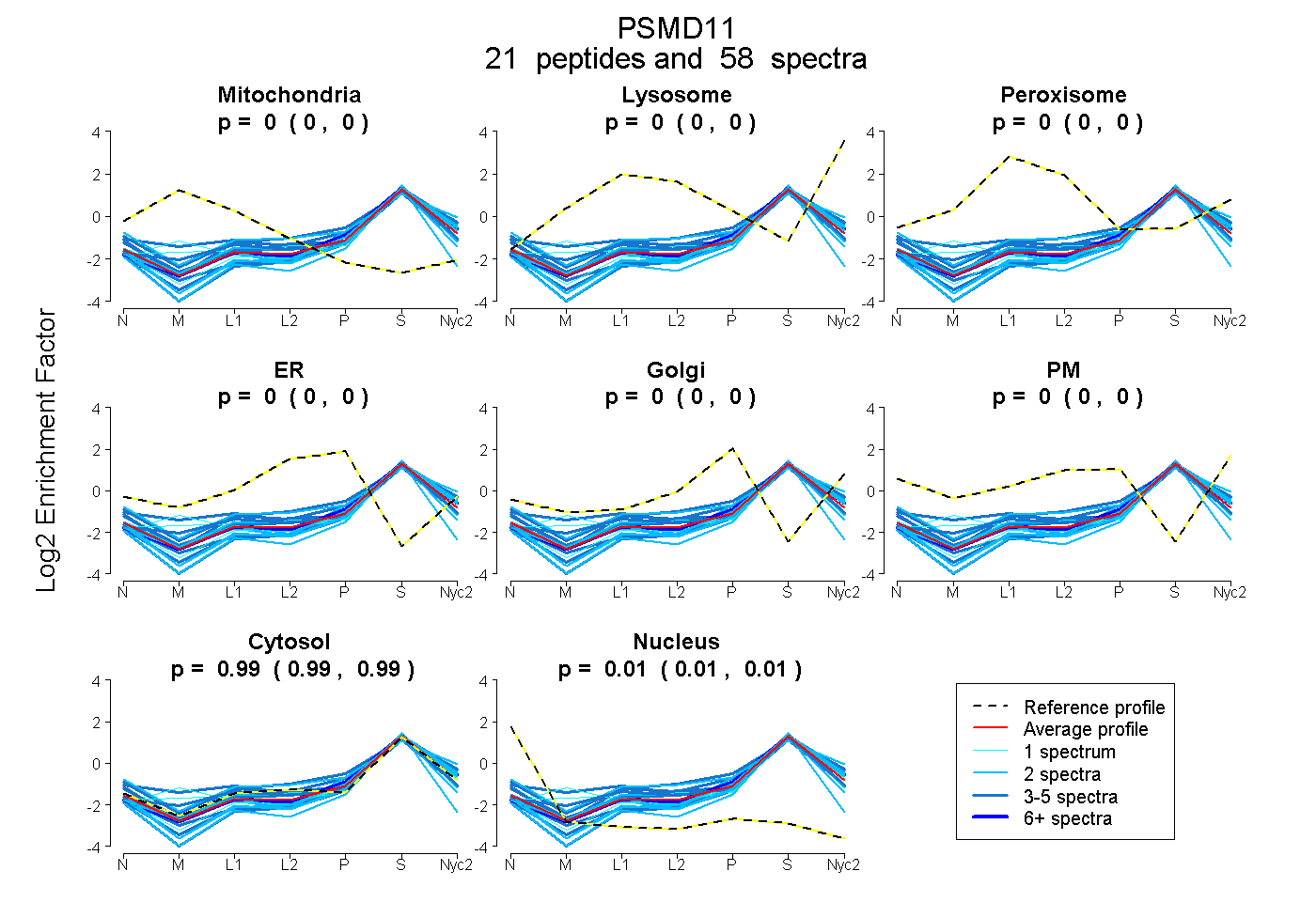
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.986 | 0.991
0.008 | 0.013
peptides
spectra
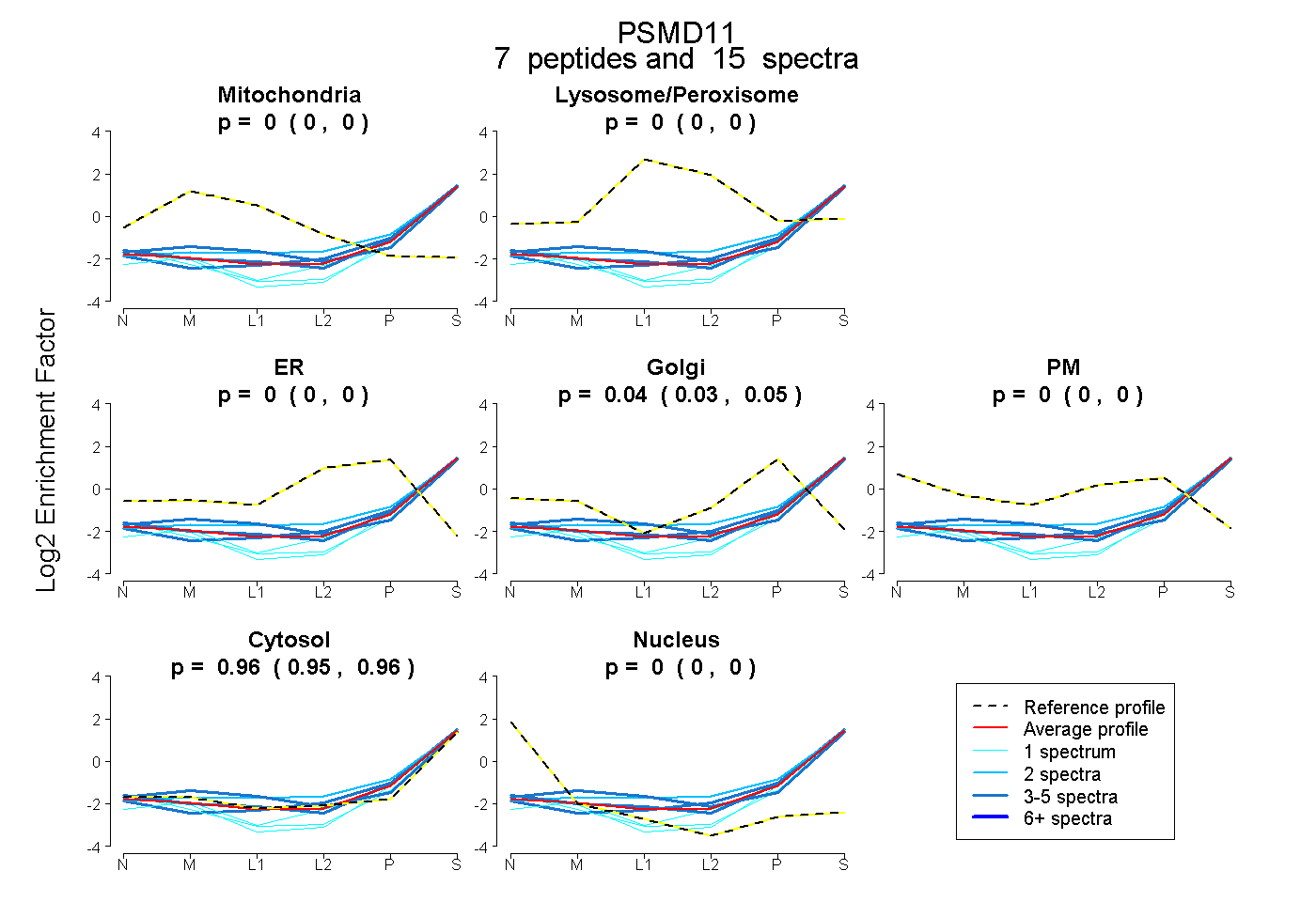
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.035 | 0.050
0.000 | 0.000
0.949 | 0.963
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
58 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.989 0.986 | 0.991 |
0.011 0.008 | 0.013 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
15 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.043 0.035 | 0.050 |
0.000 0.000 | 0.000 |
0.957 0.949 | 0.963 |
0.000 0.000 | 0.000 |
| 3 spectra, YVRPFLNSISK | 0.000 | 0.000 | 0.000 | 0.057 | 0.000 | 0.943 | 0.000 | |||
| 1 spectrum, TGQAAELGGLLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.945 | 0.055 | |||
| 1 spectrum, AALTSAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.963 | 0.037 | |||
| 2 spectra, EQSILELGSLLAK | 0.000 | 0.062 | 0.062 | 0.013 | 0.000 | 0.864 | 0.000 | |||
| 4 spectra, AQSLLSTDR | 0.000 | 0.000 | 0.000 | 0.045 | 0.000 | 0.955 | 0.000 | |||
| 1 spectrum, IMLNTPEDVQALVSGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 3 spectra, YQEALHLGSQLLR | 0.017 | 0.066 | 0.000 | 0.000 | 0.000 | 0.917 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
43 spectra |
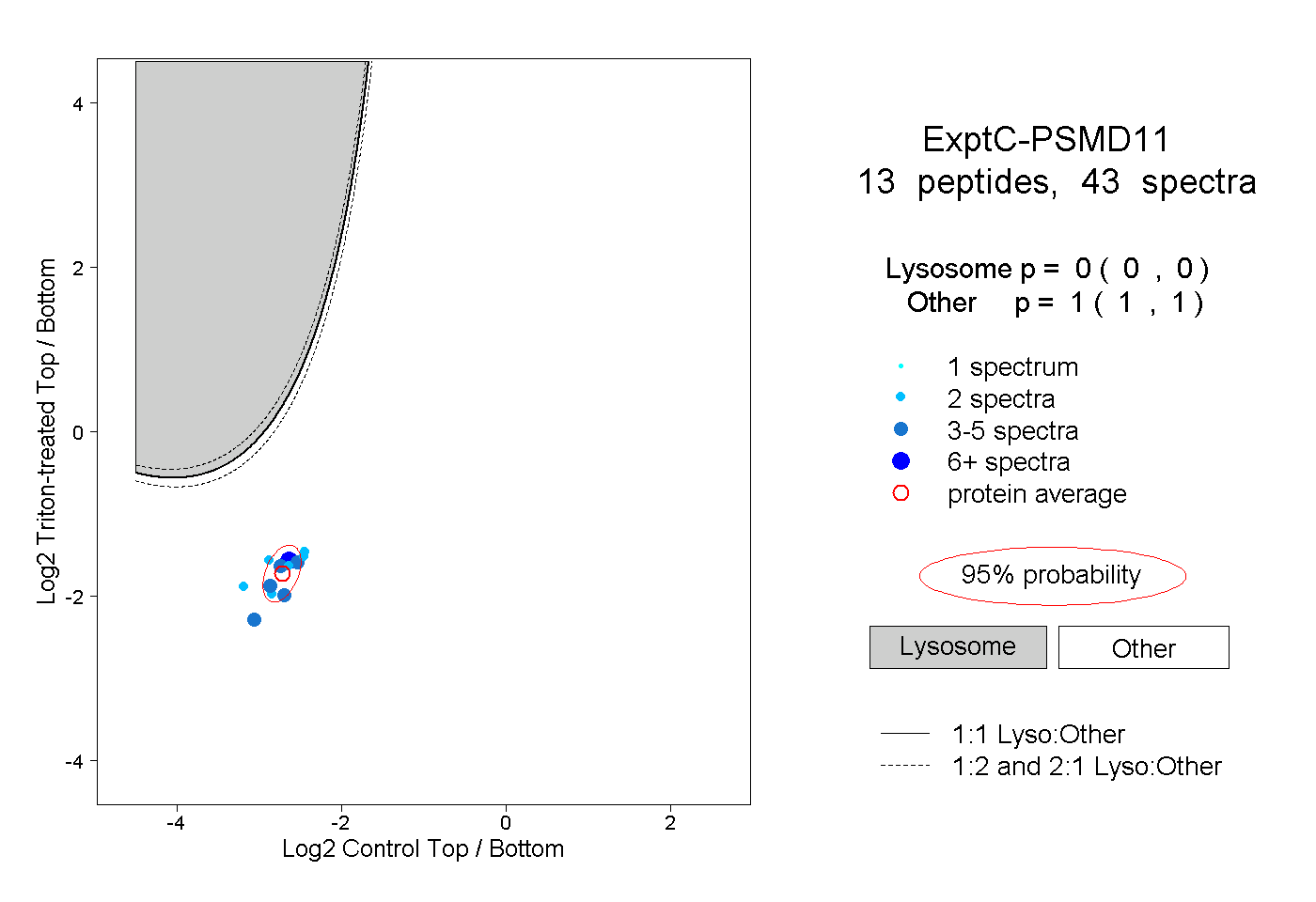 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
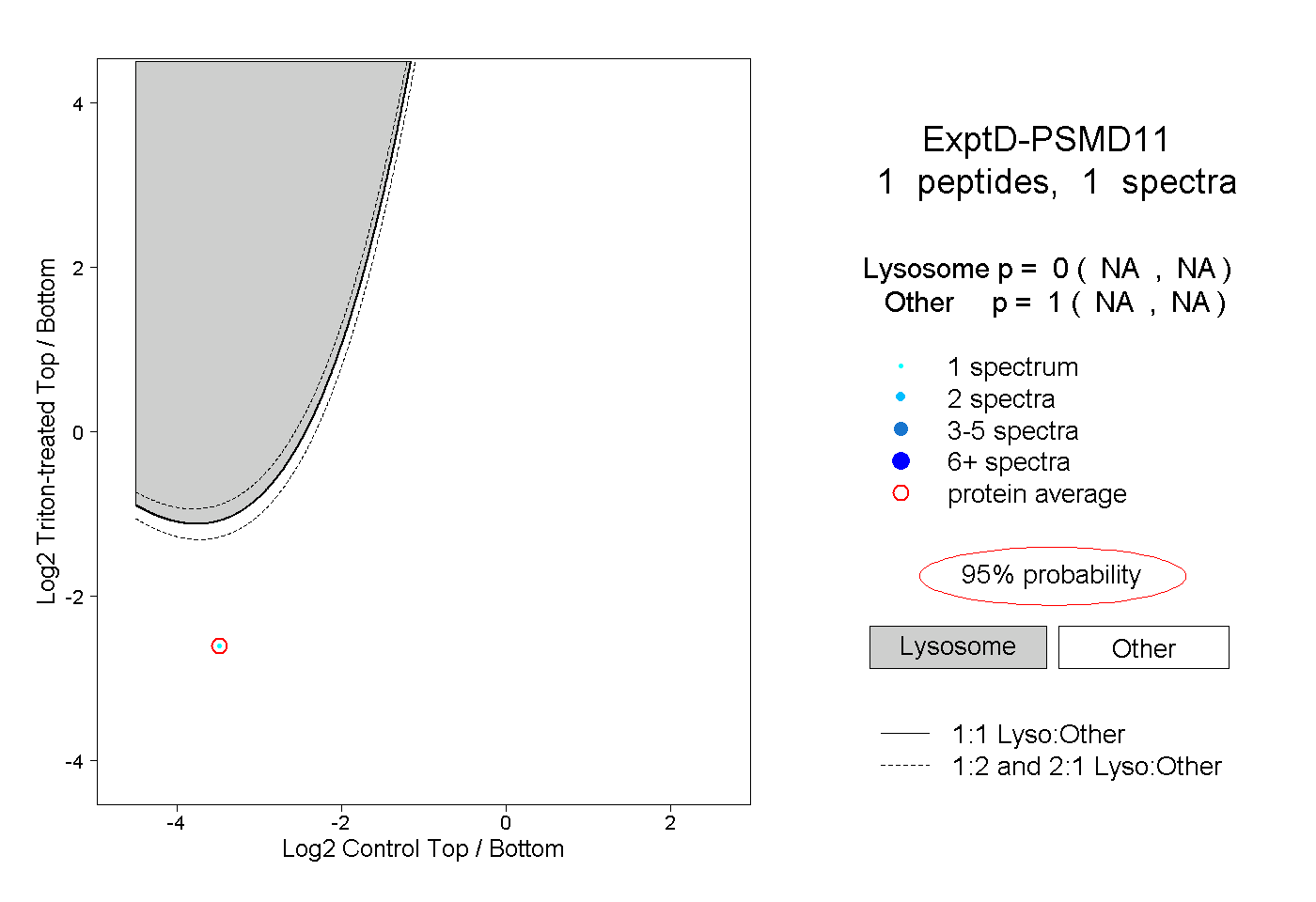 |
0.000 NA | NA |
1.000 NA | NA |