peptides
spectra
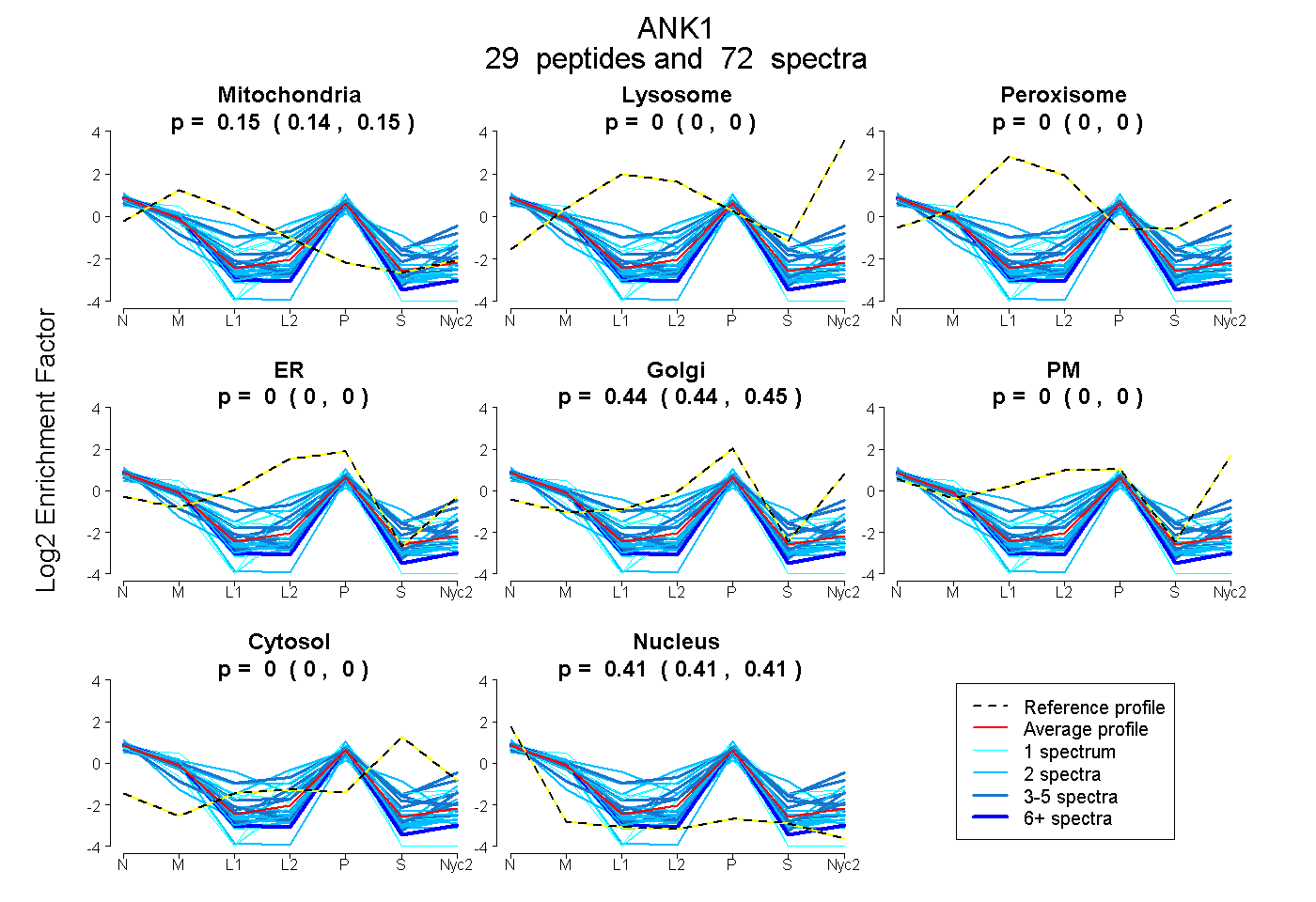
0.142 | 0.151
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.439 | 0.446
0.000 | 0.000
0.000 | 0.000
0.406 | 0.414
peptides
spectra
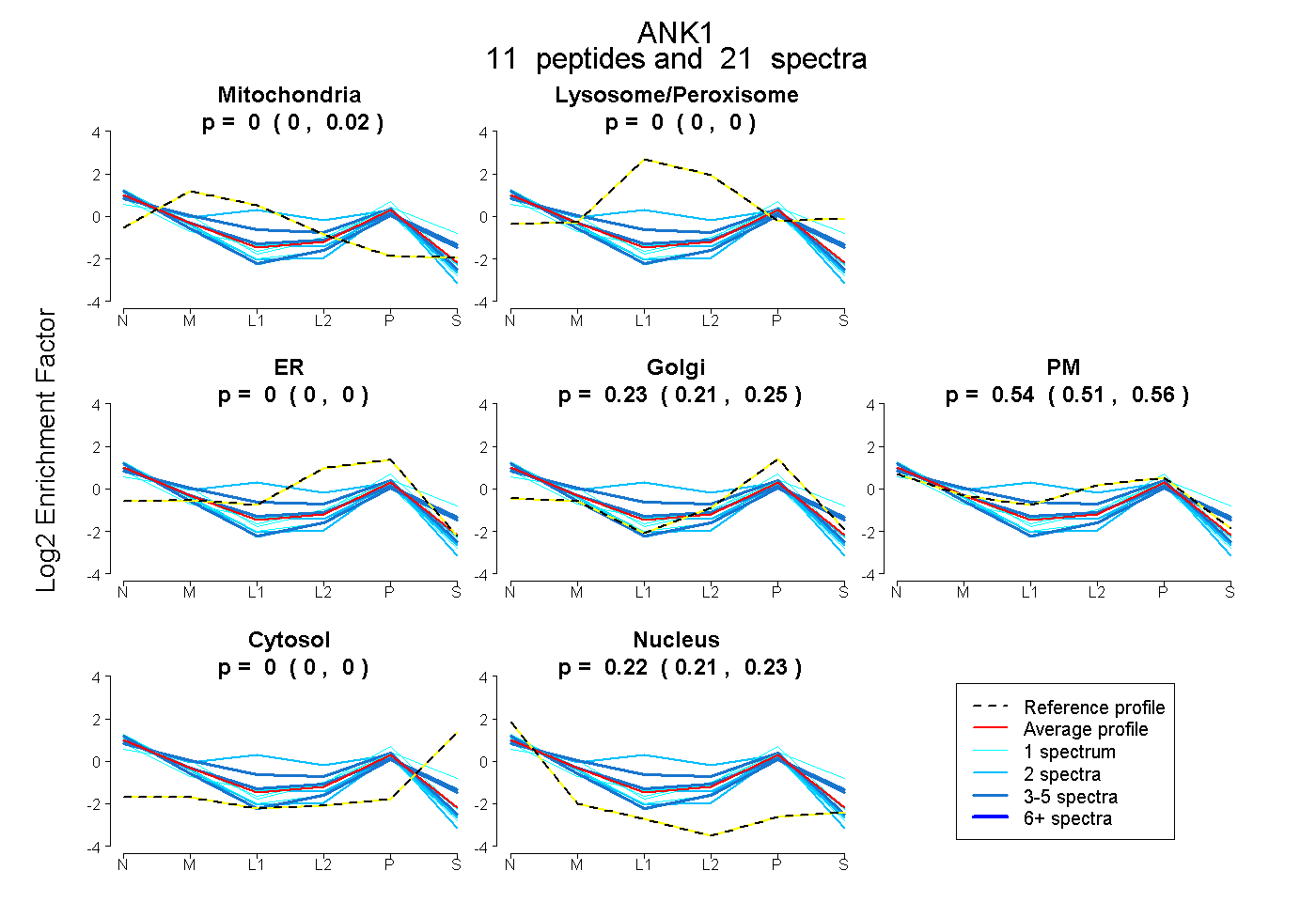
0.000 | 0.016
0.000 | 0.000
0.000 | 0.000
0.209 | 0.254
0.509 | 0.564
0.000 | 0.000
0.213 | 0.230
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
72 spectra |
 |
0.146 0.142 | 0.151 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.443 0.439 | 0.446 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.411 0.406 | 0.414 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
21 spectra |
 |
0.004 0.000 | 0.016 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.232 0.209 | 0.254 |
0.542 0.509 | 0.564 |
0.000 0.000 | 0.000 |
0.222 0.213 | 0.230 |
| 2 spectra, EPGGFLSFLR | 0.000 | 0.000 | 0.000 | 0.445 | 0.239 | 0.000 | 0.316 | |||
| 1 spectrum, ITDSPSVR | 0.000 | 0.000 | 0.000 | 0.163 | 0.563 | 0.165 | 0.108 | |||
| 2 spectra, DSGEGDTTSLR | 0.000 | 0.000 | 0.000 | 0.444 | 0.210 | 0.000 | 0.346 | |||
| 2 spectra, AGHTEVAK | 0.174 | 0.073 | 0.000 | 0.000 | 0.753 | 0.000 | 0.000 | |||
| 3 spectra, TLTPLTLR | 0.000 | 0.000 | 0.000 | 0.366 | 0.292 | 0.015 | 0.327 | |||
| 3 spectra, TLEQHENFVEVAR | 0.001 | 0.000 | 0.000 | 0.086 | 0.665 | 0.079 | 0.169 | |||
| 1 spectrum, EGHVDTALALLEK | 0.047 | 0.000 | 0.000 | 0.510 | 0.325 | 0.000 | 0.118 | |||
| 3 spectra, LPALHIAAR | 0.129 | 0.000 | 0.000 | 0.078 | 0.711 | 0.000 | 0.082 | |||
| 1 spectrum, TAEAVHFATLLYK | 0.000 | 0.000 | 0.000 | 0.236 | 0.567 | 0.000 | 0.197 | |||
| 1 spectrum, LCQDYDTIGPEGGSLR | 0.000 | 0.000 | 0.000 | 0.306 | 0.352 | 0.000 | 0.342 | |||
| 2 spectra, ELVVLR | 0.008 | 0.000 | 0.000 | 0.166 | 0.555 | 0.000 | 0.271 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
7 spectra |
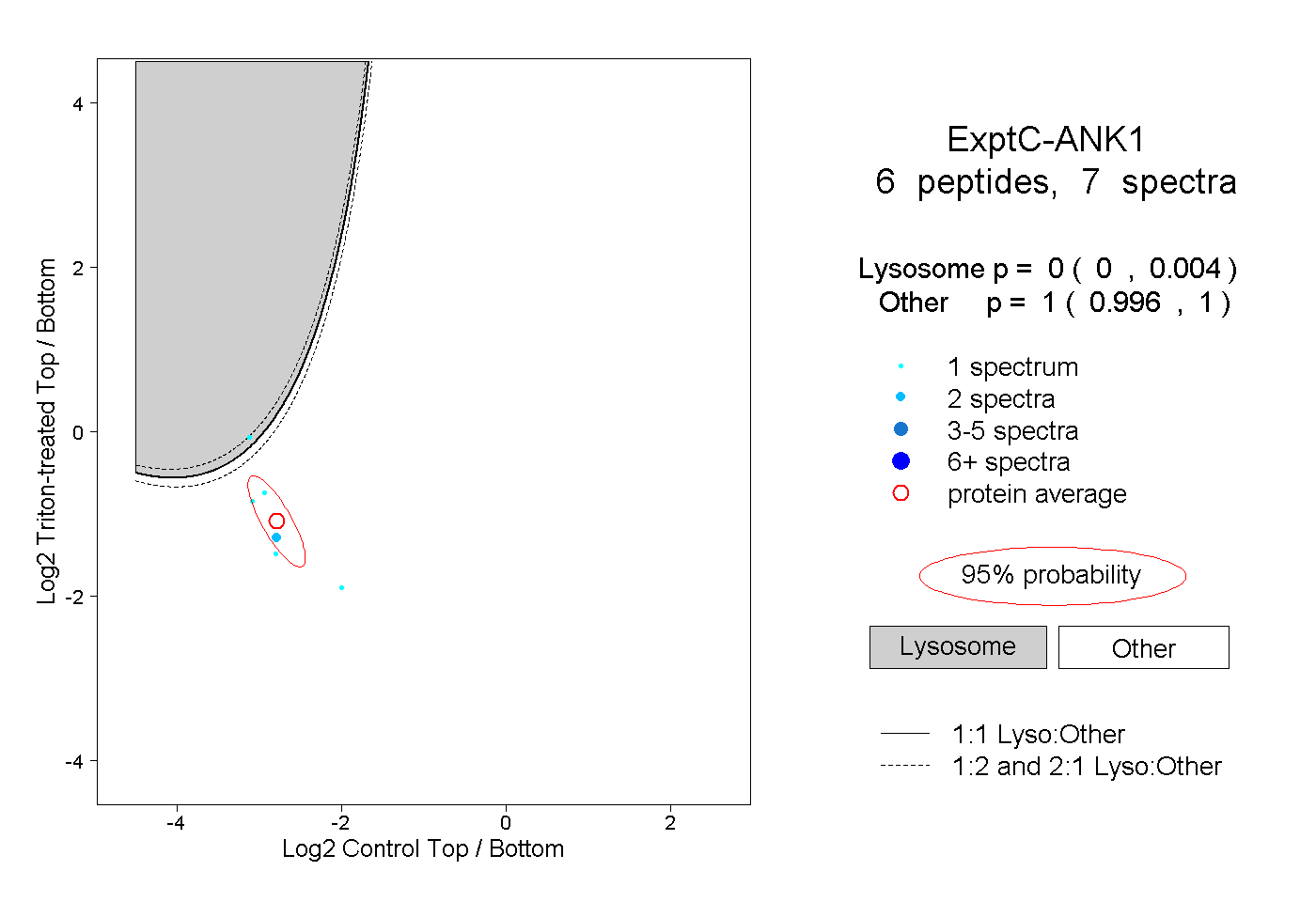 |
0.000 0.000 | 0.004 |
1.000 0.996 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
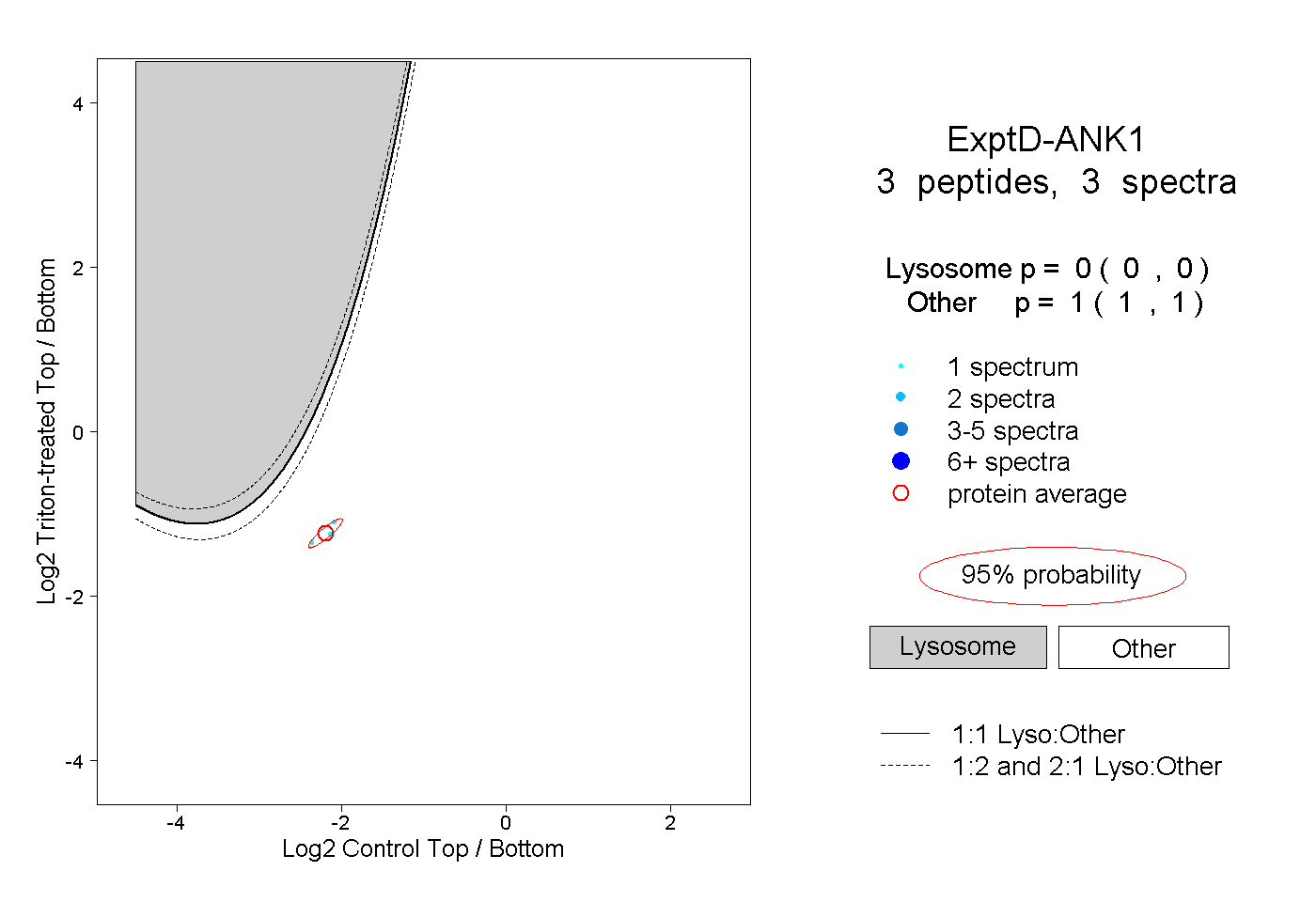 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |