peptides
spectra
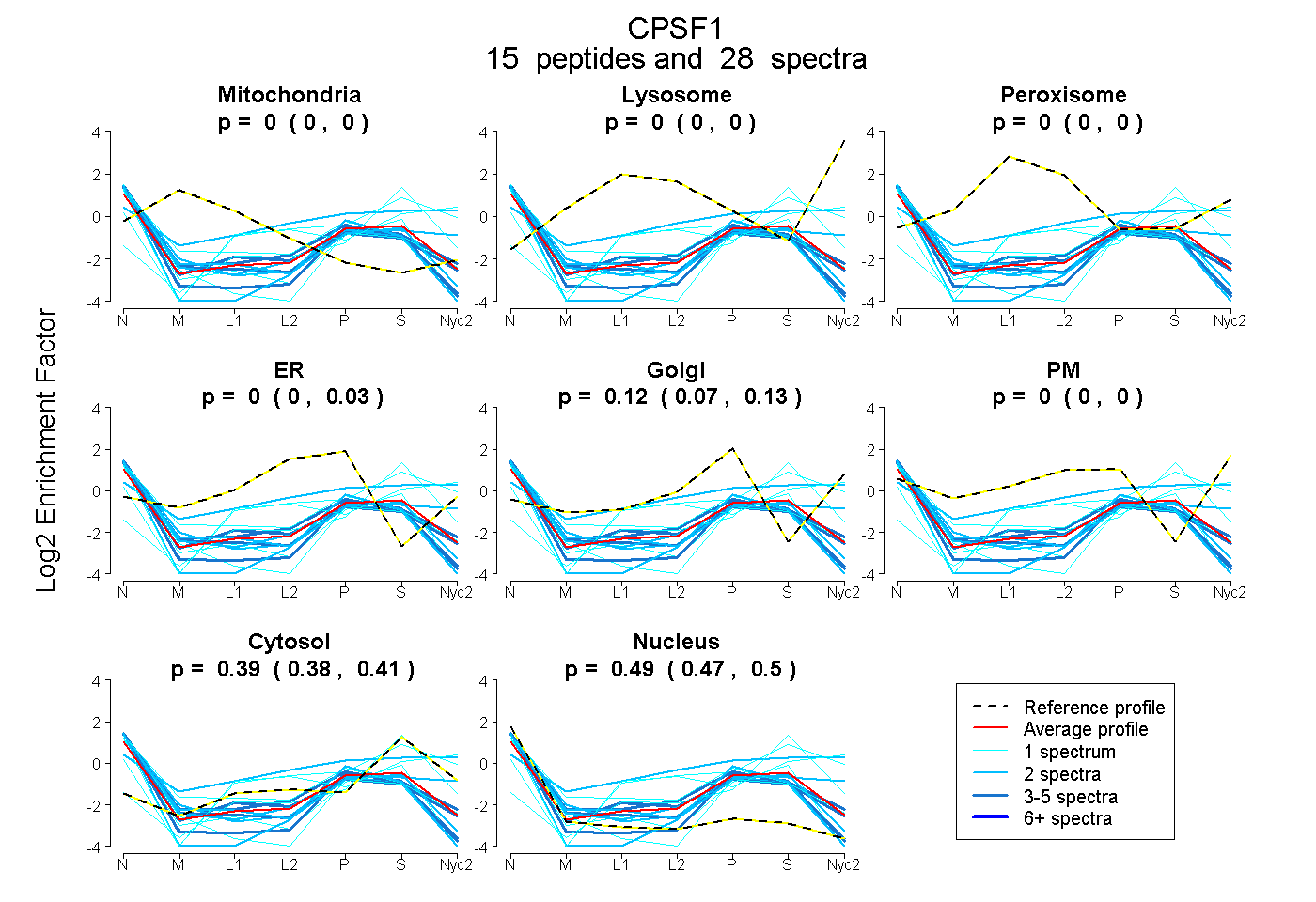
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.031
0.070 | 0.132
0.000 | 0.000
0.377 | 0.405
0.472 | 0.500
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
28 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.031 |
0.120 0.070 | 0.132 |
0.000 0.000 | 0.000 |
0.392 0.377 | 0.405 |
0.487 0.472 | 0.500 |
| 1 spectrum, LVFLVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.177 | 0.823 | ||
| 3 spectra, ESLAEEHEGLMGEGQR | 0.000 | 0.000 | 0.000 | 0.190 | 0.000 | 0.000 | 0.214 | 0.596 | ||
| 2 spectra, EVLLVALGSR | 0.000 | 0.000 | 0.000 | 0.094 | 0.000 | 0.000 | 0.204 | 0.703 | ||
| 1 spectrum, DALLLSFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.192 | 0.791 | 0.017 | ||
| 3 spectra, LVVLPFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.002 | 0.000 | 0.258 | 0.740 | ||
| 2 spectra, VPHNINFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.001 | 0.000 | 0.236 | 0.763 | ||
| 2 spectra, NVLDGELLNR | 0.000 | 0.000 | 0.000 | 0.060 | 0.001 | 0.000 | 0.336 | 0.603 | ||
| 1 spectrum, YIVQVSPLGIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.279 | 0.573 | 0.147 | ||
| 1 spectrum, MVLSLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.918 | 0.082 | ||
| 3 spectra, GFLYFNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.148 | 0.000 | 0.251 | 0.602 | ||
| 1 spectrum, HGFLILSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.353 | 0.647 | ||
| 2 spectra, DGFVQNVHTPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.457 | 0.541 | 0.002 | ||
| 1 spectrum, SEETVSGLK | 0.000 | 0.000 | 0.001 | 0.230 | 0.062 | 0.000 | 0.238 | 0.468 | ||
| 3 spectra, ADPTHWCLLVR | 0.000 | 0.000 | 0.000 | 0.037 | 0.138 | 0.008 | 0.299 | 0.518 | ||
| 2 spectra, LQEPPASSVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.234 | 0.018 | 0.325 | 0.423 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
10 spectra |
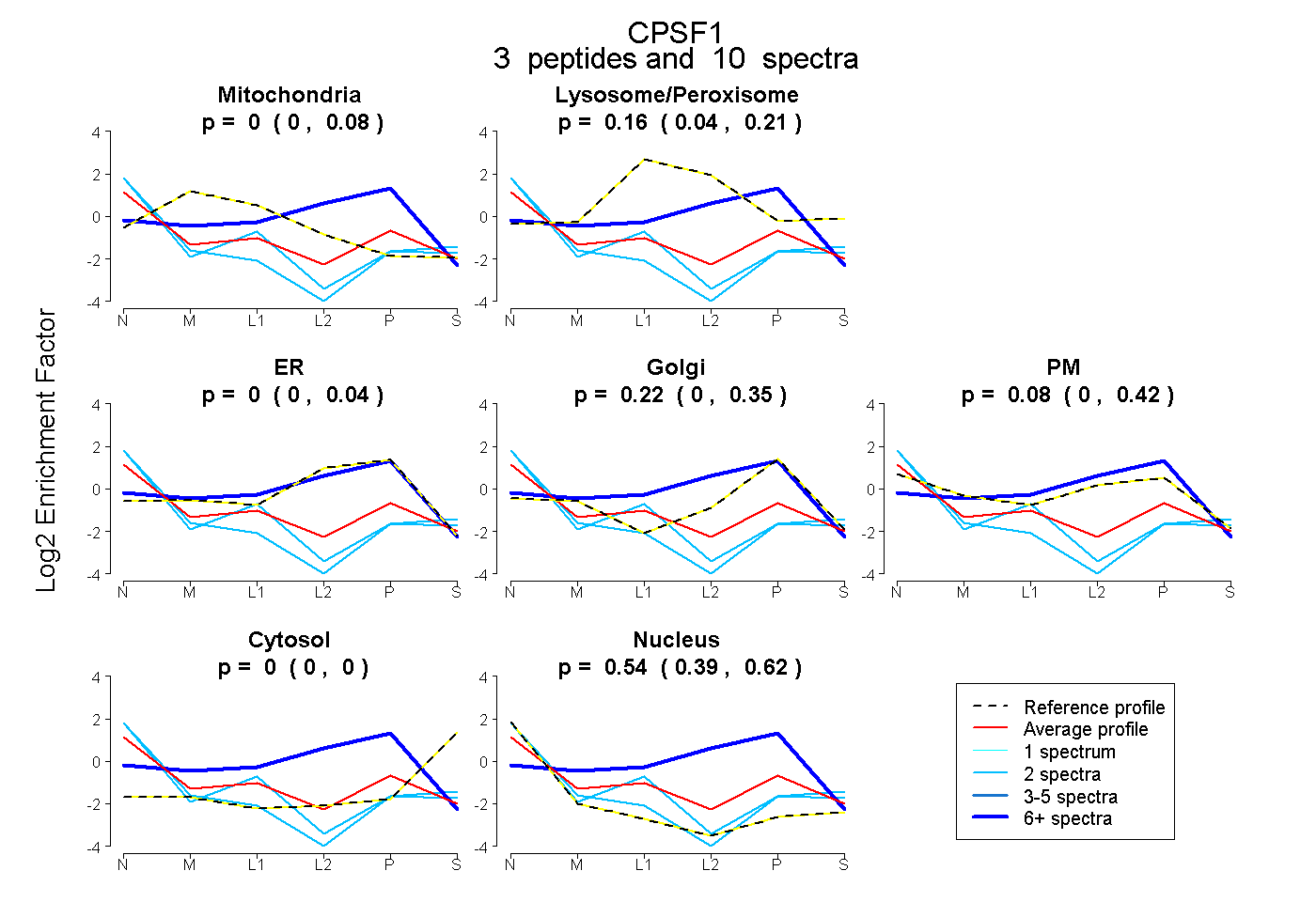 |
0.000 0.000 | 0.079 |
0.163 0.039 | 0.210 |
0.000 0.000 | 0.044 |
0.215 0.000 | 0.351 |
0.084 0.000 | 0.422 |
0.000 0.000 | 0.000 |
0.538 0.388 | 0.625 |