peptides
spectra
0.005 | 0.008
0.000 | 0.000
0.000 | 0.000
0.907 | 0.910
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.083 | 0.086
peptides
spectra
0.000 | 0.000
0.066 | 0.083
0.878 | 0.898
0.000 | 0.000
0.026 | 0.043
0.000 | 0.000
0.000 | 0.000
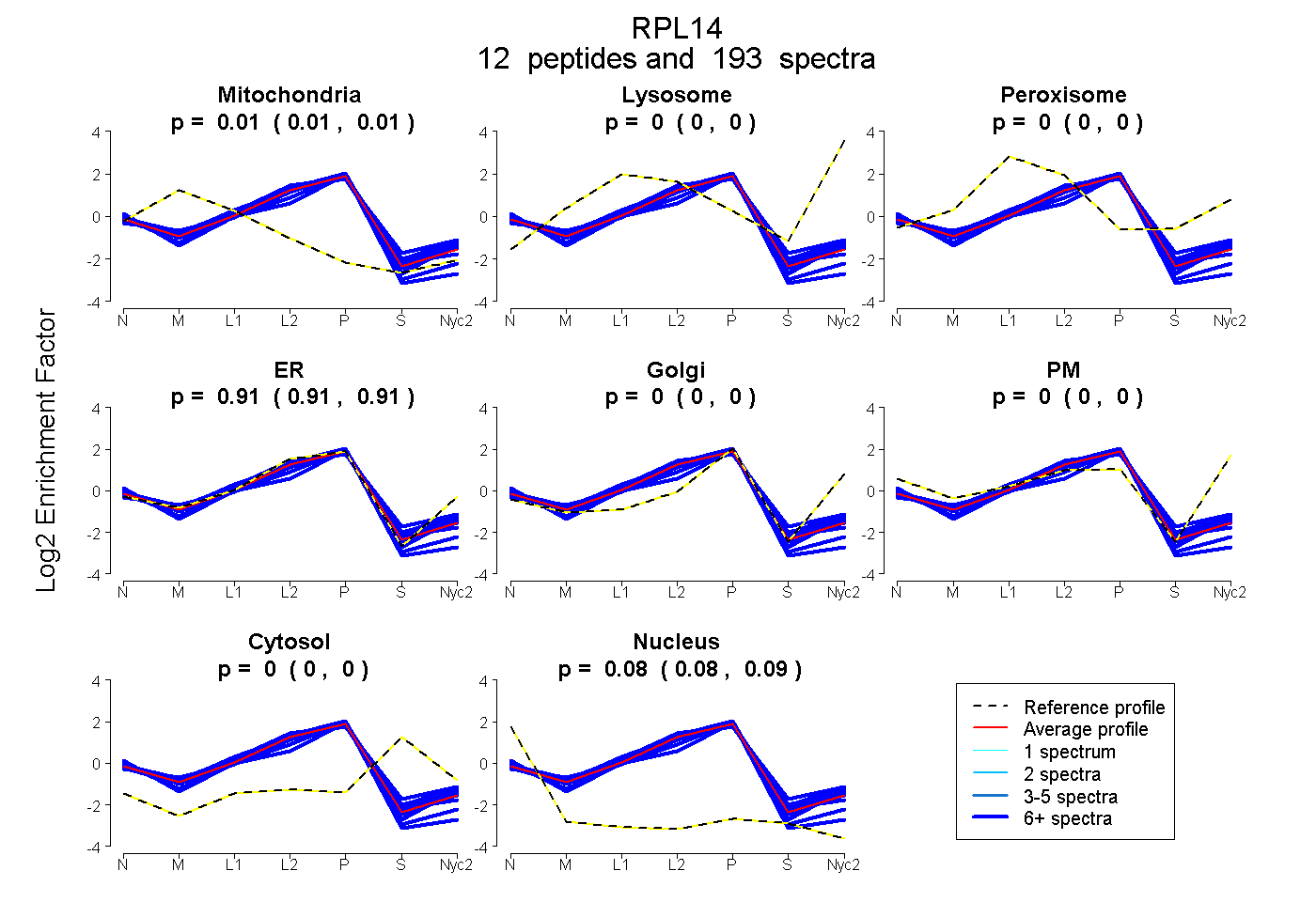
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
193 spectra |
 |
0.007 0.005 | 0.008 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.908 0.907 | 0.910 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.085 0.083 | 0.086 |
||
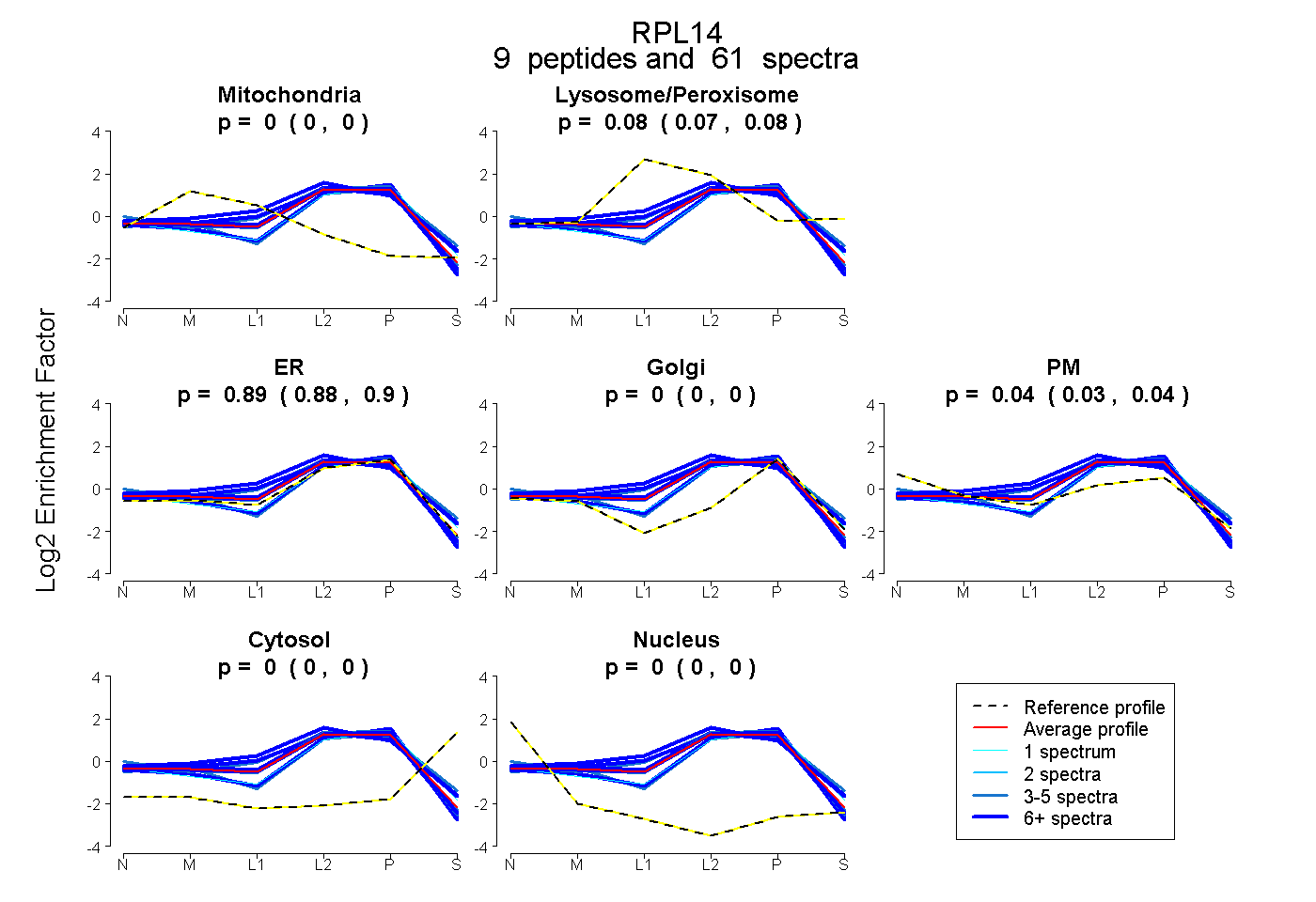
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
61 spectra |
 |
0.000 0.000 | 0.000 |
0.076 0.066 | 0.083 |
0.889 0.878 | 0.898 |
0.000 0.000 | 0.000 |
0.035 0.026 | 0.043 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, ALVDGPCTR | 0.000 | 0.243 | 0.586 | 0.000 | 0.171 | 0.000 | 0.000 | |||
| 13 spectra, LVAIVDVIDQNR | 0.000 | 0.040 | 0.960 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, VAYISFGPHAGK | 0.000 | 0.309 | 0.653 | 0.000 | 0.038 | 0.000 | 0.000 | |||
| 11 spectra, FPHSAR | 0.021 | 0.119 | 0.860 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, AAPPAK | 0.000 | 0.000 | 0.968 | 0.032 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, AAIAAAAAAK | 0.000 | 0.000 | 0.908 | 0.092 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, CMQLTDFILK | 0.000 | 0.170 | 0.782 | 0.000 | 0.047 | 0.001 | 0.000 | |||
| 5 spectra, FVEVGR | 0.000 | 0.027 | 0.973 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, ATGPGQK | 0.000 | 0.000 | 0.884 | 0.041 | 0.051 | 0.025 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
241 spectra |
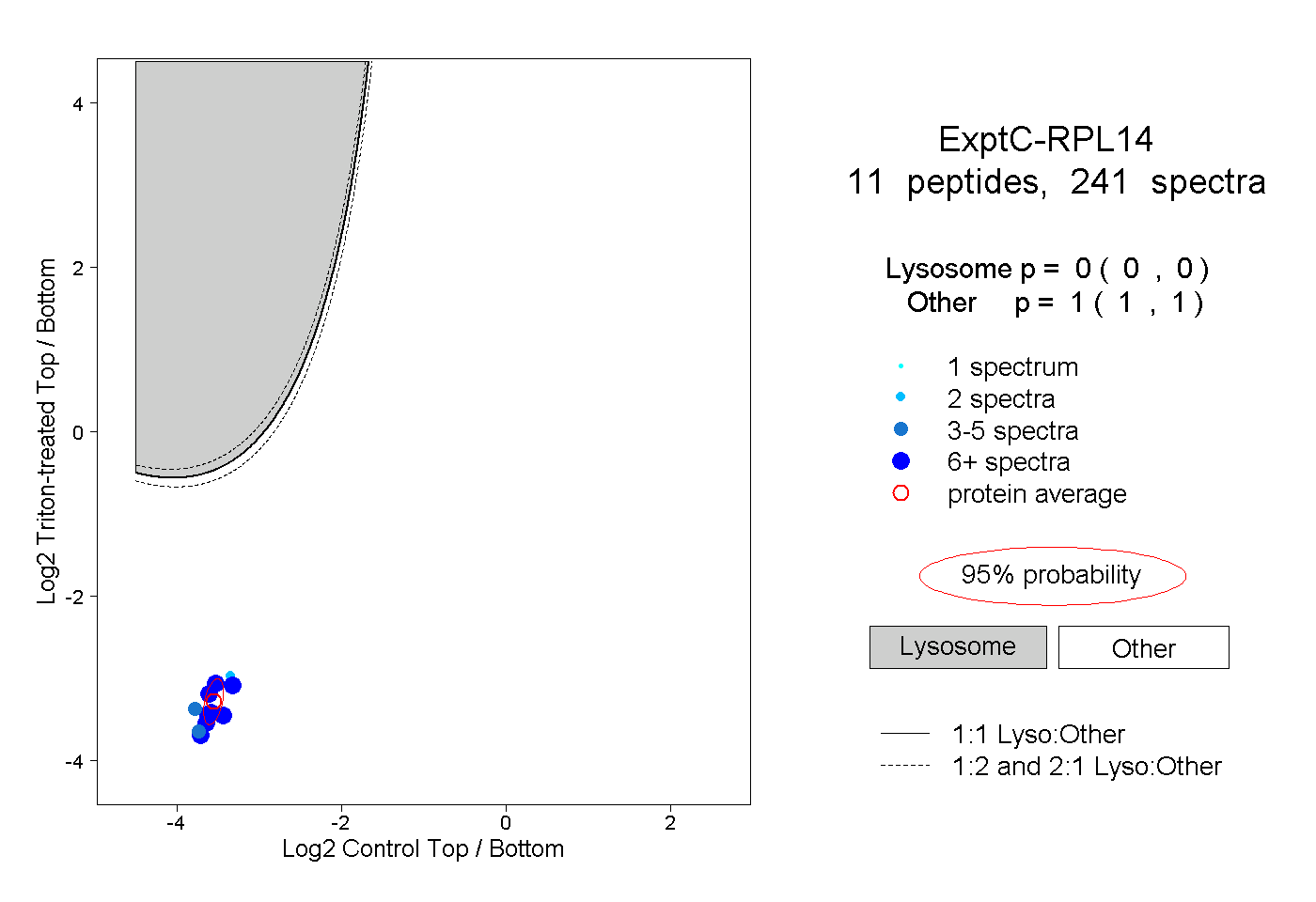 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
32 spectra |
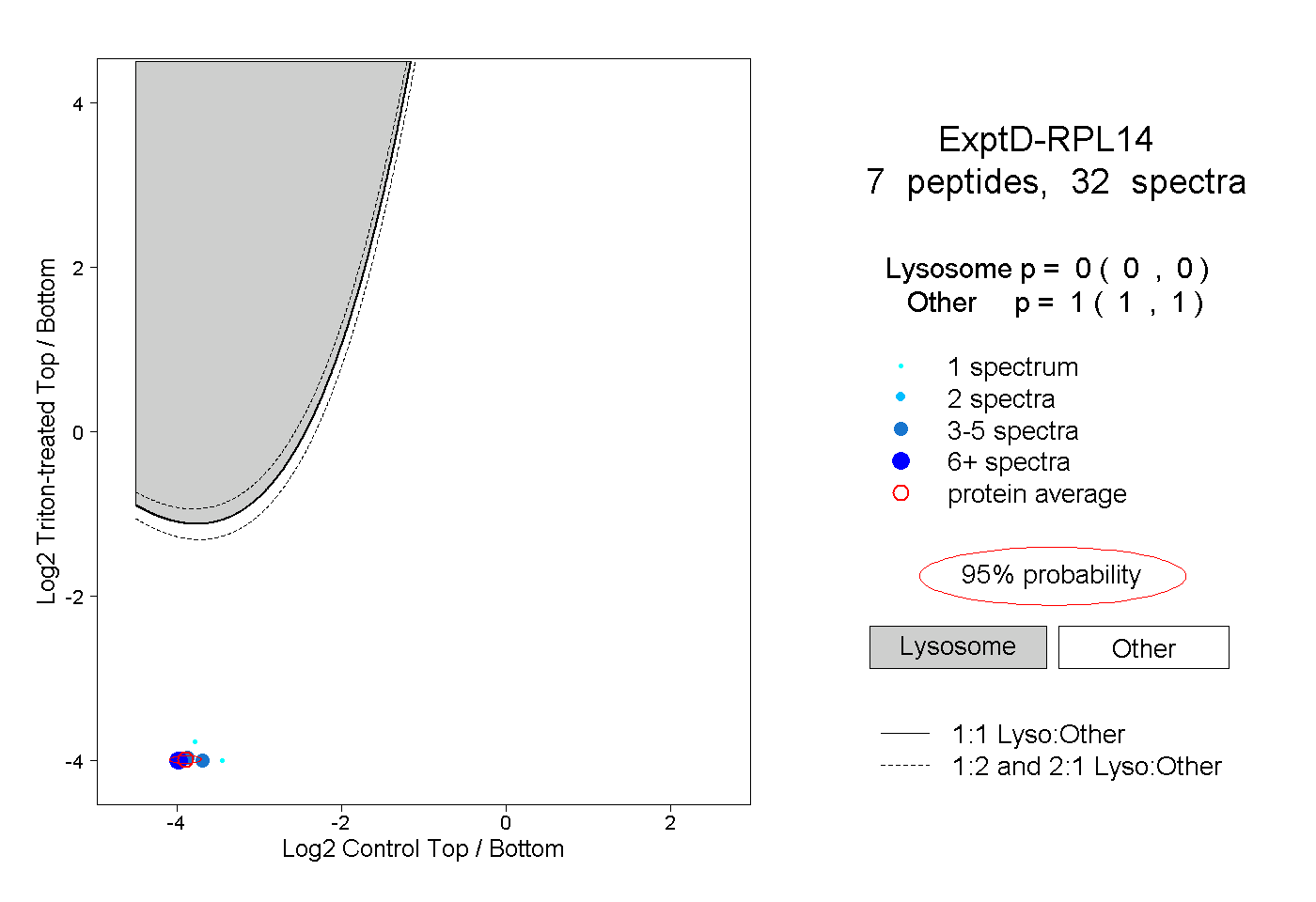 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |