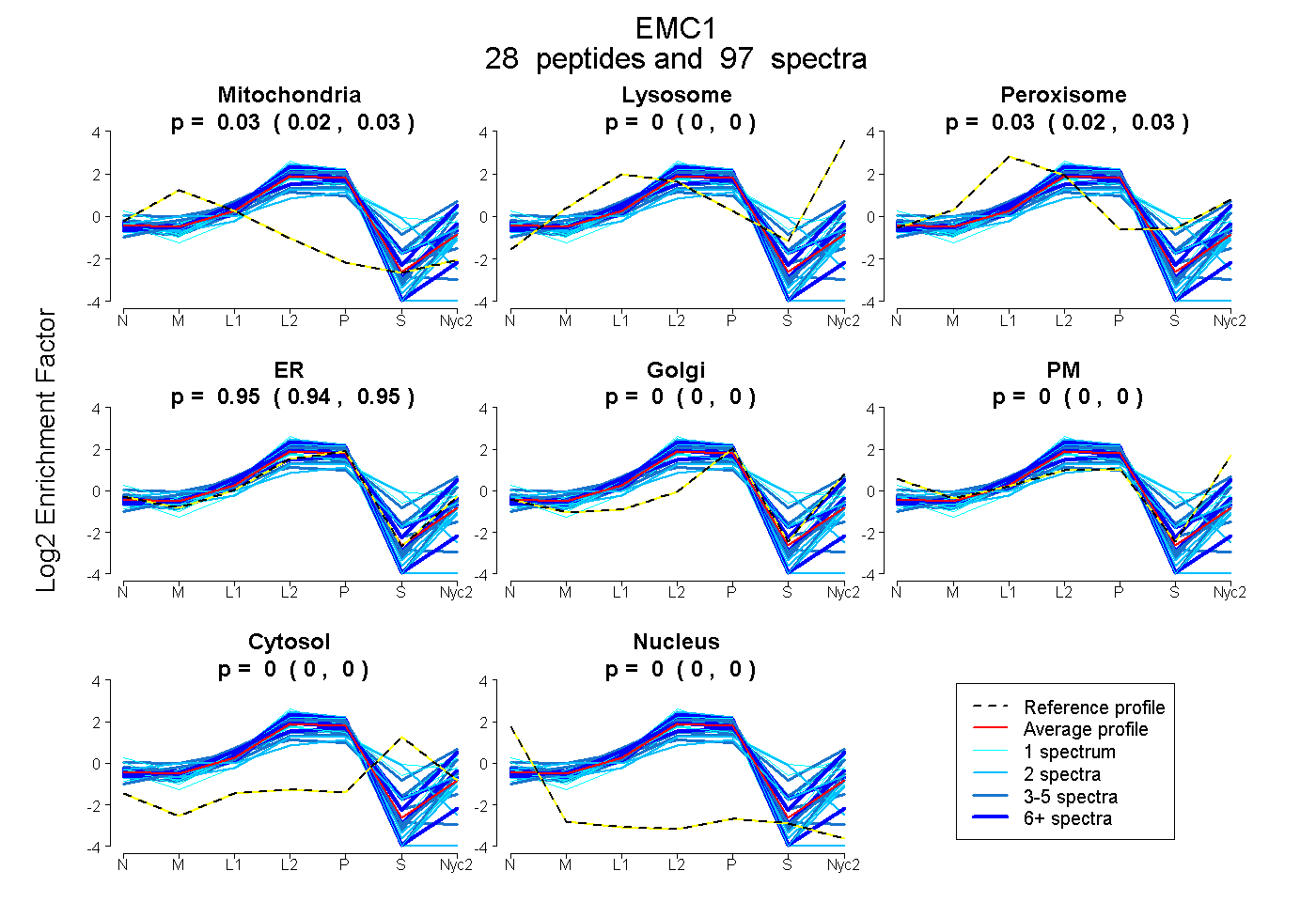
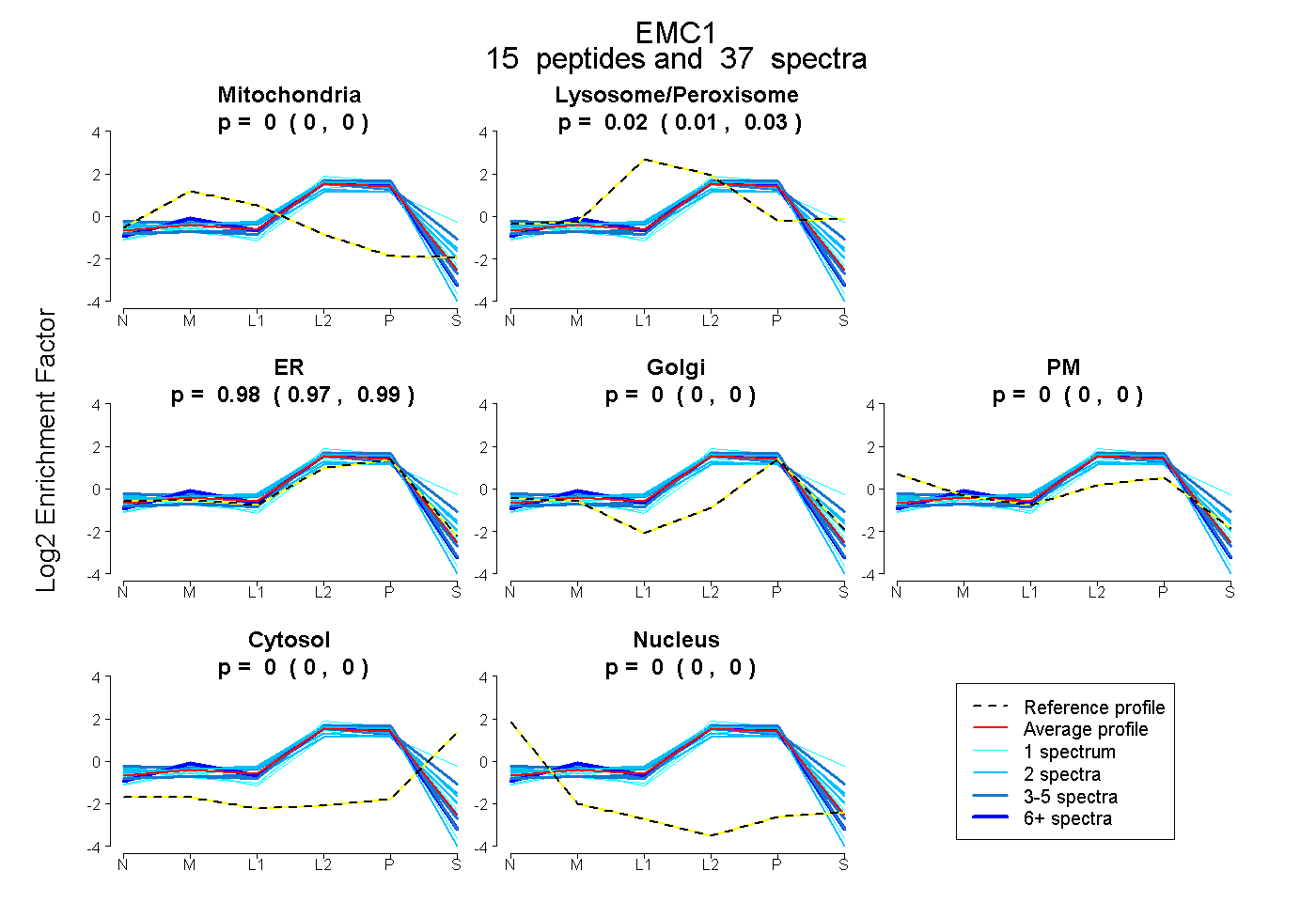
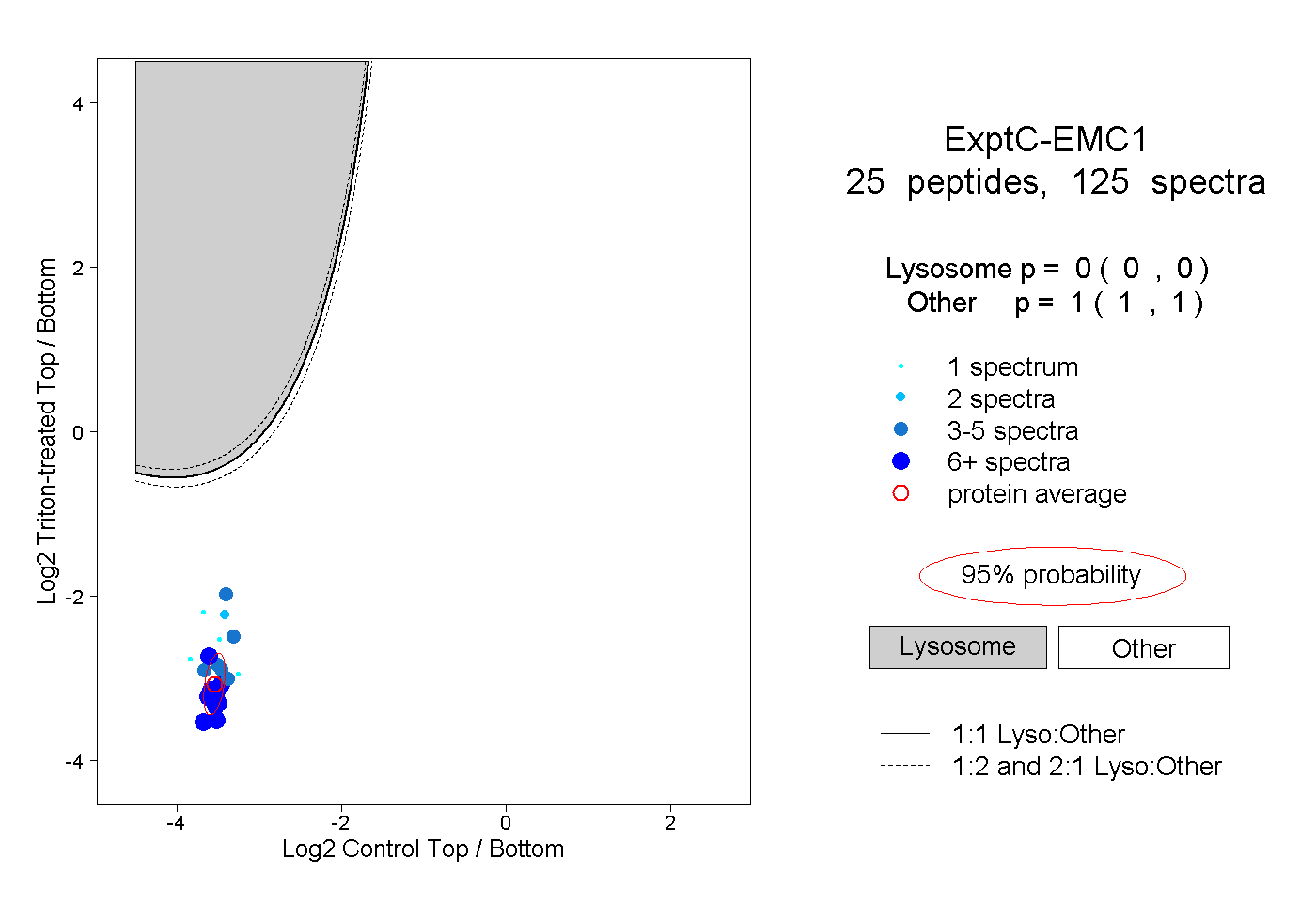
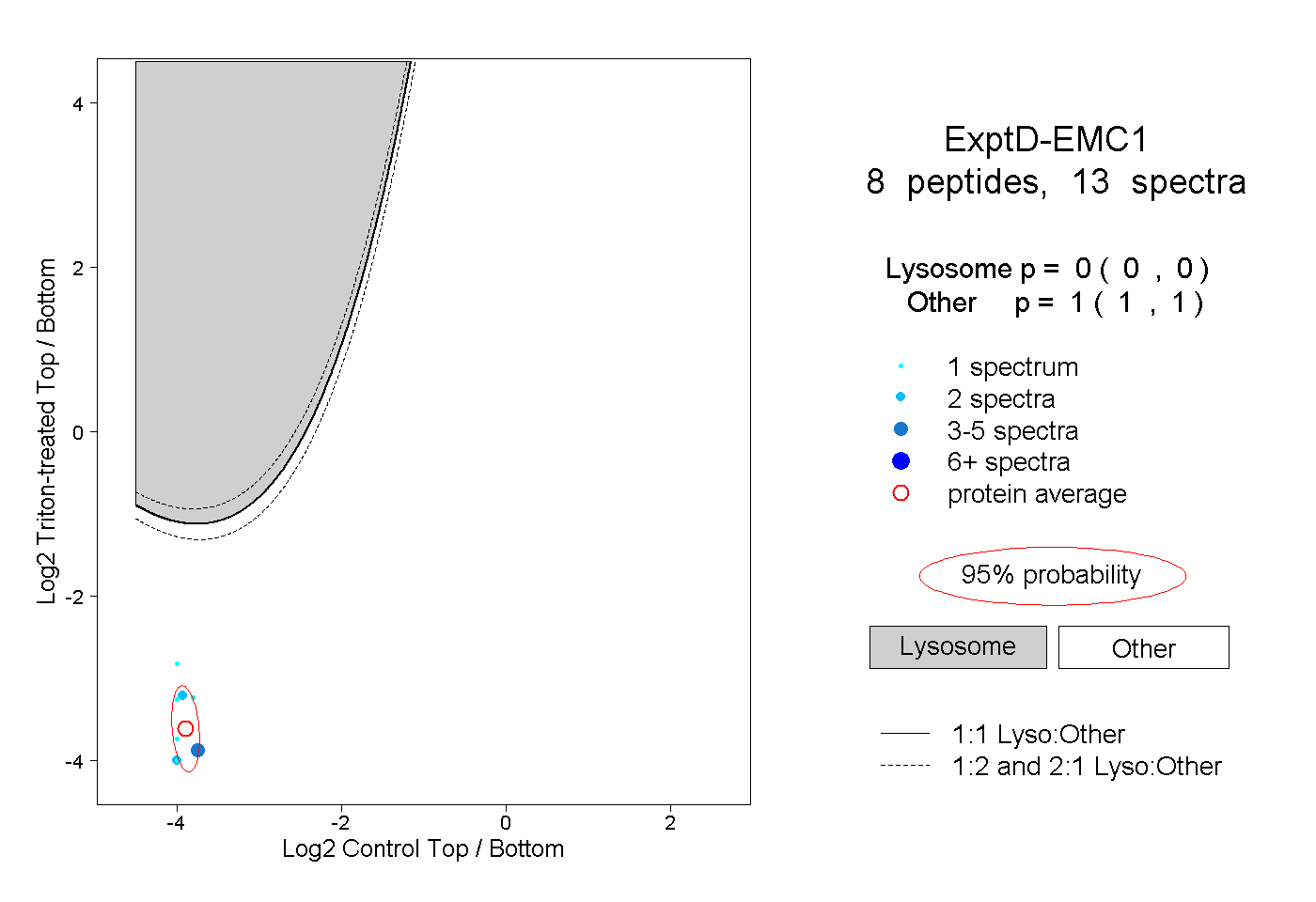
| 10 spectra, RPEIPTEQSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, ADGLLGMFLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, MMVMVTASGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ALLDPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VVLWSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, QQYVGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, DDSVGYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, RPILQSLLLPVMDQDYAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, YVAVLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, VTAFPATR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, WSQVAPPVLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, TVAAVMTCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, FNVEDGEIVQQVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, NEINIDTLAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SLNPNLLAVVTESTDVHHER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, GTRPEQLYVQVFLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EENLIPYSPDVQVHAER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, NVIAALNSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, QYLPNVKPDSSFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LLDTSISFSLEQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, DEFNLQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, FASLEFSPGSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, IIHSSVQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LVVATEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VLLLVDDEYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |