peptides
spectra
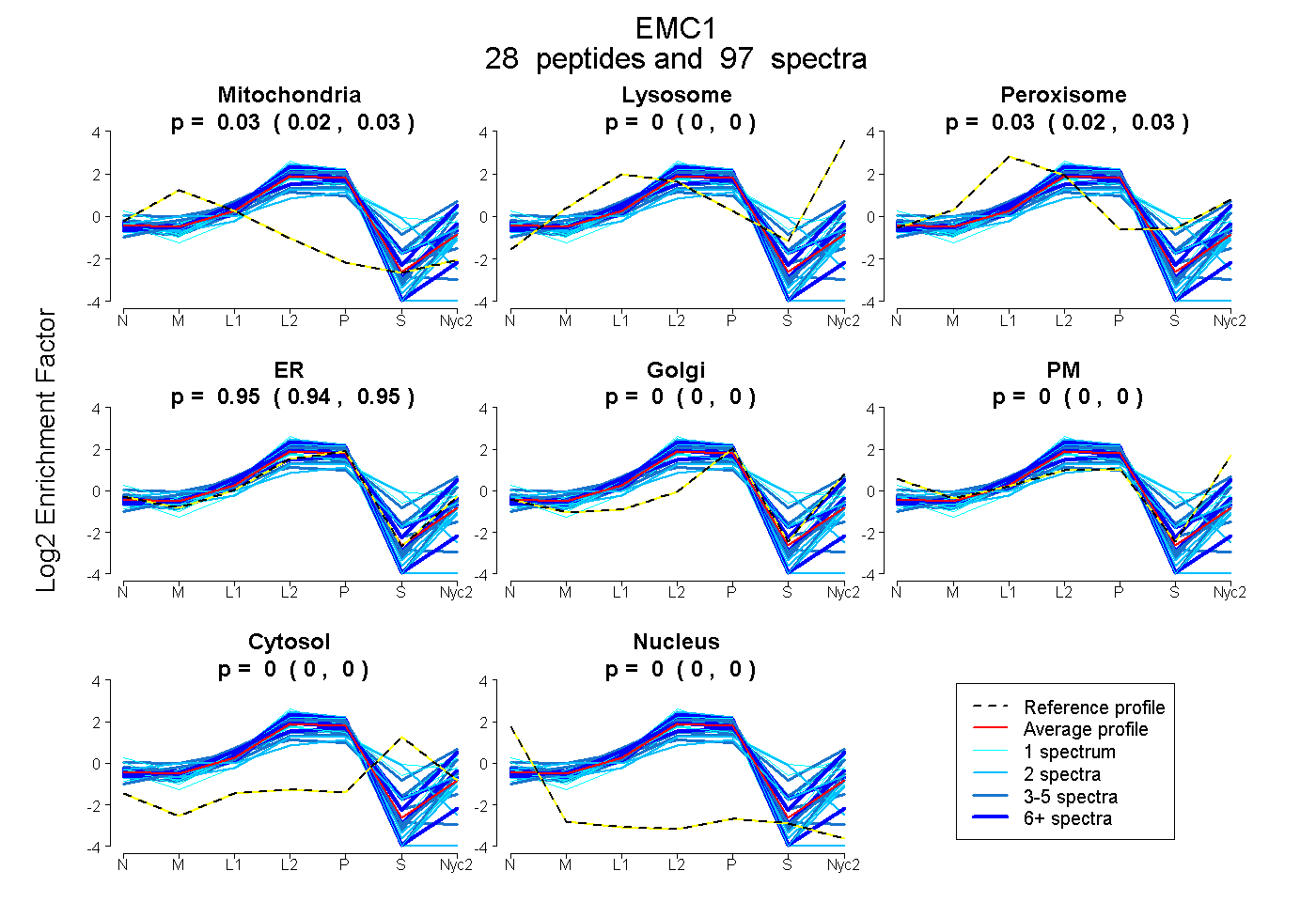
0.024 | 0.033
0.000 | 0.000
0.018 | 0.031
0.942 | 0.950
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
97 spectra |
 |
0.029 0.024 | 0.033 |
0.000 0.000 | 0.000 |
0.025 0.018 | 0.031 |
0.946 0.942 | 0.950 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 3 spectra, GTAEGAVDAMLVHGQDAITVSNGGR | 0.123 | 0.000 | 0.000 | 0.840 | 0.000 | 0.000 | 0.000 | 0.037 | ||
| 9 spectra, RPEIPTEQSR | 0.000 | 0.000 | 0.142 | 0.803 | 0.000 | 0.000 | 0.056 | 0.000 | ||
| 3 spectra, ADGLLGMFLK | 0.006 | 0.000 | 0.000 | 0.958 | 0.000 | 0.000 | 0.036 | 0.000 | ||
| 4 spectra, MMVMVTASGK | 0.000 | 0.146 | 0.069 | 0.442 | 0.000 | 0.187 | 0.156 | 0.000 | ||
| 8 spectra, VVLWSR | 0.000 | 0.200 | 0.013 | 0.787 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, QQYVGK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, LFGIESSSGTILWK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, DDSVGYR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, TTAHFPHPPQCTLLVK | 0.038 | 0.000 | 0.022 | 0.599 | 0.000 | 0.000 | 0.341 | 0.000 | ||
| 1 spectrum, RPILQSLLLPVMDQDYAK | 0.000 | 0.241 | 0.000 | 0.755 | 0.000 | 0.000 | 0.004 | 0.000 | ||
| 2 spectra, YVAVLK | 0.155 | 0.000 | 0.086 | 0.617 | 0.064 | 0.000 | 0.078 | 0.000 | ||
| 4 spectra, VTAFPATR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, TGEILWR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 14 spectra, TVAAVMTCR | 0.036 | 0.000 | 0.000 | 0.964 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, TFIGIFLIDGVTGR | 0.082 | 0.000 | 0.000 | 0.889 | 0.000 | 0.000 | 0.000 | 0.029 | ||
| 4 spectra, FNVEDGEIVQQVR | 0.045 | 0.000 | 0.262 | 0.271 | 0.142 | 0.258 | 0.022 | 0.000 | ||
| 2 spectra, NEINIDTLAR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, SLNPNLLAVVTESTDVHHER | 0.000 | 0.086 | 0.185 | 0.585 | 0.000 | 0.000 | 0.144 | 0.000 | ||
| 3 spectra, GTRPEQLYVQVFLK | 0.000 | 0.051 | 0.113 | 0.699 | 0.000 | 0.054 | 0.083 | 0.000 | ||
| 12 spectra, NVIAALNSR | 0.000 | 0.001 | 0.014 | 0.984 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LLDTSISFSLEQK | 0.000 | 0.000 | 0.161 | 0.570 | 0.000 | 0.000 | 0.270 | 0.000 | ||
| 3 spectra, DEFNLQK | 0.000 | 0.102 | 0.000 | 0.898 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, FASLEFSPGSK | 0.000 | 0.056 | 0.081 | 0.828 | 0.000 | 0.000 | 0.035 | 0.000 | ||
| 1 spectrum, NFPQATLVSFATTGEK | 0.115 | 0.000 | 0.000 | 0.822 | 0.000 | 0.000 | 0.000 | 0.063 | ||
| 1 spectrum, MFYDAR | 0.000 | 0.006 | 0.000 | 0.793 | 0.000 | 0.201 | 0.000 | 0.000 | ||
| 2 spectra, QFDVLK | 0.005 | 0.000 | 0.000 | 0.995 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LVVATEK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, VLLLVDDEYK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
37 spectra |
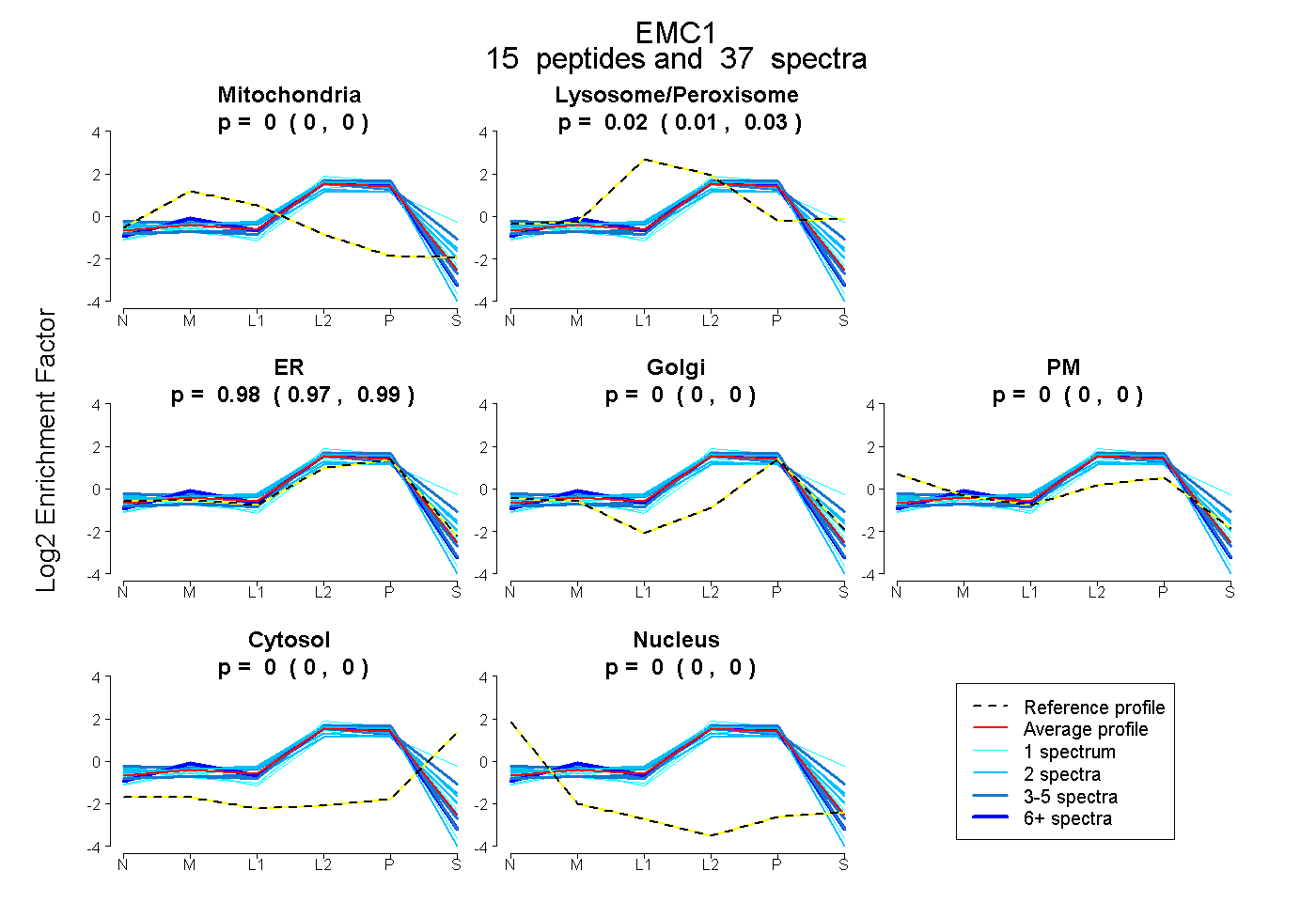 |
0.000 0.000 | 0.000 |
0.018 0.008 | 0.026 |
0.982 0.972 | 0.990 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
125 spectra |
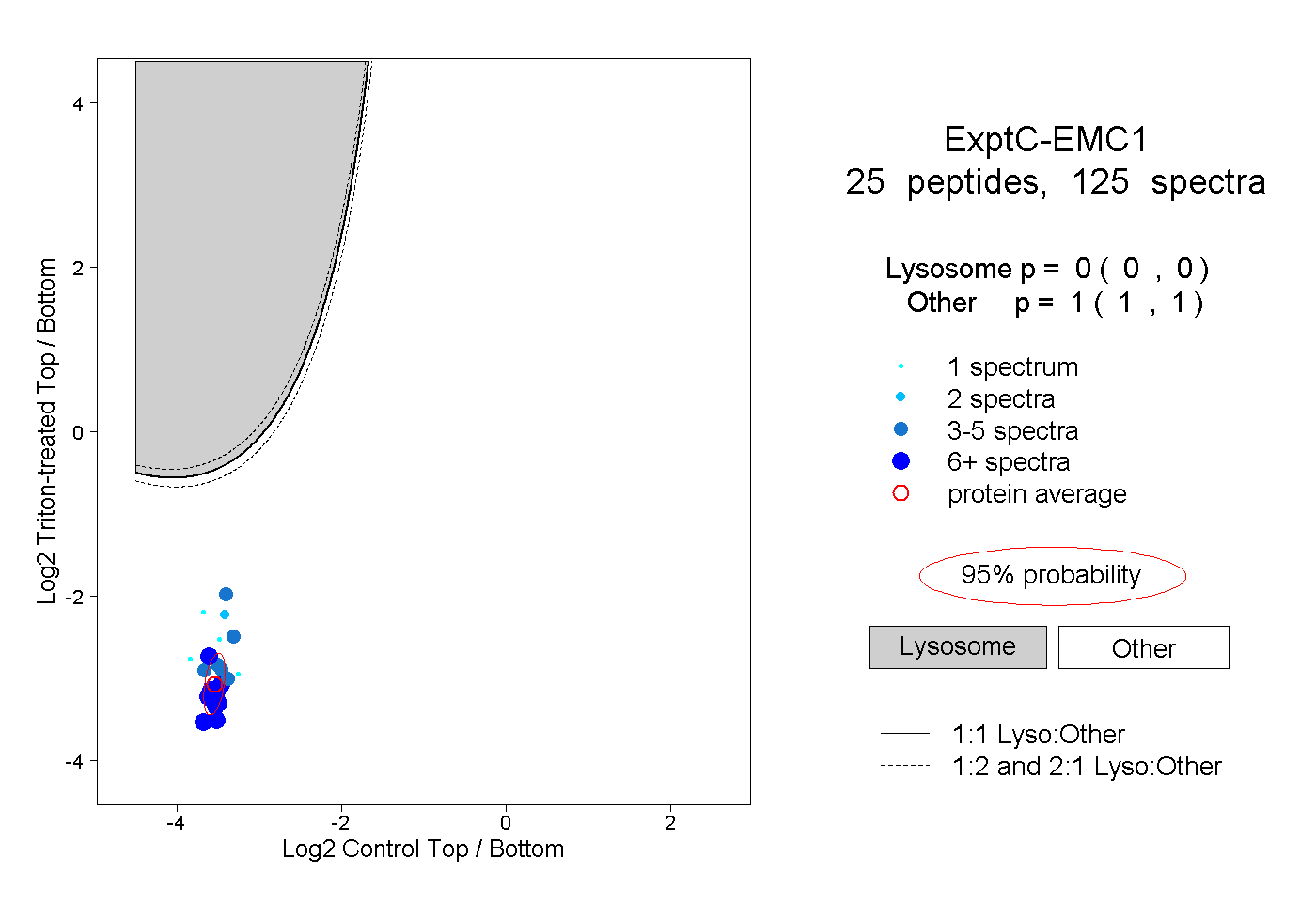 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
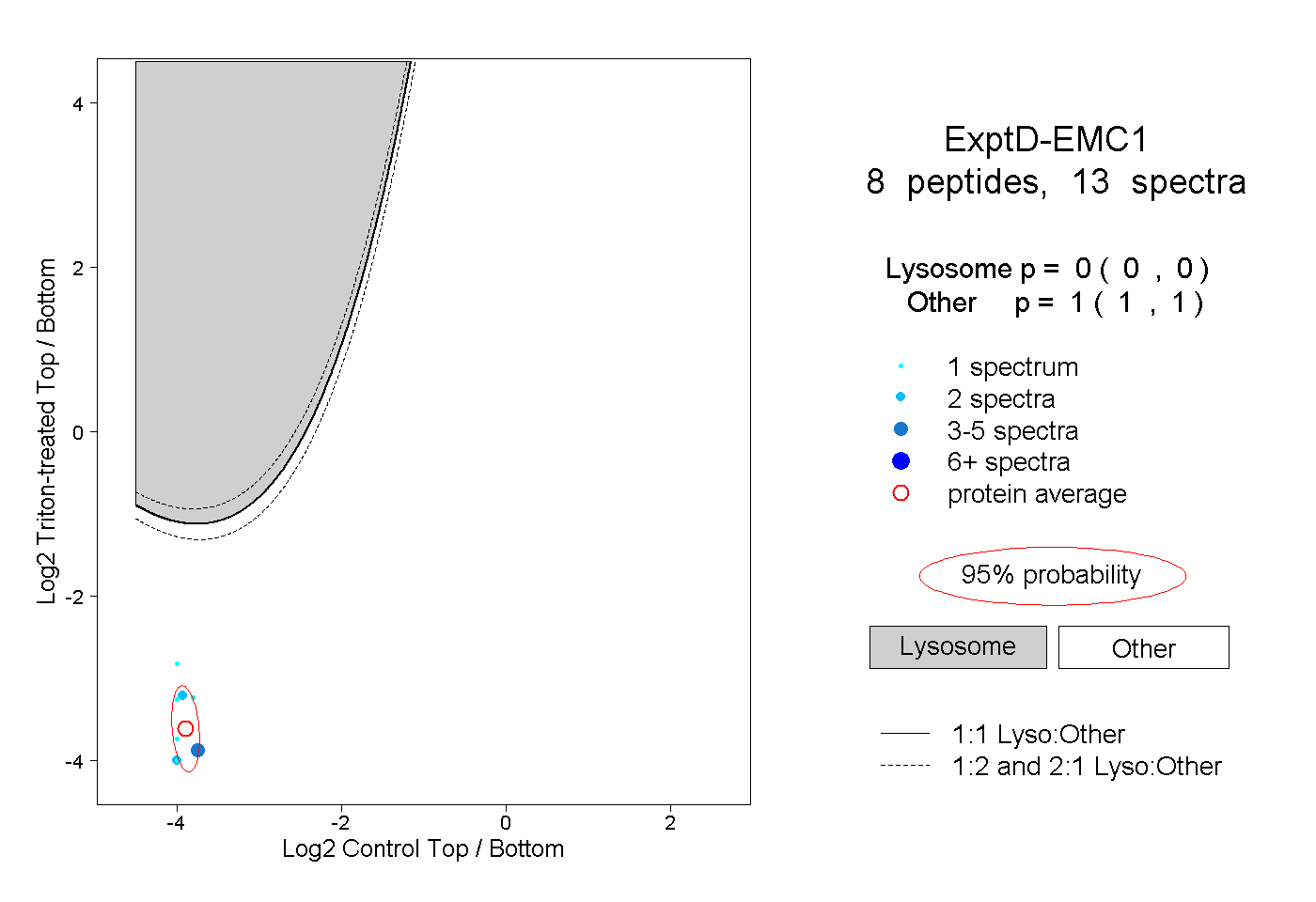 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |