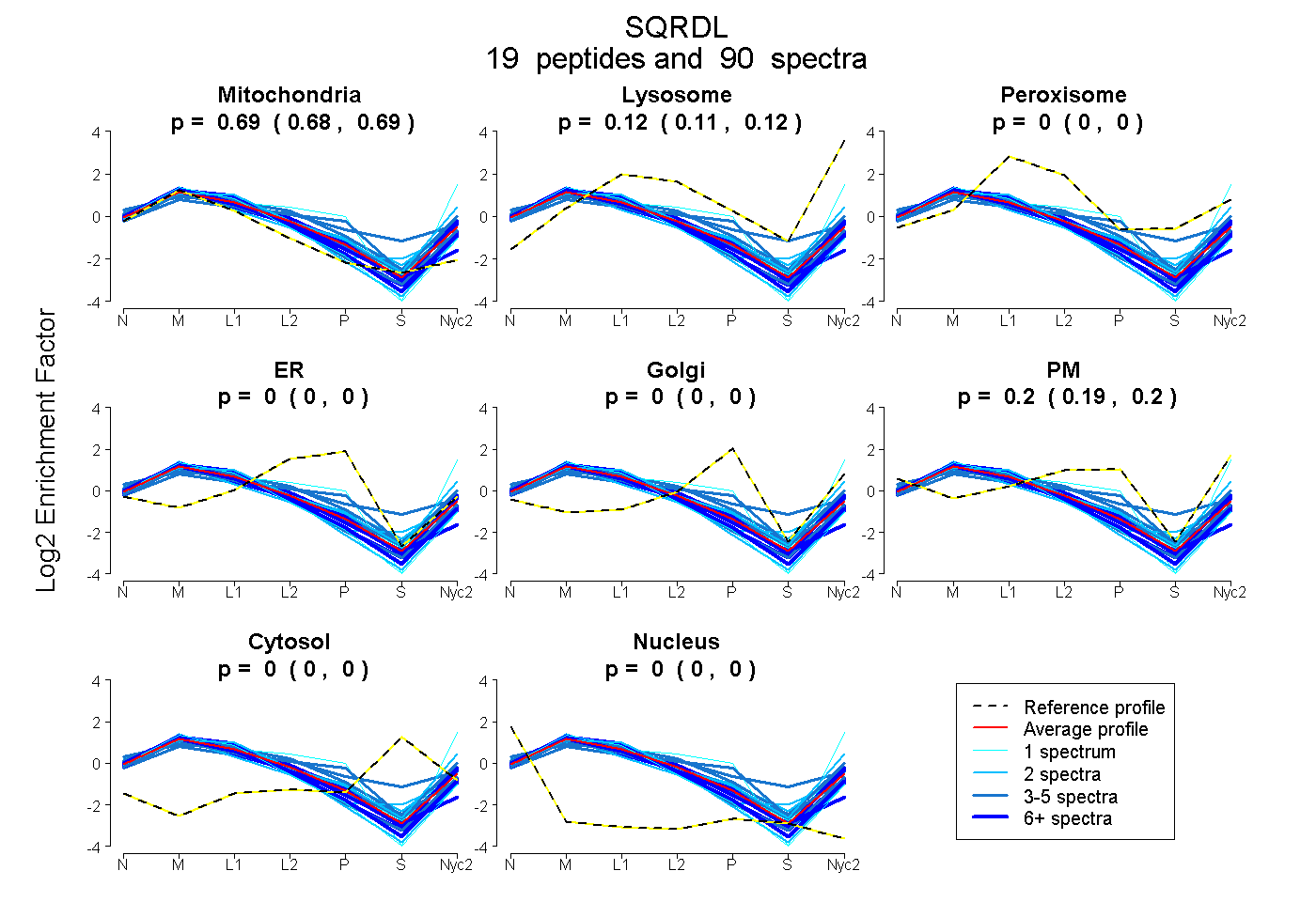
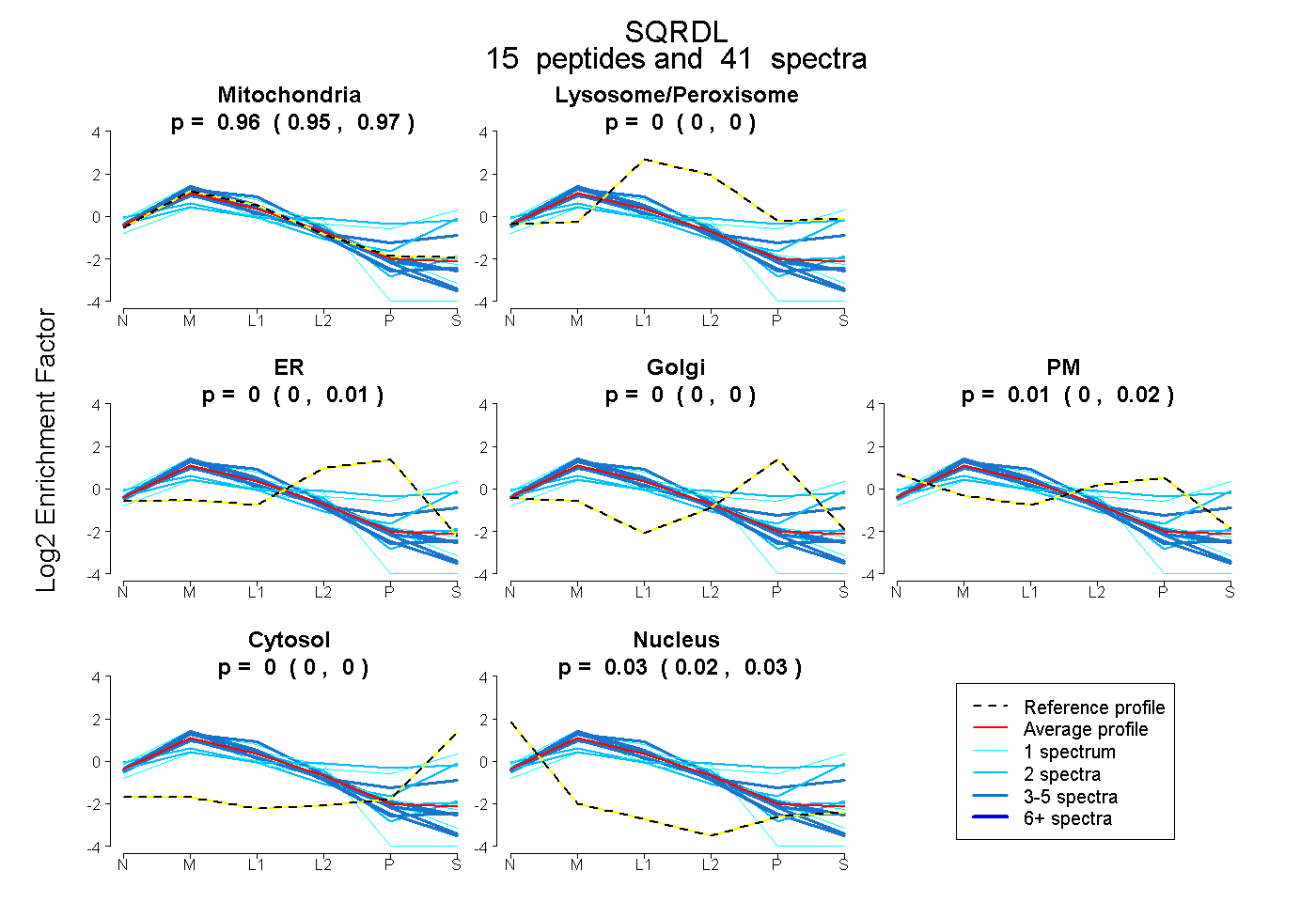
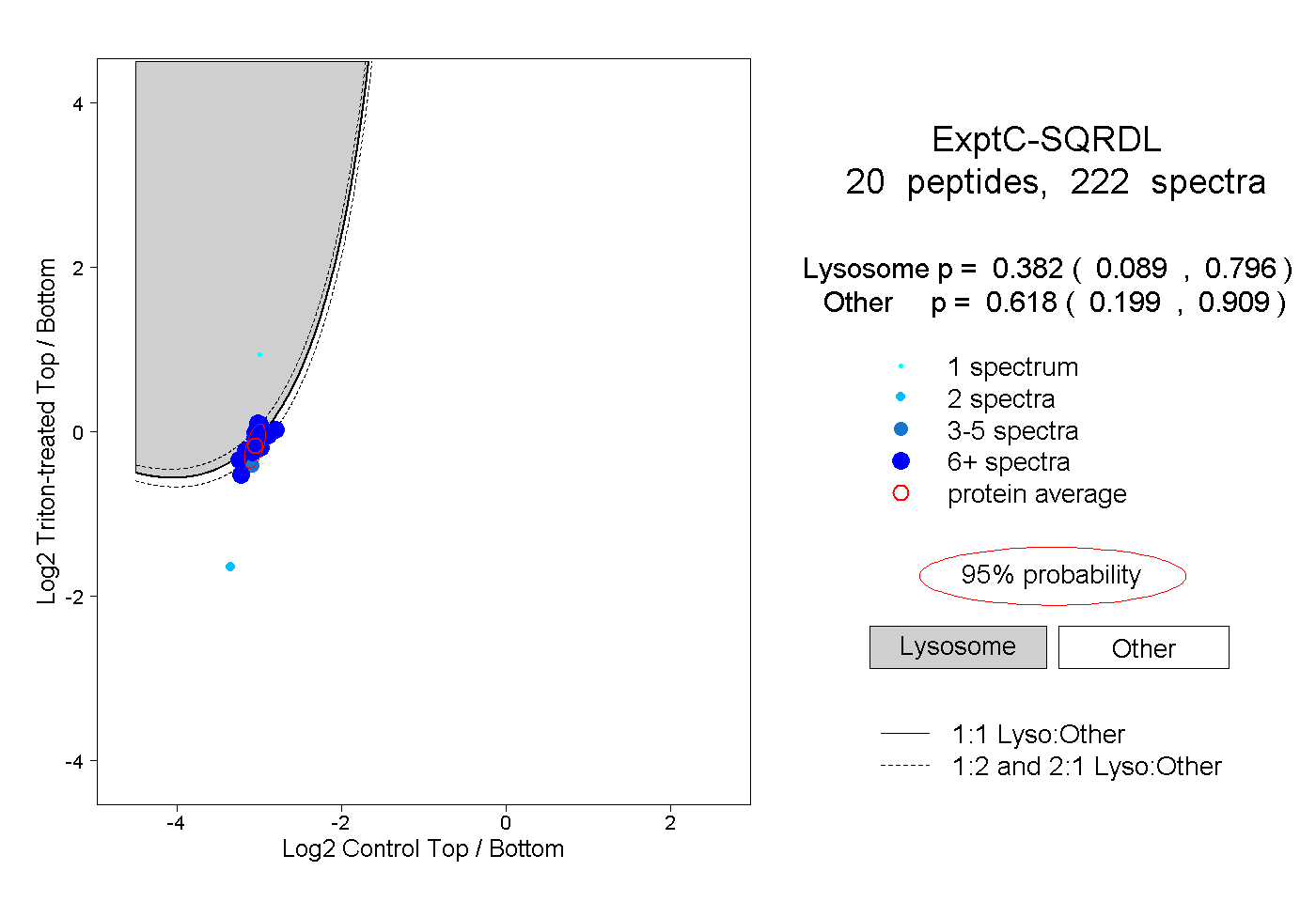
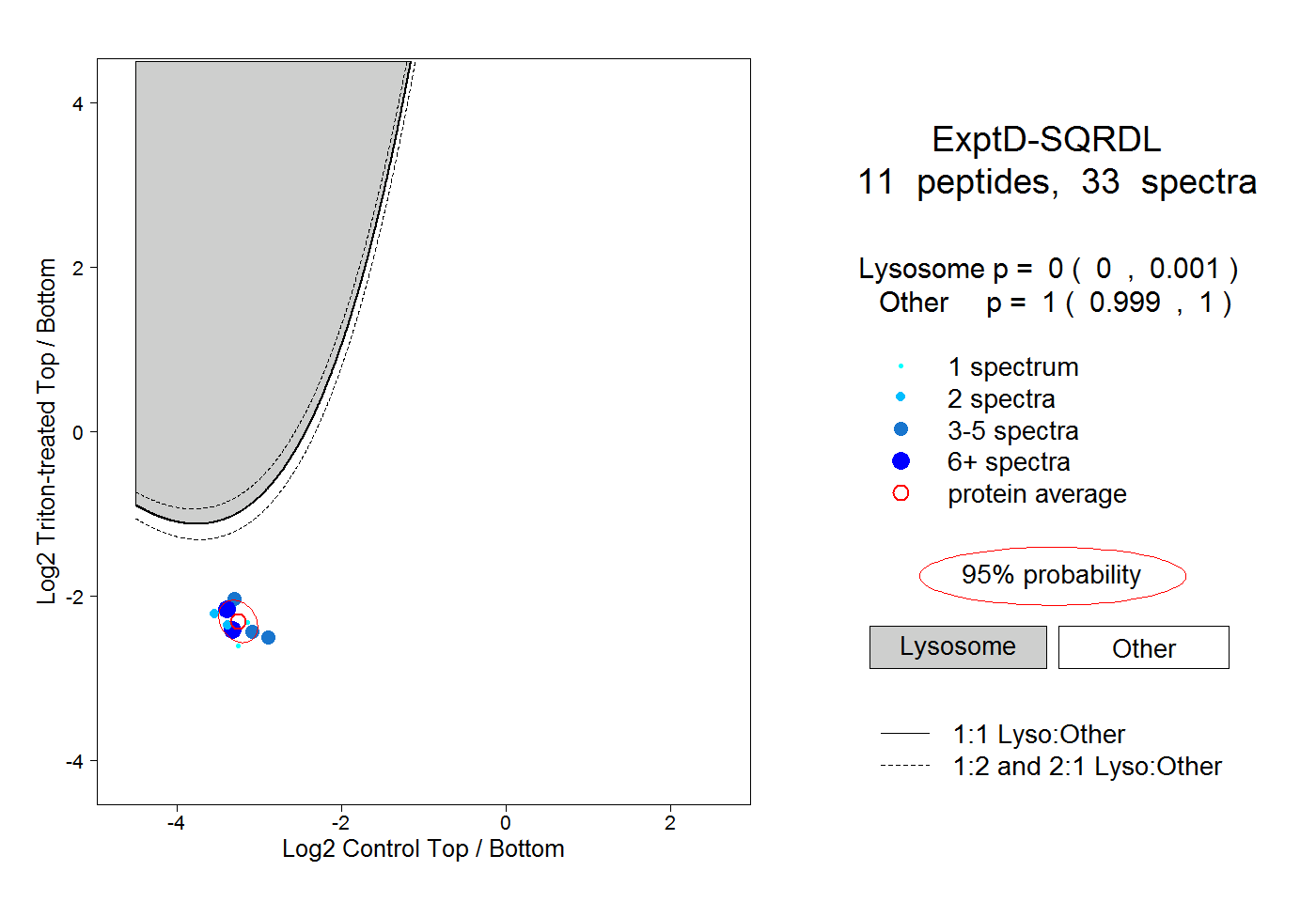
| 17 spectra, HNLIEVR |
|
0.130 |
|
|
|
|
|
|
|
0.870 |
| 14 spectra, YADALQEIIR |
|
0.293 |
|
|
|
|
|
|
|
0.707 |
| 2 spectra, STLSVIPSGVQWIQDR |
|
0.141 |
|
|
|
|
|
|
|
0.859 |
| 2 spectra, NHYEVLVLGGGSGGITMATR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, GYWGGPAFLR |
|
0.227 |
|
|
|
|
|
|
|
0.773 |
| 16 spectra, NVSVNYK |
|
0.862 |
|
|
|
|
|
|
|
0.138 |
| 28 spectra, IGSNYSVK |
|
0.305 |
|
|
|
|
|
|
|
0.695 |
| 13 spectra, IMYLSEAYFR |
|
0.500 |
|
|
|
|
|
|
|
0.500 |
| 8 spectra, NQTPTK |
|
0.465 |
|
|
|
|
|
|
|
0.535 |
| 13 spectra, ALQDFK |
|
0.813 |
|
|
|
|
|
|
|
0.187 |
| 12 spectra, CAGAPQK |
|
0.200 |
|
|
|
|
|
|
|
0.800 |
| 12 spectra, ISMYLMK |
|
0.386 |
|
|
|
|
|
|
|
0.614 |
| 6 spectra, ETLQHK |
|
0.220 |
|
|
|
|
|
|
|
0.780 |
| 4 spectra, TAAAVAAQSGILDR |
|
0.080 |
|
|
|
|
|
|
|
0.920 |
| 7 spectra, GLPEGFAYPK |
|
0.762 |
|
|
|
|
|
|
|
0.238 |
| 19 spectra, VAELNPDQNCIR |
|
0.609 |
|
|
|
|
|
|
|
0.391 |
| 7 spectra, VGAENVAIVEPSER |
|
0.077 |
|
|
|
|
|
|
|
0.923 |
| 4 spectra, ELSSSDR |
|
0.130 |
|
|
|
|
|
|
|
0.870 |
| 1 spectrum, LFHLGLS |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 26 spectra, TISLIMK |
|
0.271 |
|
|
|
|
|
|
|
0.729 |