peptides
spectra
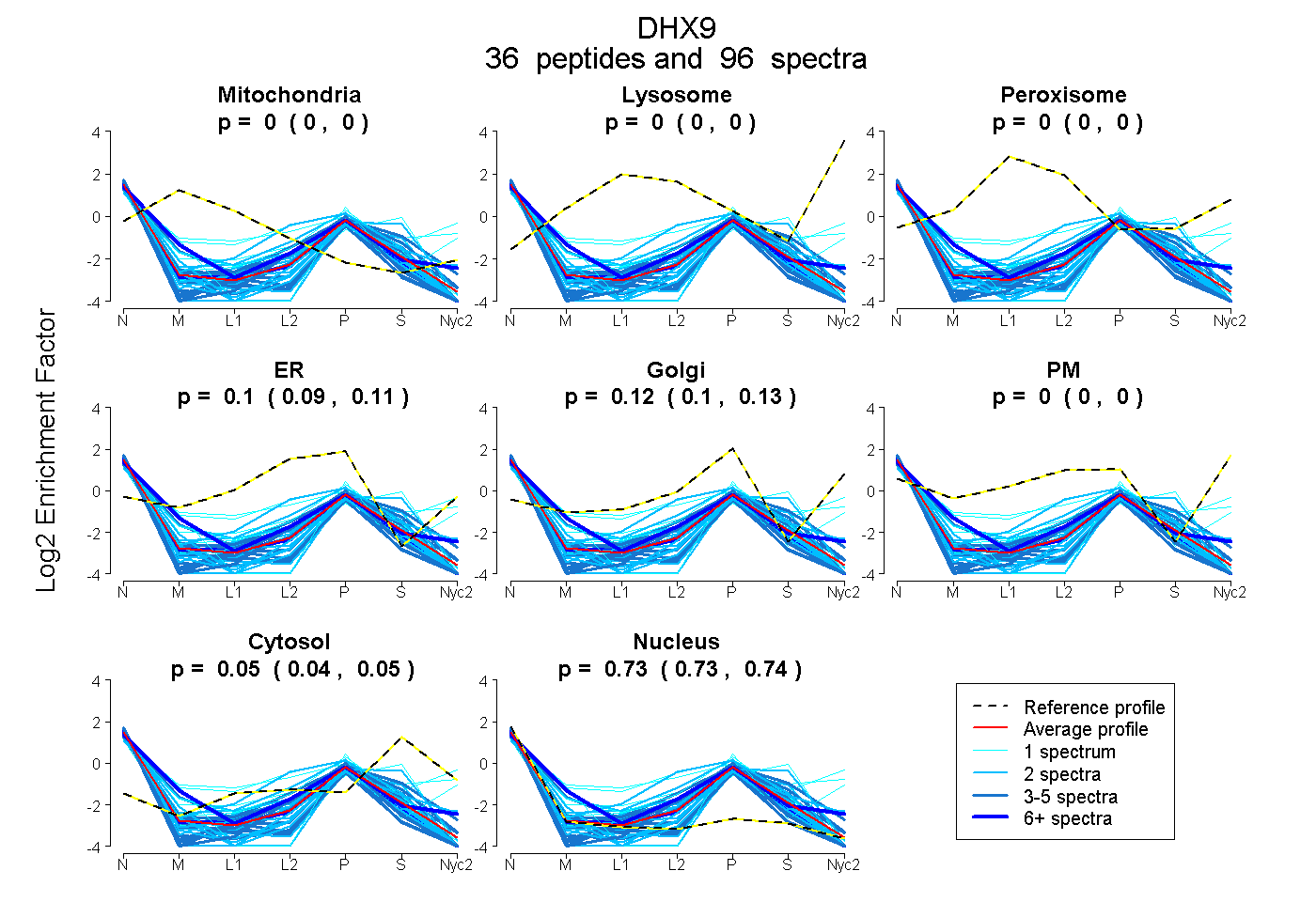
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.091 | 0.113
0.104 | 0.127
0.000 | 0.000
0.043 | 0.050
0.731 | 0.736
peptides
spectra
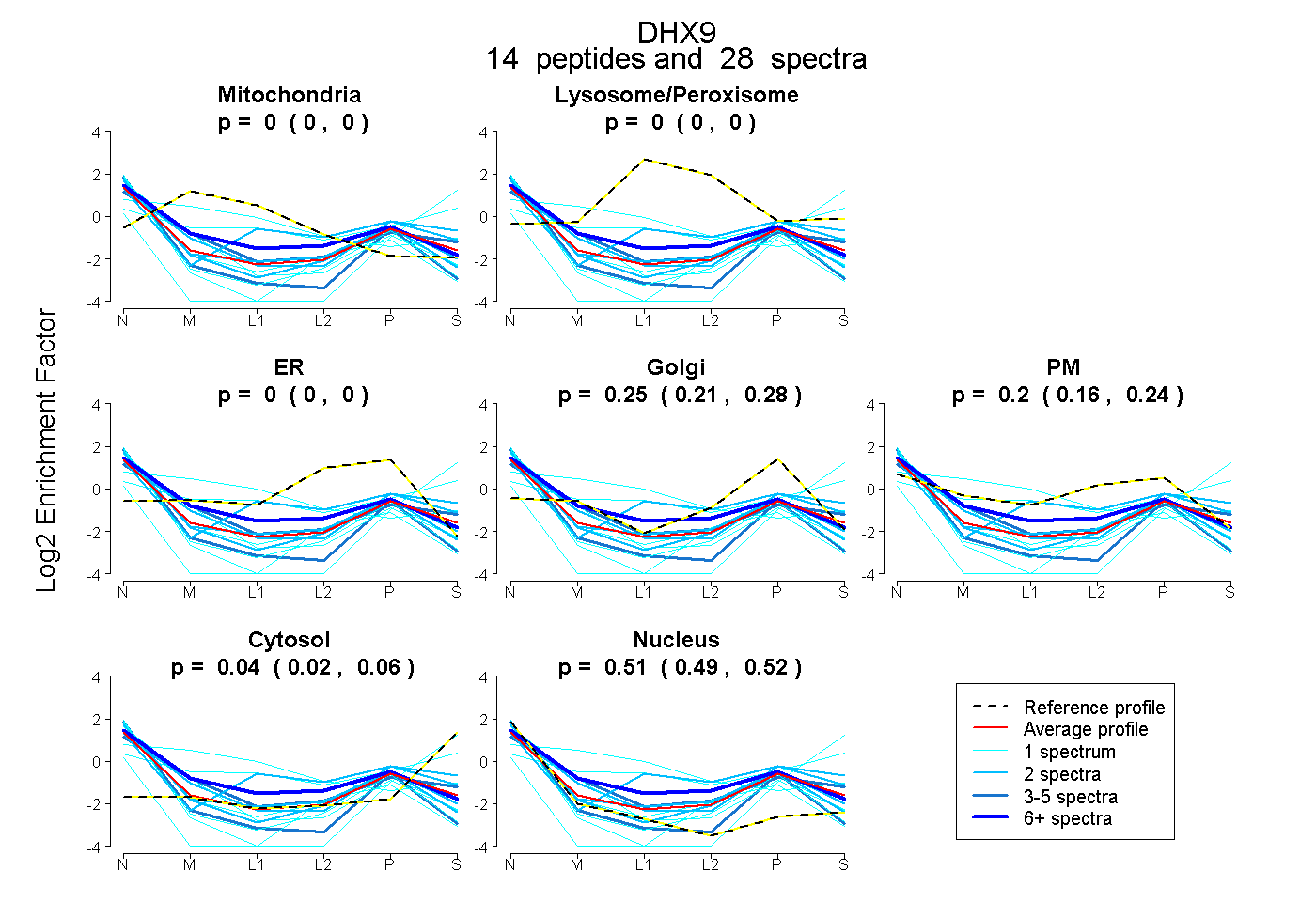
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.209 | 0.281
0.160 | 0.237
0.021 | 0.060
0.491 | 0.523
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
96 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.103 0.091 | 0.113 |
0.116 0.104 | 0.127 |
0.000 0.000 | 0.000 |
0.047 0.043 | 0.050 |
0.734 0.731 | 0.736 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
28 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.246 0.209 | 0.281 |
0.203 0.160 | 0.237 |
0.042 0.021 | 0.060 |
0.508 0.491 | 0.523 |
| 2 spectra, ILTTEGR | 0.000 | 0.000 | 0.000 | 0.345 | 0.130 | 0.089 | 0.436 | |||
| 4 spectra, DFVNYLVR | 0.000 | 0.000 | 0.000 | 0.247 | 0.000 | 0.000 | 0.753 | |||
| 1 spectrum, VFDPVPDGVTK | 0.000 | 0.223 | 0.000 | 0.000 | 0.305 | 0.379 | 0.093 | |||
| 2 spectra, MSGEEAEIR | 0.000 | 0.000 | 0.000 | 0.370 | 0.043 | 0.000 | 0.587 | |||
| 1 spectrum, LQISHEAAACITALR | 0.000 | 0.000 | 0.000 | 0.337 | 0.031 | 0.000 | 0.632 | |||
| 1 spectrum, LGYIHR | 0.000 | 0.000 | 0.000 | 0.261 | 0.000 | 0.000 | 0.739 | |||
| 6 spectra, YQILPLHSQIPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.620 | 0.000 | 0.380 | |||
| 1 spectrum, YPSPFFVFGEK | 0.000 | 0.000 | 0.000 | 0.305 | 0.000 | 0.000 | 0.695 | |||
| 2 spectra, VRPGFCFHLCSR | 0.000 | 0.316 | 0.000 | 0.101 | 0.116 | 0.065 | 0.402 | |||
| 2 spectra, NALIHK | 0.000 | 0.000 | 0.000 | 0.183 | 0.290 | 0.000 | 0.527 | |||
| 3 spectra, GISHVIVDEIHER | 0.000 | 0.000 | 0.000 | 0.113 | 0.344 | 0.144 | 0.399 | |||
| 1 spectrum, LAAQSCALSLVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.641 | 0.359 | |||
| 1 spectrum, DVVLAYPEVR | 0.444 | 0.193 | 0.000 | 0.000 | 0.120 | 0.021 | 0.222 | |||
| 1 spectrum, AAMEALVVEVSK | 0.000 | 0.000 | 0.000 | 0.211 | 0.198 | 0.000 | 0.591 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
19 spectra |
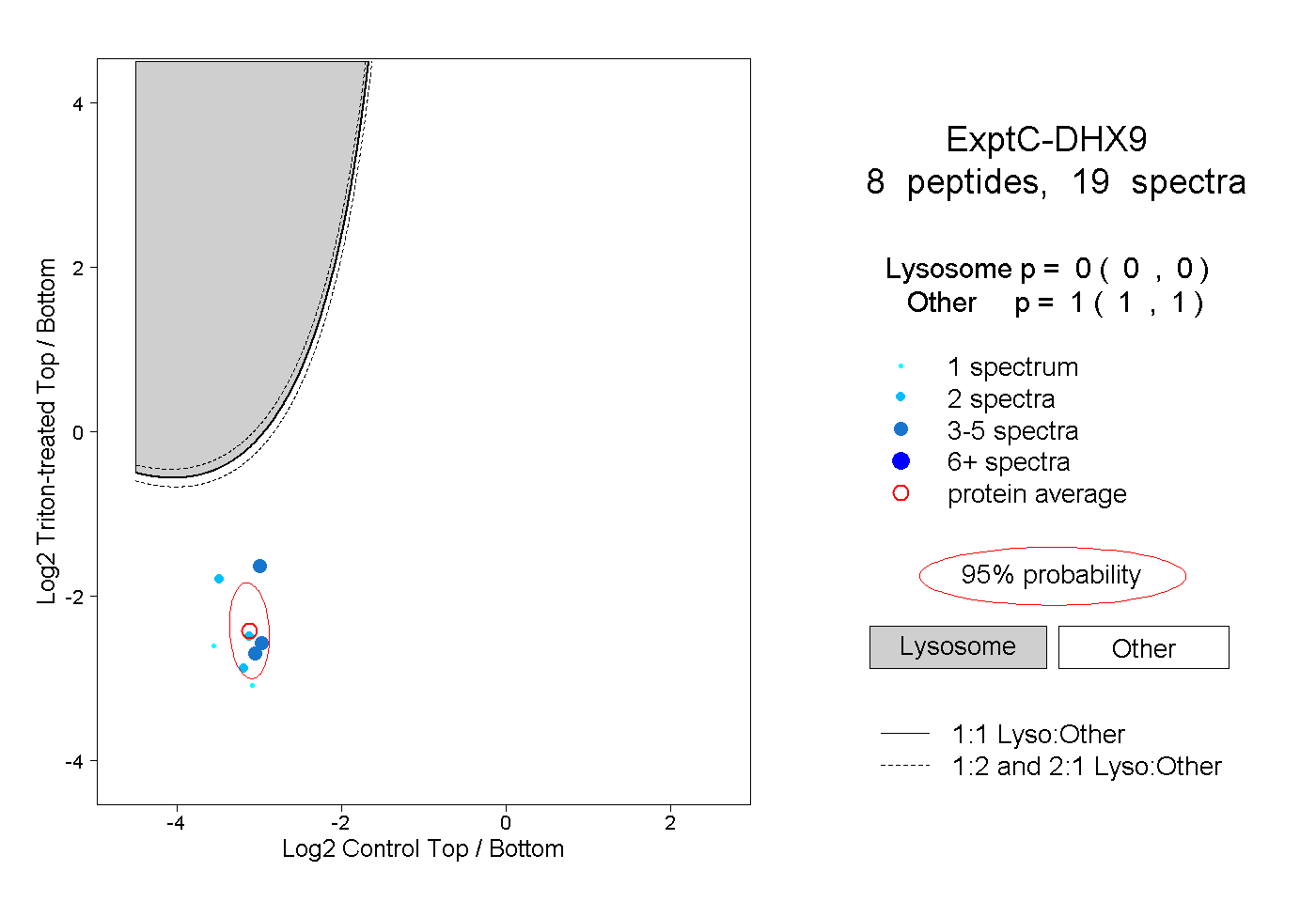 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
8 spectra |
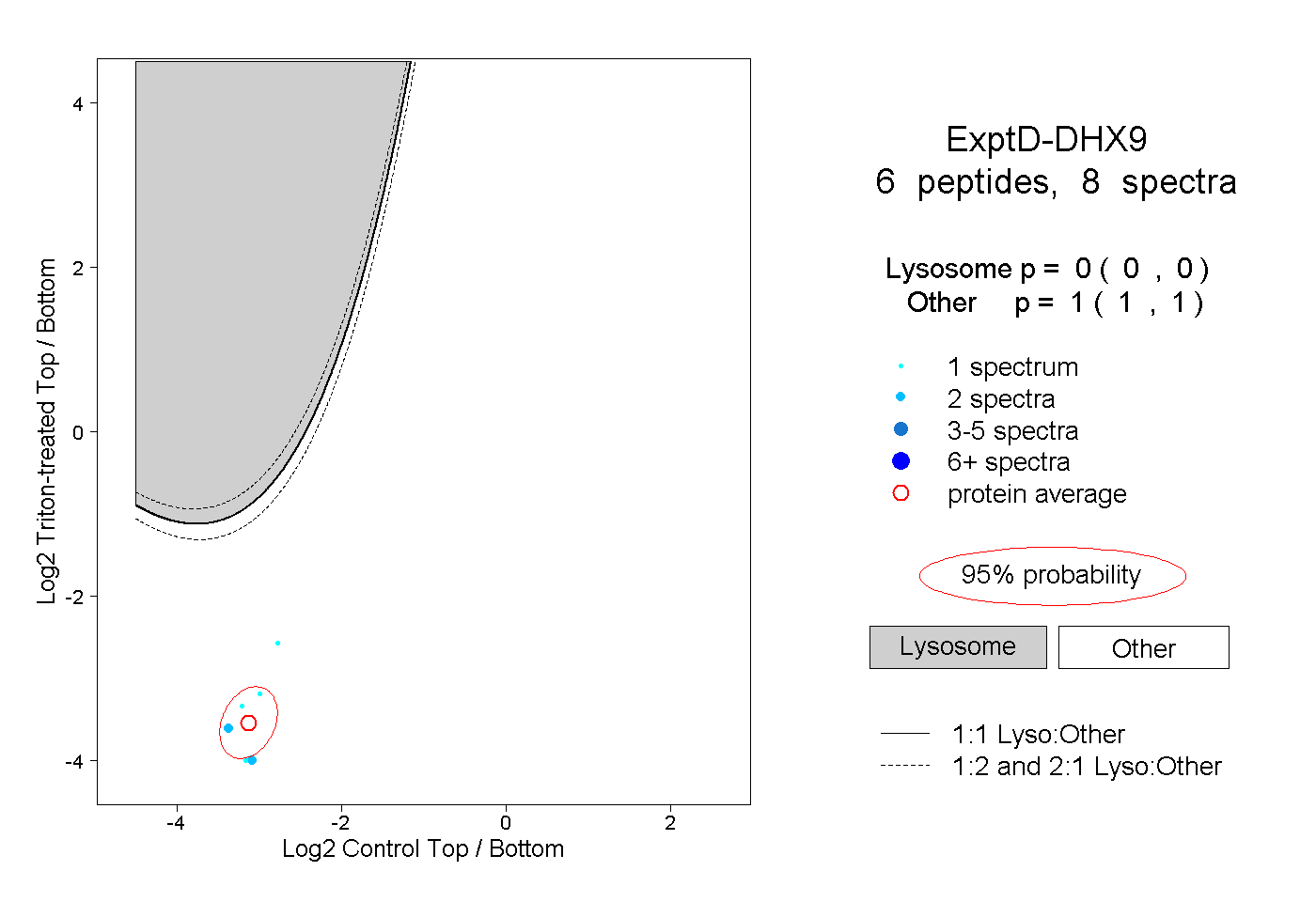 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |