peptides
spectra
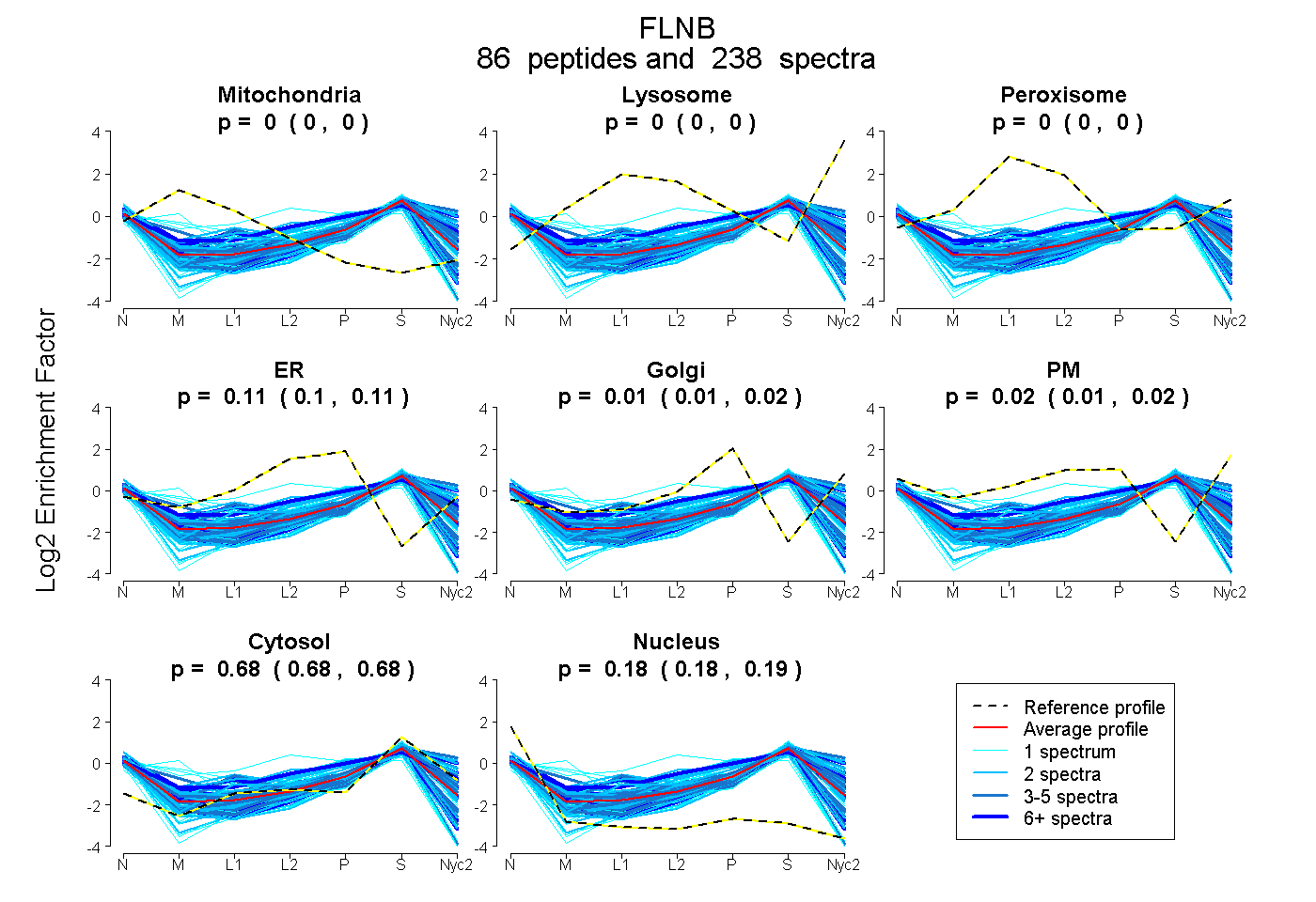
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.099 | 0.110
0.008 | 0.016
0.012 | 0.020
0.681 | 0.682
0.183 | 0.185
peptides
spectra
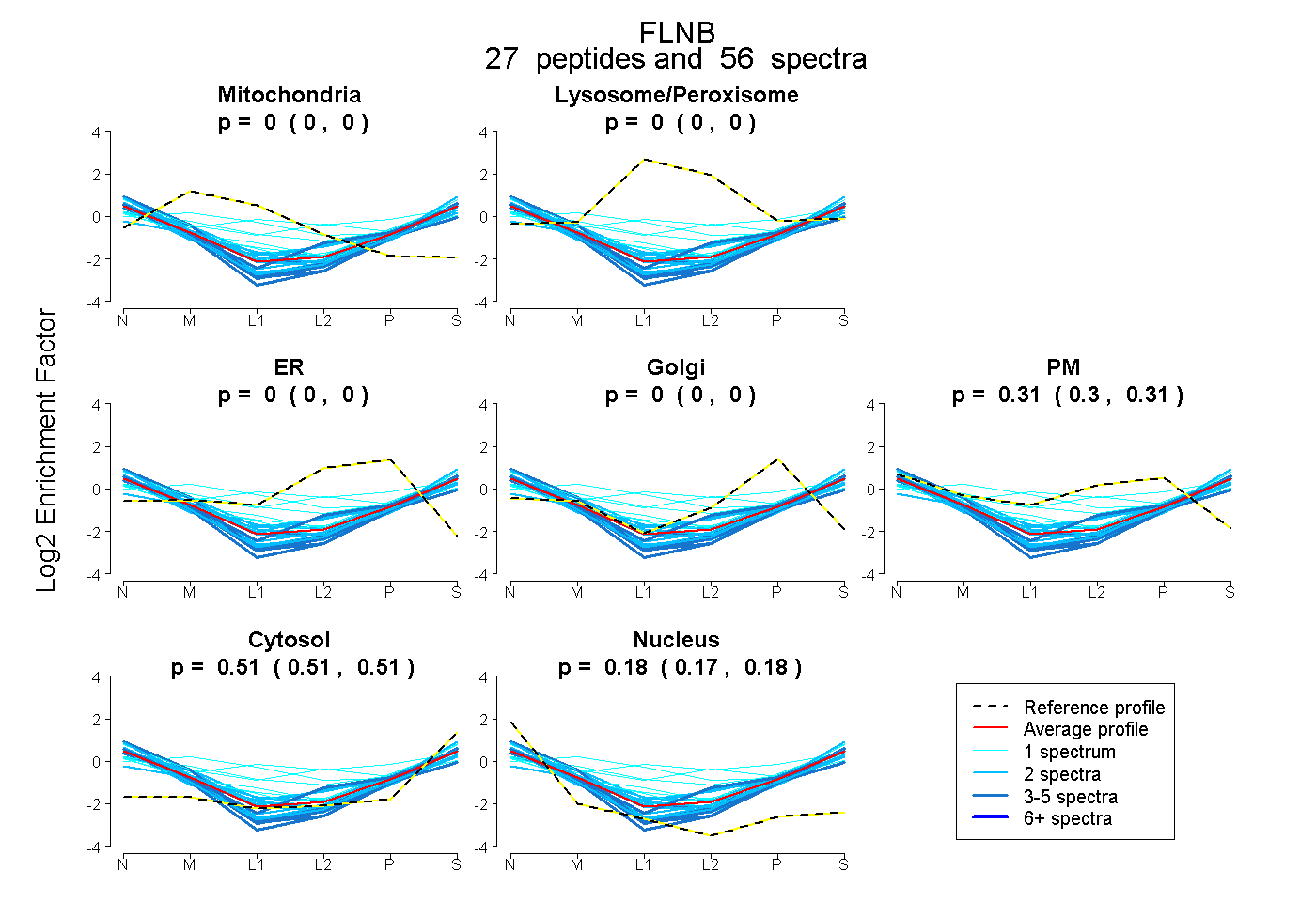
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.305 | 0.313
0.510 | 0.515
0.174 | 0.182
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
238 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.105 0.099 | 0.110 |
0.012 0.008 | 0.016 |
0.016 0.012 | 0.020 |
0.682 0.681 | 0.682 |
0.184 0.183 | 0.185 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
56 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.309 0.305 | 0.313 |
0.513 0.510 | 0.515 |
0.178 0.174 | 0.182 |
| 1 spectrum, TFEMSDFIVDTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.287 | 0.612 | 0.102 | |||
| 3 spectra, LDVTILSPSR | 0.000 | 0.000 | 0.000 | 0.166 | 0.069 | 0.514 | 0.252 | |||
| 2 spectra, AGGPGLER | 0.000 | 0.000 | 0.000 | 0.034 | 0.174 | 0.456 | 0.335 | |||
| 1 spectrum, EATTDFTVDARPLTQVGGDHIK | 0.000 | 0.016 | 0.000 | 0.000 | 0.288 | 0.514 | 0.183 | |||
| 1 spectrum, SPFEVNVDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.299 | 0.520 | 0.180 | |||
| 1 spectrum, DNADGTYQVEYTPFEK | 0.000 | 0.037 | 0.000 | 0.000 | 0.335 | 0.503 | 0.125 | |||
| 3 spectra, IQQNTFTR | 0.000 | 0.000 | 0.000 | 0.207 | 0.049 | 0.360 | 0.384 | |||
| 2 spectra, DLDIIDNYDYSHTVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.376 | 0.537 | 0.087 | |||
| 2 spectra, AGLAPLEVR | 0.000 | 0.000 | 0.000 | 0.157 | 0.109 | 0.471 | 0.262 | |||
| 2 spectra, WCNEHLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.307 | 0.418 | 0.275 | |||
| 1 spectrum, APSVATVGSICDLNLK | 0.249 | 0.180 | 0.000 | 0.000 | 0.217 | 0.353 | 0.000 | |||
| 5 spectra, EAFTNKPNVFTVVTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.272 | 0.540 | 0.188 | |||
| 2 spectra, YADEEIPR | 0.000 | 0.000 | 0.000 | 0.178 | 0.070 | 0.497 | 0.256 | |||
| 4 spectra, VNQPASFAIR | 0.000 | 0.000 | 0.000 | 0.167 | 0.031 | 0.522 | 0.280 | |||
| 1 spectrum, LLGWIQNK | 0.000 | 0.208 | 0.000 | 0.000 | 0.400 | 0.271 | 0.121 | |||
| 2 spectra, YAPTEVGLHEMHIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.325 | 0.671 | 0.005 | |||
| 1 spectrum, FADEHVPGSPFTVK | 0.000 | 0.115 | 0.000 | 0.000 | 0.198 | 0.548 | 0.138 | |||
| 1 spectrum, FNDEHIPDSPYLVPVIAPSDDAR | 0.080 | 0.131 | 0.000 | 0.000 | 0.327 | 0.424 | 0.038 | |||
| 4 spectra, NSVELLVEDR | 0.000 | 0.000 | 0.000 | 0.151 | 0.000 | 0.530 | 0.319 | |||
| 2 spectra, IAGPGLSSCVR | 0.000 | 0.000 | 0.000 | 0.018 | 0.270 | 0.479 | 0.232 | |||
| 1 spectrum, ILAQDGEGQPIDIQMK | 0.000 | 0.299 | 0.000 | 0.000 | 0.357 | 0.345 | 0.000 | |||
| 4 spectra, YVPPAPGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.380 | 0.493 | 0.127 | |||
| 2 spectra, IGNLQTDLSDGLR | 0.000 | 0.000 | 0.000 | 0.081 | 0.146 | 0.514 | 0.259 | |||
| 2 spectra, ACIPQSFTVDTSK | 0.000 | 0.011 | 0.000 | 0.000 | 0.335 | 0.473 | 0.181 | |||
| 2 spectra, EAGAGGLSIAVEGPSK | 0.000 | 0.009 | 0.000 | 0.000 | 0.356 | 0.515 | 0.120 | |||
| 2 spectra, GEAGIPAEFSIWTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.240 | 0.522 | 0.238 | |||
| 2 spectra, TGEEVGFVVDAK | 0.000 | 0.000 | 0.000 | 0.098 | 0.206 | 0.491 | 0.205 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
215 spectra |
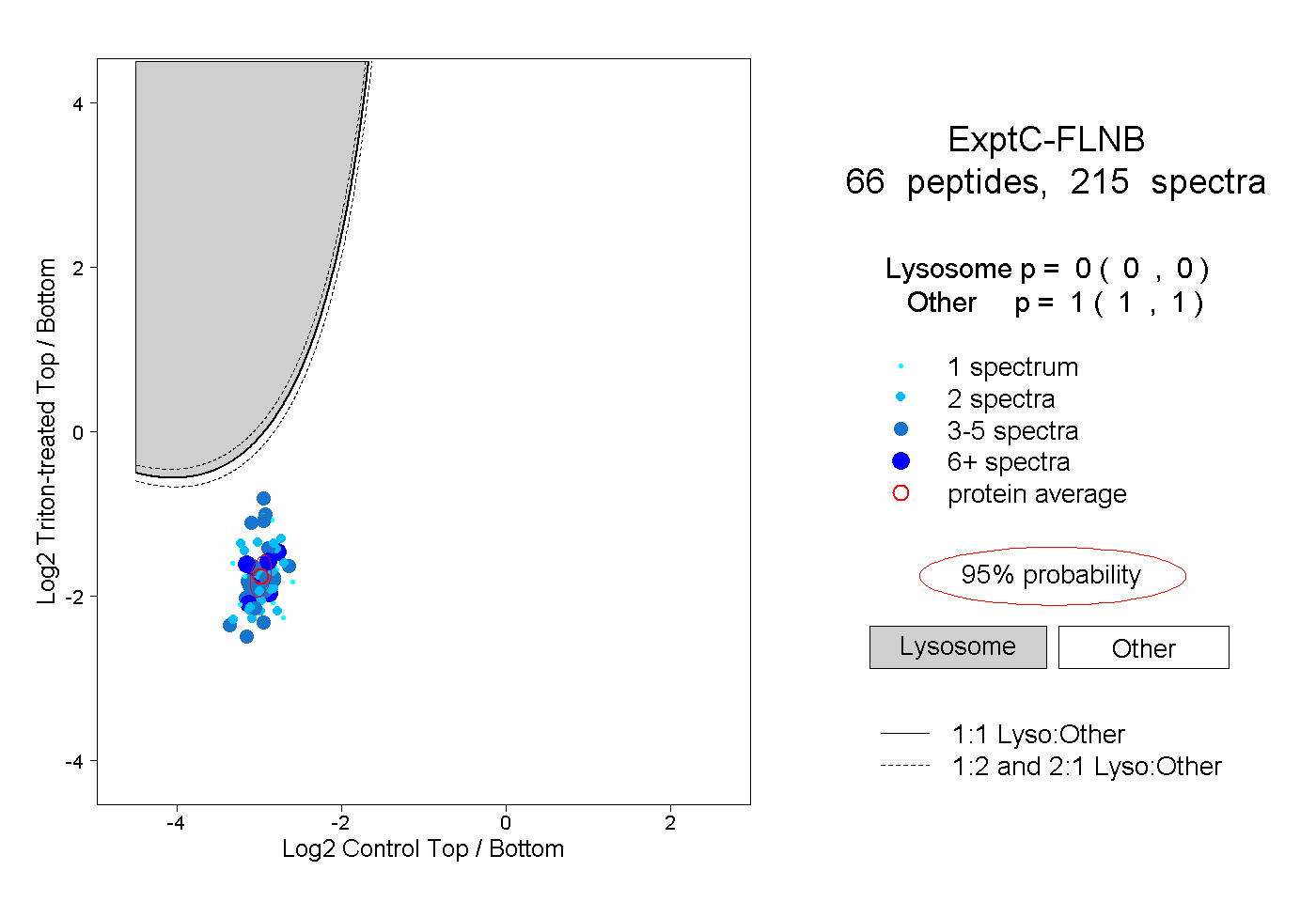 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
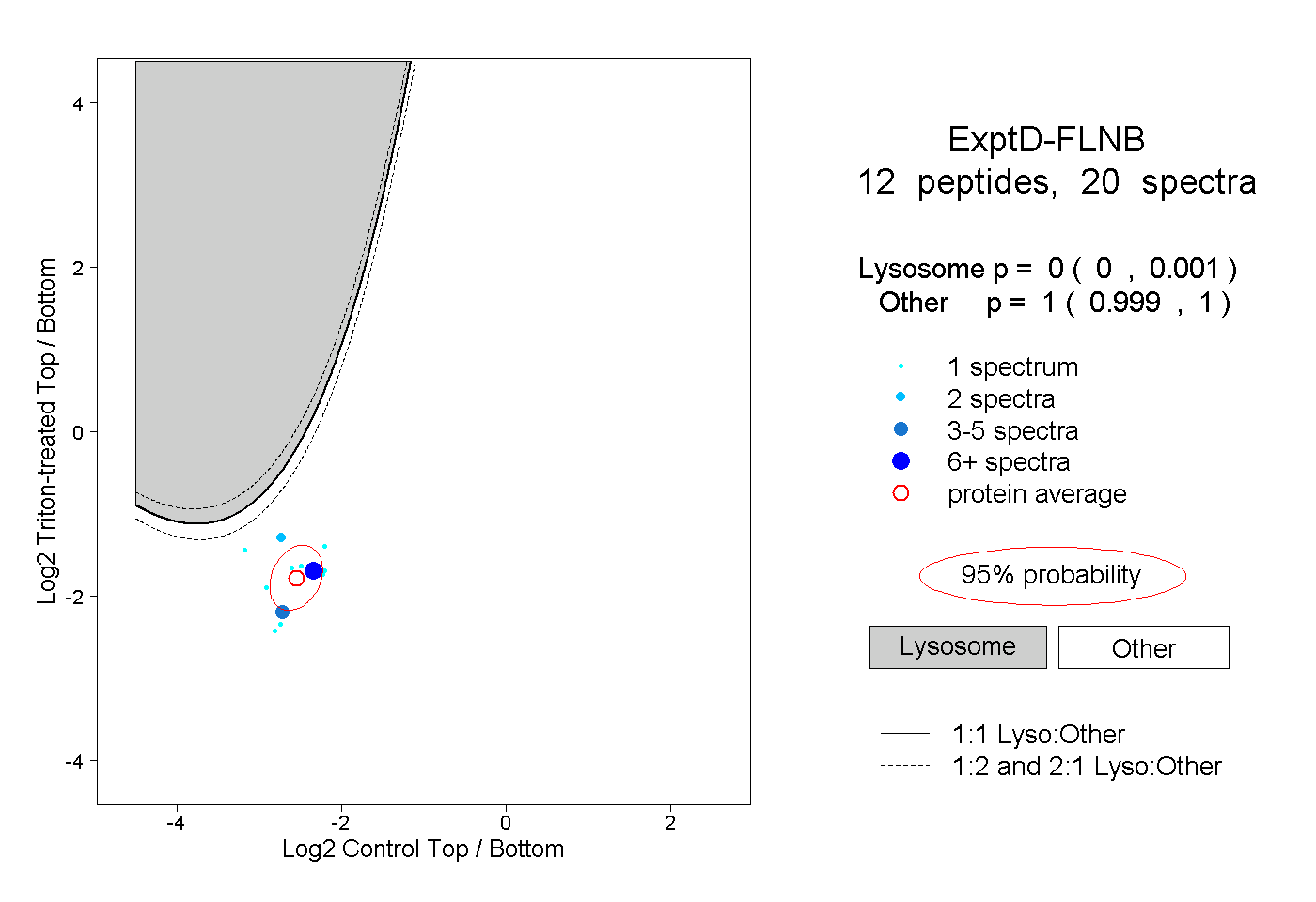 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |