peptides
spectra
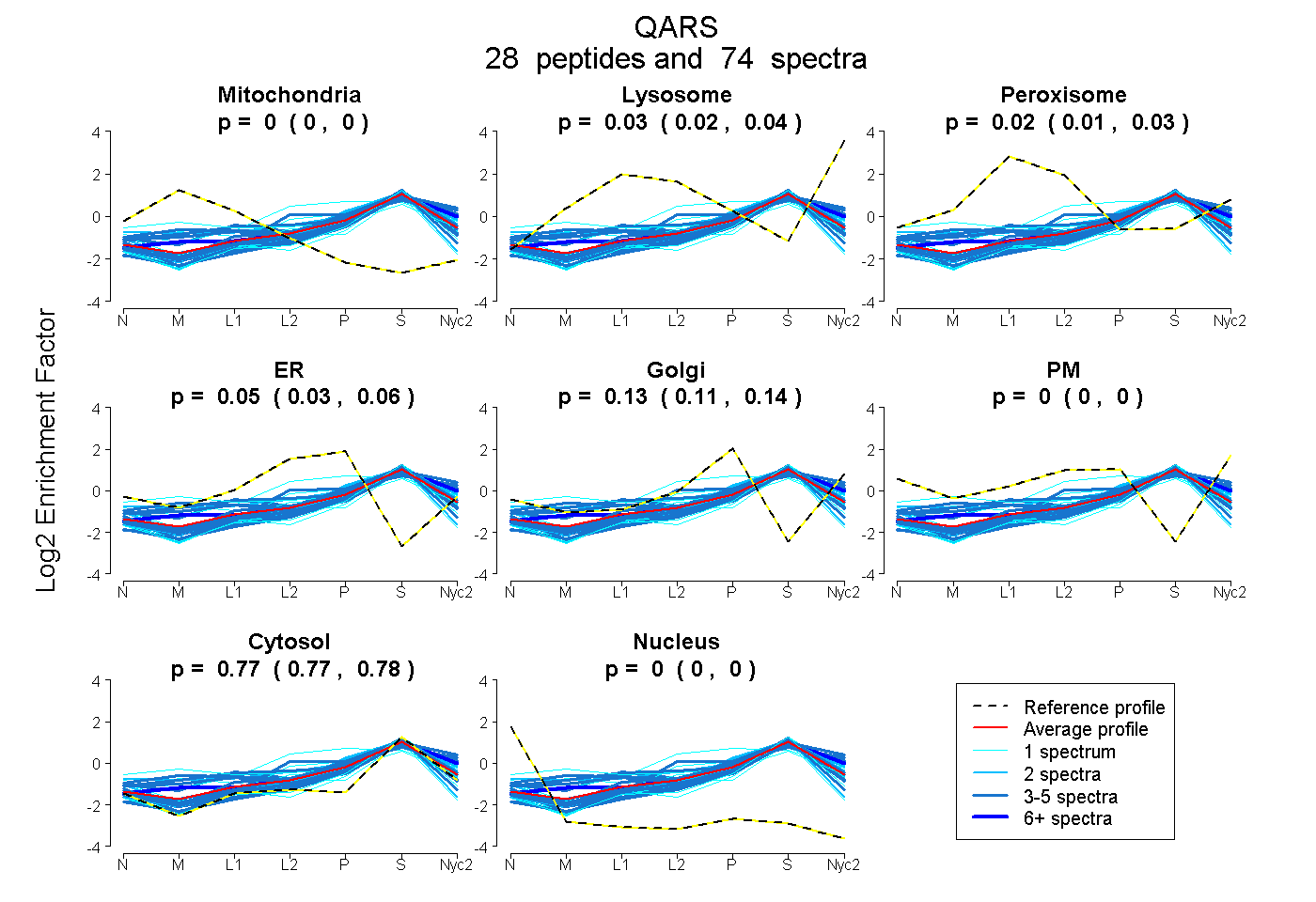
0.000 | 0.000
0.022 | 0.040
0.009 | 0.031
0.029 | 0.058
0.114 | 0.143
0.000 | 0.000
0.768 | 0.776
0.000 | 0.000
peptides
spectra
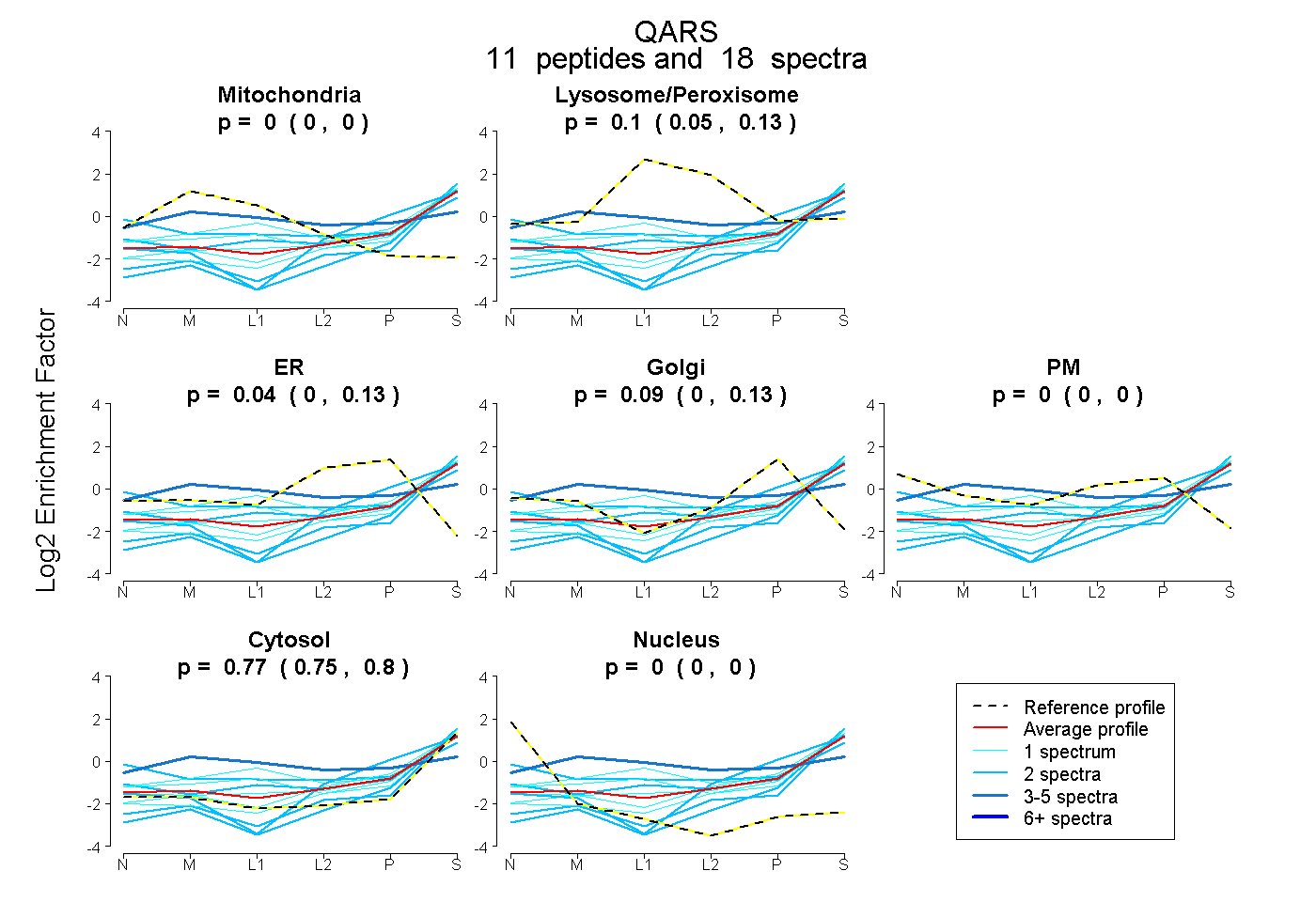
0.000 | 0.000
0.046 | 0.132
0.000 | 0.132
0.000 | 0.133
0.000 | 0.000
0.746 | 0.797
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
74 spectra |
 |
0.000 0.000 | 0.000 |
0.032 0.022 | 0.040 |
0.021 0.009 | 0.031 |
0.045 0.029 | 0.058 |
0.129 0.114 | 0.143 |
0.000 0.000 | 0.000 |
0.772 0.768 | 0.776 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
18 spectra |
 |
0.000 0.000 | 0.000 |
0.099 0.046 | 0.132 |
0.041 0.000 | 0.132 |
0.090 0.000 | 0.133 |
0.000 0.000 | 0.000 |
0.770 0.746 | 0.797 |
0.000 0.000 | 0.000 |
| 2 spectra, HRPQLLVER | 0.000 | 0.208 | 0.000 | 0.062 | 0.000 | 0.730 | 0.000 | |||
| 1 spectrum, LNLHYAVVSK | 0.000 | 0.346 | 0.000 | 0.027 | 0.000 | 0.627 | 0.000 | |||
| 1 spectrum, FAEGEATLR | 0.000 | 0.000 | 0.174 | 0.000 | 0.000 | 0.826 | 0.000 | |||
| 2 spectra, DRPIEESLLLFEAMR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, AFIHWVSQPLVCEIR | 0.000 | 0.216 | 0.000 | 0.000 | 0.221 | 0.538 | 0.024 | |||
| 3 spectra, QHLEITGGQVR | 0.172 | 0.348 | 0.000 | 0.193 | 0.000 | 0.287 | 0.000 | |||
| 1 spectrum, ANNGICFLR | 0.000 | 0.139 | 0.000 | 0.081 | 0.000 | 0.780 | 0.000 | |||
| 2 spectra, NAALSTQLR | 0.000 | 0.000 | 0.000 | 0.311 | 0.000 | 0.689 | 0.000 | |||
| 1 spectrum, HTGYVIELQHVVR | 0.000 | 0.234 | 0.000 | 0.038 | 0.000 | 0.728 | 0.000 | |||
| 2 spectra, ILQLVAAGAVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, LFTLTALR | 0.000 | 0.000 | 0.057 | 0.000 | 0.000 | 0.943 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
53 spectra |
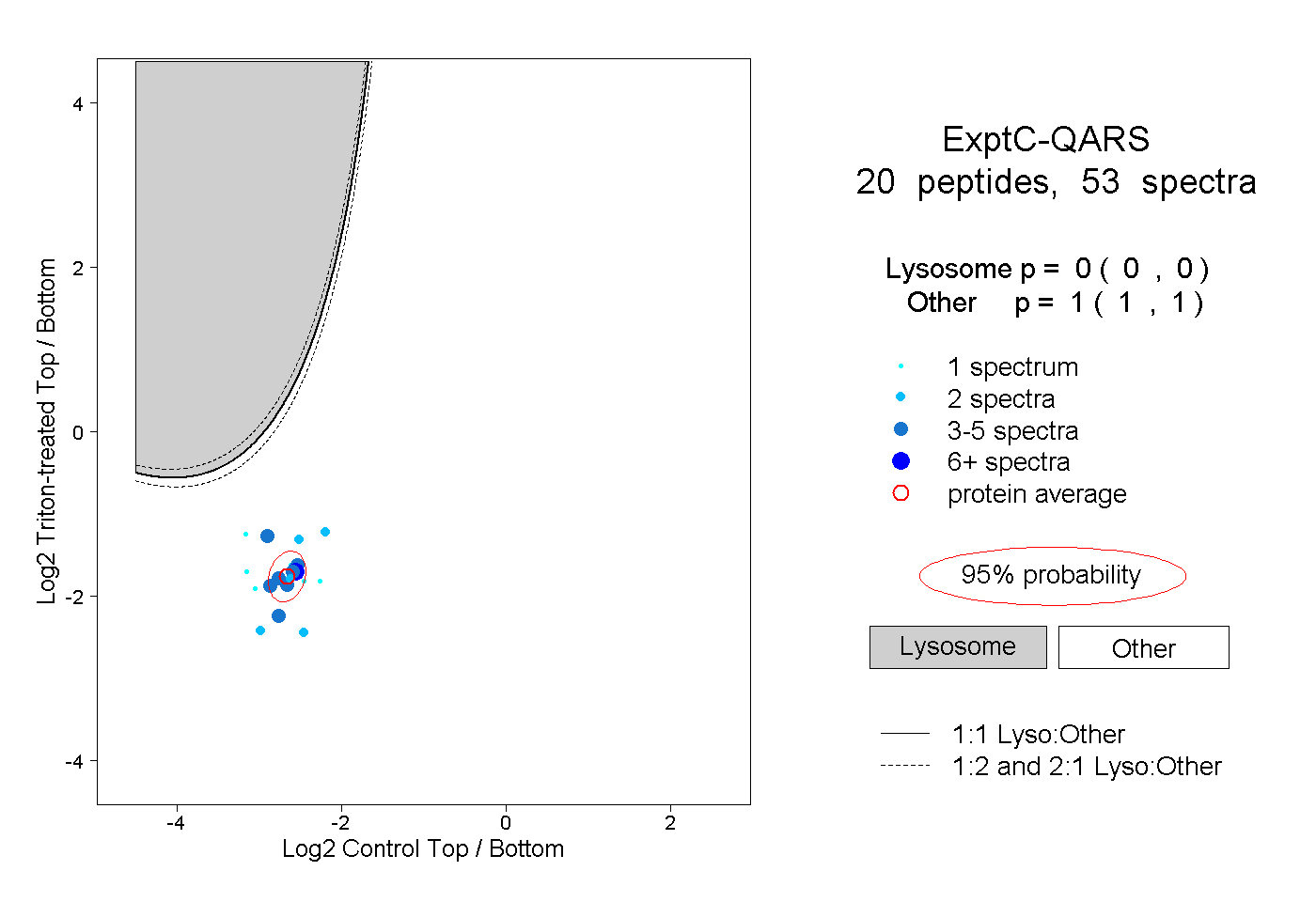 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
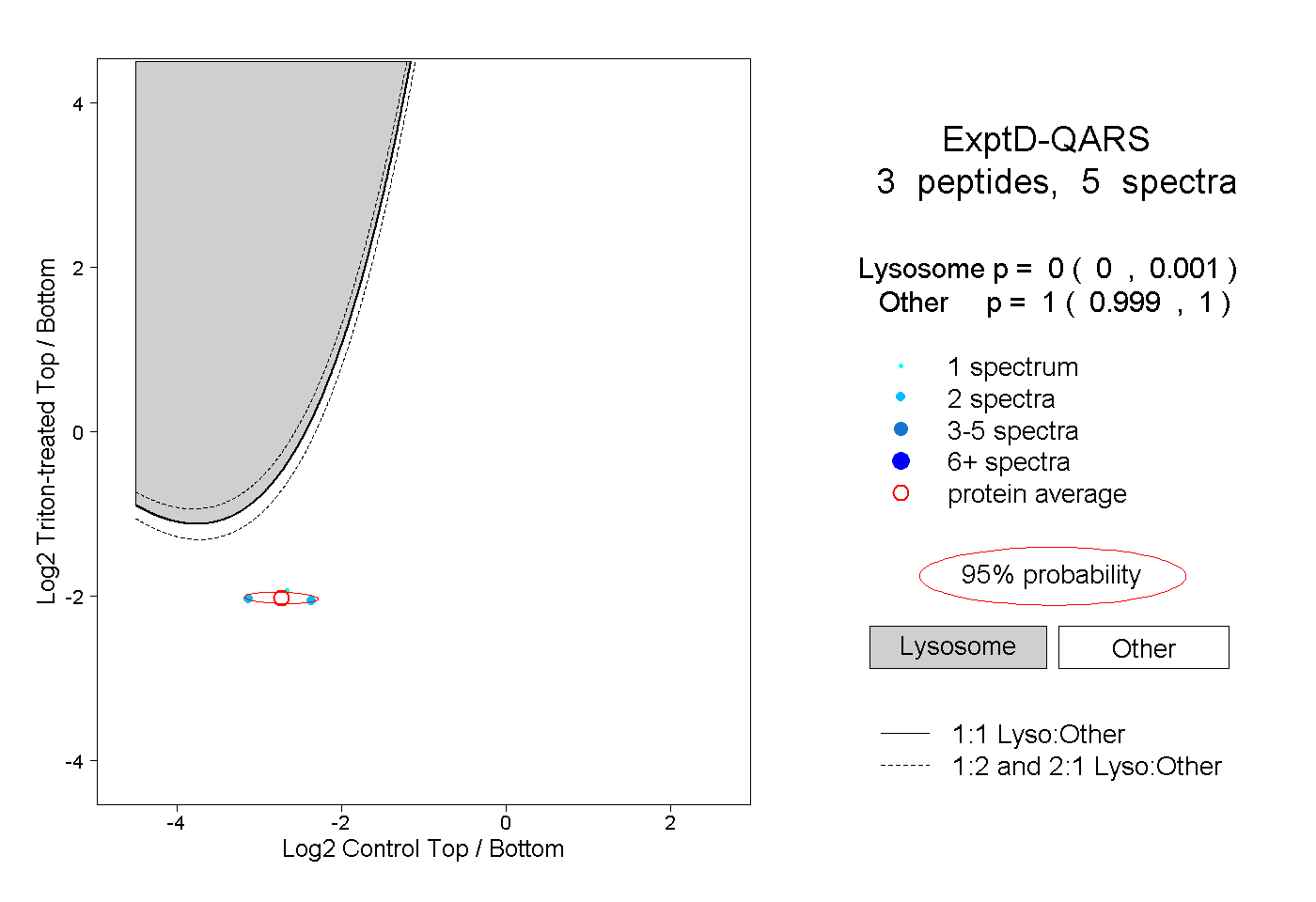 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |