peptides
spectra
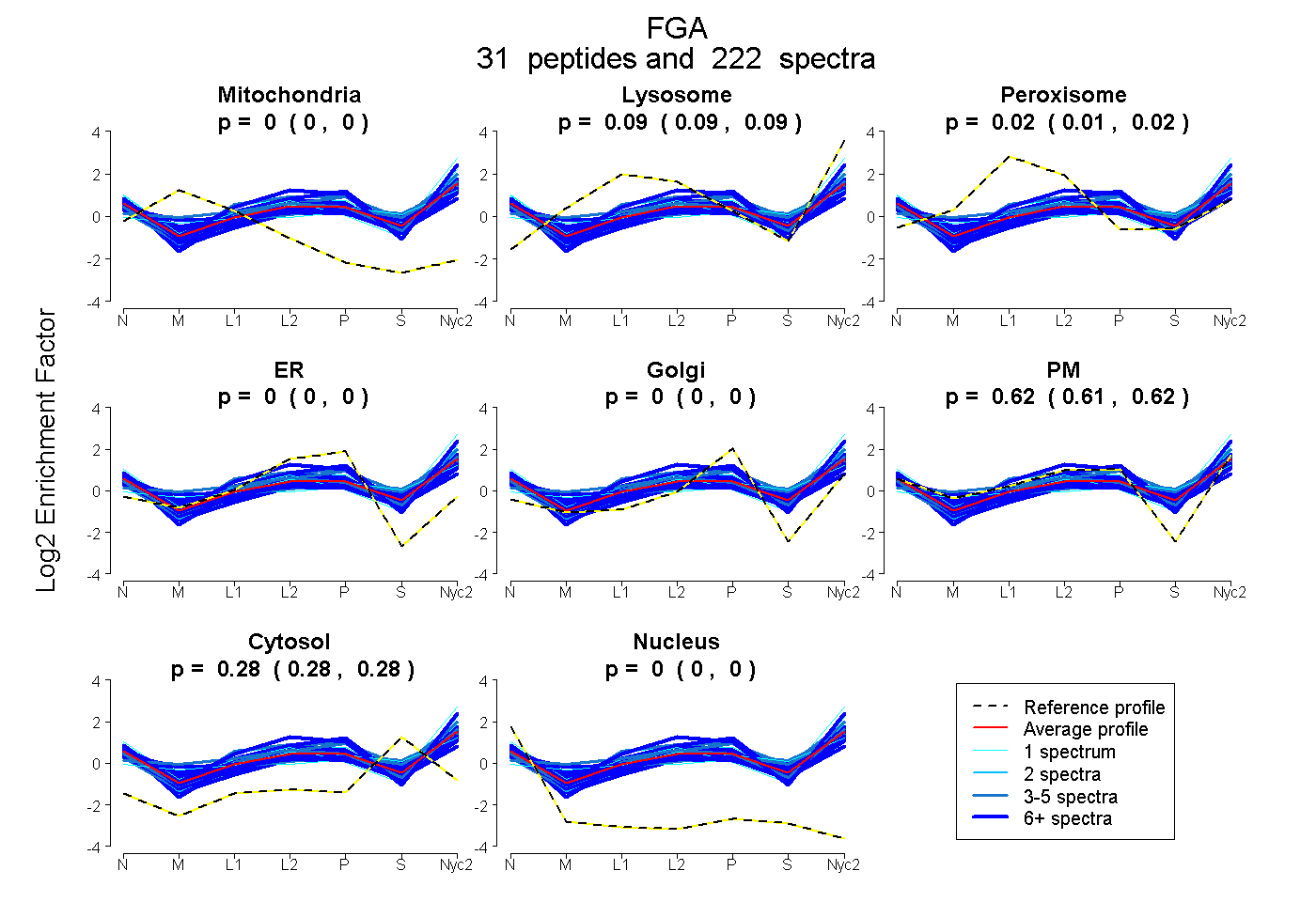
0.000 | 0.000
0.085 | 0.090
0.013 | 0.018
0.000 | 0.000
0.000 | 0.000
0.614 | 0.618
0.279 | 0.281
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
222 spectra |
 |
0.000 0.000 | 0.000 |
0.088 0.085 | 0.090 |
0.015 0.013 | 0.018 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.616 0.614 | 0.618 |
0.280 0.279 | 0.281 |
0.000 0.000 | 0.000 |
| 5 spectra, MSPVPDLVPGSFK | 0.000 | 0.108 | 0.000 | 0.000 | 0.000 | 0.520 | 0.372 | 0.000 | ||
| 11 spectra, QPSQCK | 0.000 | 0.000 | 0.095 | 0.000 | 0.000 | 0.635 | 0.270 | 0.000 | ||
| 4 spectra, EAYAEYHFR | 0.000 | 0.156 | 0.000 | 0.000 | 0.000 | 0.470 | 0.374 | 0.000 | ||
| 8 spectra, MADEAASEAHQEGDTR | 0.000 | 0.052 | 0.081 | 0.052 | 0.071 | 0.562 | 0.182 | 0.000 | ||
| 17 spectra, DYEGQQK | 0.000 | 0.033 | 0.054 | 0.000 | 0.000 | 0.613 | 0.300 | 0.000 | ||
| 10 spectra, GDLPGDSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.664 | 0.336 | 0.000 | ||
| 1 spectrum, LEVDIDIK | 0.000 | 0.068 | 0.000 | 0.000 | 0.000 | 0.692 | 0.241 | 0.000 | ||
| 9 spectra, AQQIQVLQK | 0.000 | 0.101 | 0.000 | 0.000 | 0.000 | 0.576 | 0.323 | 0.000 | ||
| 1 spectrum, TWQDYK | 0.000 | 0.177 | 0.083 | 0.000 | 0.000 | 0.409 | 0.330 | 0.000 | ||
| 8 spectra, FGSLTSNFK | 0.000 | 0.108 | 0.049 | 0.000 | 0.000 | 0.660 | 0.183 | 0.000 | ||
| 2 spectra, CPSGCR | 0.000 | 0.008 | 0.000 | 0.000 | 0.000 | 0.616 | 0.375 | 0.000 | ||
| 7 spectra, DSNSLTR | 0.000 | 0.066 | 0.000 | 0.000 | 0.000 | 0.531 | 0.403 | 0.000 | ||
| 2 spectra, LDELSR | 0.000 | 0.026 | 0.000 | 0.000 | 0.000 | 0.714 | 0.260 | 0.000 | ||
| 4 spectra, EYHTGK | 0.000 | 0.192 | 0.040 | 0.000 | 0.000 | 0.593 | 0.174 | 0.000 | ||
| 10 spectra, SQLQEGPPEWK | 0.000 | 0.041 | 0.037 | 0.000 | 0.000 | 0.637 | 0.285 | 0.000 | ||
| 10 spectra, NIMEYLR | 0.000 | 0.067 | 0.000 | 0.000 | 0.000 | 0.680 | 0.253 | 0.000 | ||
| 6 spectra, ETDWPFCSDEDWNHK | 0.000 | 0.000 | 0.065 | 0.000 | 0.000 | 0.607 | 0.328 | 0.000 | ||
| 5 spectra, GADYSLR | 0.000 | 0.208 | 0.000 | 0.000 | 0.000 | 0.506 | 0.287 | 0.000 | ||
| 7 spectra, QYLPAIK | 0.000 | 0.000 | 0.057 | 0.000 | 0.000 | 0.669 | 0.273 | 0.000 | ||
| 18 spectra, DQLIDMK | 0.000 | 0.085 | 0.028 | 0.000 | 0.000 | 0.581 | 0.306 | 0.000 | ||
| 2 spectra, EVVTSDDGSDCGDGMDLGLTHSFSGR | 0.000 | 0.055 | 0.046 | 0.000 | 0.000 | 0.551 | 0.348 | 0.000 | ||
| 14 spectra, GLIDEANQDFTNR | 0.000 | 0.034 | 0.009 | 0.000 | 0.000 | 0.645 | 0.311 | 0.000 | ||
| 1 spectrum, QLEQVIAK | 0.000 | 0.133 | 0.023 | 0.000 | 0.000 | 0.678 | 0.167 | 0.000 | ||
| 4 spectra, VELEDWAGK | 0.000 | 0.196 | 0.075 | 0.000 | 0.000 | 0.527 | 0.201 | 0.000 | ||
| 1 spectrum, ELLIGNEK | 0.000 | 0.320 | 0.000 | 0.000 | 0.000 | 0.532 | 0.149 | 0.000 | ||
| 7 spectra, MELERPGK | 0.000 | 0.045 | 0.000 | 0.000 | 0.000 | 0.605 | 0.350 | 0.000 | ||
| 8 spectra, MHPELGSFYDSR | 0.027 | 0.000 | 0.119 | 0.000 | 0.000 | 0.600 | 0.254 | 0.000 | ||
| 9 spectra, NSLFDFQK | 0.000 | 0.052 | 0.000 | 0.000 | 0.000 | 0.669 | 0.279 | 0.000 | ||
| 7 spectra, ALTEMR | 0.000 | 0.056 | 0.034 | 0.000 | 0.000 | 0.661 | 0.249 | 0.000 | ||
| 23 spectra, VTSTGTSTTR | 0.000 | 0.224 | 0.000 | 0.000 | 0.000 | 0.692 | 0.084 | 0.000 | ||
| 1 spectrum, GDFANANNFDNTFGQVSEDLR | 0.000 | 0.130 | 0.000 | 0.000 | 0.000 | 0.570 | 0.300 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
65 spectra |
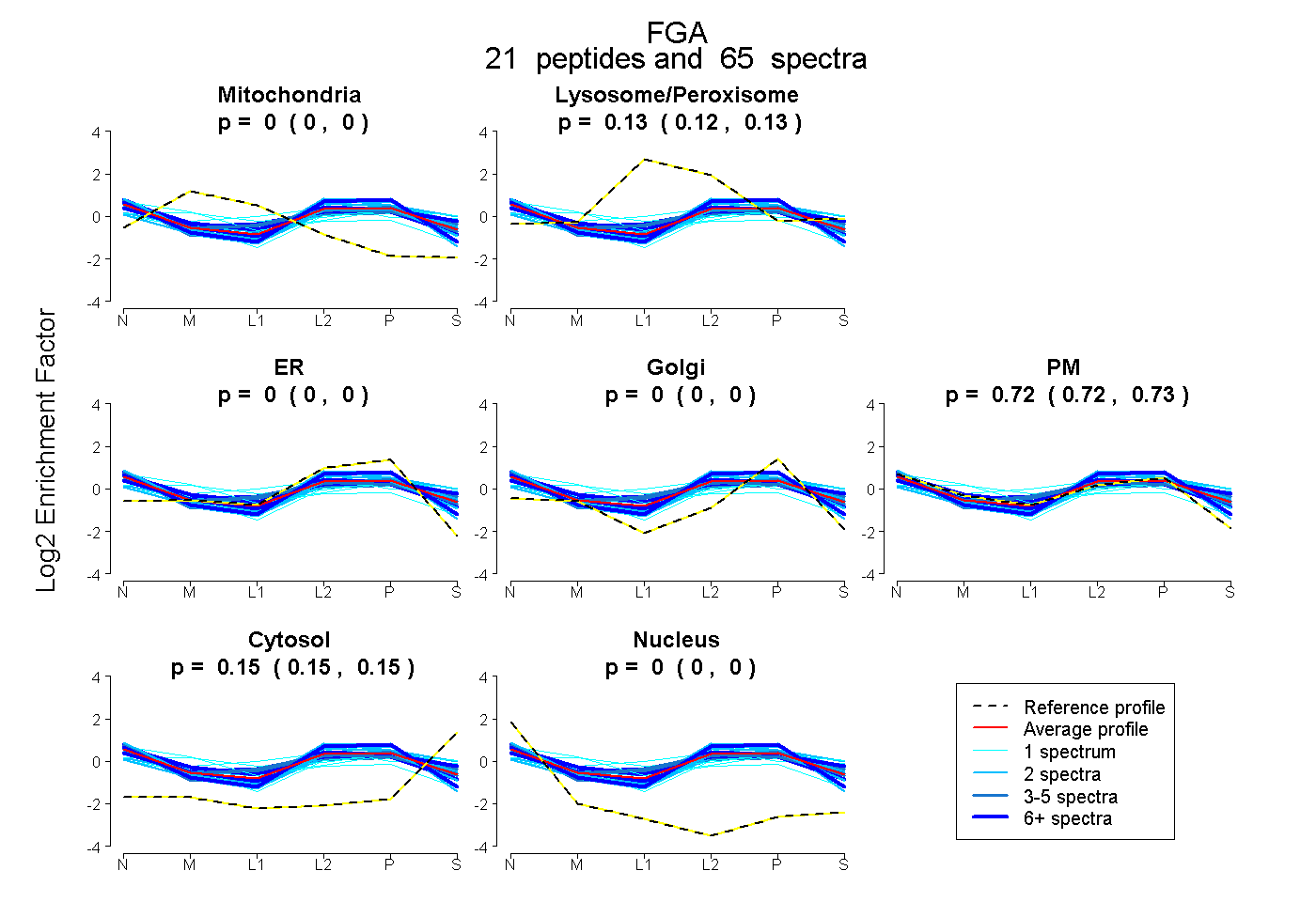 |
0.000 0.000 | 0.000 |
0.125 0.121 | 0.129 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.724 0.718 | 0.728 |
0.151 0.148 | 0.154 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
516 spectra |
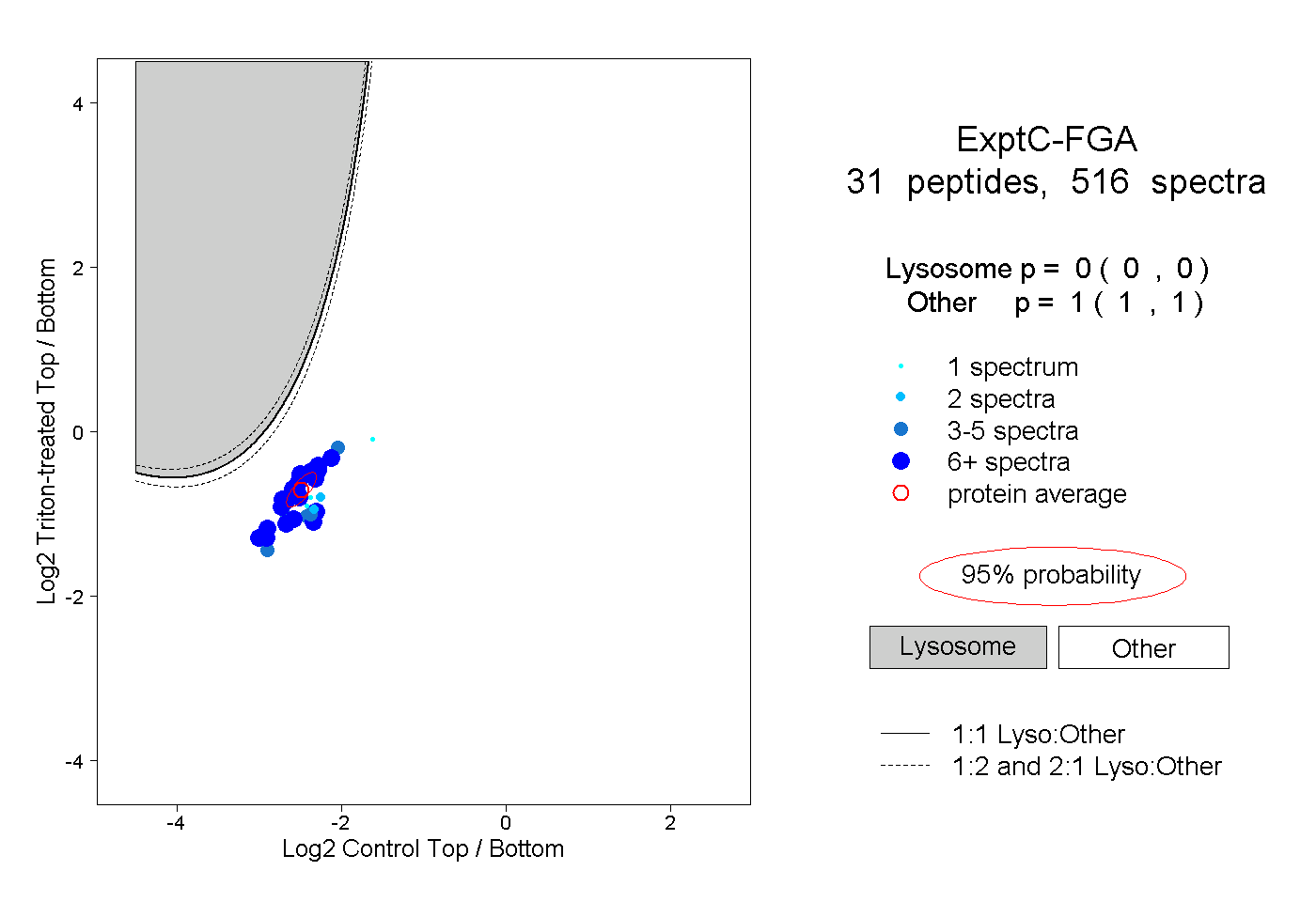 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
49 spectra |
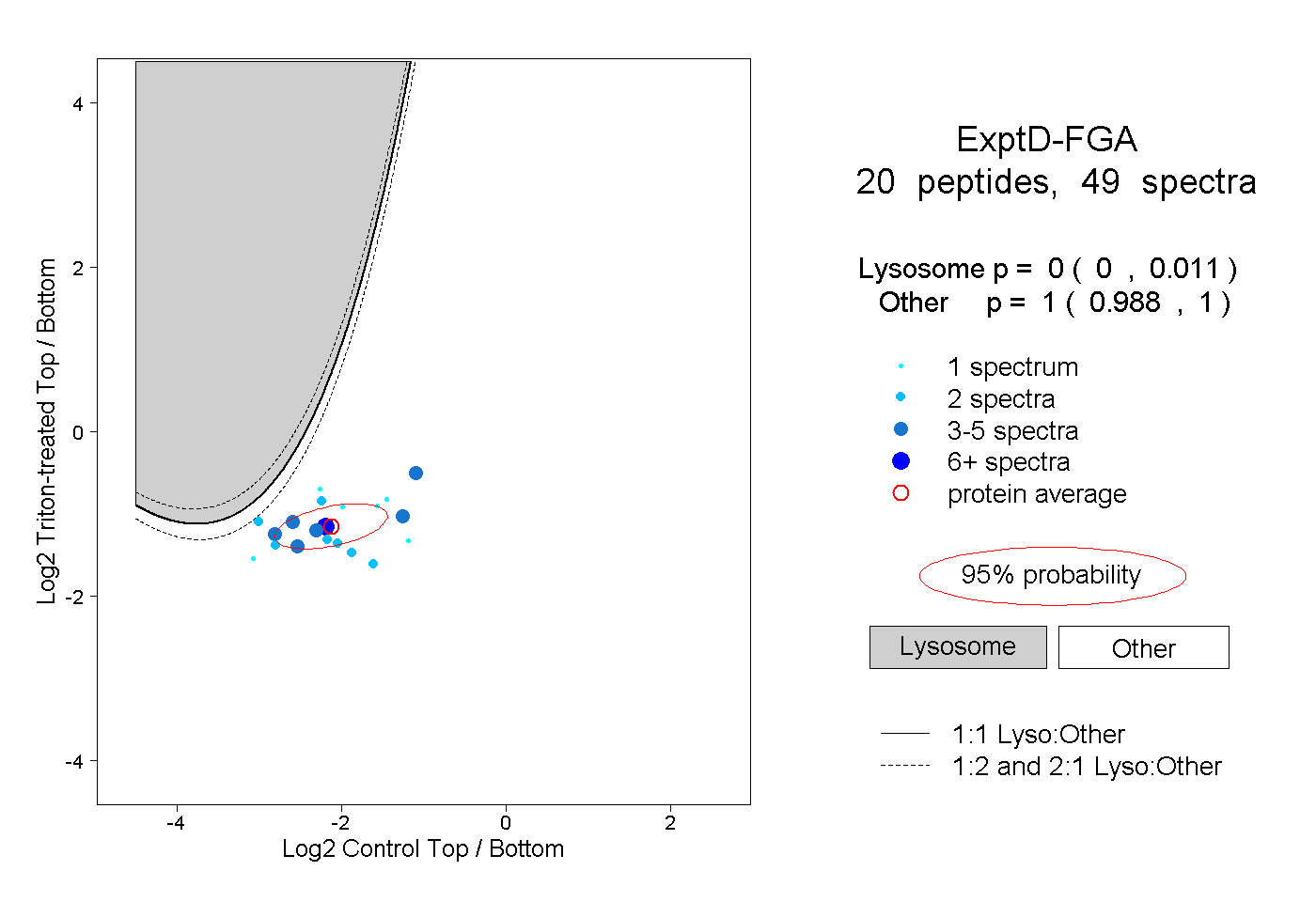 |
0.000 0.000 | 0.011 |
1.000 0.988 | 1.000 |