peptides
spectra
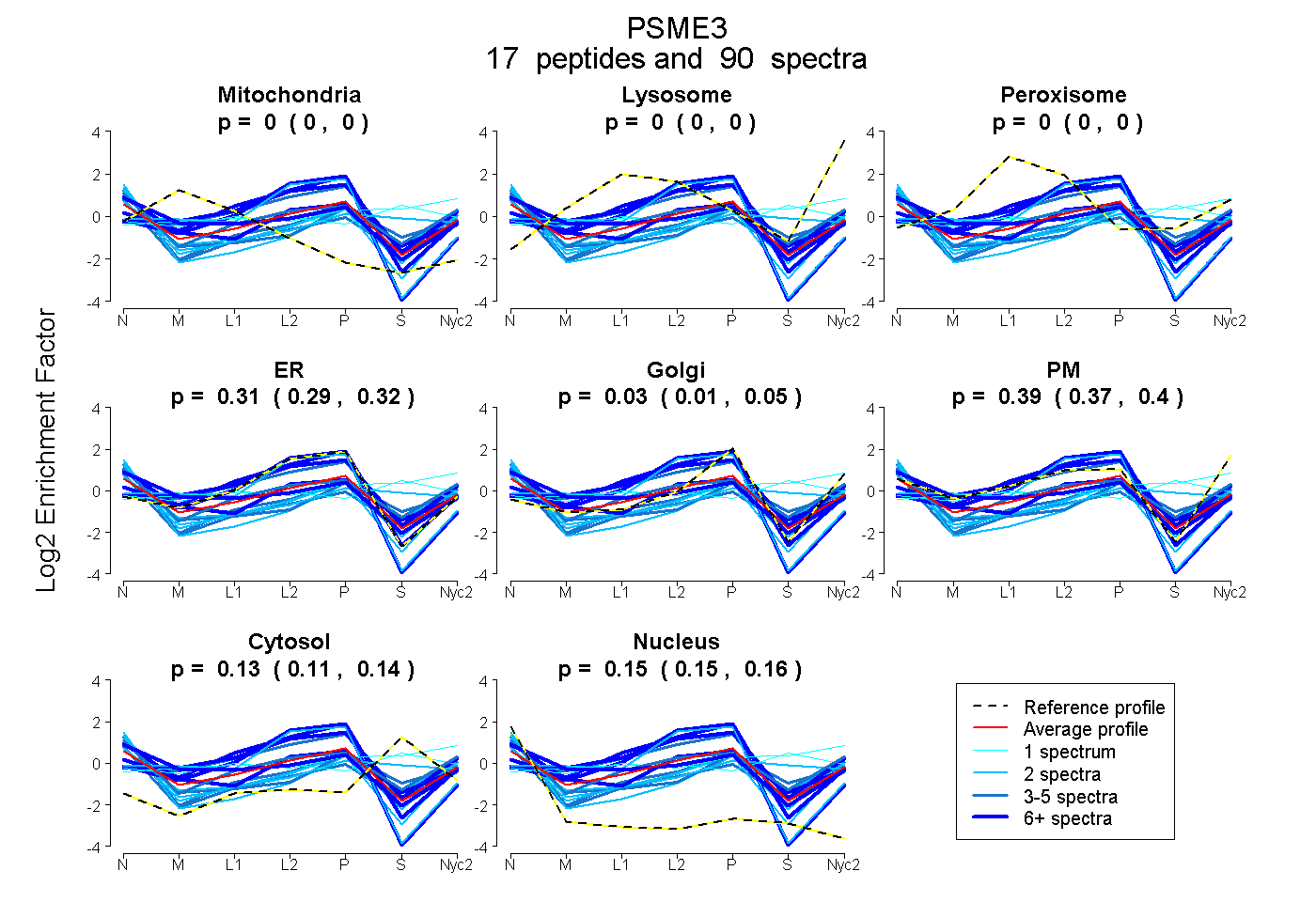
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.288 | 0.319
0.008 | 0.047
0.370 | 0.399
0.115 | 0.136
0.146 | 0.158
peptides
spectra
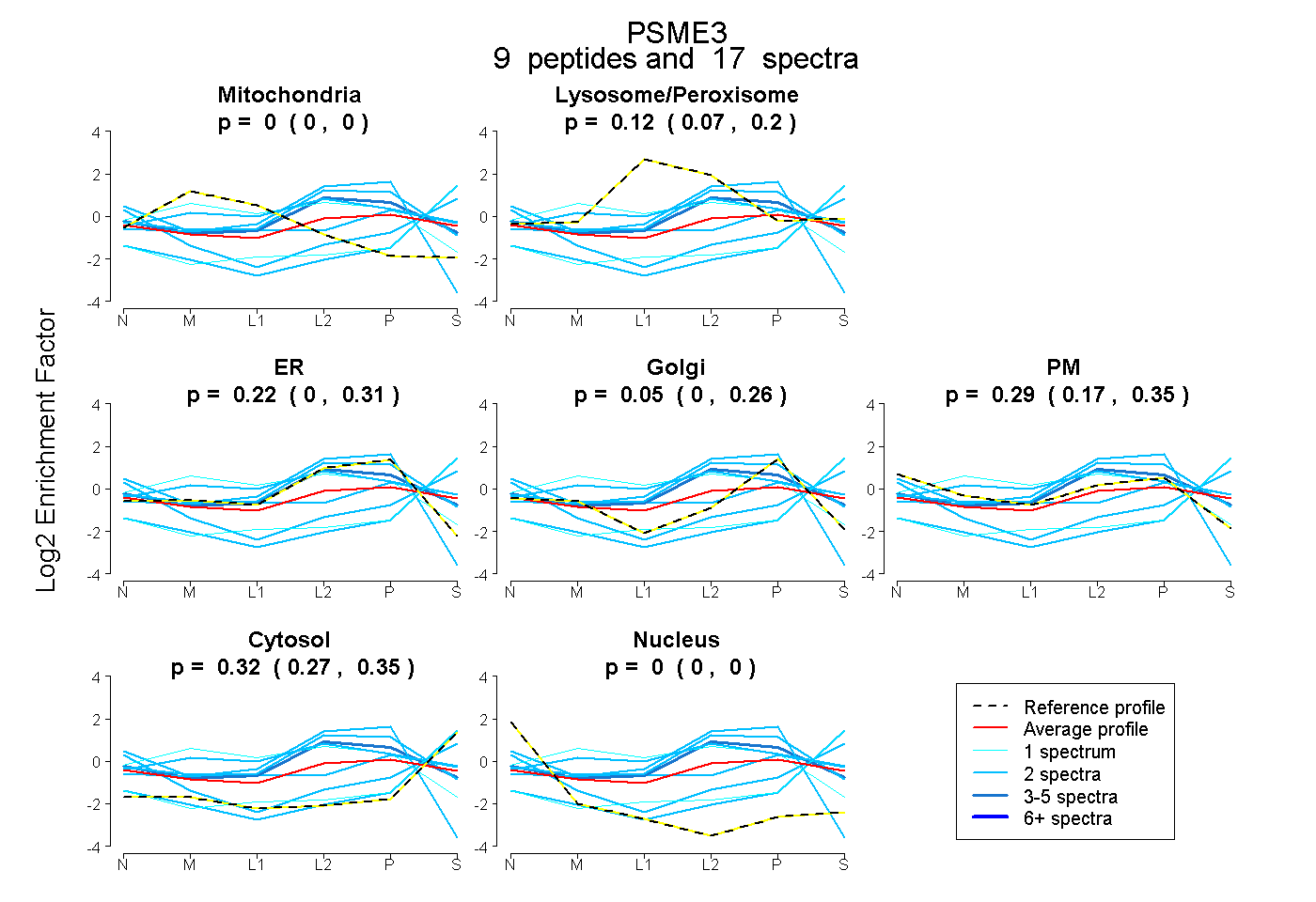
0.000 | 0.000
0.067 | 0.198
0.000 | 0.311
0.000 | 0.261
0.168 | 0.354
0.266 | 0.354
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
90 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.306 0.288 | 0.319 |
0.029 0.008 | 0.047 |
0.386 0.370 | 0.399 |
0.126 0.115 | 0.136 |
0.152 0.146 | 0.158 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
 |
0.000 0.000 | 0.000 |
0.118 0.067 | 0.198 |
0.220 0.000 | 0.311 |
0.050 0.000 | 0.261 |
0.287 0.168 | 0.354 |
0.325 0.266 | 0.354 |
0.000 0.000 | 0.000 |
| 2 spectra, DPEVGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.307 | 0.603 | 0.090 | |||
| 2 spectra, APPLQFHPEGPR | 0.000 | 0.100 | 0.000 | 0.000 | 0.628 | 0.270 | 0.003 | |||
| 2 spectra, WCERPEWVHLDTTPFASLFK | 0.000 | 0.179 | 0.693 | 0.000 | 0.036 | 0.092 | 0.000 | |||
| 2 spectra, LLGQTHK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, MWVQLLIPR | 0.000 | 0.052 | 0.000 | 0.000 | 0.000 | 0.943 | 0.006 | |||
| 2 spectra, LIISELR | 0.000 | 0.000 | 0.000 | 0.013 | 0.000 | 0.959 | 0.028 | |||
| 3 spectra, GIYNASLQR | 0.000 | 0.177 | 0.503 | 0.000 | 0.158 | 0.163 | 0.000 | |||
| 1 spectrum, GLGVDLLWTLEK | 0.255 | 0.167 | 0.412 | 0.000 | 0.166 | 0.000 | 0.000 | |||
| 2 spectra, MNVLHDFGIQSTR | 0.000 | 0.480 | 0.052 | 0.286 | 0.073 | 0.109 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
74 spectra |
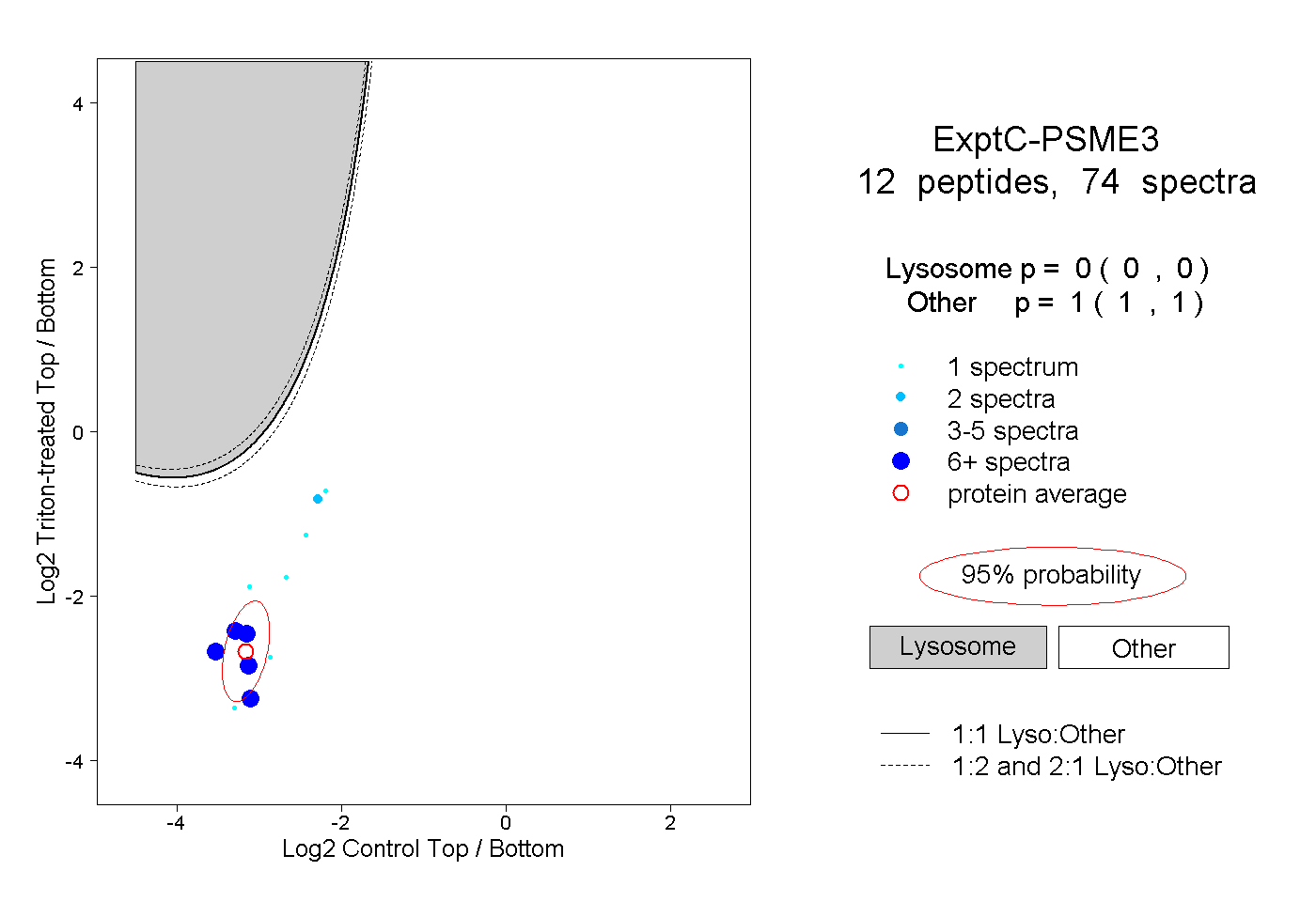 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
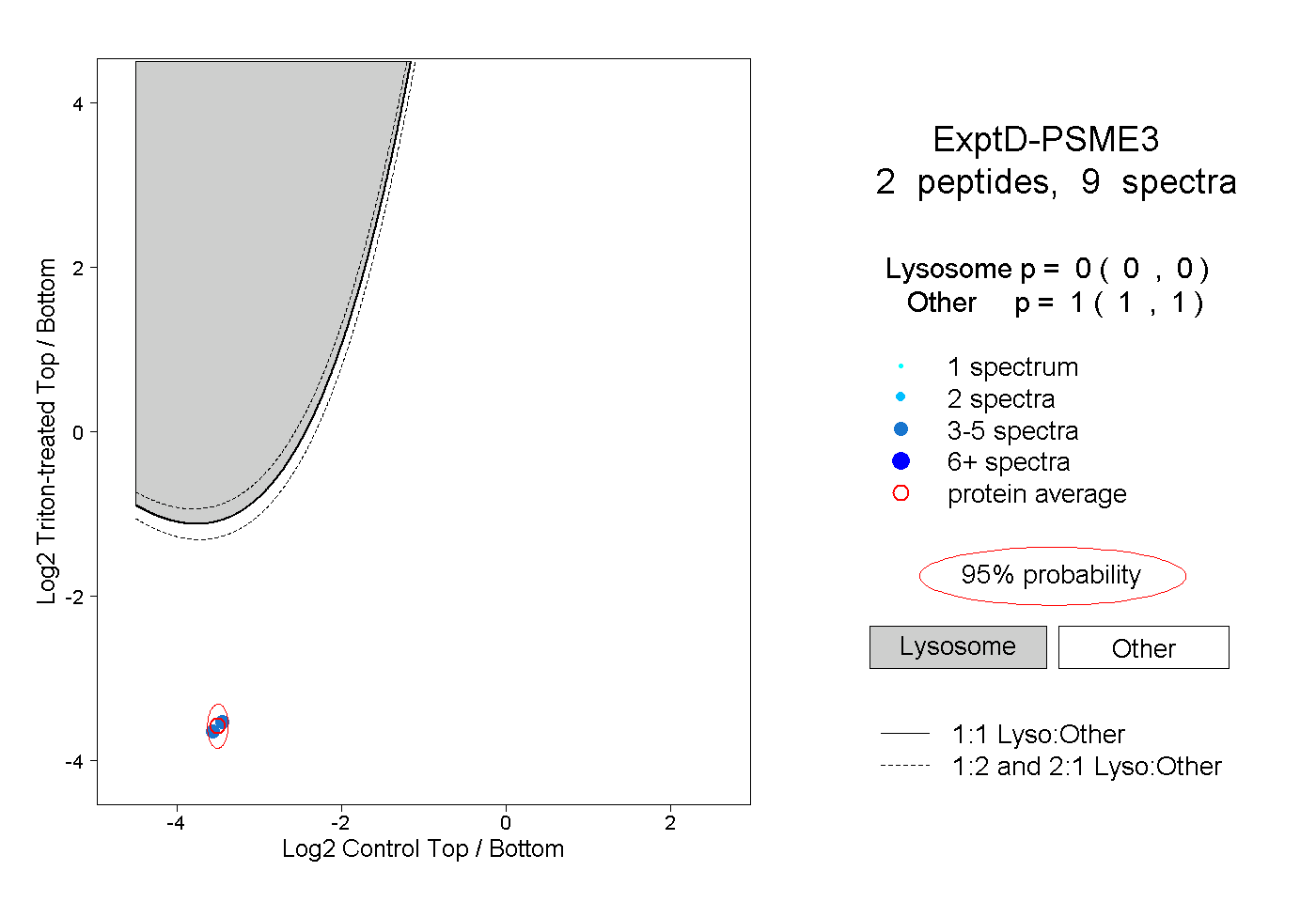 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |