peptides
spectra
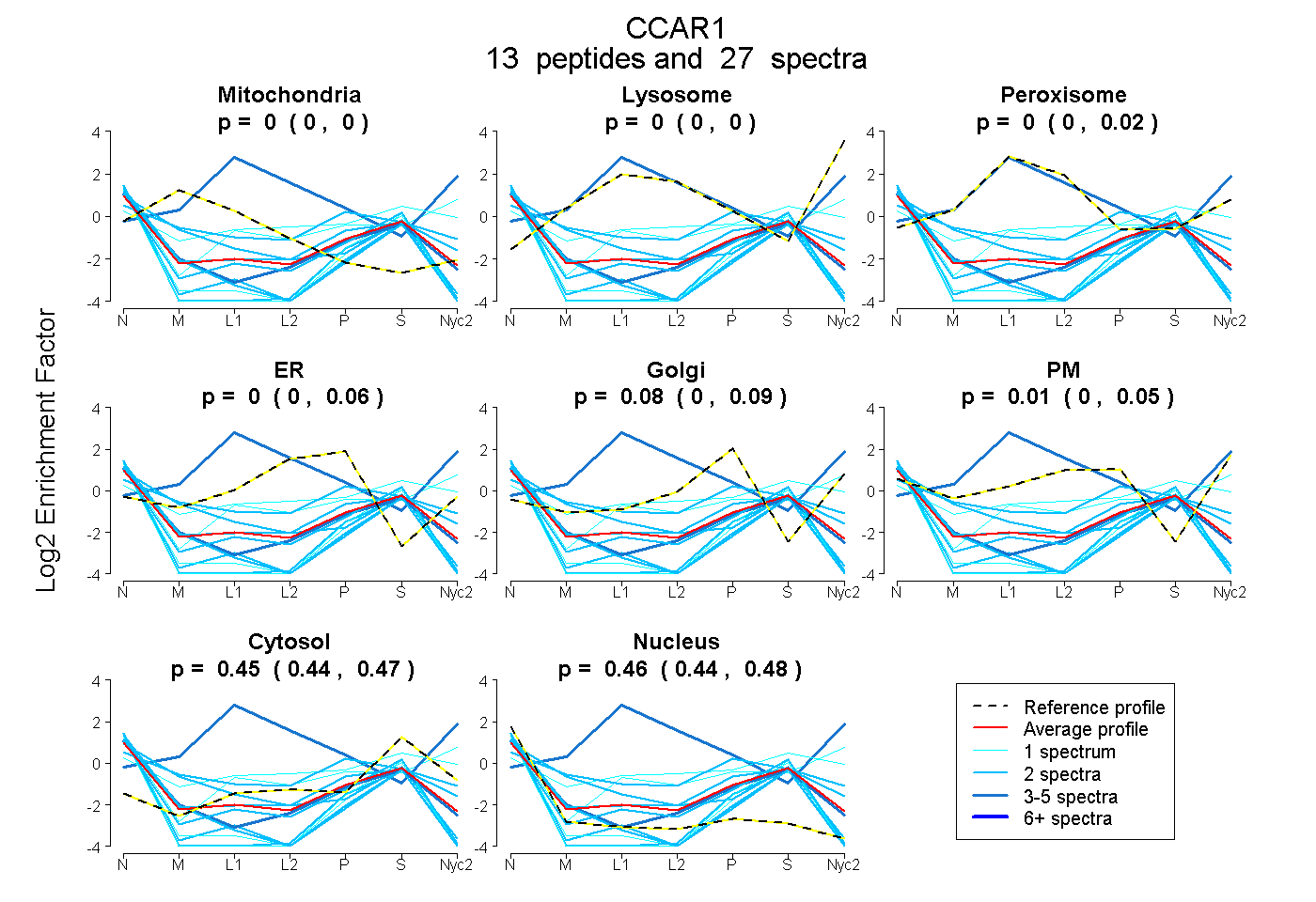
0.000 | 0.000
0.000 | 0.000
0.000 | 0.025
0.000 | 0.065
0.000 | 0.091
0.000 | 0.053
0.435 | 0.465
0.438 | 0.476
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
27 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.005 0.000 | 0.025 |
0.000 0.000 | 0.065 |
0.077 0.000 | 0.091 |
0.007 0.000 | 0.053 |
0.453 0.435 | 0.465 |
0.458 0.438 | 0.476 |
| 2 spectra, IVSQPQPAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.211 | 0.789 | ||
| 2 spectra, YTVQFSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.229 | 0.771 | ||
| 2 spectra, SSQQQTQPQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.431 | 0.569 | ||
| 5 spectra, SCALAEDPQDLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.056 | 0.000 | 0.403 | 0.540 | ||
| 2 spectra, LTDTSK | 0.201 | 0.000 | 0.000 | 0.168 | 0.155 | 0.000 | 0.356 | 0.120 | ||
| 1 spectrum, DLGQLQENLK | 0.000 | 0.000 | 0.100 | 0.000 | 0.000 | 0.310 | 0.558 | 0.032 | ||
| 4 spectra, DDGEVK | 0.000 | 0.285 | 0.578 | 0.000 | 0.000 | 0.137 | 0.000 | 0.000 | ||
| 1 spectrum, FSLDCPSCDMMELR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.281 | 0.719 | ||
| 2 spectra, TILNLENSNK | 0.000 | 0.000 | 0.000 | 0.000 | 0.091 | 0.131 | 0.412 | 0.366 | ||
| 1 spectrum, LQLLEEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.250 | 0.750 | ||
| 1 spectrum, AGLLQPPVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.441 | 0.407 | 0.152 | ||
| 2 spectra, LLLPTPTVK | 0.311 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.303 | 0.386 | ||
| 2 spectra, FLVGMK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.237 | 0.763 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
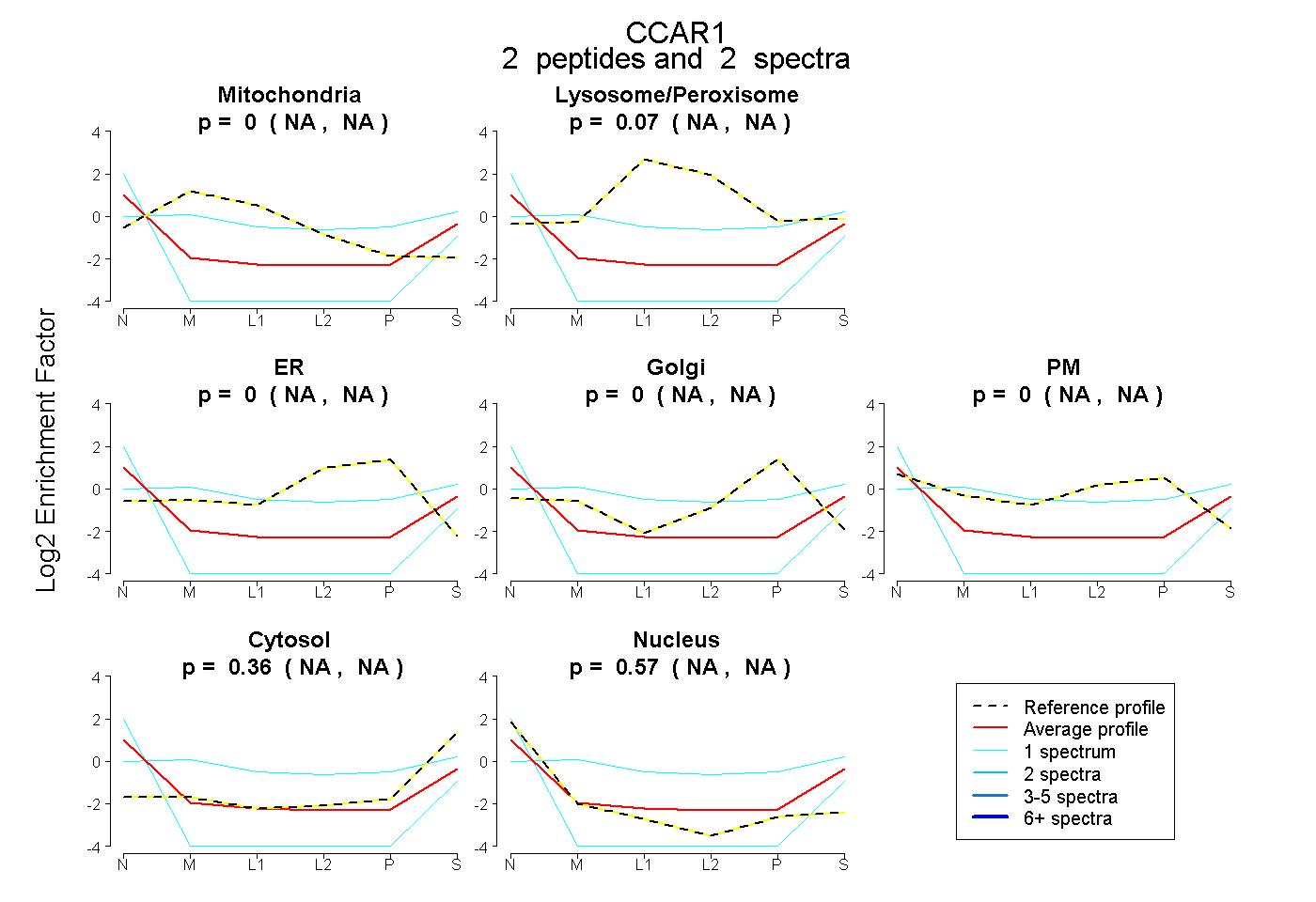 |
0.000 NA | NA |
0.075 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.358 NA | NA |
0.567 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
2 spectra |
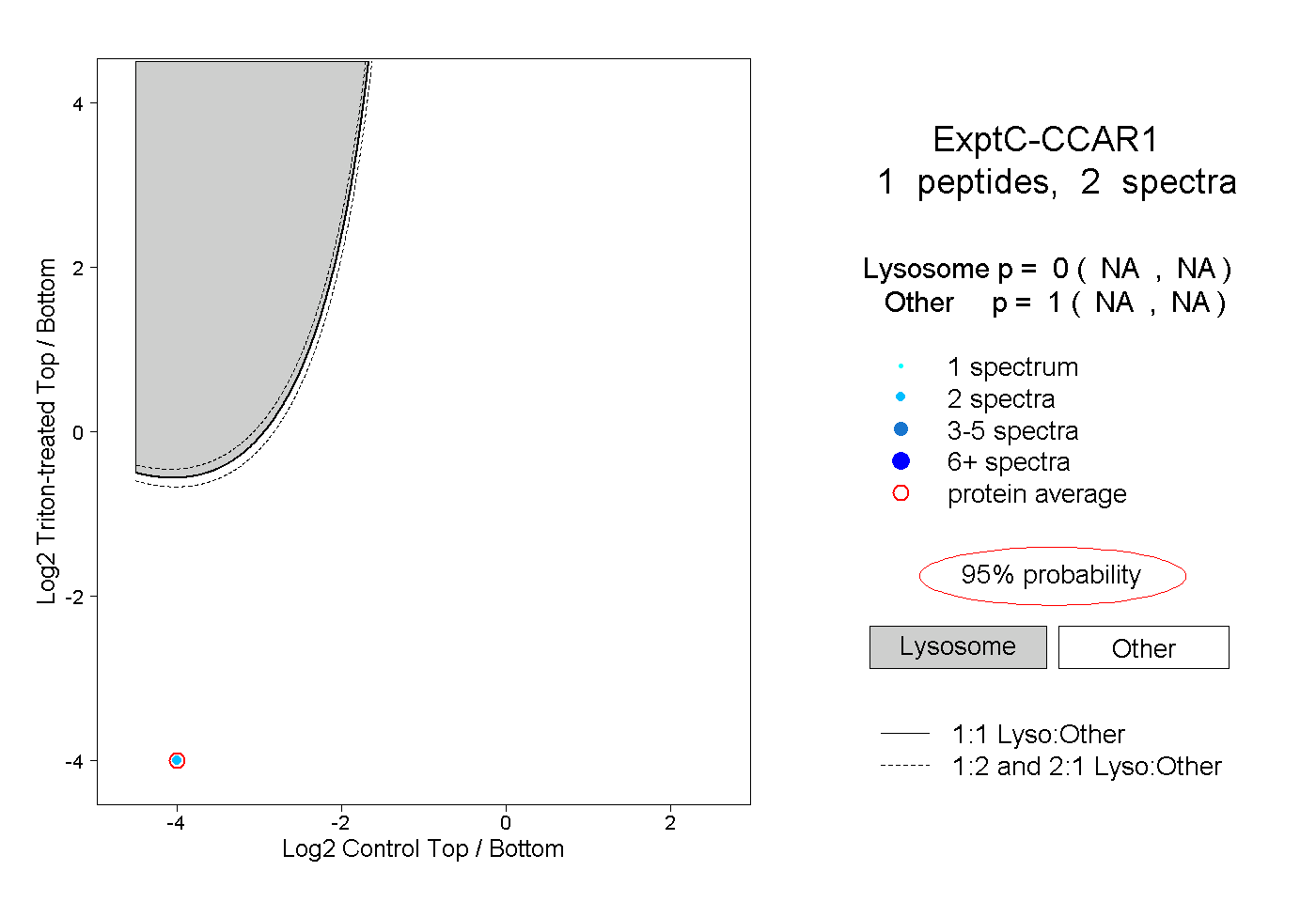 |
0.000 NA | NA |
1.000 NA | NA |