peptides
spectra
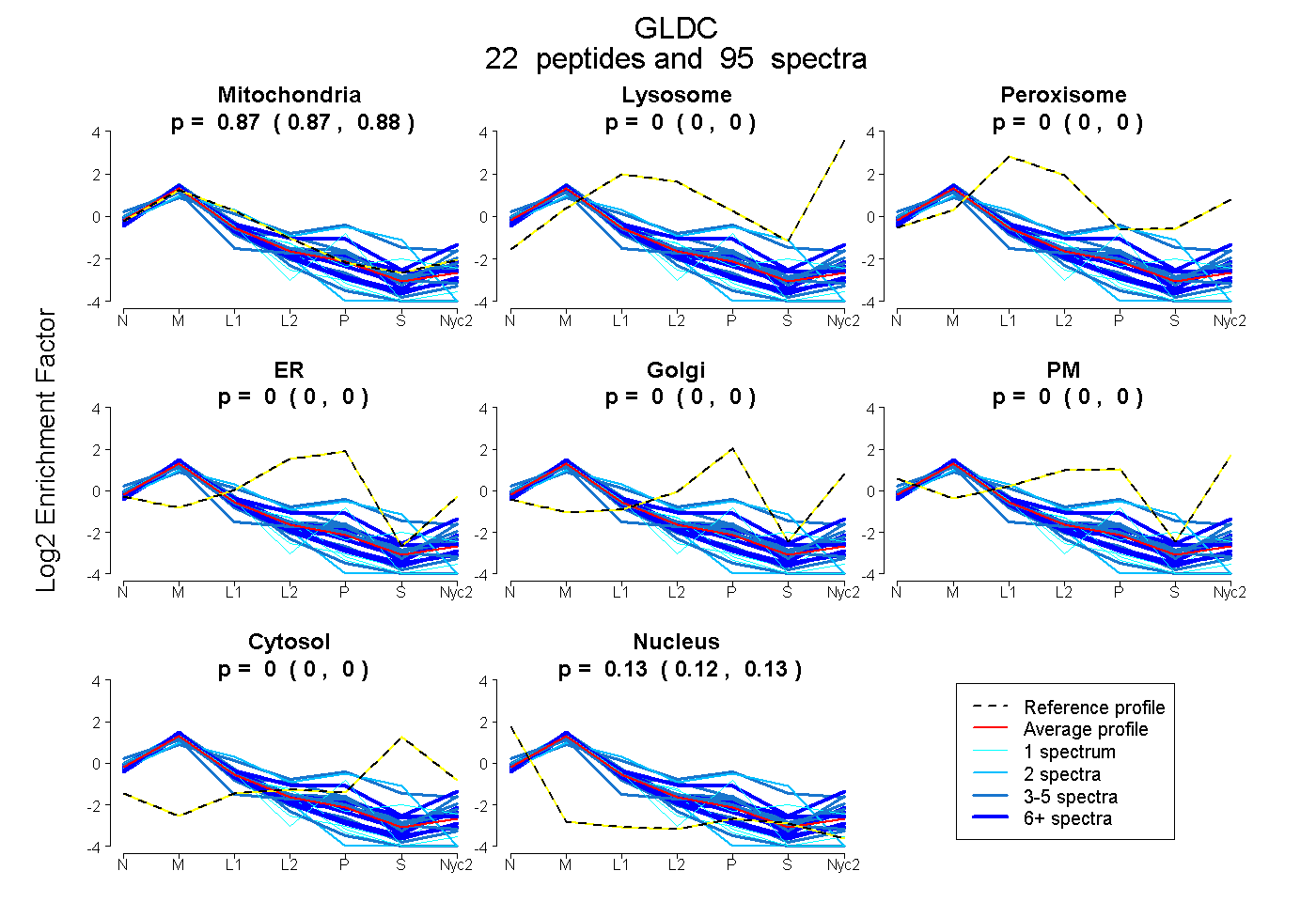
0.871 | 0.875
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.124 | 0.129
peptides
spectra
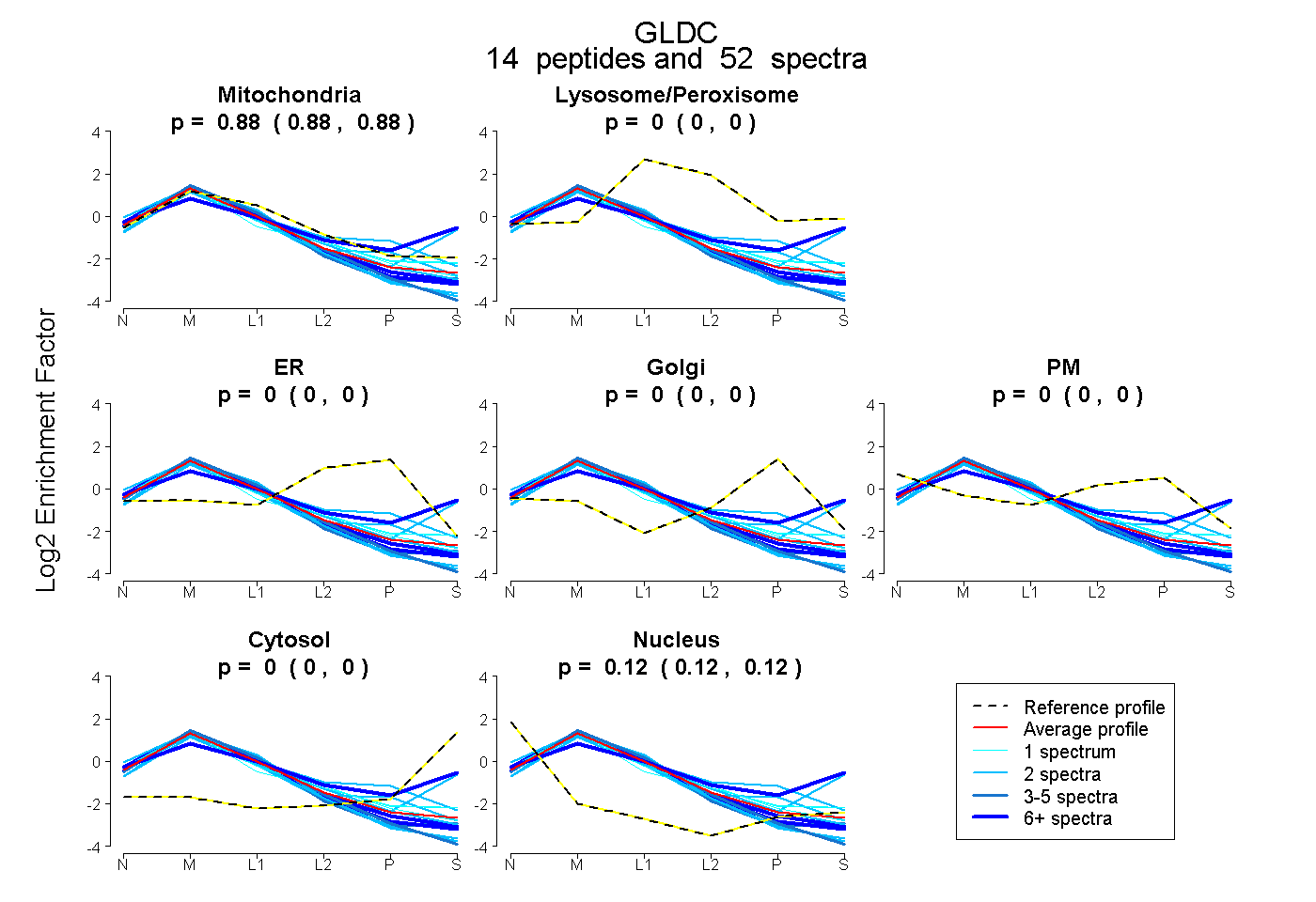
0.877 | 0.883
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.117 | 0.122
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
95 spectra |
 |
0.873 0.871 | 0.875 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.127 0.124 | 0.129 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
52 spectra |
 |
0.880 0.877 | 0.883 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.120 0.117 | 0.122 |
| 2 spectra, SANIEAVDVAK | 0.830 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.170 | |||
| 4 spectra, FWPTIAR | 0.860 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.140 | |||
| 2 spectra, TVPASIR | 0.839 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.161 | |||
| 12 spectra, QEIADIEEGR | 0.850 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.150 | |||
| 1 spectrum, WDRPYSR | 0.883 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.117 | |||
| 4 spectra, VEDFTELVER | 0.881 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.119 | |||
| 1 spectrum, FCDAMISIR | 0.879 | 0.000 | 0.000 | 0.008 | 0.000 | 0.011 | 0.103 | |||
| 6 spectra, YGNIDVAHLK | 0.675 | 0.061 | 0.000 | 0.000 | 0.023 | 0.242 | 0.000 | |||
| 2 spectra, GLLGSSFK | 0.821 | 0.000 | 0.000 | 0.179 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, IQPVEVDR | 0.880 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.120 | |||
| 2 spectra, DLCELTGYDR | 0.856 | 0.000 | 0.000 | 0.030 | 0.000 | 0.000 | 0.114 | |||
| 2 spectra, MVGVTR | 0.917 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.083 | |||
| 2 spectra, EMLQALGLASIDELIEK | 0.739 | 0.000 | 0.000 | 0.000 | 0.000 | 0.261 | 0.000 | |||
| 1 spectrum, LALQTR | 0.935 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.065 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
349 spectra |
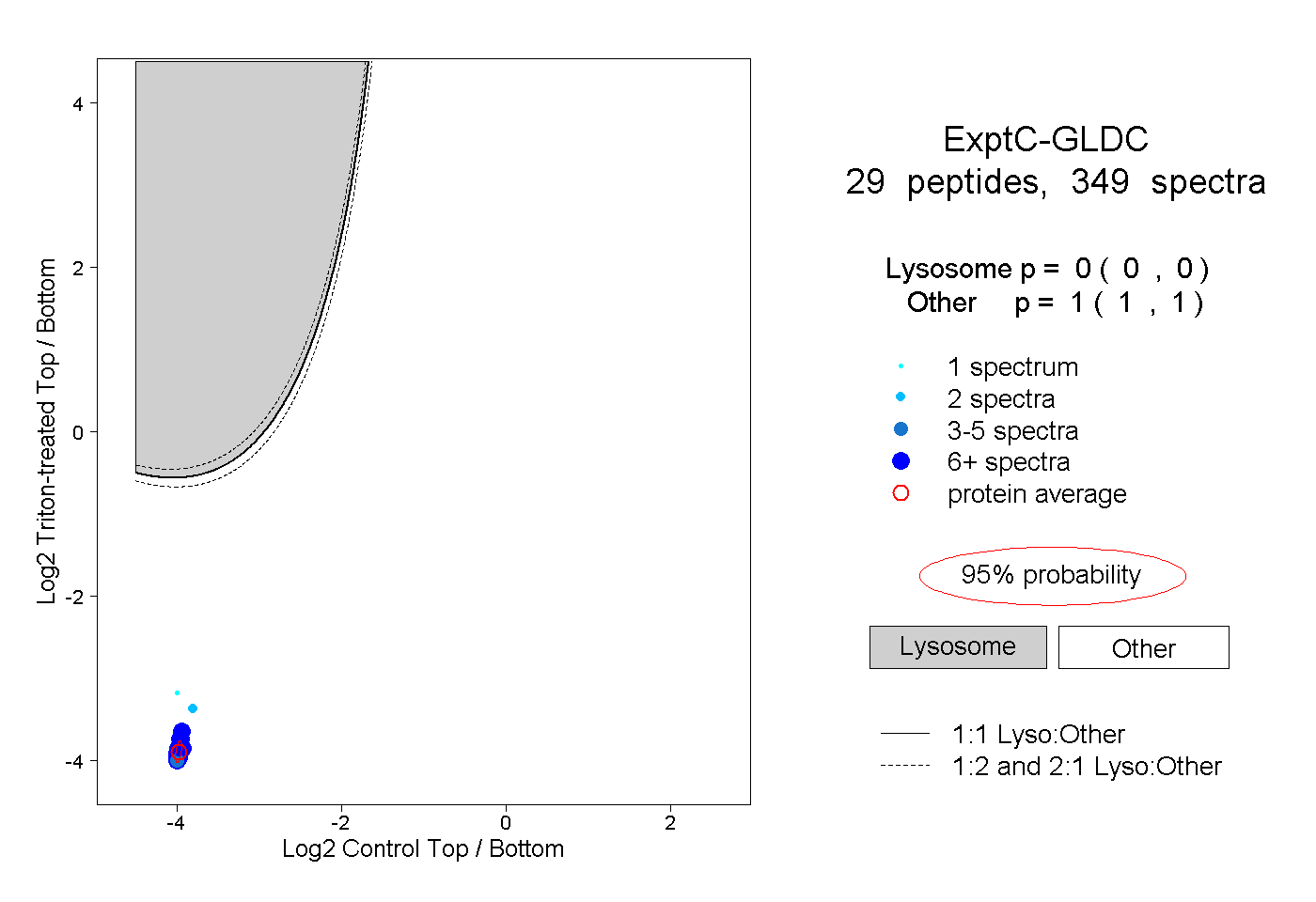 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
32 spectra |
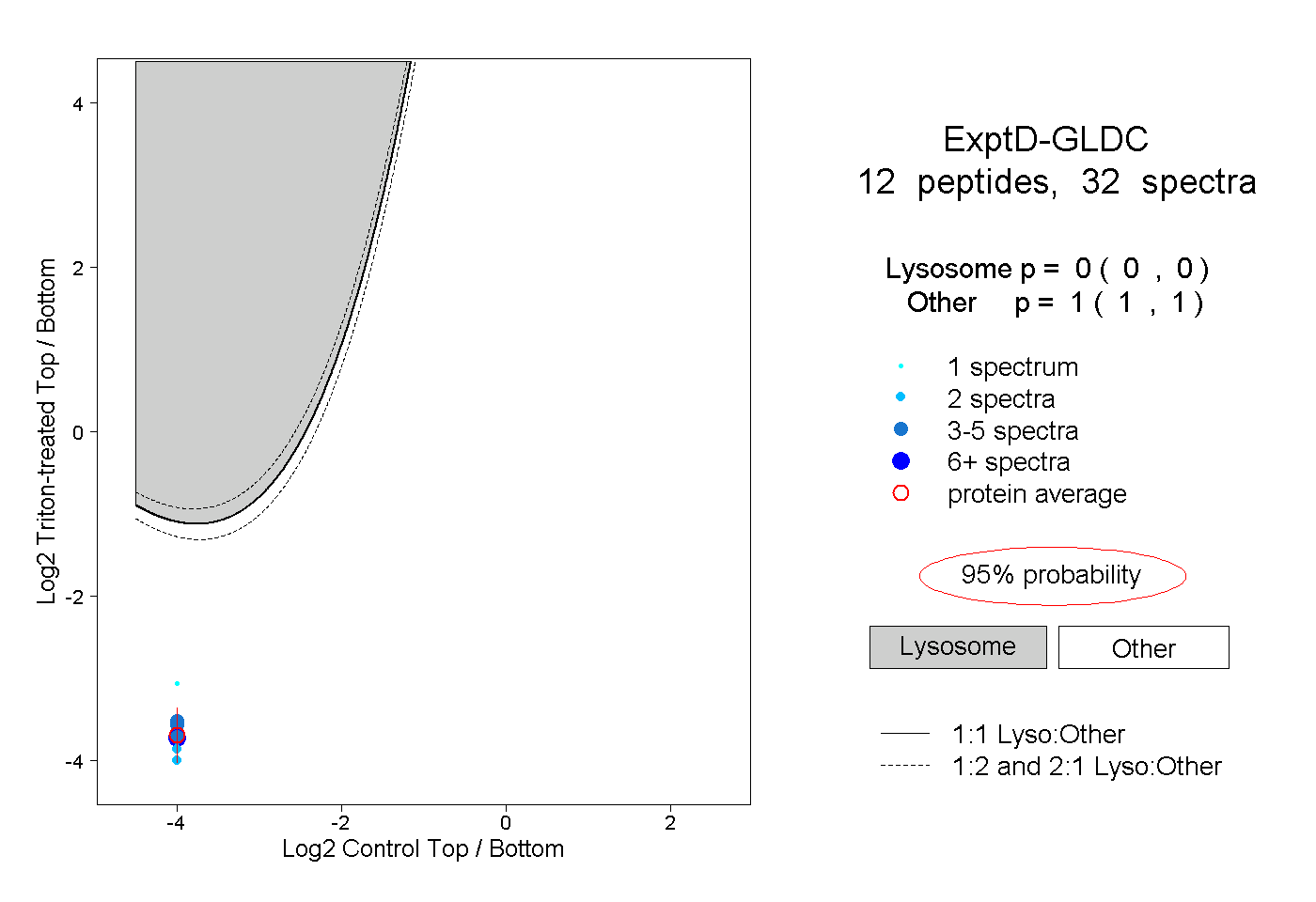 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |