peptides
spectra
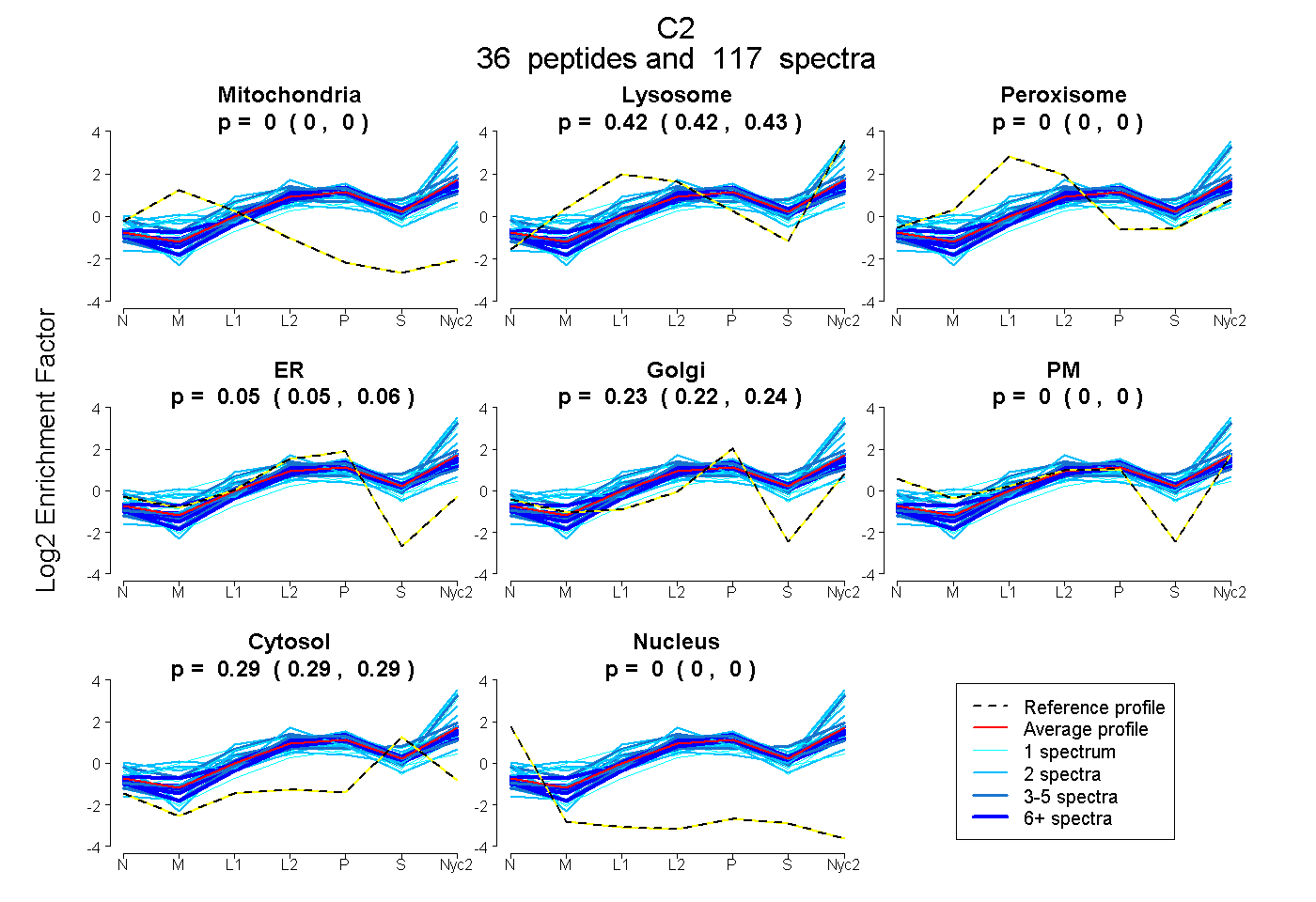
0.000 | 0.000
0.420 | 0.426
0.000 | 0.000
0.045 | 0.060
0.225 | 0.238
0.000 | 0.000
0.290 | 0.294
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
117 spectra |
 |
0.000 0.000 | 0.000 |
0.423 0.420 | 0.426 |
0.000 0.000 | 0.000 |
0.053 0.045 | 0.060 |
0.232 0.225 | 0.238 |
0.000 0.000 | 0.000 |
0.292 0.290 | 0.294 |
0.000 0.000 | 0.000 |
| 7 spectra, VNVEGK | 0.000 | 0.390 | 0.000 | 0.176 | 0.155 | 0.000 | 0.279 | 0.000 | ||
| 1 spectrum, SGTNTK | 0.000 | 0.346 | 0.000 | 0.061 | 0.114 | 0.000 | 0.479 | 0.000 | ||
| 2 spectra, QQLVPSYAR | 0.000 | 0.165 | 0.000 | 0.000 | 0.149 | 0.310 | 0.376 | 0.000 | ||
| 3 spectra, DMEDLENVFYK | 0.000 | 0.447 | 0.000 | 0.155 | 0.091 | 0.000 | 0.307 | 0.000 | ||
| 2 spectra, VGSQYR | 0.000 | 0.435 | 0.000 | 0.163 | 0.000 | 0.173 | 0.228 | 0.000 | ||
| 5 spectra, STGSWSVLQTR | 0.000 | 0.453 | 0.000 | 0.000 | 0.111 | 0.000 | 0.436 | 0.000 | ||
| 4 spectra, ALFVSEEGK | 0.000 | 0.355 | 0.000 | 0.073 | 0.213 | 0.000 | 0.359 | 0.000 | ||
| 9 spectra, AQGYEK | 0.000 | 0.309 | 0.000 | 0.107 | 0.237 | 0.000 | 0.347 | 0.000 | ||
| 4 spectra, SLGLCGMVWEHQK | 0.000 | 0.458 | 0.000 | 0.097 | 0.156 | 0.000 | 0.288 | 0.000 | ||
| 1 spectrum, AVCKPVR | 0.000 | 0.302 | 0.048 | 0.000 | 0.000 | 0.400 | 0.251 | 0.000 | ||
| 1 spectrum, LNQISYEDHK | 0.000 | 0.248 | 0.000 | 0.196 | 0.136 | 0.049 | 0.370 | 0.000 | ||
| 9 spectra, SSDADWVTEK | 0.000 | 0.380 | 0.000 | 0.079 | 0.238 | 0.000 | 0.304 | 0.000 | ||
| 2 spectra, CLANLIEK | 0.000 | 0.014 | 0.322 | 0.000 | 0.353 | 0.150 | 0.162 | 0.000 | ||
| 1 spectrum, FLCTGGVDPYADPNTCK | 0.000 | 0.210 | 0.006 | 0.000 | 0.305 | 0.291 | 0.188 | 0.000 | ||
| 3 spectra, LPQTATCK | 0.000 | 0.356 | 0.000 | 0.084 | 0.222 | 0.000 | 0.338 | 0.000 | ||
| 1 spectrum, MNINLR | 0.000 | 0.695 | 0.000 | 0.000 | 0.117 | 0.036 | 0.152 | 0.000 | ||
| 1 spectrum, EELLPMK | 0.000 | 0.000 | 0.288 | 0.000 | 0.491 | 0.000 | 0.221 | 0.000 | ||
| 8 spectra, VASEVVTPR | 0.000 | 0.305 | 0.000 | 0.024 | 0.326 | 0.000 | 0.345 | 0.000 | ||
| 1 spectrum, GGDYYK | 0.000 | 0.495 | 0.000 | 0.000 | 0.179 | 0.000 | 0.326 | 0.000 | ||
| 8 spectra, ISVTRPLK | 0.000 | 0.403 | 0.000 | 0.072 | 0.258 | 0.000 | 0.267 | 0.000 | ||
| 2 spectra, LGMETSAWQEIR | 0.000 | 0.712 | 0.000 | 0.000 | 0.137 | 0.000 | 0.151 | 0.000 | ||
| 2 spectra, DLLDIGR | 0.000 | 0.393 | 0.000 | 0.024 | 0.219 | 0.000 | 0.364 | 0.000 | ||
| 5 spectra, YSQTLRPICLPCTEGTTR | 0.000 | 0.331 | 0.000 | 0.337 | 0.017 | 0.000 | 0.315 | 0.000 | ||
| 1 spectrum, SGQSTK | 0.000 | 0.267 | 0.000 | 0.000 | 0.197 | 0.000 | 0.536 | 0.000 | ||
| 2 spectra, EILGISR | 0.000 | 0.555 | 0.000 | 0.000 | 0.000 | 0.238 | 0.208 | 0.000 | ||
| 2 spectra, NNEQHVFK | 0.000 | 0.378 | 0.000 | 0.212 | 0.078 | 0.000 | 0.332 | 0.000 | ||
| 8 spectra, VASYGVKPR | 0.000 | 0.347 | 0.000 | 0.185 | 0.153 | 0.022 | 0.293 | 0.000 | ||
| 2 spectra, ELNELGSK | 0.000 | 0.402 | 0.000 | 0.000 | 0.000 | 0.343 | 0.255 | 0.000 | ||
| 1 spectrum, CPRPQDFENGEFWPR | 0.000 | 0.449 | 0.000 | 0.074 | 0.004 | 0.042 | 0.430 | 0.000 | ||
| 1 spectrum, KPPHGVVPR | 0.000 | 0.682 | 0.000 | 0.000 | 0.120 | 0.109 | 0.090 | 0.000 | ||
| 2 spectra, QPWQAK | 0.000 | 0.373 | 0.000 | 0.046 | 0.275 | 0.000 | 0.305 | 0.000 | ||
| 3 spectra, GDSGGPLIVHK | 0.000 | 0.343 | 0.000 | 0.122 | 0.195 | 0.000 | 0.340 | 0.000 | ||
| 4 spectra, LQPWLR | 0.000 | 0.582 | 0.000 | 0.000 | 0.000 | 0.297 | 0.121 | 0.000 | ||
| 1 spectrum, MDLETK | 0.000 | 0.273 | 0.105 | 0.049 | 0.365 | 0.000 | 0.207 | 0.000 | ||
| 2 spectra, ASSLPTLR | 0.000 | 0.389 | 0.000 | 0.000 | 0.034 | 0.297 | 0.281 | 0.000 | ||
| 6 spectra, MIDETK | 0.000 | 0.380 | 0.000 | 0.122 | 0.191 | 0.000 | 0.307 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
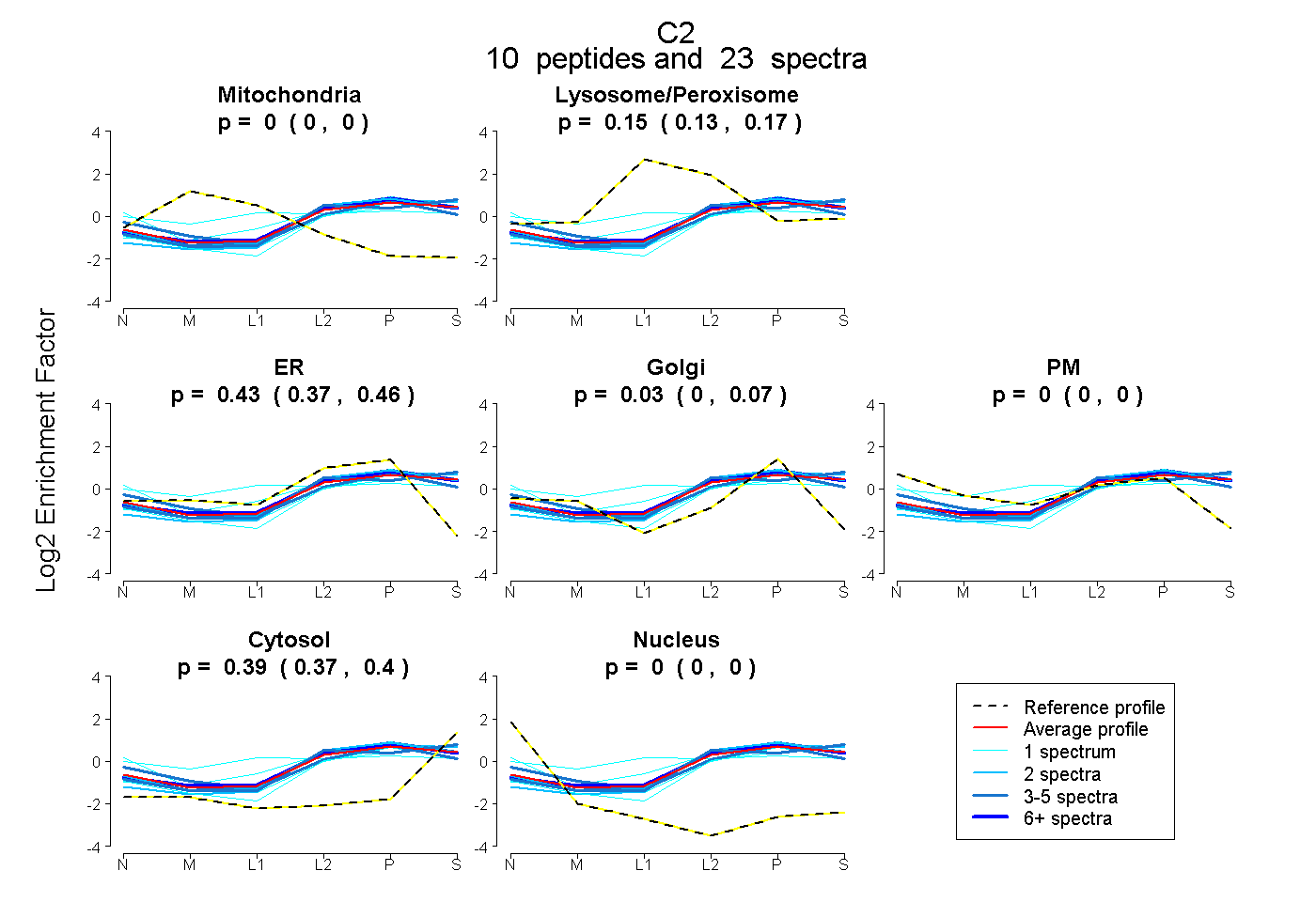 |
0.000 0.000 | 0.000 |
0.154 0.134 | 0.173 |
0.426 0.375 | 0.460 |
0.032 0.000 | 0.067 |
0.000 0.000 | 0.000 |
0.388 0.373 | 0.400 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
235 spectra |
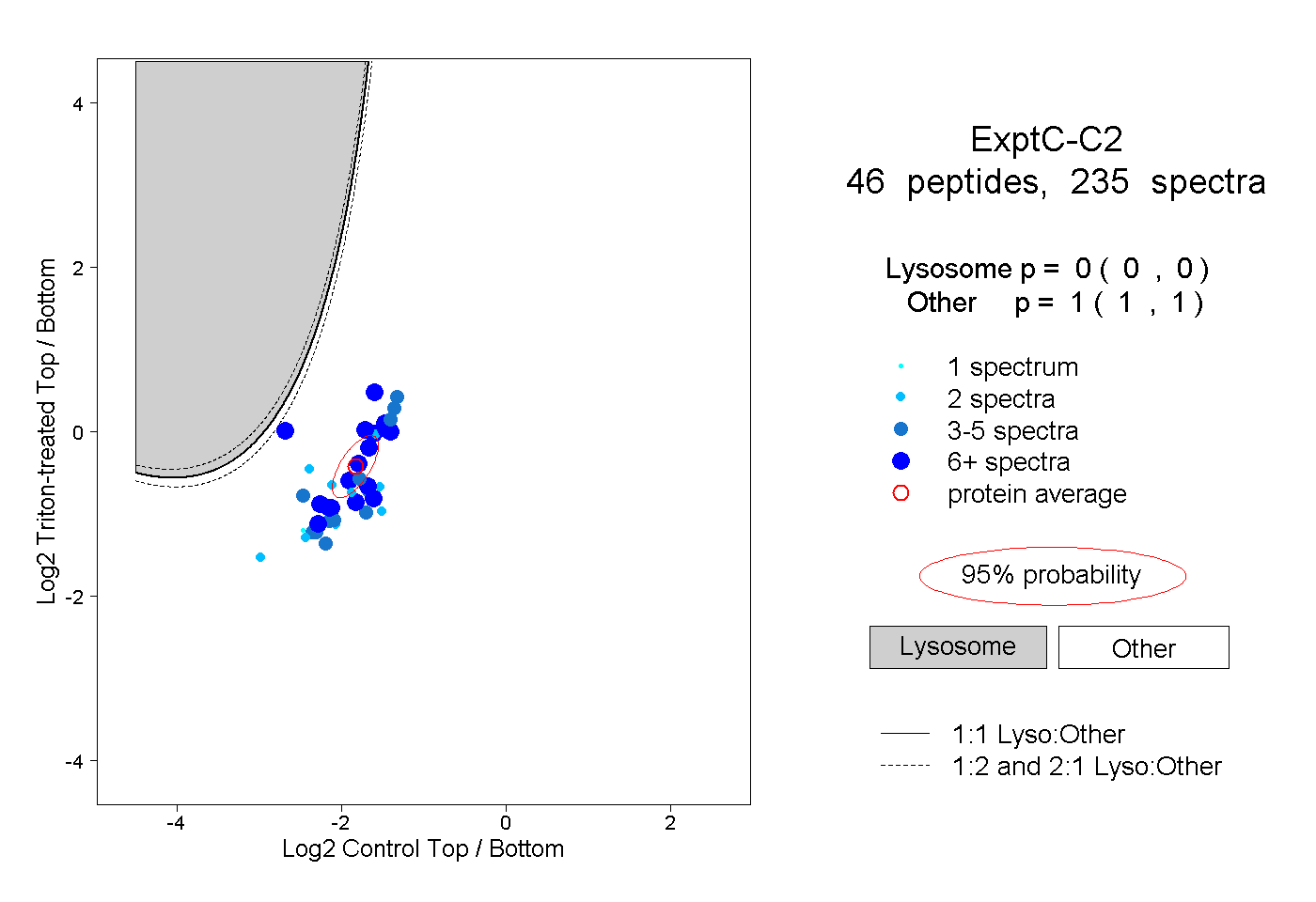 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
22 spectra |
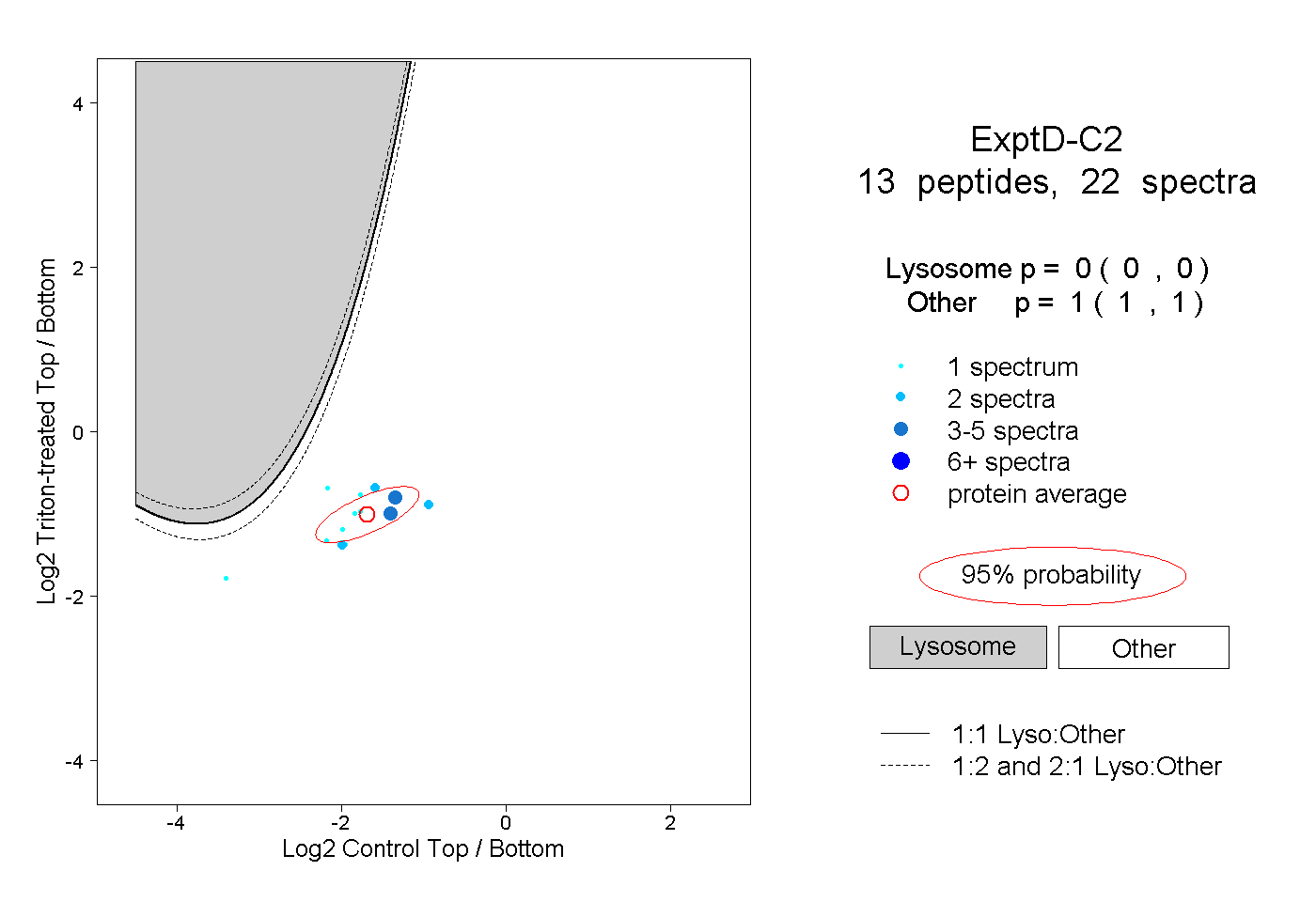 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |