peptides
spectra
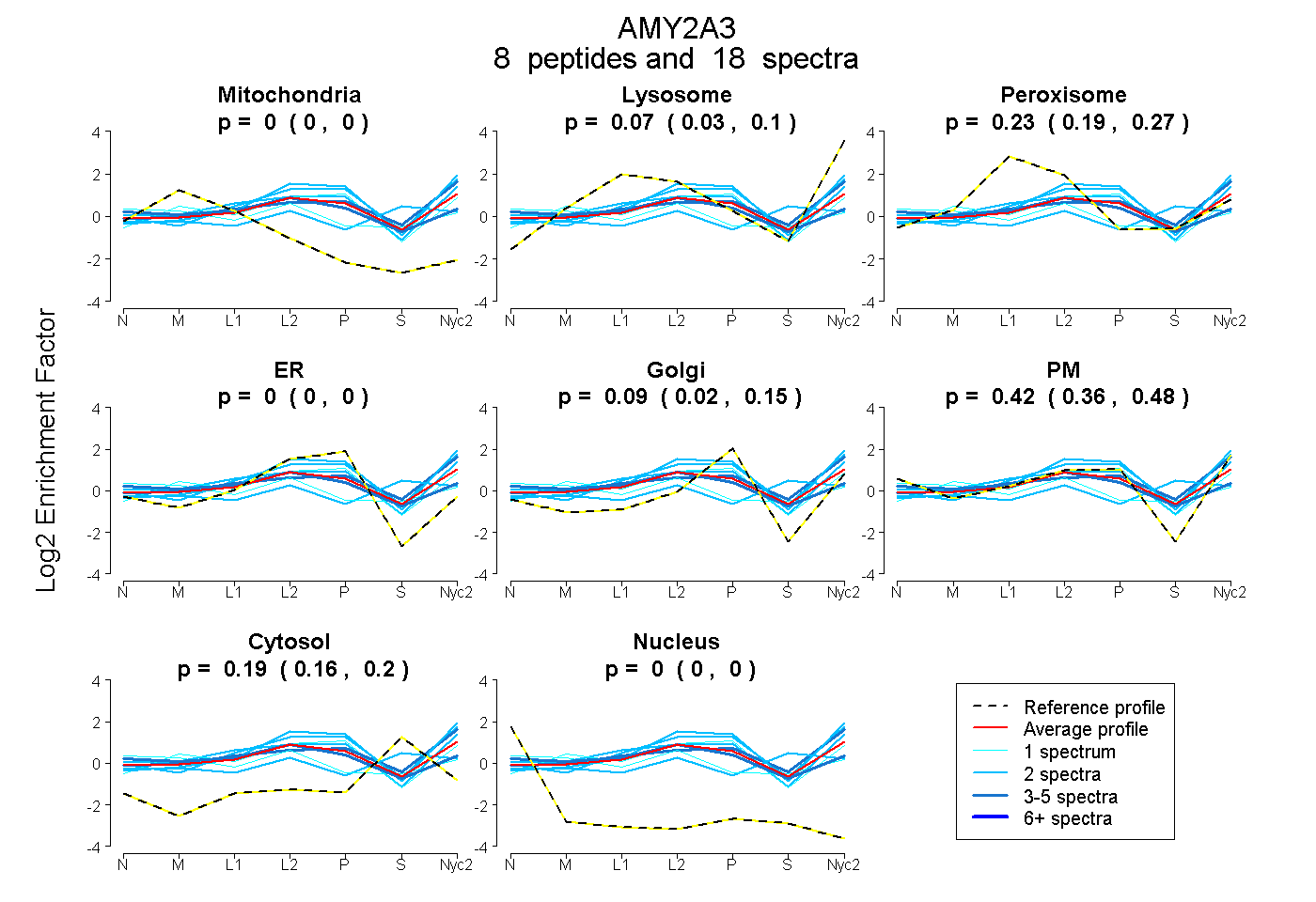
0.000 | 0.000
0.032 | 0.101
0.189 | 0.265
0.000 | 0.000
0.024 | 0.146
0.361 | 0.477
0.165 | 0.205
0.000 | 0.000
peptides
spectra
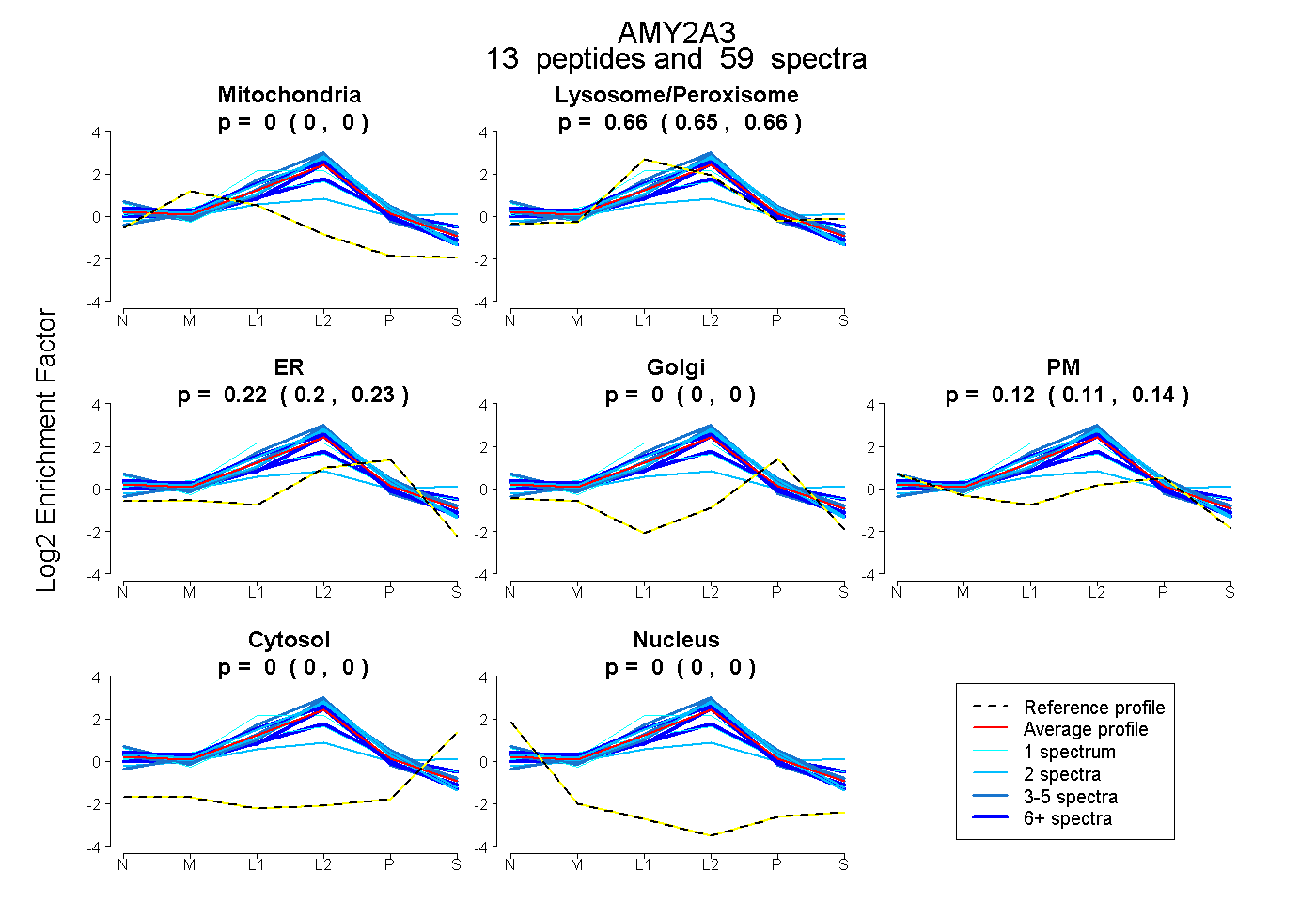
0.000 | 0.000
0.651 | 0.663
0.204 | 0.230
0.000 | 0.000
0.109 | 0.138
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
18 spectra |
 |
0.000 0.000 | 0.000 |
0.071 0.032 | 0.101 |
0.230 0.189 | 0.265 |
0.000 0.000 | 0.000 |
0.089 0.024 | 0.146 |
0.424 0.361 | 0.477 |
0.187 0.165 | 0.205 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
59 spectra |
 |
0.000 0.000 | 0.000 |
0.658 0.651 | 0.663 |
0.218 0.204 | 0.230 |
0.000 0.000 | 0.000 |
0.124 0.109 | 0.138 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 3 spectra, HMWPGDIK | 0.000 | 0.667 | 0.333 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, TAIVHLFEWR | 0.000 | 0.693 | 0.156 | 0.000 | 0.151 | 0.000 | 0.000 | |||
| 1 spectrum, LGTVIR | 0.000 | 0.682 | 0.000 | 0.000 | 0.318 | 0.000 | 0.000 | |||
| 2 spectra, VADYMNHLIDIGVAGFR | 0.000 | 0.599 | 0.401 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, GHGAGGASILTFWDAR | 0.000 | 0.554 | 0.000 | 0.075 | 0.197 | 0.173 | 0.000 | |||
| 1 spectrum, GSEYFGNGR | 0.000 | 0.816 | 0.090 | 0.000 | 0.094 | 0.000 | 0.000 | |||
| 4 spectra, EVTINPDTTCGNDWVCEHR | 0.000 | 0.773 | 0.062 | 0.000 | 0.165 | 0.000 | 0.000 | |||
| 4 spectra, NMVAFR | 0.000 | 0.653 | 0.347 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, CNGEINNYNDANQVR | 0.054 | 0.593 | 0.091 | 0.000 | 0.261 | 0.000 | 0.000 | |||
| 11 spectra, MAVGFMLAHPYGFTR | 0.000 | 0.583 | 0.187 | 0.000 | 0.230 | 0.000 | 0.000 | |||
| 13 spectra, ALVFVDNHDNQR | 0.000 | 0.595 | 0.143 | 0.000 | 0.251 | 0.012 | 0.000 | |||
| 2 spectra, VMSSYR | 0.000 | 0.673 | 0.319 | 0.000 | 0.008 | 0.000 | 0.000 | |||
| 3 spectra, LHNLNTK | 0.000 | 0.691 | 0.309 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
78 spectra |
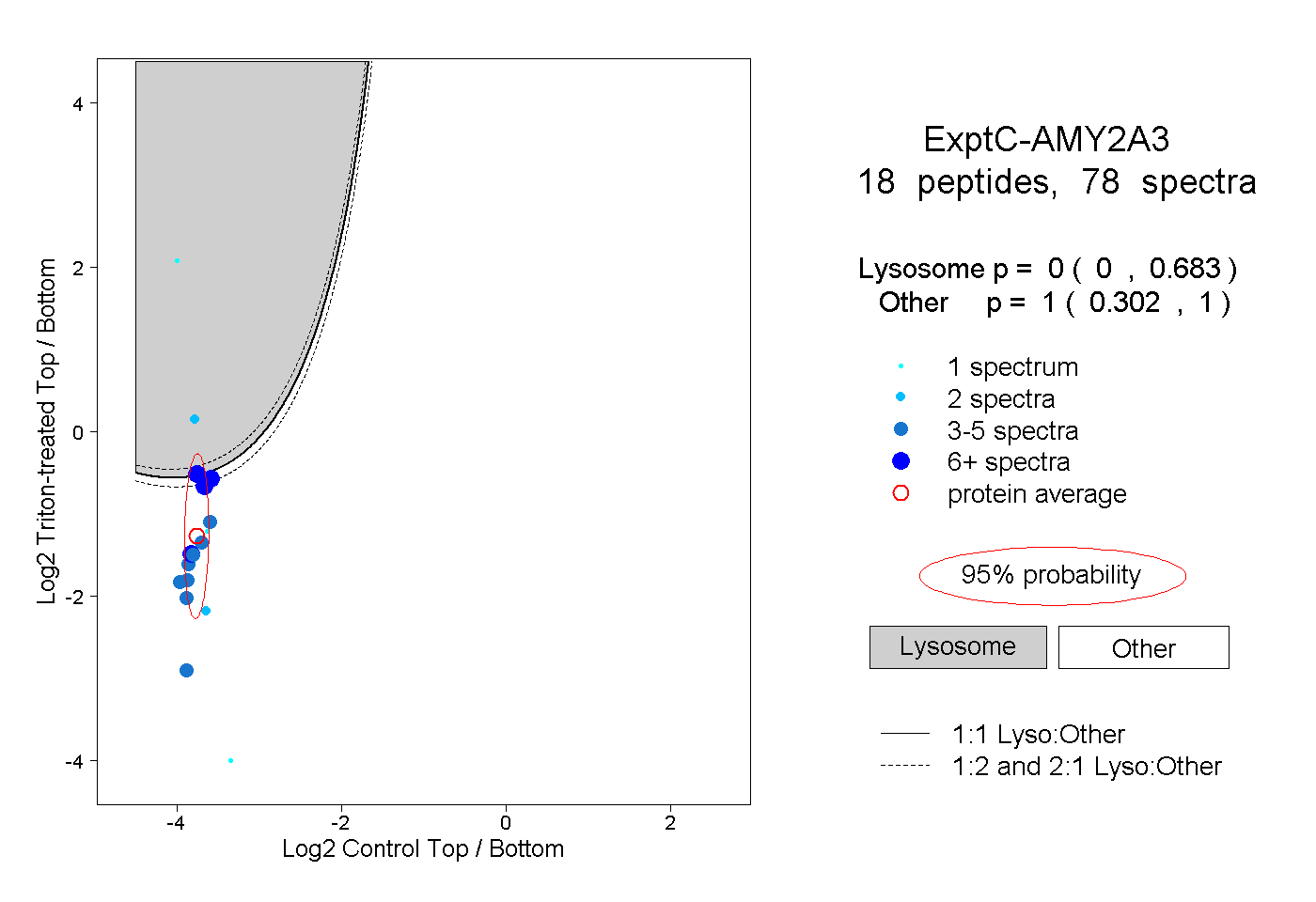 |
0.000 0.000 | 0.683 |
1.000 0.302 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
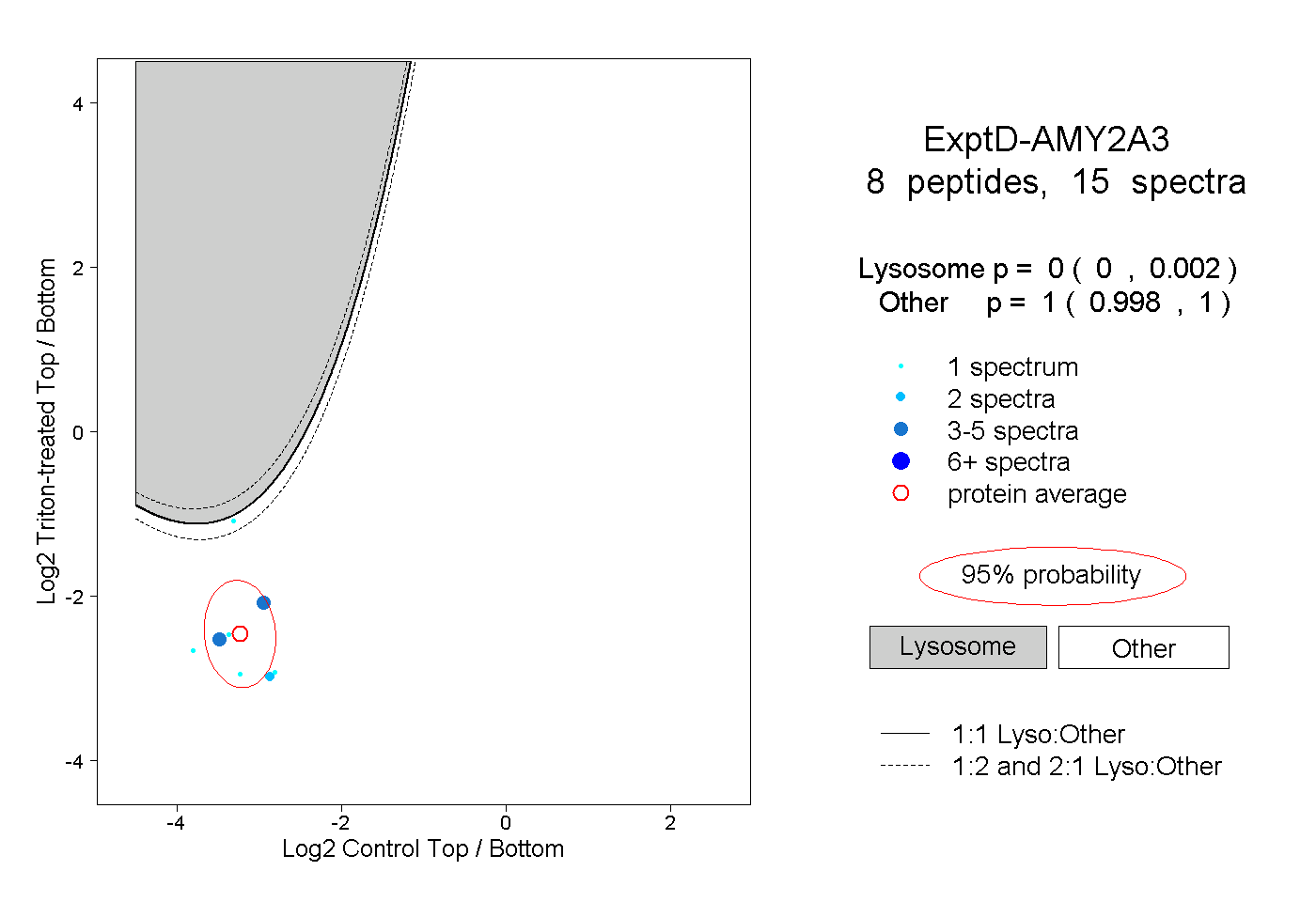 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |