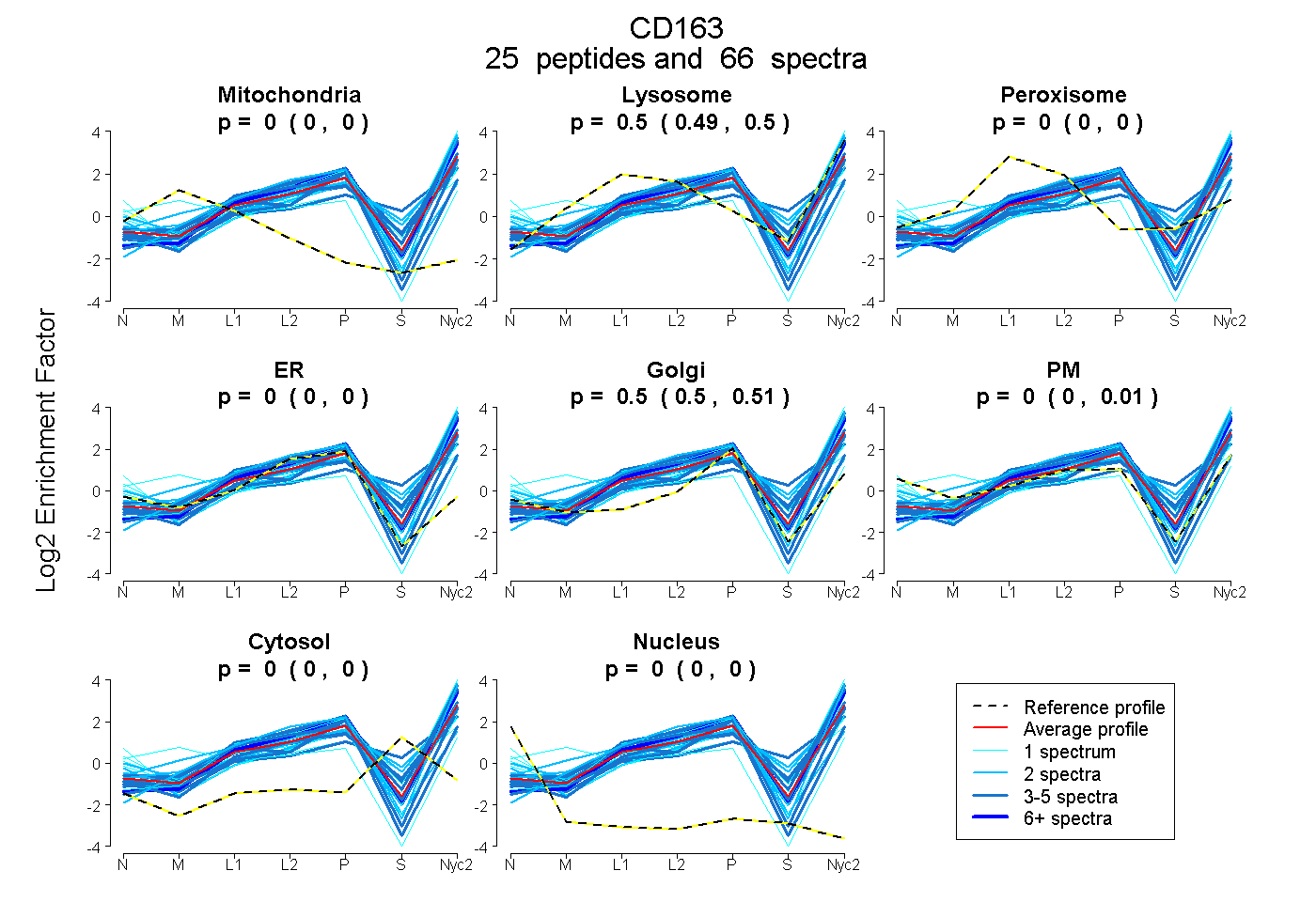
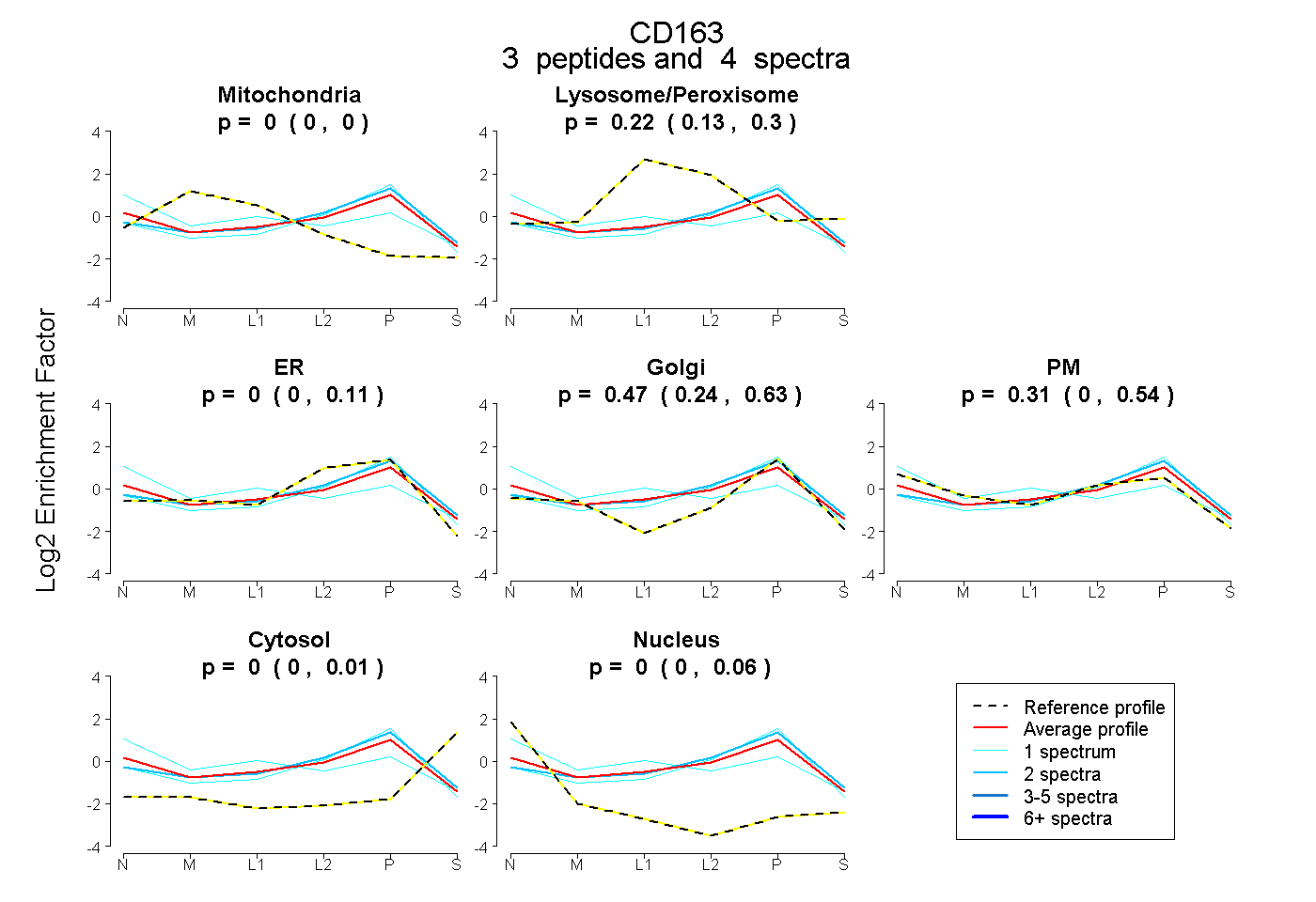
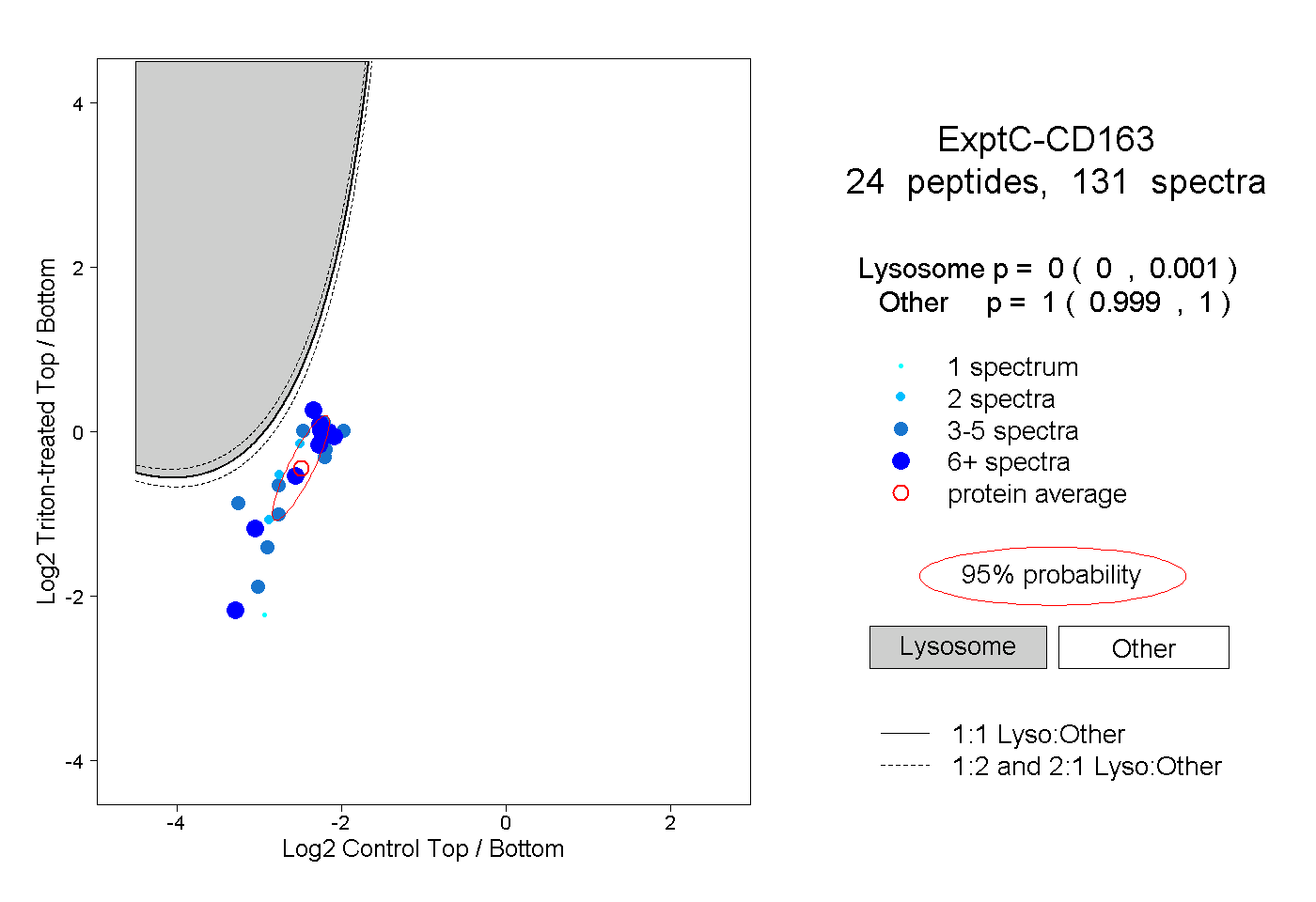
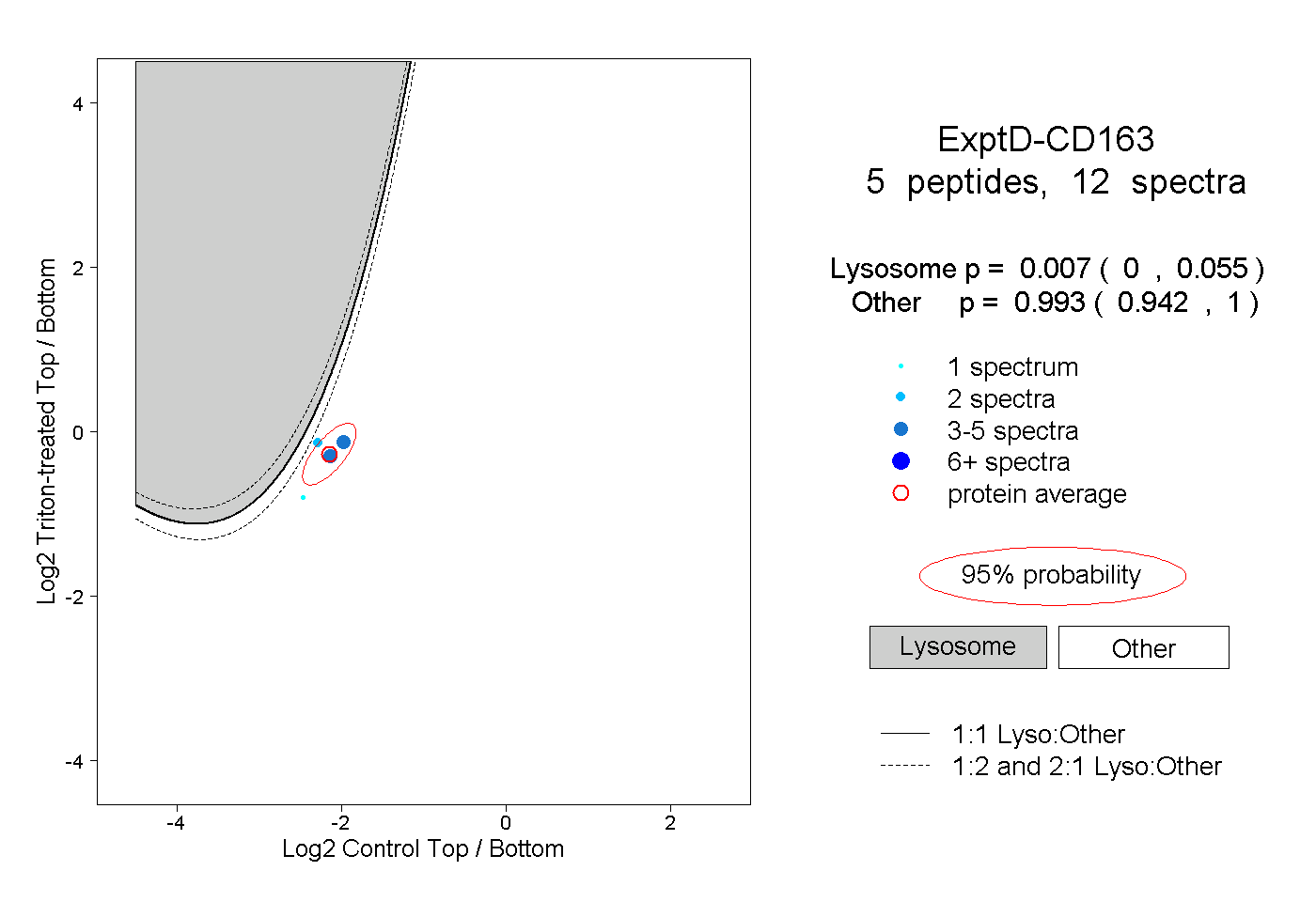
| 2 spectra, LVGGGSR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 4 spectra, GWTLTDADVVCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, HQEWGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LVGGEIPCSGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, DVSIVCSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LTVSSR |
|
0.003 |
|
|
|
|
|
|
|
0.997 |
| 3 spectra, LTNEAHR |
|
0.002 |
|
|
|
|
|
|
|
0.998 |
| 5 spectra, GAGQVWR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LQEGHTDCSGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LVGGGGR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 5 spectra, DASVVCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GEVLIHQVQYQEMDSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, QLGCGQAVEALK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QLGCGSAISFSGSAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DHASVICK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, CGVALSTPGGAHFGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LAGGENNCSGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, LVNSGDNR |
|
0.002 |
|
|
|
|
|
|
|
0.998 |
| 8 spectra, LVDGVSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, VEIWHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, QLGCPTAITAIGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, TDDLDLLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, EDASVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, DSDVPCIASGQLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |