peptides
spectra
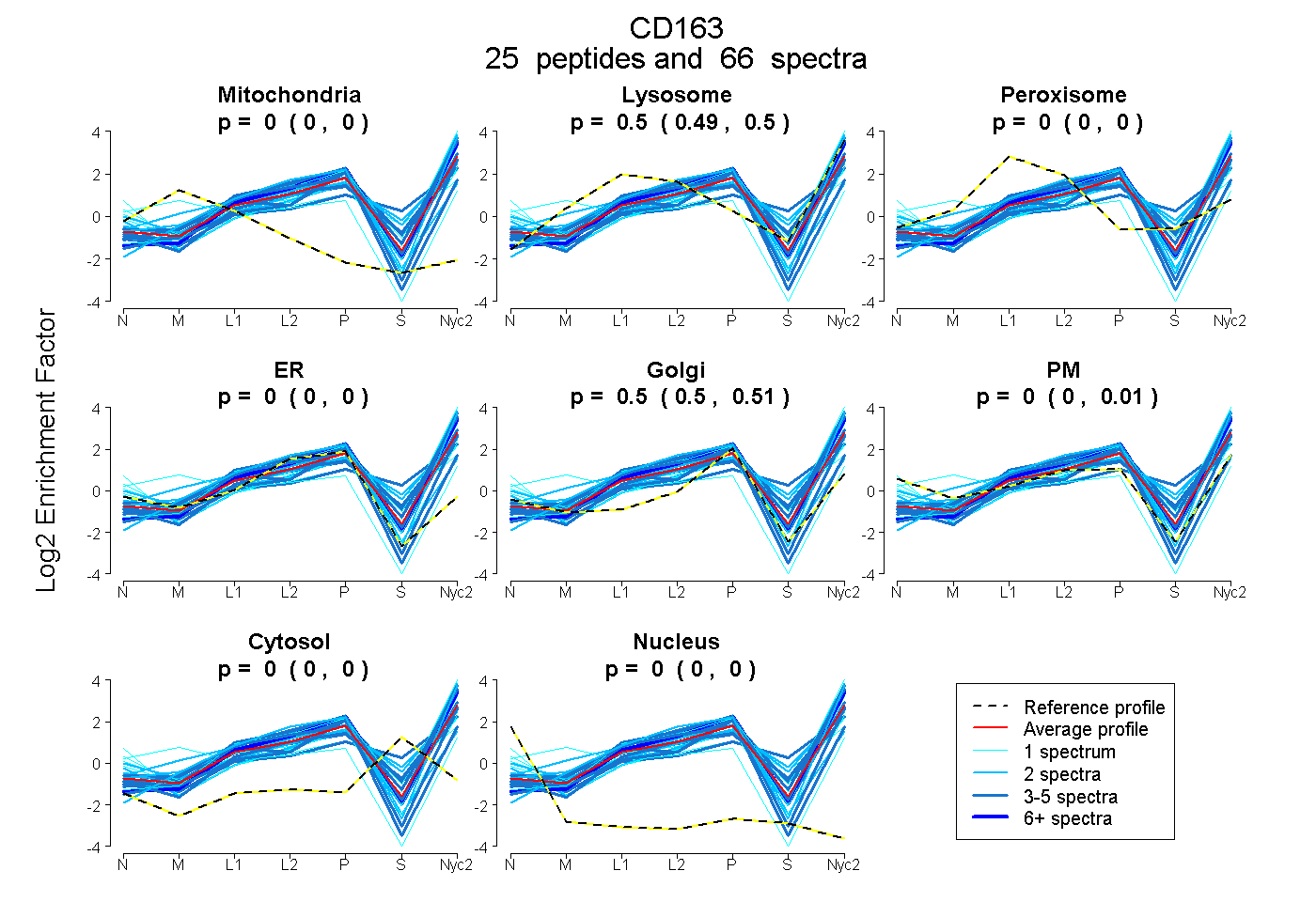
0.000 | 0.000
0.491 | 0.502
0.000 | 0.000
0.000 | 0.000
0.495 | 0.506
0.000 | 0.006
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
66 spectra |
 |
0.000 0.000 | 0.000 |
0.498 0.491 | 0.502 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.502 0.495 | 0.506 |
0.000 0.000 | 0.006 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, GWTLTDADVVCR | 0.000 | 0.549 | 0.000 | 0.084 | 0.366 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, HQEWGK | 0.000 | 0.593 | 0.000 | 0.000 | 0.407 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, LVGGEIPCSGR | 0.000 | 0.566 | 0.000 | 0.000 | 0.434 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, DVSIVCSR | 0.000 | 0.309 | 0.000 | 0.506 | 0.185 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, LTVSSR | 0.000 | 0.192 | 0.000 | 0.161 | 0.425 | 0.222 | 0.000 | 0.000 | ||
| 2 spectra, LTNEAHR | 0.000 | 0.318 | 0.000 | 0.000 | 0.269 | 0.413 | 0.000 | 0.000 | ||
| 2 spectra, GAGQVWR | 0.000 | 0.542 | 0.000 | 0.000 | 0.207 | 0.251 | 0.000 | 0.000 | ||
| 2 spectra, EAAFGPGTGPIWLNEMK | 0.000 | 0.659 | 0.000 | 0.000 | 0.341 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, WGTVCDDNFSK | 0.000 | 0.672 | 0.000 | 0.000 | 0.328 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LQEGHTDCSGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.231 | 0.769 | 0.000 | 0.000 | ||
| 4 spectra, DASVVCK | 0.000 | 0.453 | 0.000 | 0.000 | 0.244 | 0.000 | 0.303 | 0.000 | ||
| 3 spectra, QLGCGQAVEALK | 0.000 | 0.484 | 0.000 | 0.000 | 0.407 | 0.000 | 0.109 | 0.000 | ||
| 1 spectrum, CAGMVEVEIQK | 0.000 | 0.145 | 0.000 | 0.000 | 0.030 | 0.572 | 0.253 | 0.000 | ||
| 5 spectra, CGVALSTPGGAHFGK | 0.000 | 0.498 | 0.000 | 0.083 | 0.385 | 0.000 | 0.034 | 0.000 | ||
| 2 spectra, LAGGENNCSGR | 0.000 | 0.362 | 0.000 | 0.000 | 0.327 | 0.124 | 0.187 | 0.000 | ||
| 1 spectrum, EDAGVVCSEFMSLR | 0.000 | 0.276 | 0.000 | 0.000 | 0.266 | 0.410 | 0.048 | 0.000 | ||
| 2 spectra, LVDGVSK | 0.000 | 0.537 | 0.000 | 0.000 | 0.357 | 0.106 | 0.000 | 0.000 | ||
| 1 spectrum, HYCNHK | 0.000 | 0.388 | 0.000 | 0.000 | 0.271 | 0.341 | 0.000 | 0.000 | ||
| 5 spectra, VEIWHR | 0.000 | 0.691 | 0.000 | 0.000 | 0.309 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, QLGCPTAITAIGR | 0.000 | 0.652 | 0.000 | 0.000 | 0.348 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, TDDLDLLK | 0.000 | 0.317 | 0.000 | 0.000 | 0.683 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, TPTRPMWTDSVQCPK | 0.000 | 0.691 | 0.000 | 0.000 | 0.309 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, HNCDHAEDVGVICLDGADLSLR | 0.207 | 0.000 | 0.000 | 0.000 | 0.000 | 0.793 | 0.000 | 0.000 | ||
| 2 spectra, EDASVK | 0.000 | 0.488 | 0.000 | 0.000 | 0.409 | 0.000 | 0.104 | 0.000 | ||
| 3 spectra, DSDVPCIASGQLR | 0.000 | 0.527 | 0.000 | 0.000 | 0.351 | 0.050 | 0.072 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
4 spectra |
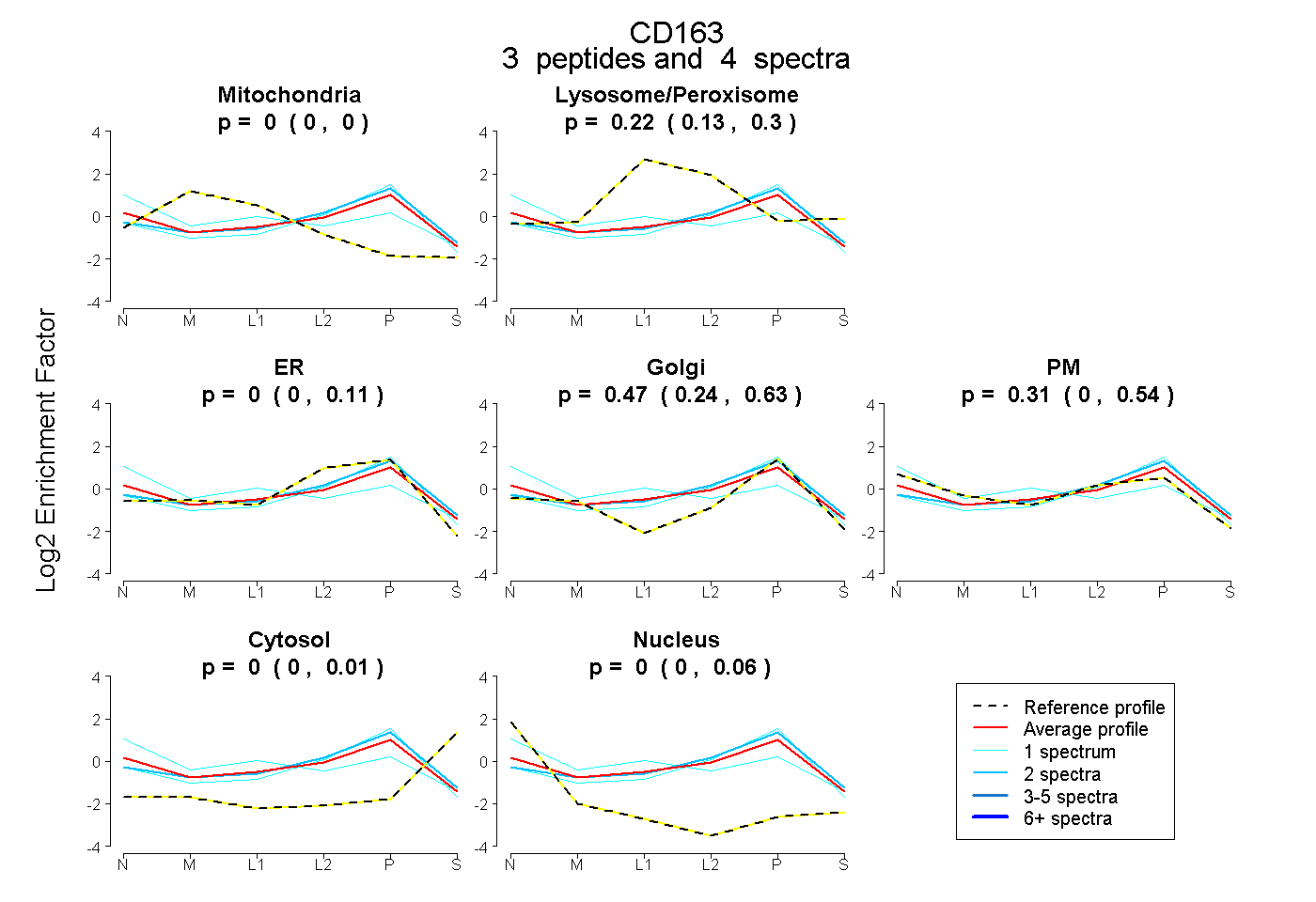 |
0.000 0.000 | 0.000 |
0.223 0.126 | 0.299 |
0.000 0.000 | 0.112 |
0.466 0.237 | 0.634 |
0.307 0.000 | 0.538 |
0.000 0.000 | 0.006 |
0.004 0.000 | 0.063 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
131 spectra |
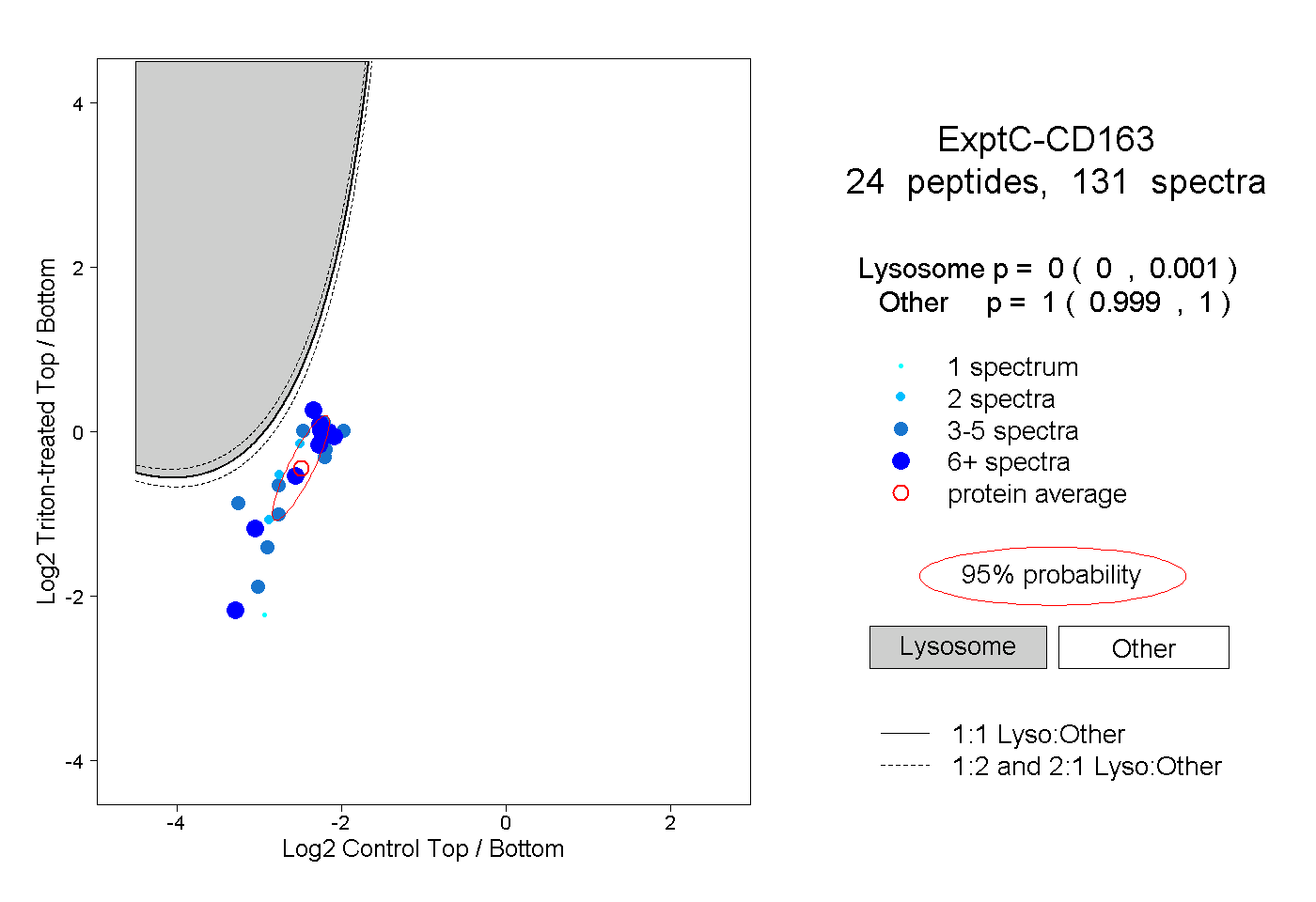 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
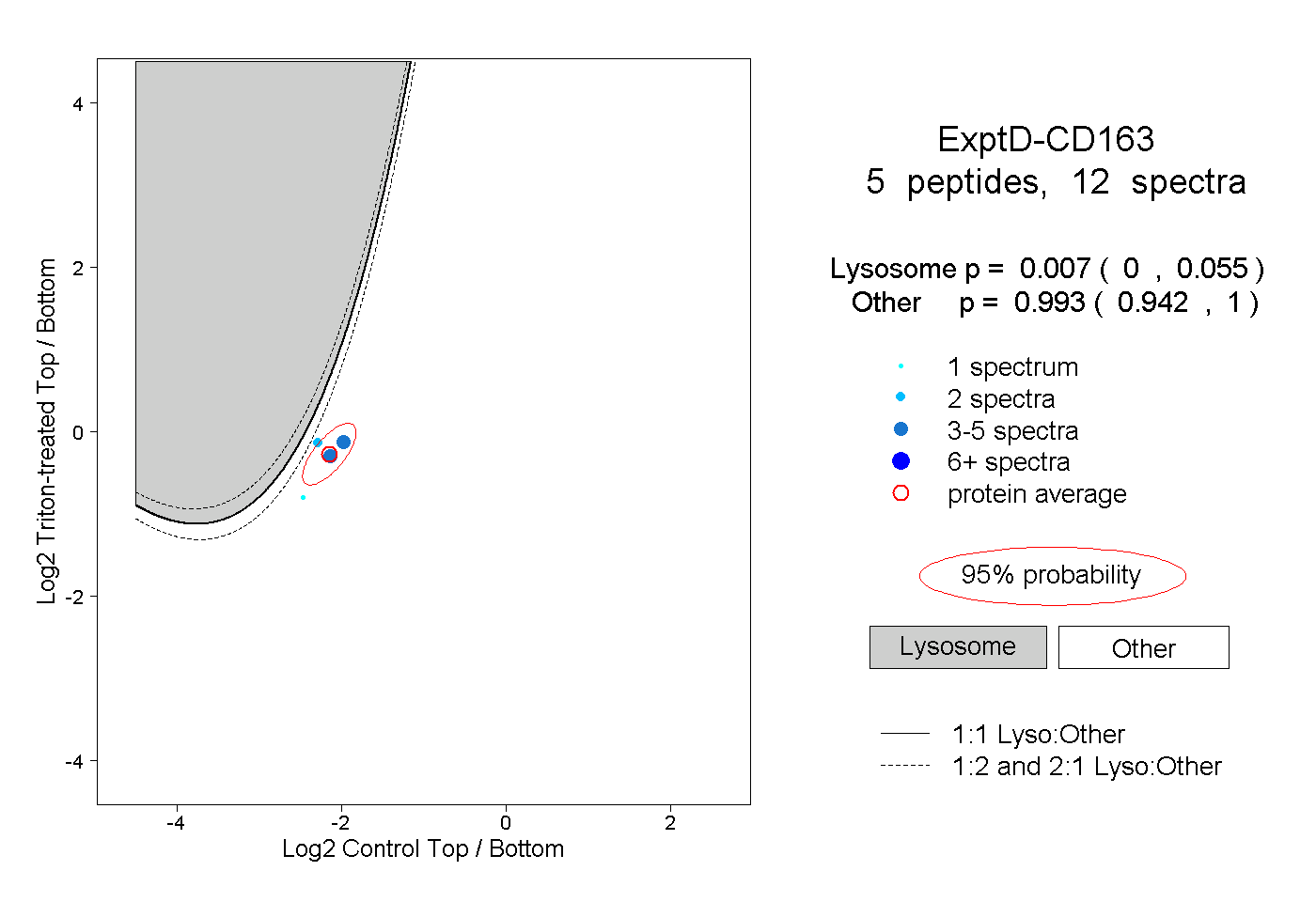 |
0.007 0.000 | 0.055 |
0.993 0.942 | 1.000 |