peptides
spectra
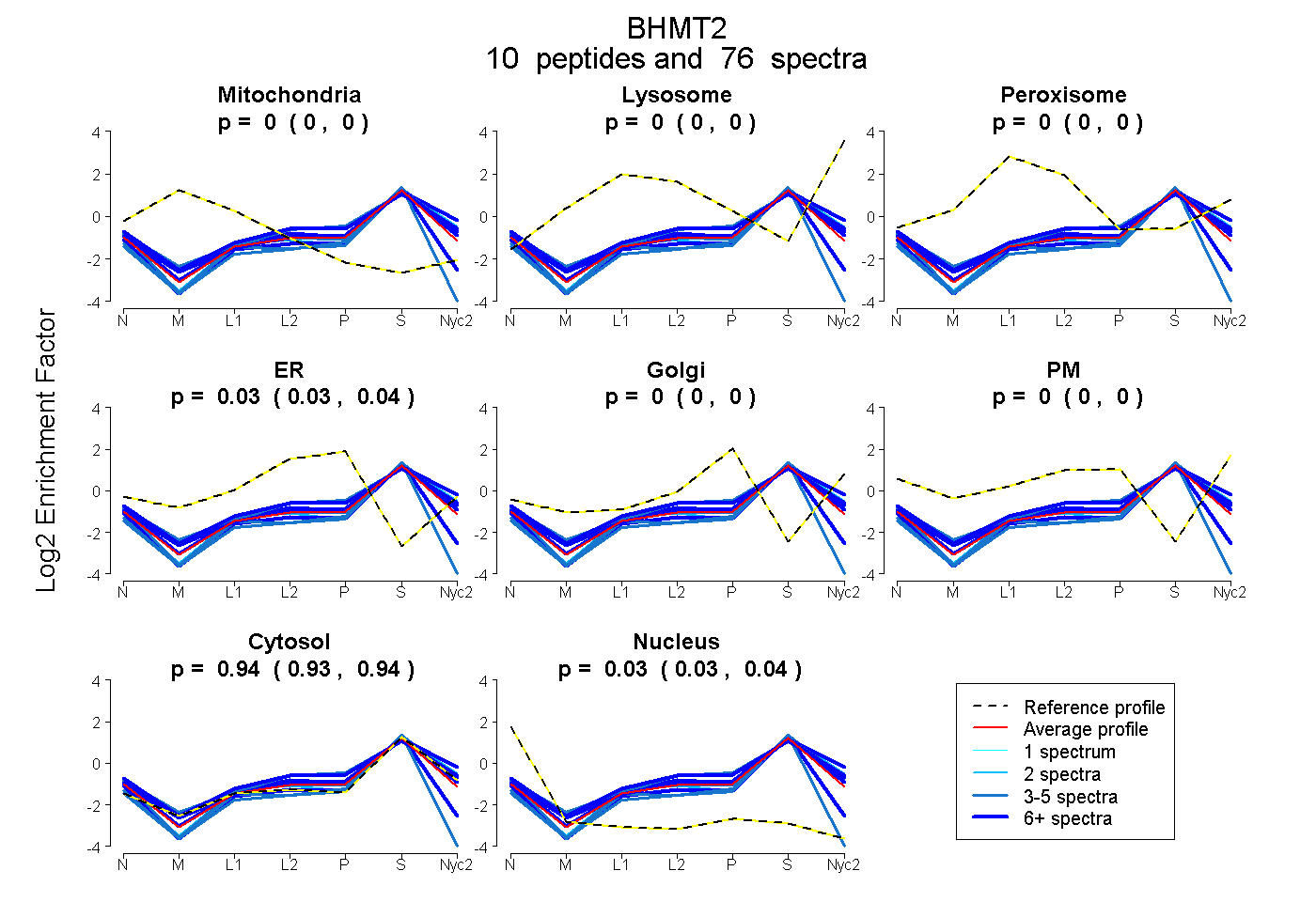
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.029 | 0.036
0.000 | 0.000
0.000 | 0.000
0.931 | 0.940
0.025 | 0.037
peptides
spectra
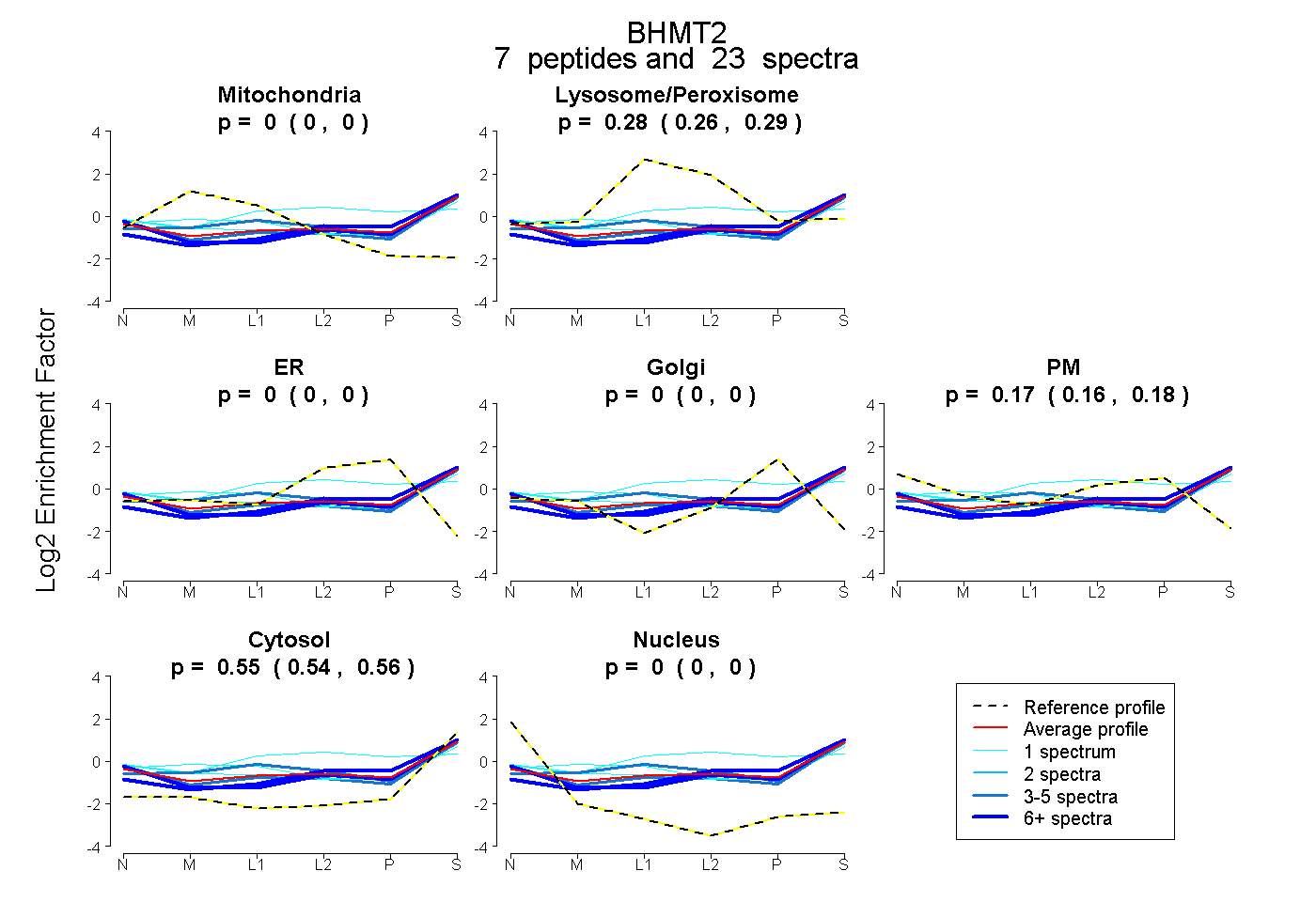
0.000 | 0.000
0.262 | 0.290
0.000 | 0.000
0.000 | 0.000
0.160 | 0.184
0.541 | 0.556
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
76 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.032 0.029 | 0.036 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.936 0.931 | 0.940 |
0.032 0.025 | 0.037 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
 |
0.000 0.000 | 0.000 |
0.277 0.262 | 0.290 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.174 0.160 | 0.184 |
0.549 0.541 | 0.556 |
0.000 0.000 | 0.000 |
| 1 spectrum, APAGGPR | 0.000 | 0.278 | 0.000 | 0.000 | 0.170 | 0.514 | 0.039 | |||
| 1 spectrum, FGPWTSLQTMK | 0.154 | 0.278 | 0.000 | 0.000 | 0.112 | 0.456 | 0.000 | |||
| 6 spectra, QLHTEFLR | 0.000 | 0.264 | 0.051 | 0.099 | 0.000 | 0.586 | 0.000 | |||
| 1 spectrum, EYWETLLPASGRPFCPSLSKPDA | 0.000 | 0.488 | 0.000 | 0.142 | 0.137 | 0.232 | 0.000 | |||
| 3 spectra, GGFVDLPEYPFGLEPR | 0.044 | 0.380 | 0.000 | 0.000 | 0.064 | 0.513 | 0.000 | |||
| 7 spectra, LQLGVFAR | 0.000 | 0.172 | 0.000 | 0.000 | 0.230 | 0.597 | 0.000 | |||
| 4 spectra, AGANIIGVNCR | 0.000 | 0.301 | 0.000 | 0.000 | 0.073 | 0.553 | 0.074 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
107 spectra |
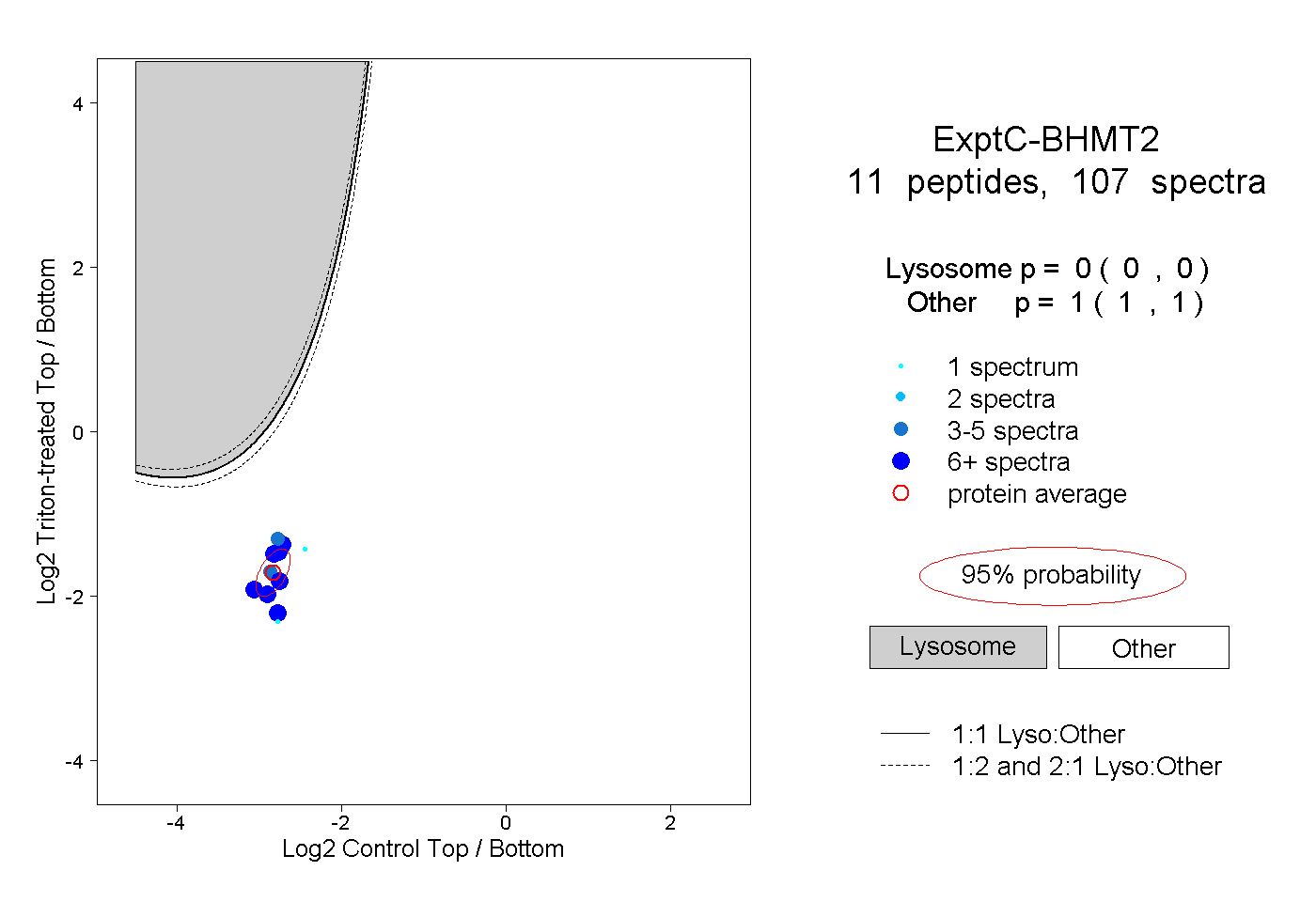 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
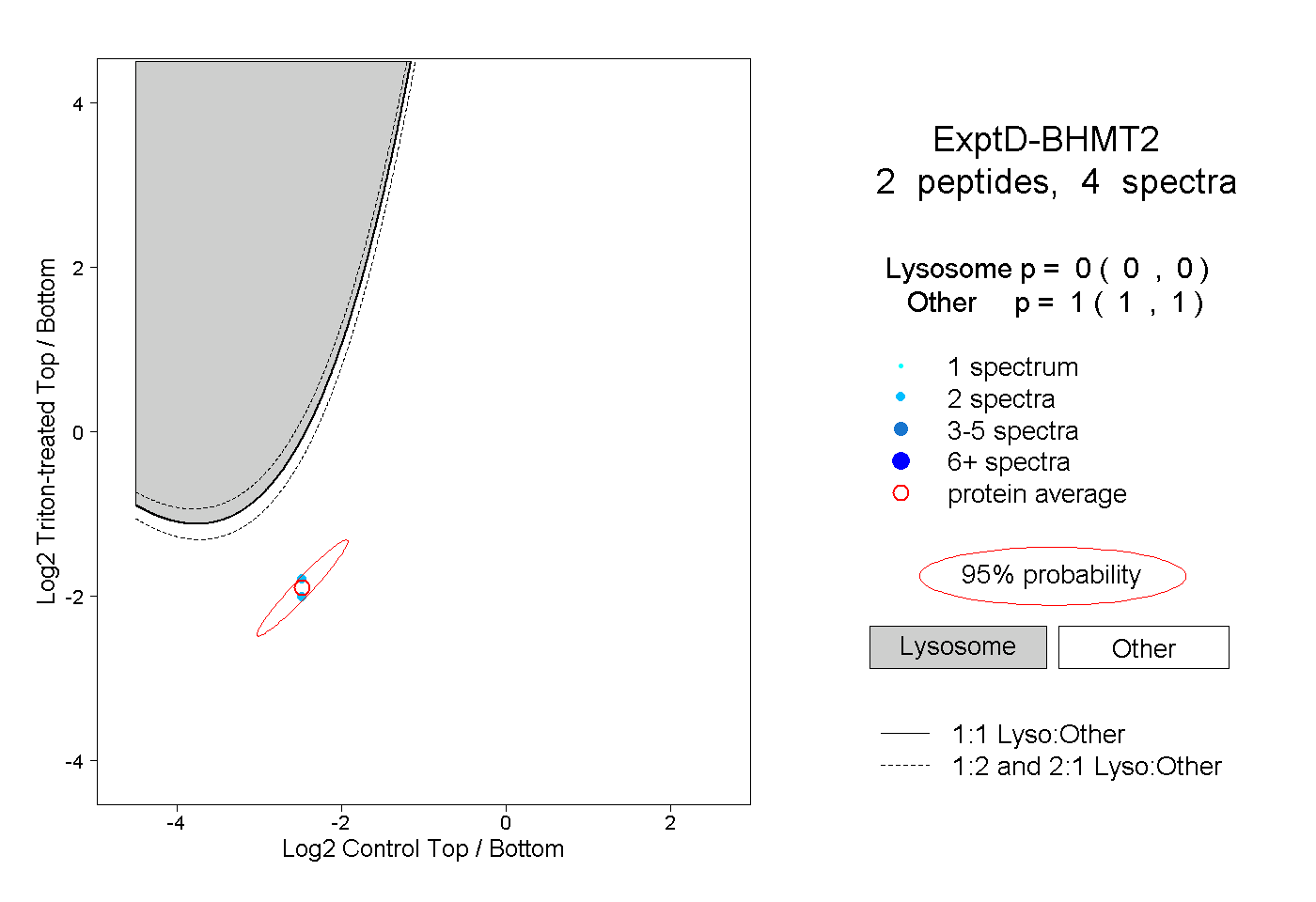 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |