peptides
spectra
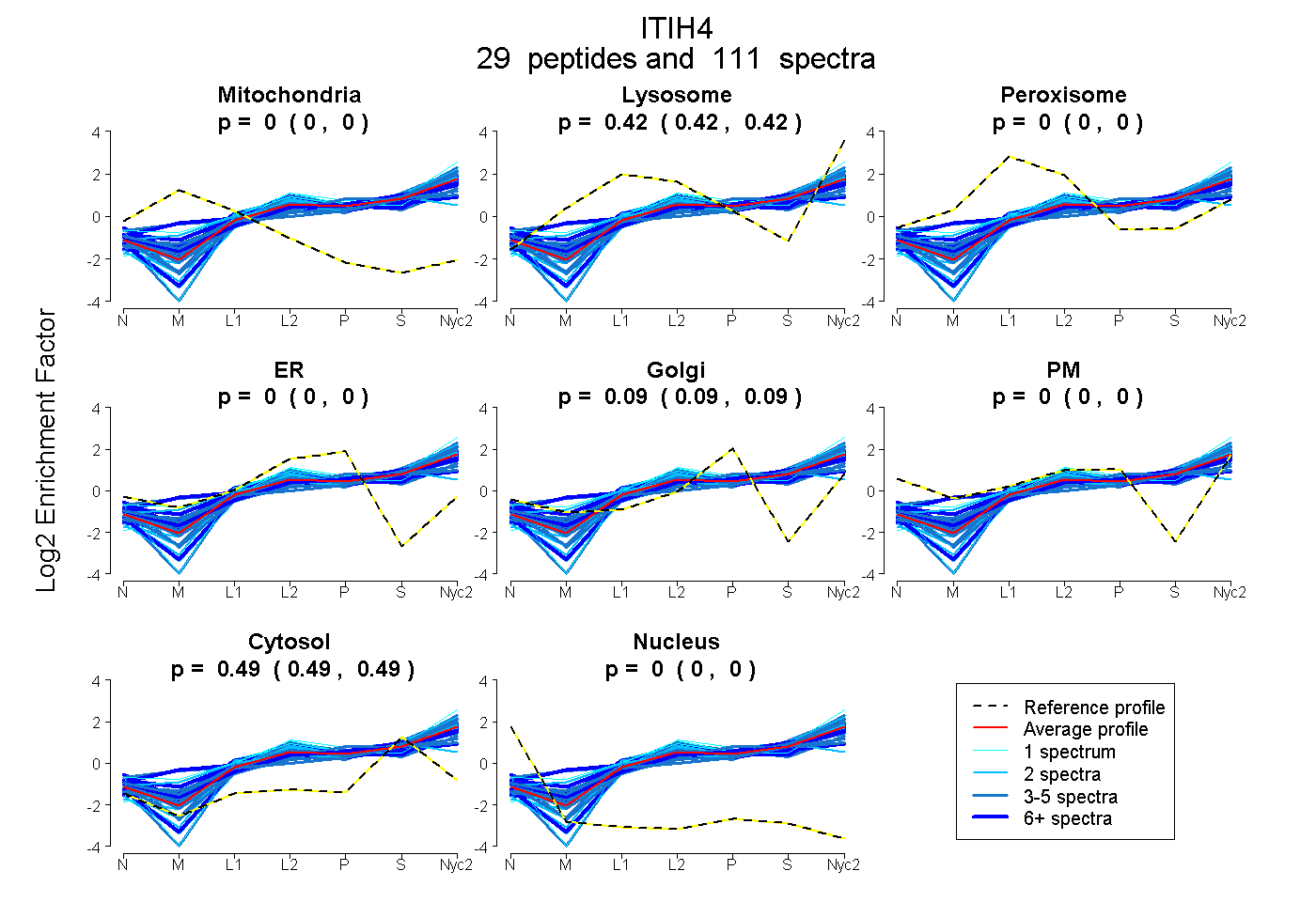
0.000 | 0.000
0.416 | 0.421
0.000 | 0.000
0.000 | 0.000
0.088 | 0.092
0.000 | 0.000
0.489 | 0.493
0.000 | 0.000
peptides
spectra
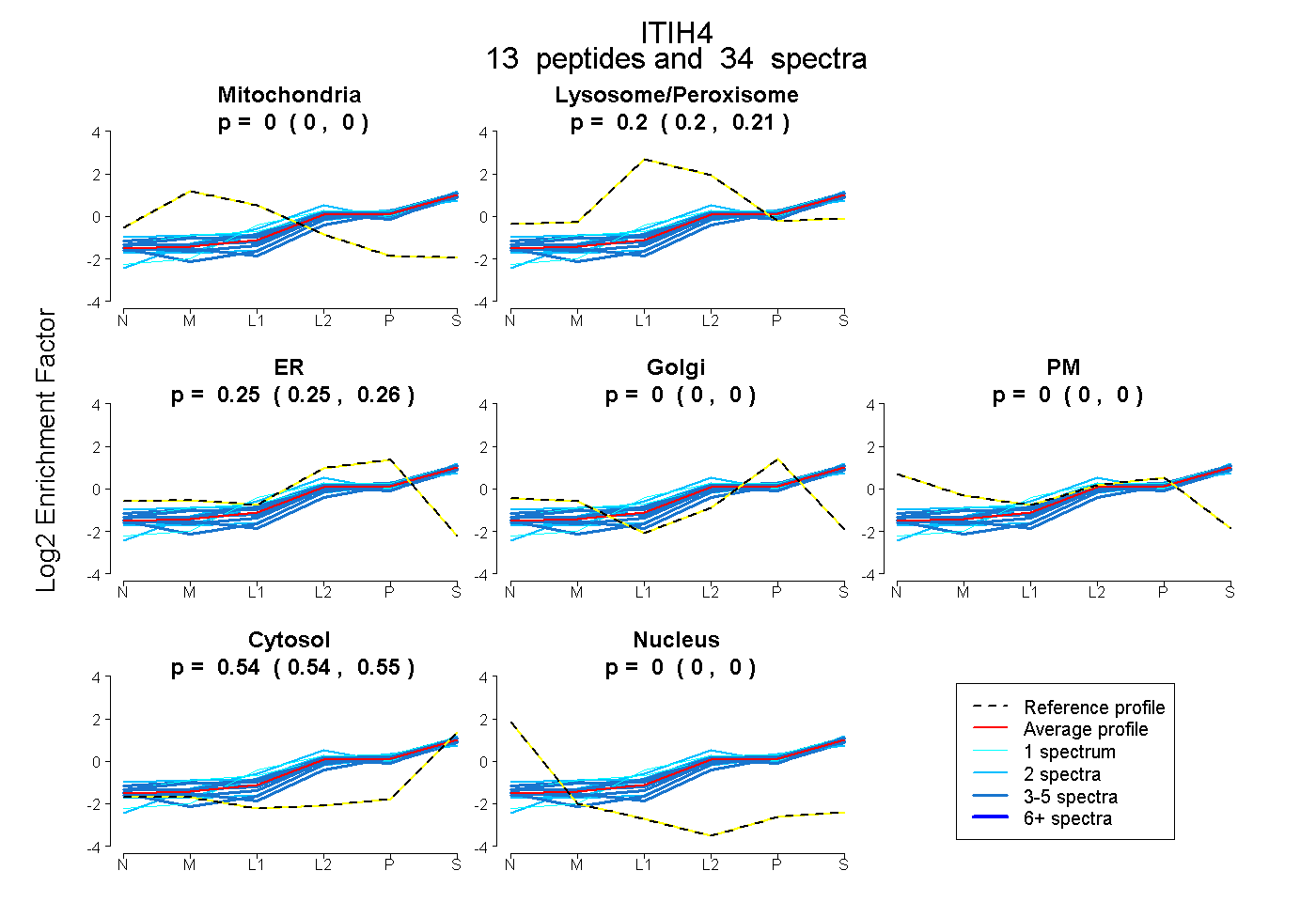
0.000 | 0.000
0.196 | 0.210
0.246 | 0.257
0.000 | 0.000
0.000 | 0.000
0.541 | 0.548
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
111 spectra |
 |
0.000 0.000 | 0.000 |
0.419 0.416 | 0.421 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.090 0.088 | 0.092 |
0.000 0.000 | 0.000 |
0.491 0.489 | 0.493 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
34 spectra |
 |
0.000 0.000 | 0.000 |
0.204 0.196 | 0.210 |
0.252 0.246 | 0.257 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.544 0.541 | 0.548 |
0.000 0.000 | 0.000 |
| 1 spectrum, NTQEAINGR | 0.000 | 0.292 | 0.214 | 0.000 | 0.000 | 0.494 | 0.000 | |||
| 3 spectra, YNFQHHFK | 0.000 | 0.213 | 0.224 | 0.000 | 0.000 | 0.562 | 0.000 | |||
| 3 spectra, QYTAAVGR | 0.000 | 0.240 | 0.255 | 0.000 | 0.000 | 0.505 | 0.000 | |||
| 2 spectra, FQTLSR | 0.000 | 0.099 | 0.296 | 0.000 | 0.000 | 0.605 | 0.000 | |||
| 1 spectrum, TTFELIYQELLQR | 0.000 | 0.322 | 0.151 | 0.000 | 0.000 | 0.527 | 0.000 | |||
| 4 spectra, VLGIDYPATR | 0.000 | 0.153 | 0.267 | 0.000 | 0.000 | 0.580 | 0.000 | |||
| 2 spectra, AVLSAVELLDK | 0.000 | 0.268 | 0.208 | 0.000 | 0.000 | 0.524 | 0.000 | |||
| 3 spectra, AHIQFKPTLSQQR | 0.000 | 0.198 | 0.278 | 0.000 | 0.000 | 0.524 | 0.000 | |||
| 2 spectra, FAHTVVTSR | 0.000 | 0.343 | 0.128 | 0.000 | 0.000 | 0.529 | 0.000 | |||
| 4 spectra, LGDGLVGSR | 0.000 | 0.076 | 0.310 | 0.000 | 0.000 | 0.613 | 0.000 | |||
| 4 spectra, VVEQEGTTPEESPNPDHPR | 0.000 | 0.031 | 0.329 | 0.000 | 0.000 | 0.639 | 0.000 | |||
| 2 spectra, AVDYASK | 0.000 | 0.259 | 0.205 | 0.105 | 0.000 | 0.430 | 0.000 | |||
| 3 spectra, LALDNGGLAR | 0.000 | 0.253 | 0.249 | 0.000 | 0.000 | 0.498 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
337 spectra |
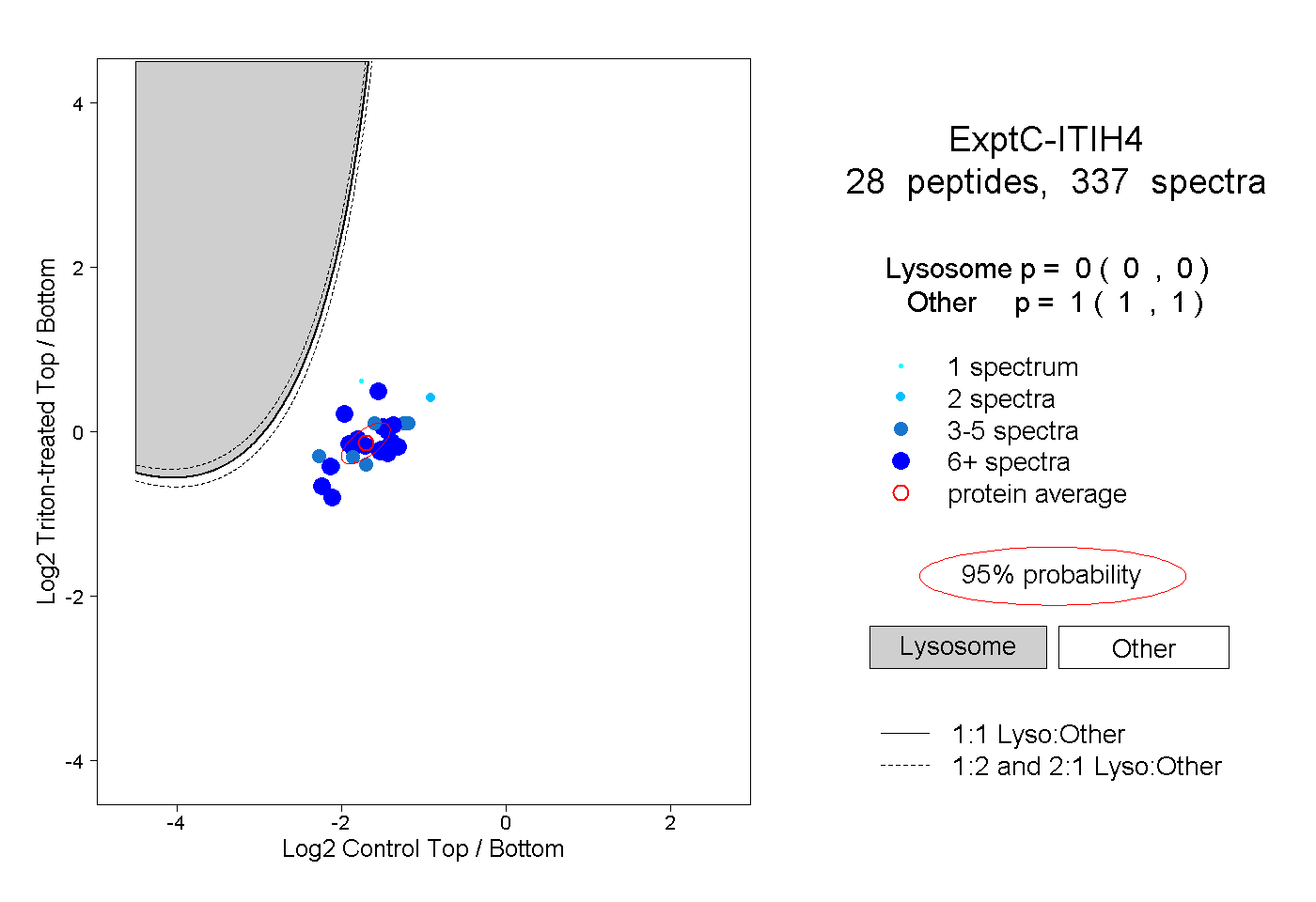 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
26 spectra |
 |
0.000 0.000 | 0.005 |
1.000 0.995 | 1.000 |