peptides
spectra
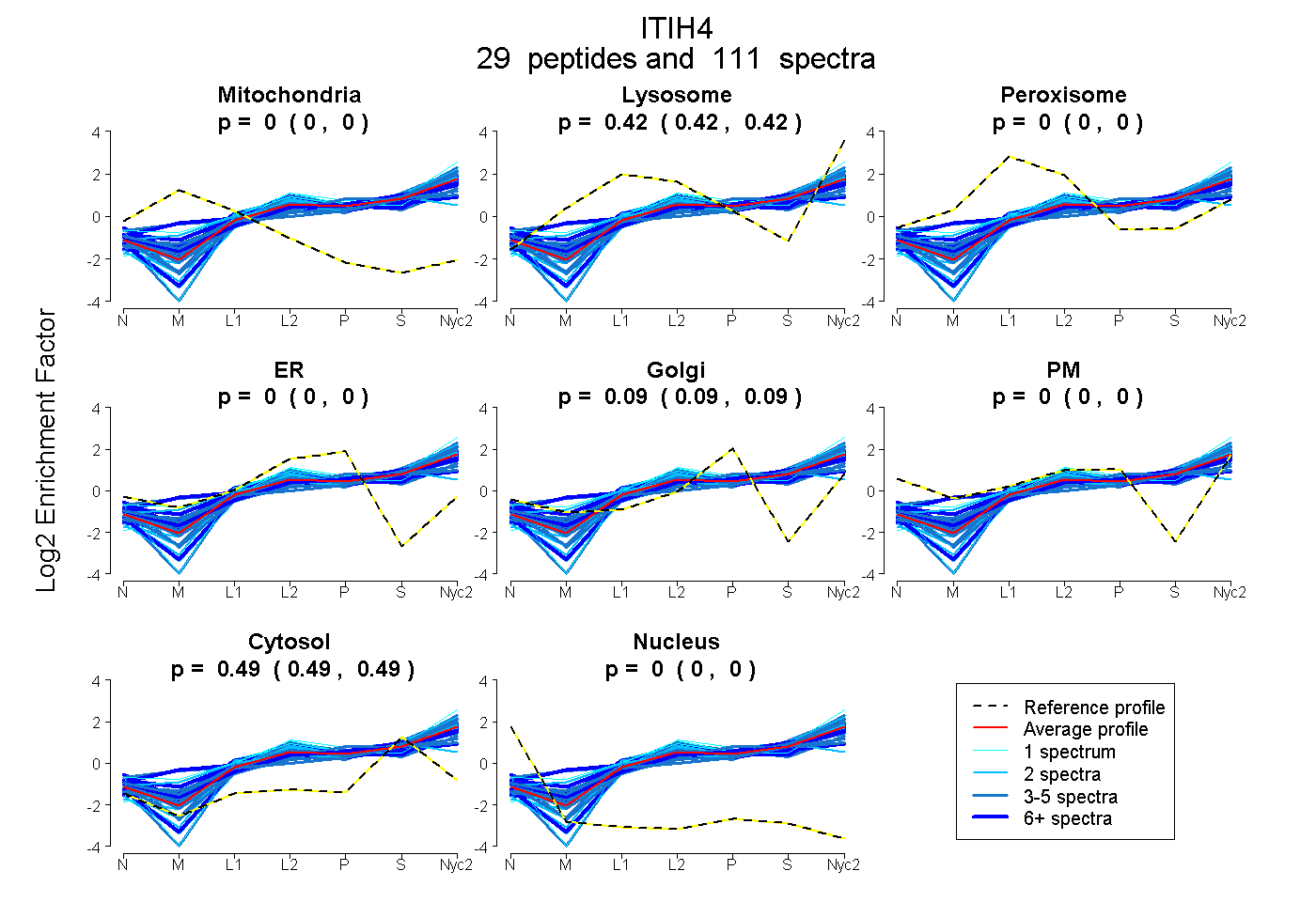
0.000 | 0.000
0.416 | 0.421
0.000 | 0.000
0.000 | 0.000
0.088 | 0.092
0.000 | 0.000
0.489 | 0.493
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
111 spectra |
 |
0.000 0.000 | 0.000 |
0.419 0.416 | 0.421 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.090 0.088 | 0.092 |
0.000 0.000 | 0.000 |
0.491 0.489 | 0.493 |
0.000 0.000 | 0.000 |
| 2 spectra, IPAQGGTNINK | 0.000 | 0.497 | 0.000 | 0.000 | 0.000 | 0.000 | 0.503 | 0.000 | ||
| 2 spectra, LFVDINQGLEVVGK | 0.000 | 0.422 | 0.000 | 0.000 | 0.035 | 0.000 | 0.543 | 0.000 | ||
| 5 spectra, YNFQHHFK | 0.000 | 0.349 | 0.000 | 0.000 | 0.117 | 0.000 | 0.533 | 0.000 | ||
| 9 spectra, YIFHNFMER | 0.000 | 0.366 | 0.000 | 0.000 | 0.157 | 0.000 | 0.477 | 0.000 | ||
| 3 spectra, QYTAAVGR | 0.000 | 0.482 | 0.000 | 0.000 | 0.105 | 0.000 | 0.413 | 0.000 | ||
| 3 spectra, FQTLSR | 0.000 | 0.349 | 0.031 | 0.000 | 0.159 | 0.105 | 0.356 | 0.000 | ||
| 3 spectra, TTFELIYQELLQR | 0.000 | 0.489 | 0.000 | 0.000 | 0.046 | 0.000 | 0.465 | 0.000 | ||
| 6 spectra, AVLSAVELLDK | 0.000 | 0.451 | 0.000 | 0.000 | 0.067 | 0.000 | 0.482 | 0.000 | ||
| 3 spectra, AHIQFKPTLSQQR | 0.000 | 0.378 | 0.000 | 0.000 | 0.000 | 0.000 | 0.622 | 0.000 | ||
| 4 spectra, LGMYELLLK | 0.000 | 0.476 | 0.000 | 0.000 | 0.057 | 0.000 | 0.467 | 0.000 | ||
| 2 spectra, LGDGLVGSR | 0.000 | 0.351 | 0.000 | 0.000 | 0.075 | 0.000 | 0.575 | 0.000 | ||
| 2 spectra, SNQAELLPSK | 0.000 | 0.493 | 0.000 | 0.000 | 0.010 | 0.000 | 0.497 | 0.000 | ||
| 4 spectra, VTISLLSLDDPQR | 0.000 | 0.472 | 0.000 | 0.000 | 0.042 | 0.000 | 0.486 | 0.000 | ||
| 1 spectrum, SGSMAGK | 0.000 | 0.478 | 0.000 | 0.000 | 0.000 | 0.172 | 0.350 | 0.000 | ||
| 7 spectra, NTQEAINGR | 0.000 | 0.515 | 0.000 | 0.000 | 0.064 | 0.084 | 0.338 | 0.000 | ||
| 2 spectra, TLFSVLPGLK | 0.000 | 0.384 | 0.000 | 0.000 | 0.051 | 0.000 | 0.565 | 0.000 | ||
| 6 spectra, GSEMVVAGK | 0.000 | 0.299 | 0.065 | 0.047 | 0.113 | 0.013 | 0.463 | 0.000 | ||
| 4 spectra, VLGIDYPATR | 0.000 | 0.366 | 0.000 | 0.000 | 0.099 | 0.000 | 0.535 | 0.000 | ||
| 1 spectrum, NVLFVIDK | 0.000 | 0.580 | 0.000 | 0.000 | 0.023 | 0.000 | 0.397 | 0.000 | ||
| 1 spectrum, VLDLPSLSSQDPAGPSLAMLPK | 0.000 | 0.364 | 0.000 | 0.000 | 0.035 | 0.069 | 0.532 | 0.000 | ||
| 8 spectra, FAHTVVTSR | 0.000 | 0.398 | 0.000 | 0.000 | 0.000 | 0.142 | 0.461 | 0.000 | ||
| 2 spectra, VRPEQLVK | 0.000 | 0.516 | 0.000 | 0.000 | 0.044 | 0.000 | 0.441 | 0.000 | ||
| 2 spectra, LSYQDGFPGTEISCWTVK | 0.000 | 0.215 | 0.000 | 0.175 | 0.000 | 0.000 | 0.610 | 0.000 | ||
| 4 spectra, EFQGPK | 0.000 | 0.242 | 0.000 | 0.000 | 0.108 | 0.117 | 0.533 | 0.000 | ||
| 2 spectra, ADTVQEATFQVELPR | 0.000 | 0.523 | 0.000 | 0.000 | 0.052 | 0.000 | 0.426 | 0.000 | ||
| 3 spectra, VVEQEGTTPEESPNPDHPR | 0.000 | 0.225 | 0.000 | 0.000 | 0.237 | 0.000 | 0.538 | 0.000 | ||
| 6 spectra, TPTTGSK | 0.000 | 0.304 | 0.000 | 0.000 | 0.112 | 0.000 | 0.584 | 0.000 | ||
| 10 spectra, AVDYASK | 0.000 | 0.452 | 0.000 | 0.000 | 0.018 | 0.000 | 0.530 | 0.000 | ||
| 4 spectra, LALDNGGLAR | 0.000 | 0.482 | 0.000 | 0.000 | 0.049 | 0.000 | 0.469 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
34 spectra |
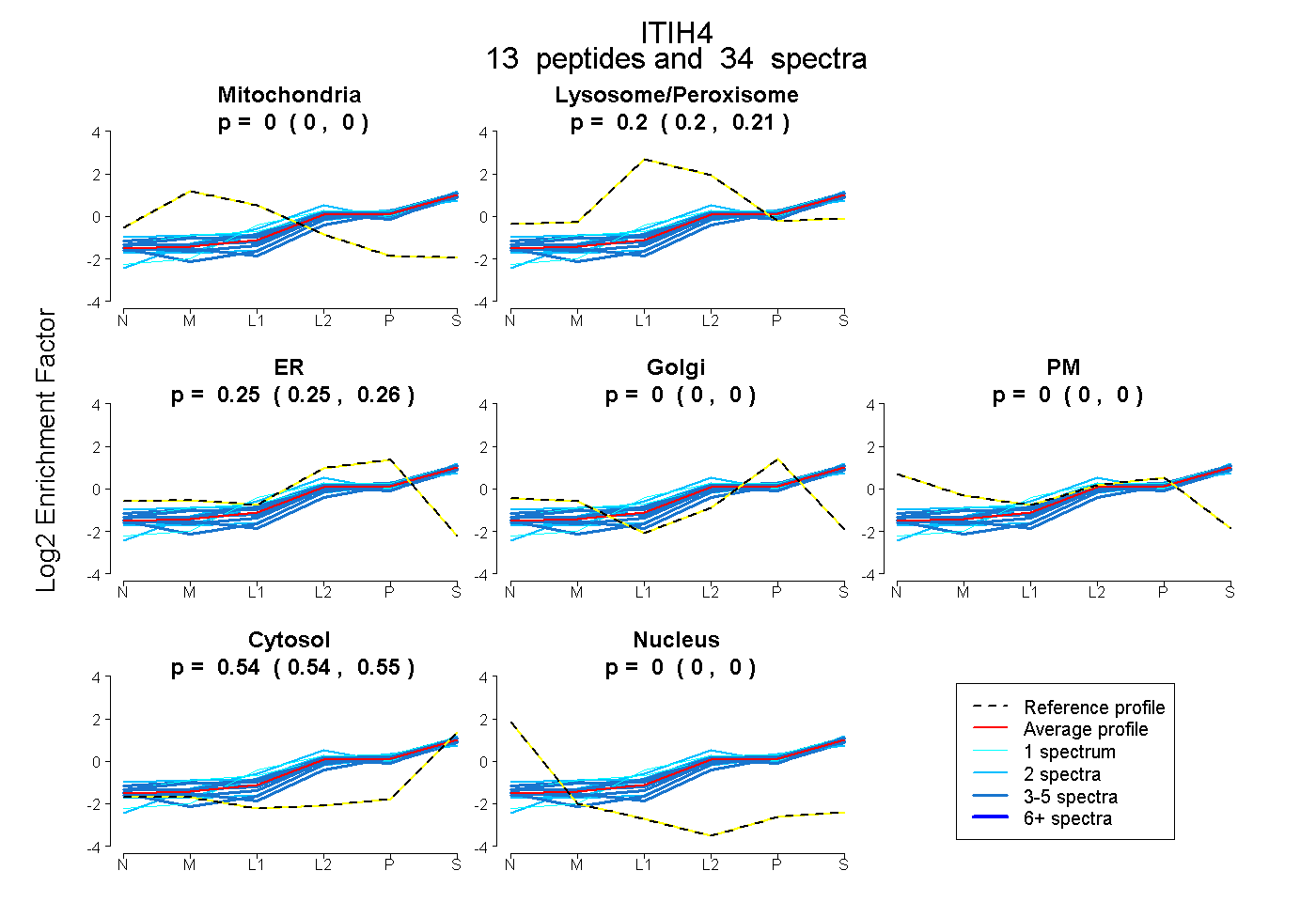 |
0.000 0.000 | 0.000 |
0.204 0.196 | 0.210 |
0.252 0.246 | 0.257 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.544 0.541 | 0.548 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
337 spectra |
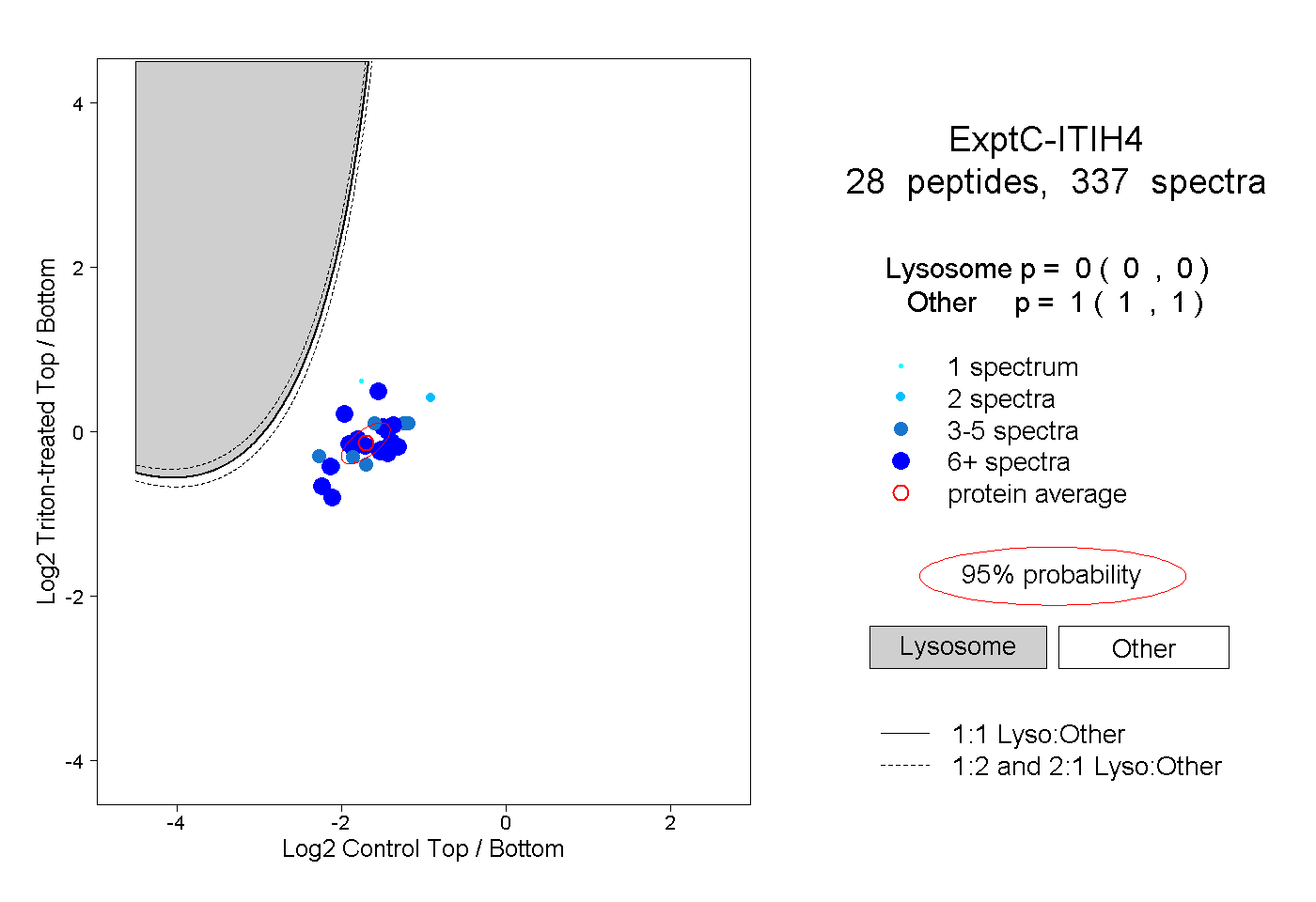 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
26 spectra |
 |
0.000 0.000 | 0.005 |
1.000 0.995 | 1.000 |