peptides
spectra
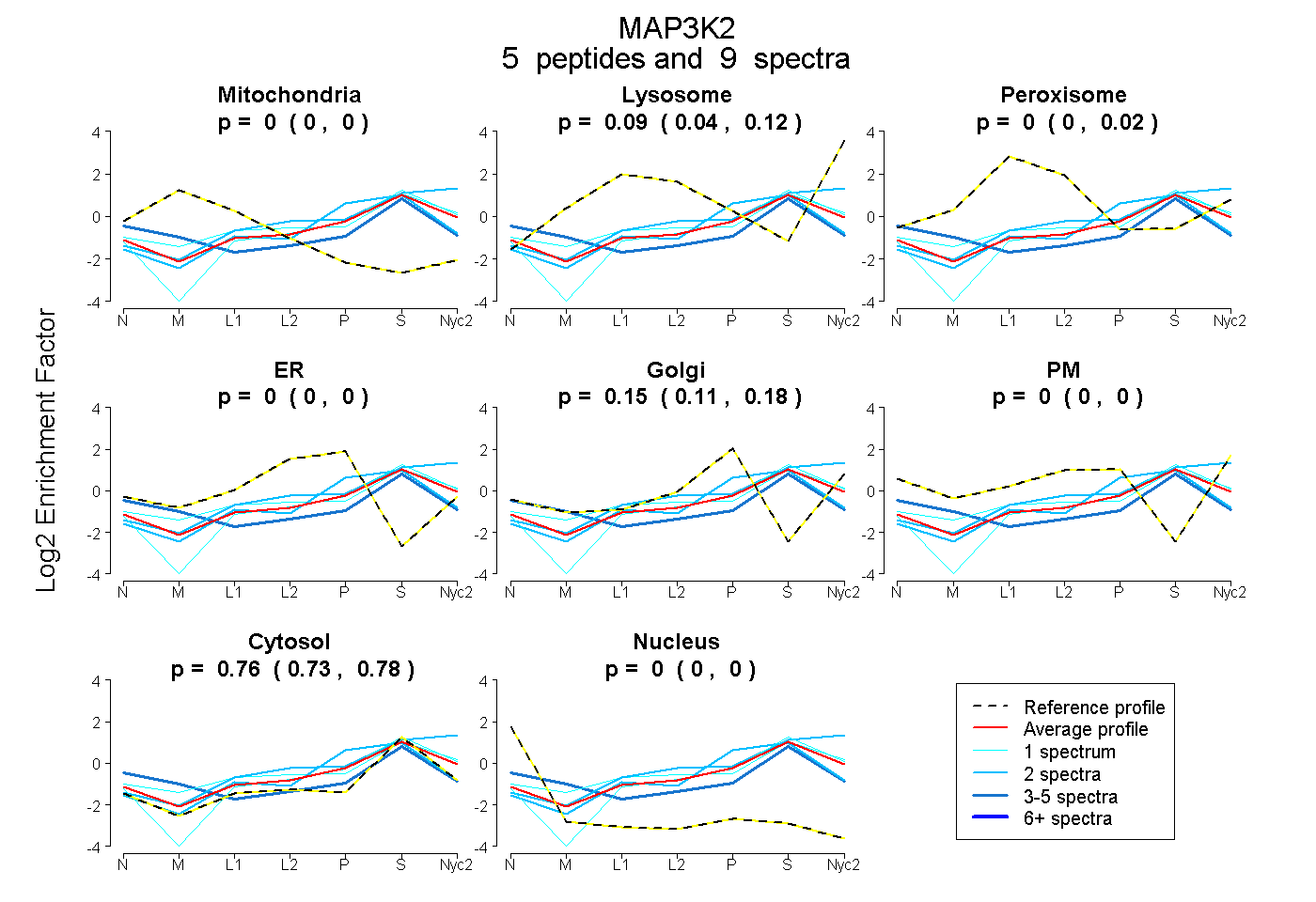
0.000 | 0.000
0.040 | 0.124
0.000 | 0.020
0.000 | 0.000
0.115 | 0.180
0.000 | 0.000
0.728 | 0.782
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
9 spectra |
 |
0.000 0.000 | 0.000 |
0.091 0.040 | 0.124 |
0.000 0.000 | 0.020 |
0.000 0.000 | 0.000 |
0.150 0.115 | 0.180 |
0.000 0.000 | 0.000 |
0.758 0.728 | 0.782 |
0.000 0.000 | 0.000 |
| 1 spectrum, LSVVGPPNR | 0.000 | 0.002 | 0.000 | 0.000 | 0.122 | 0.000 | 0.876 | 0.000 | ||
| 3 spectra, GADILR | 0.161 | 0.000 | 0.000 | 0.000 | 0.081 | 0.013 | 0.725 | 0.021 | ||
| 2 spectra, LLGQGAFGR | 0.000 | 0.329 | 0.000 | 0.000 | 0.015 | 0.000 | 0.656 | 0.000 | ||
| 1 spectrum, ILQVTRPVK | 0.000 | 0.152 | 0.059 | 0.000 | 0.028 | 0.052 | 0.708 | 0.000 | ||
| 2 spectra, IVQYYGCLR | 0.000 | 0.000 | 0.000 | 0.038 | 0.215 | 0.000 | 0.747 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
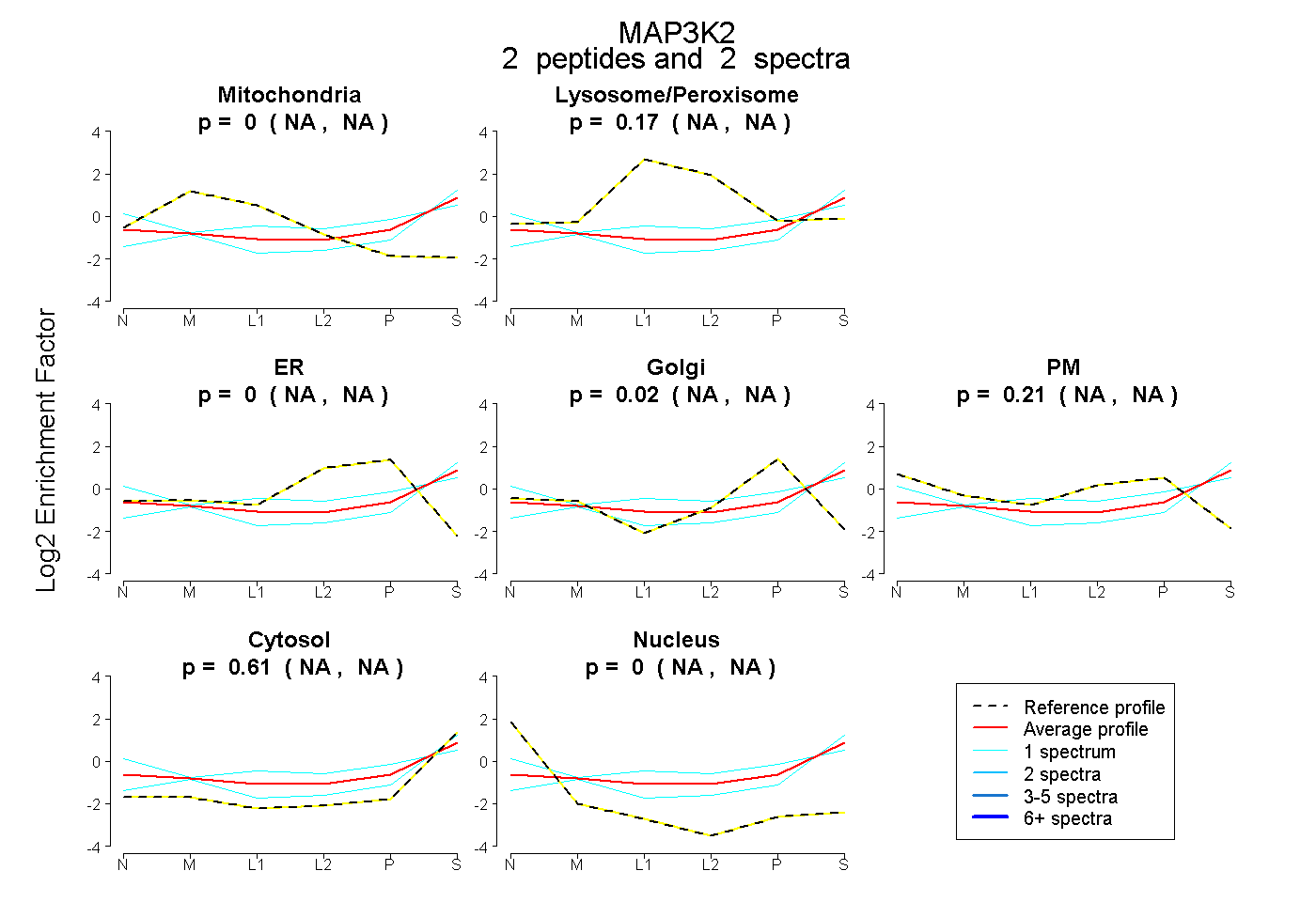 |
0.000 NA | NA |
0.169 NA | NA |
0.000 NA | NA |
0.016 NA | NA |
0.209 NA | NA |
0.606 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
5 spectra |
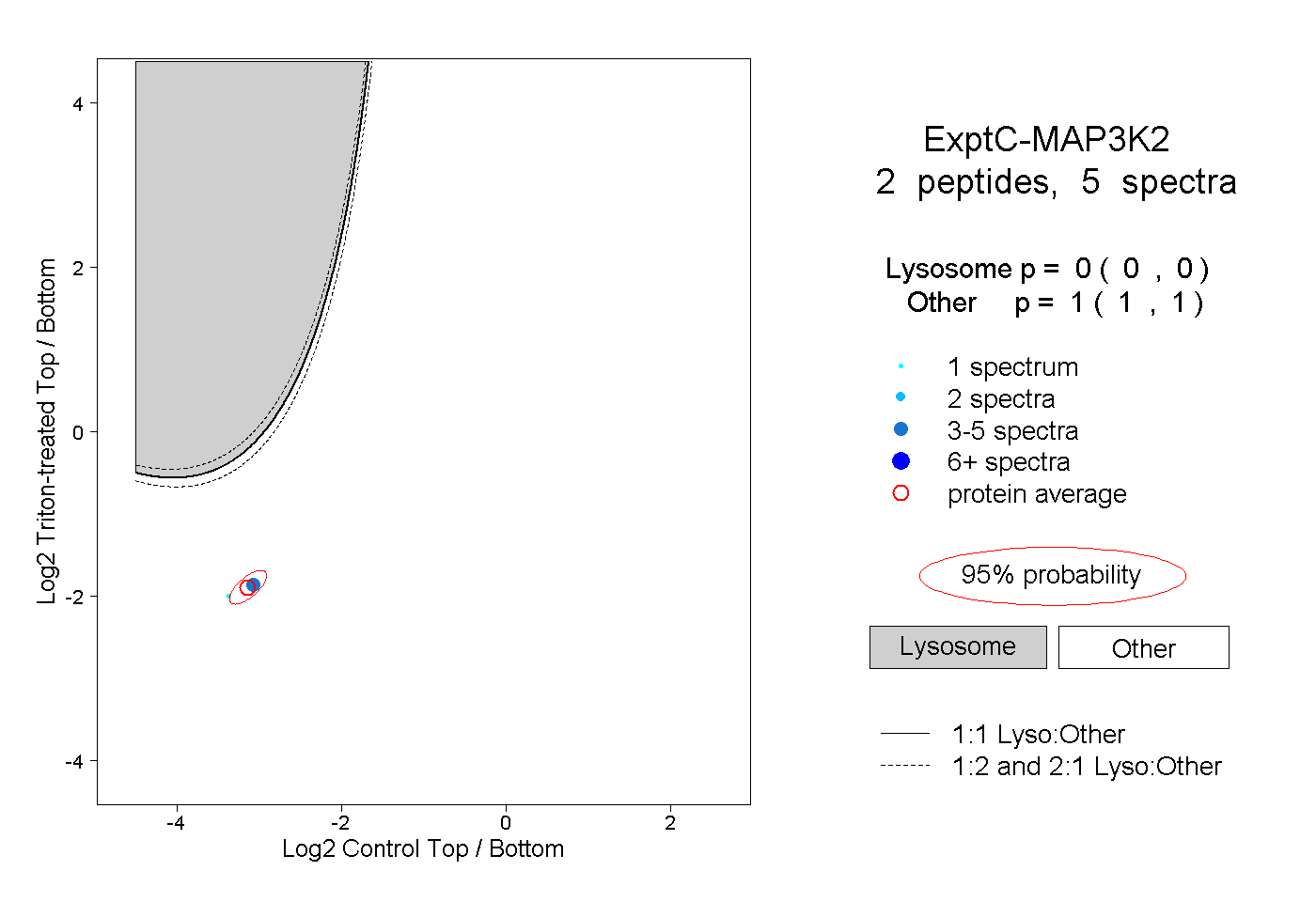 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |