peptides
spectra
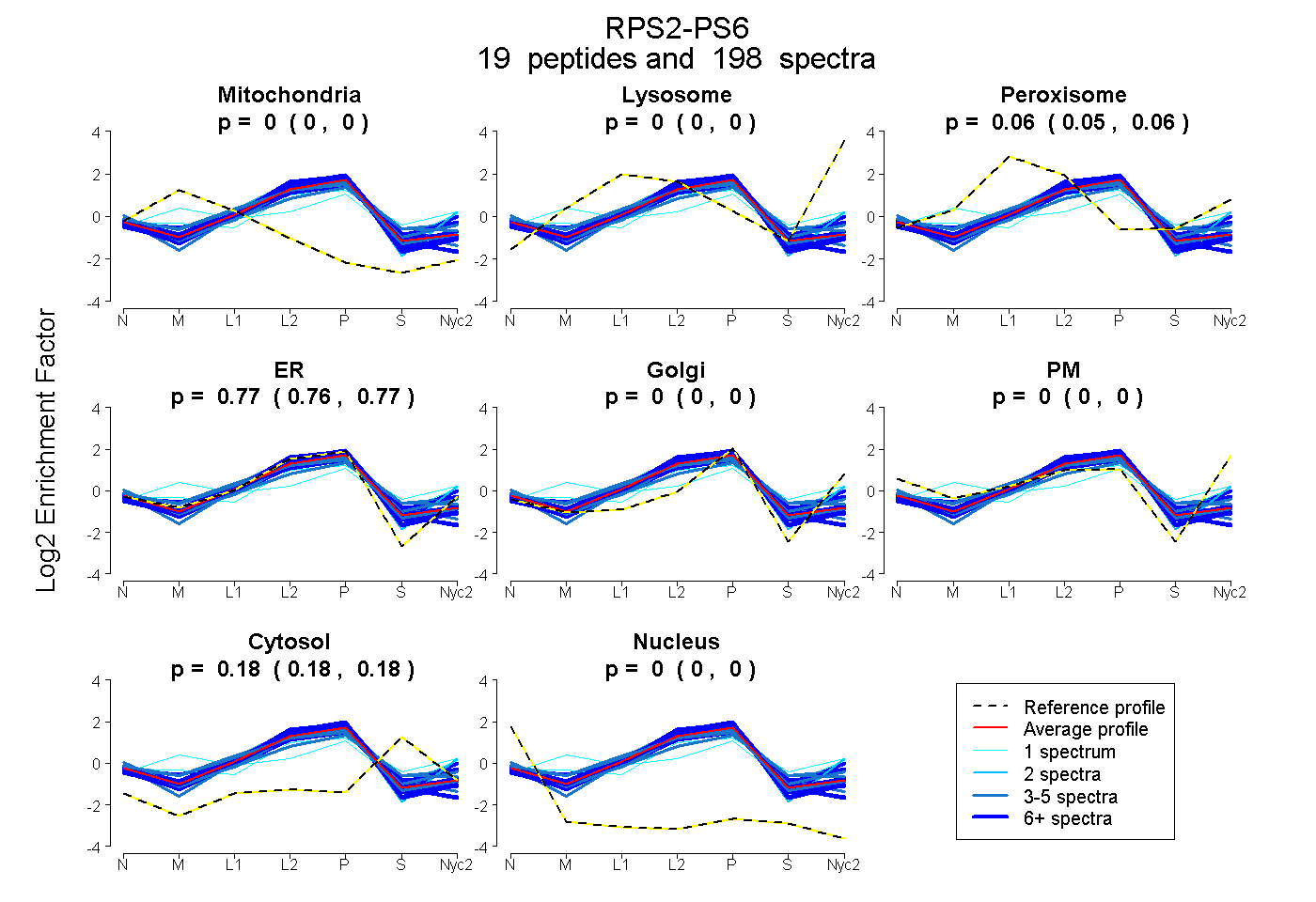
0.000 | 0.000
0.000 | 0.000
0.054 | 0.057
0.764 | 0.768
0.000 | 0.000
0.000 | 0.000
0.177 | 0.180
0.000 | 0.000
peptides
spectra
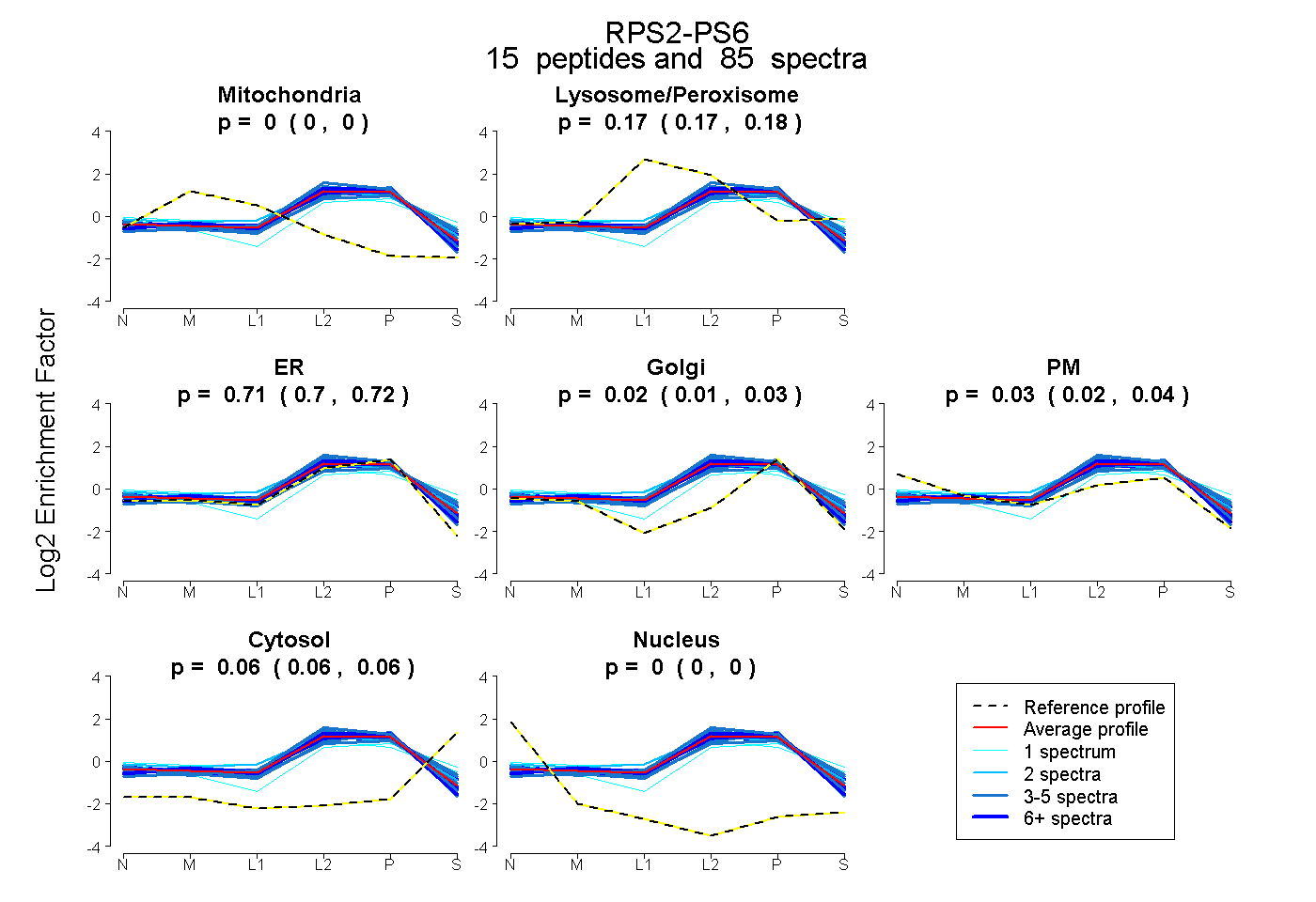
0.000 | 0.000
0.166 | 0.176
0.703 | 0.725
0.008 | 0.032
0.024 | 0.040
0.057 | 0.062
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
198 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.055 0.054 | 0.057 |
0.766 0.764 | 0.768 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.178 0.177 | 0.180 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
85 spectra |
 |
0.000 0.000 | 0.000 |
0.172 0.166 | 0.176 |
0.715 0.703 | 0.725 |
0.022 0.008 | 0.032 |
0.032 0.024 | 0.040 |
0.060 0.057 | 0.062 |
0.000 0.000 | 0.000 |
| 12 spectra, LSIVPVR | 0.000 | 0.132 | 0.811 | 0.000 | 0.024 | 0.033 | 0.000 | |||
| 1 spectrum, ETVFTK | 0.000 | 0.126 | 0.782 | 0.000 | 0.092 | 0.000 | 0.000 | |||
| 3 spectra, IMPVQK | 0.000 | 0.031 | 0.909 | 0.000 | 0.000 | 0.060 | 0.000 | |||
| 3 spectra, GCTATLGNFAK | 0.000 | 0.176 | 0.774 | 0.000 | 0.028 | 0.022 | 0.000 | |||
| 4 spectra, CGSVLVR | 0.000 | 0.214 | 0.729 | 0.000 | 0.000 | 0.057 | 0.000 | |||
| 10 spectra, SPYQEFTDHLVK | 0.000 | 0.147 | 0.785 | 0.000 | 0.000 | 0.068 | 0.000 | |||
| 1 spectrum, AFVAIGDYNGHVGLGVK | 0.000 | 0.367 | 0.167 | 0.168 | 0.226 | 0.072 | 0.000 | |||
| 1 spectrum, GAIILAK | 0.000 | 0.055 | 0.457 | 0.000 | 0.248 | 0.241 | 0.000 | |||
| 2 spectra, IGKPHTVPCK | 0.000 | 0.293 | 0.464 | 0.044 | 0.160 | 0.039 | 0.000 | |||
| 9 spectra, ATFDAISK | 0.000 | 0.226 | 0.579 | 0.171 | 0.000 | 0.024 | 0.000 | |||
| 10 spectra, EVATAIR | 0.000 | 0.203 | 0.617 | 0.000 | 0.084 | 0.096 | 0.000 | |||
| 3 spectra, TYSYLTPDLWK | 0.000 | 0.179 | 0.821 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, SLEEIYLFSLPIK | 0.000 | 0.206 | 0.524 | 0.140 | 0.000 | 0.131 | 0.000 | |||
| 3 spectra, GYWGNK | 0.000 | 0.229 | 0.640 | 0.000 | 0.000 | 0.131 | 0.000 | |||
| 20 spectra, LIPAPR | 0.000 | 0.147 | 0.774 | 0.062 | 0.000 | 0.017 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
36 spectra |
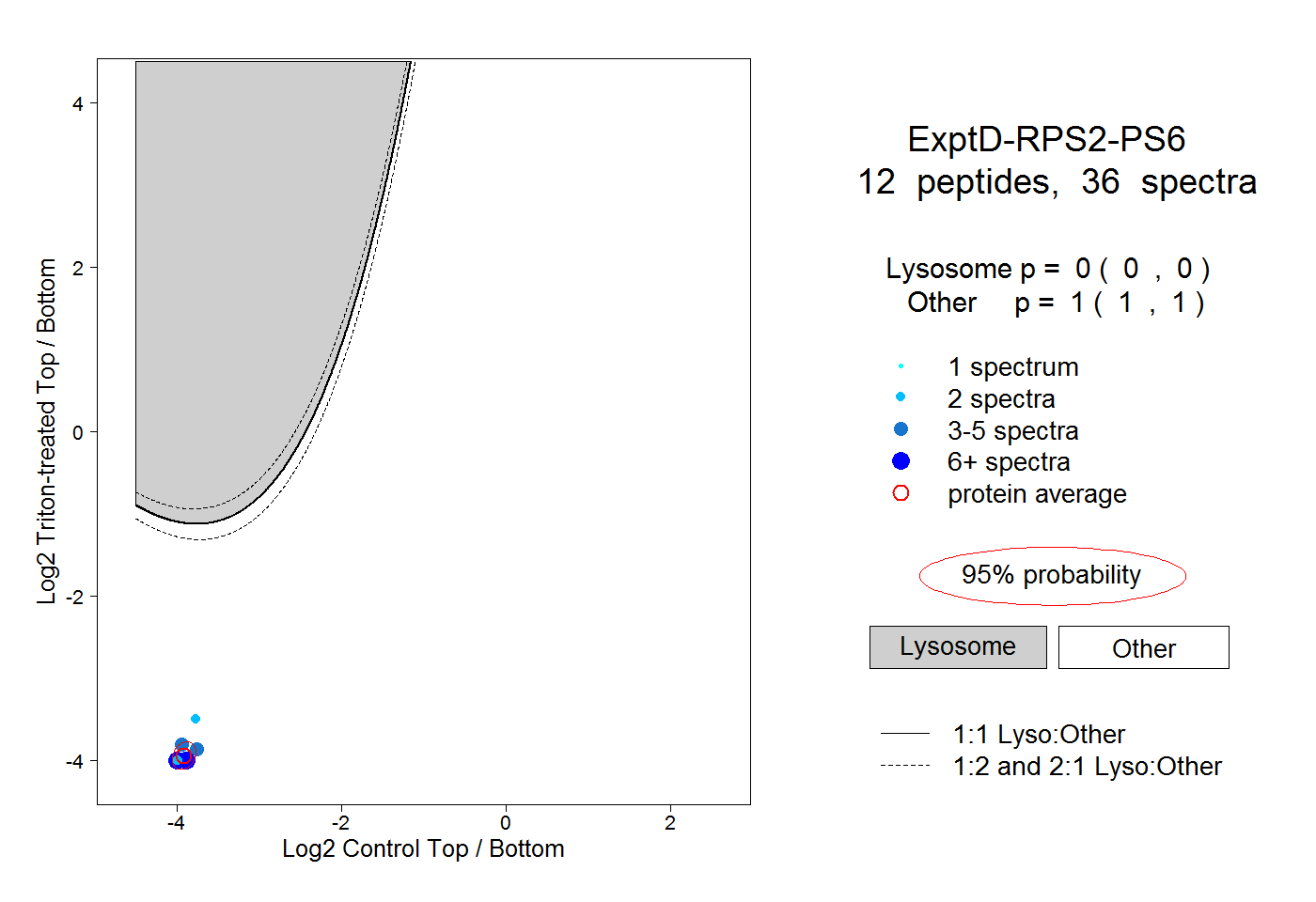 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |