peptides
spectra
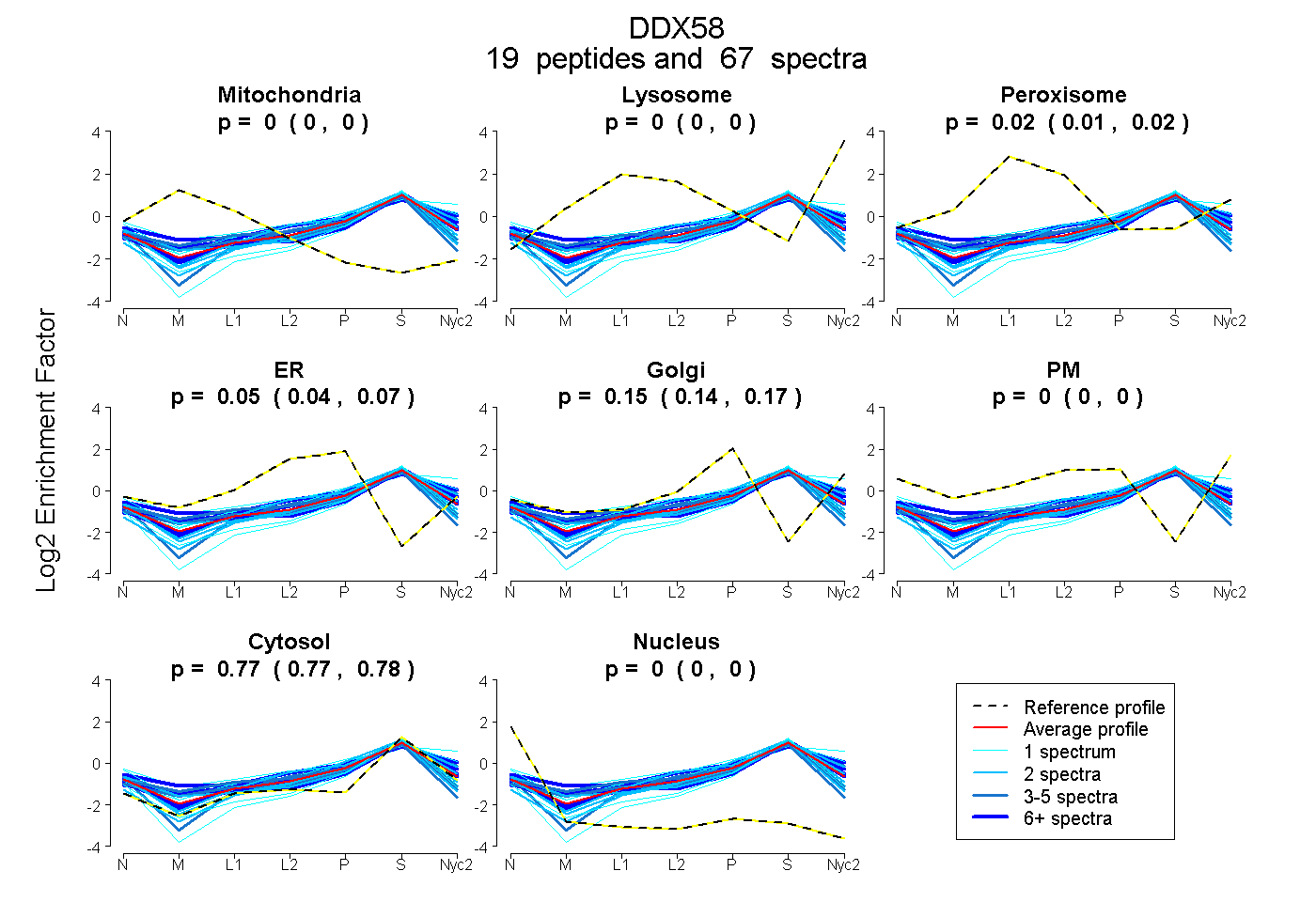
0.000 | 0.000
0.000 | 0.000
0.012 | 0.023
0.036 | 0.068
0.138 | 0.167
0.000 | 0.000
0.769 | 0.778
0.000 | 0.000
peptides
spectra
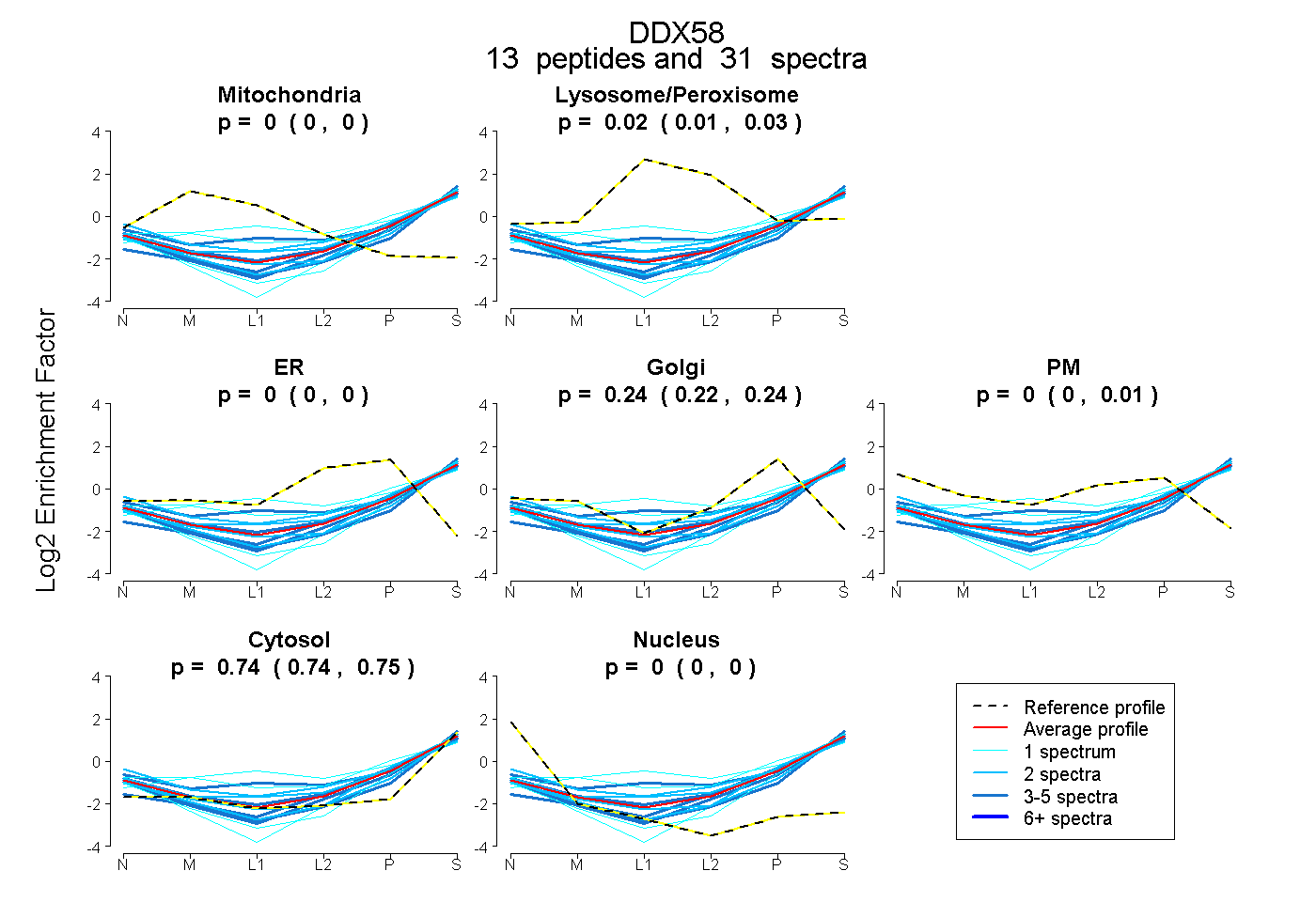
0.000 | 0.000
0.005 | 0.028
0.000 | 0.000
0.223 | 0.244
0.000 | 0.014
0.738 | 0.750
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
67 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.018 0.012 | 0.023 |
0.053 0.036 | 0.068 |
0.155 0.138 | 0.167 |
0.000 0.000 | 0.000 |
0.774 0.769 | 0.778 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
31 spectra |
 |
0.000 0.000 | 0.000 |
0.019 0.005 | 0.028 |
0.000 0.000 | 0.000 |
0.237 0.223 | 0.244 |
0.000 0.000 | 0.014 |
0.744 0.738 | 0.750 |
0.000 0.000 | 0.000 |
| 4 spectra, FFQIQNR | 0.000 | 0.000 | 0.000 | 0.184 | 0.000 | 0.816 | 0.000 | |||
| 1 spectrum, EAAFDETEQDLTR | 0.000 | 0.000 | 0.000 | 0.195 | 0.000 | 0.771 | 0.033 | |||
| 3 spectra, MVQCLLR | 0.000 | 0.000 | 0.000 | 0.072 | 0.000 | 0.928 | 0.000 | |||
| 5 spectra, AFFHDVR | 0.000 | 0.039 | 0.000 | 0.251 | 0.011 | 0.699 | 0.000 | |||
| 1 spectrum, VLQFALEK | 0.000 | 0.000 | 0.000 | 0.117 | 0.000 | 0.831 | 0.052 | |||
| 4 spectra, ALFLYTSHLR | 0.000 | 0.201 | 0.000 | 0.077 | 0.098 | 0.624 | 0.000 | |||
| 2 spectra, NFPHGQK | 0.000 | 0.104 | 0.000 | 0.193 | 0.000 | 0.703 | 0.000 | |||
| 1 spectrum, GPIEAASLFLR | 0.000 | 0.185 | 0.000 | 0.267 | 0.000 | 0.549 | 0.000 | |||
| 2 spectra, NTVICAPTGCGK | 0.000 | 0.040 | 0.000 | 0.000 | 0.320 | 0.640 | 0.000 | |||
| 1 spectrum, HHPYNQIMFR | 0.000 | 0.338 | 0.000 | 0.170 | 0.000 | 0.493 | 0.000 | |||
| 2 spectra, TFVSLLICEHHLK | 0.000 | 0.000 | 0.000 | 0.160 | 0.000 | 0.840 | 0.000 | |||
| 2 spectra, QNLQAFR | 0.000 | 0.000 | 0.000 | 0.236 | 0.000 | 0.764 | 0.000 | |||
| 3 spectra, FSELWLVDK | 0.000 | 0.000 | 0.000 | 0.249 | 0.000 | 0.751 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
79 spectra |
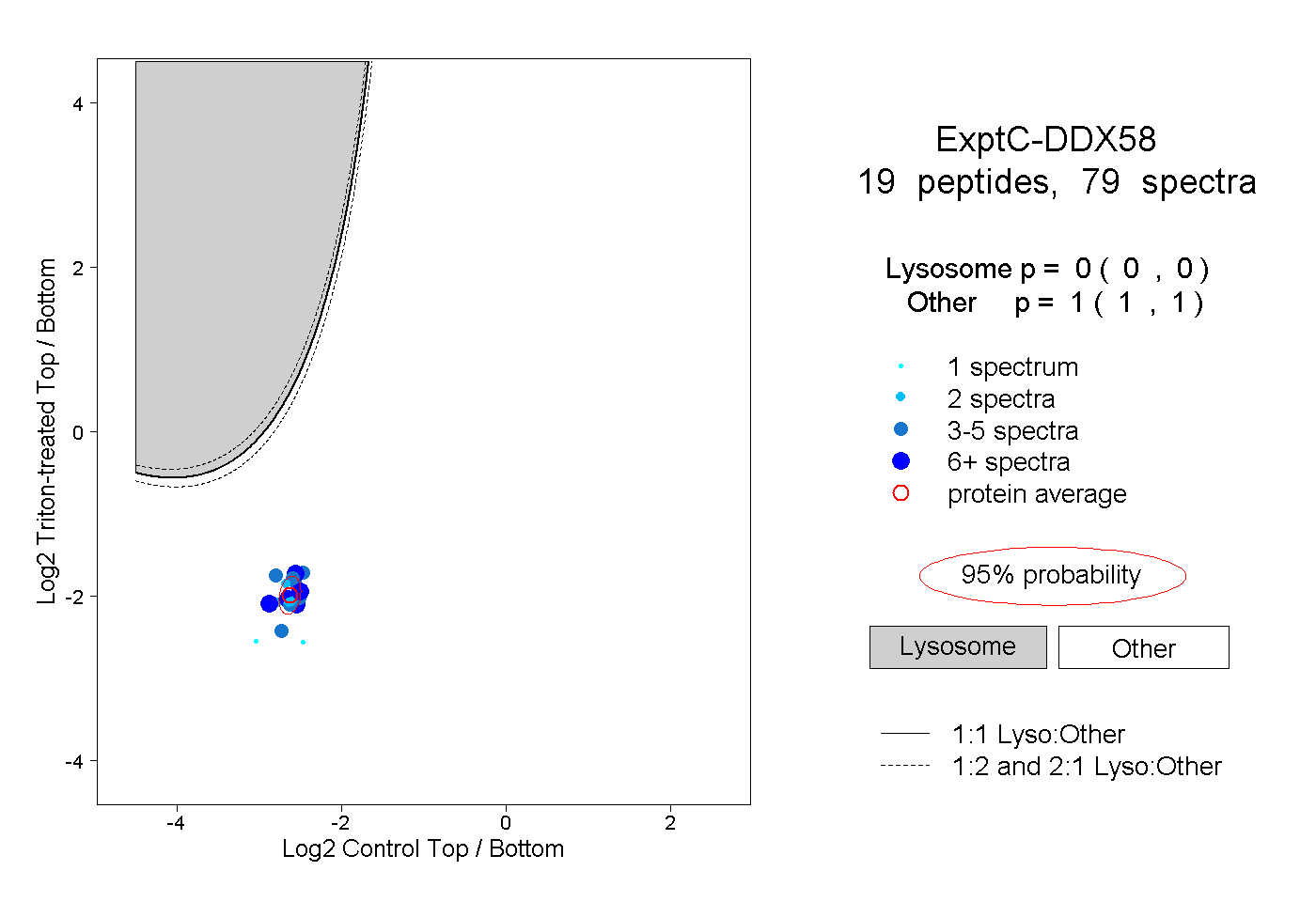 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
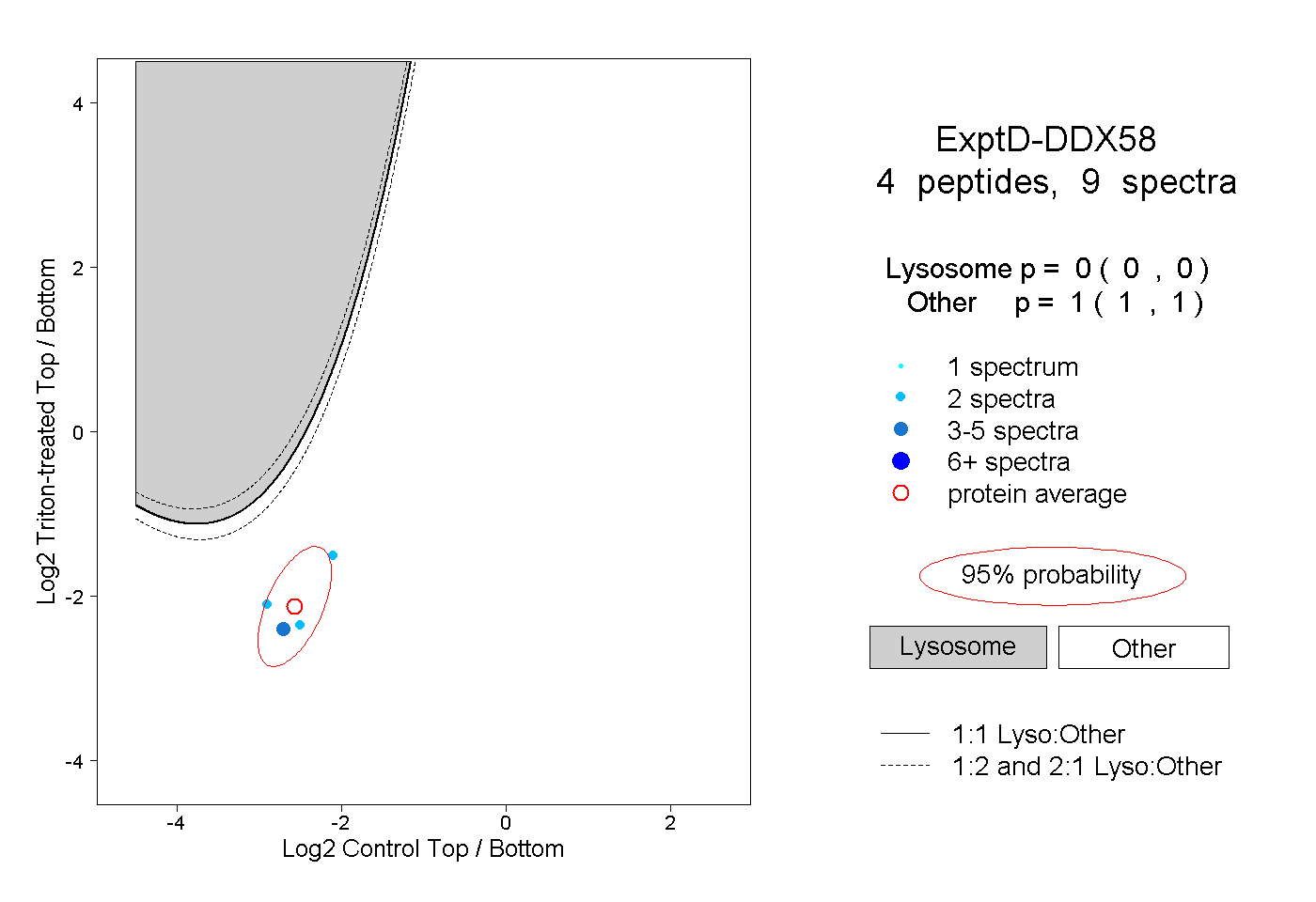 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |