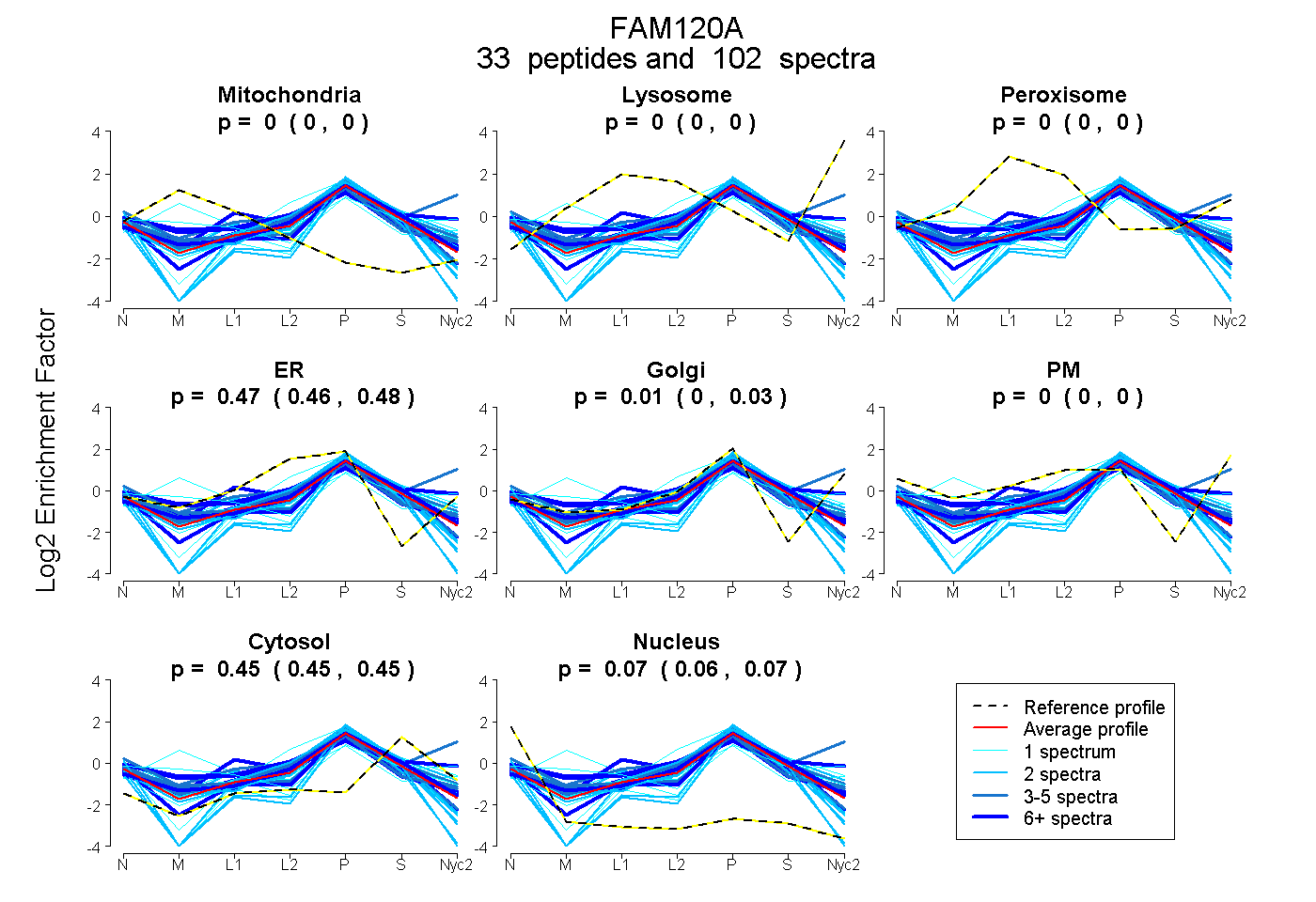
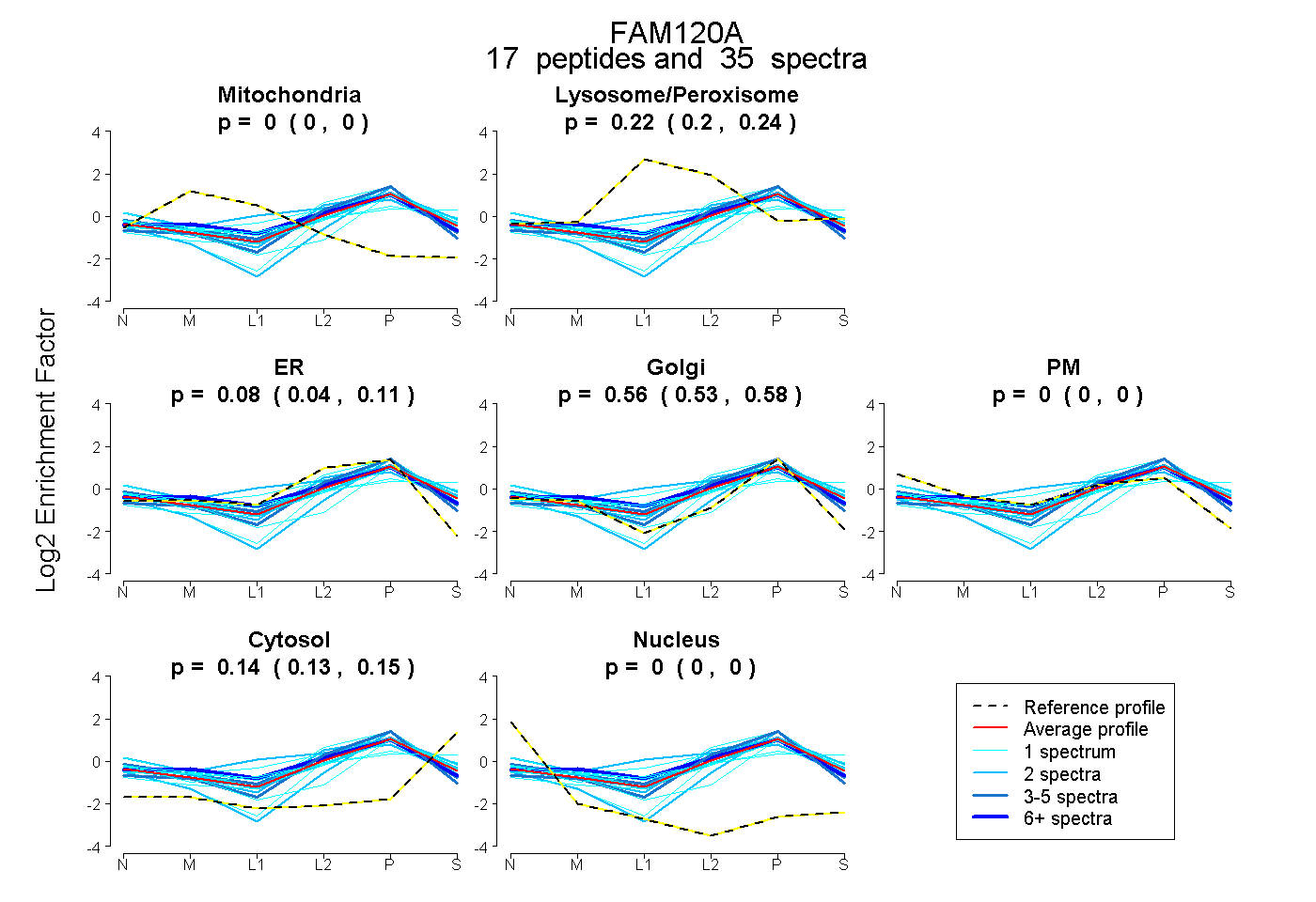
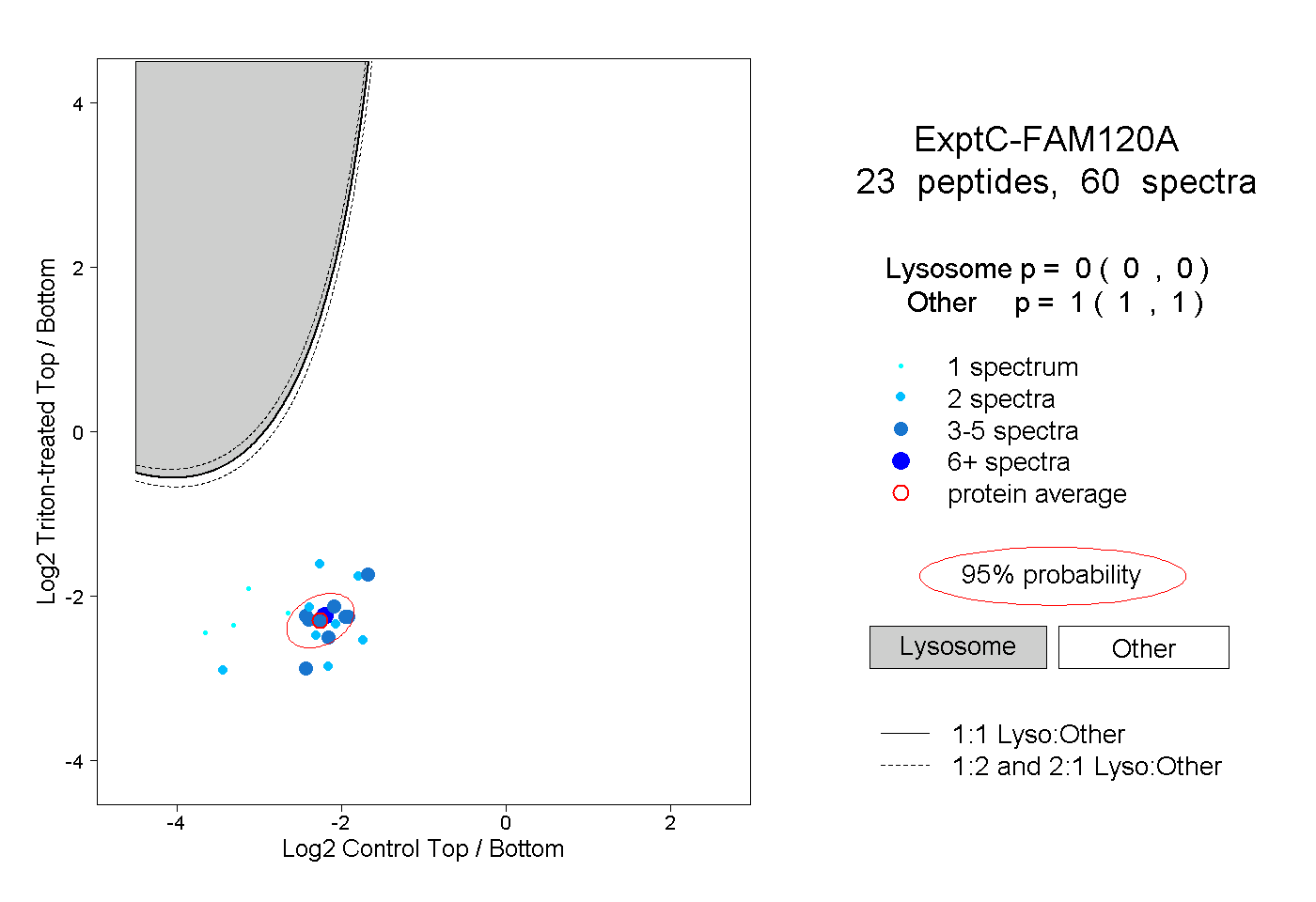
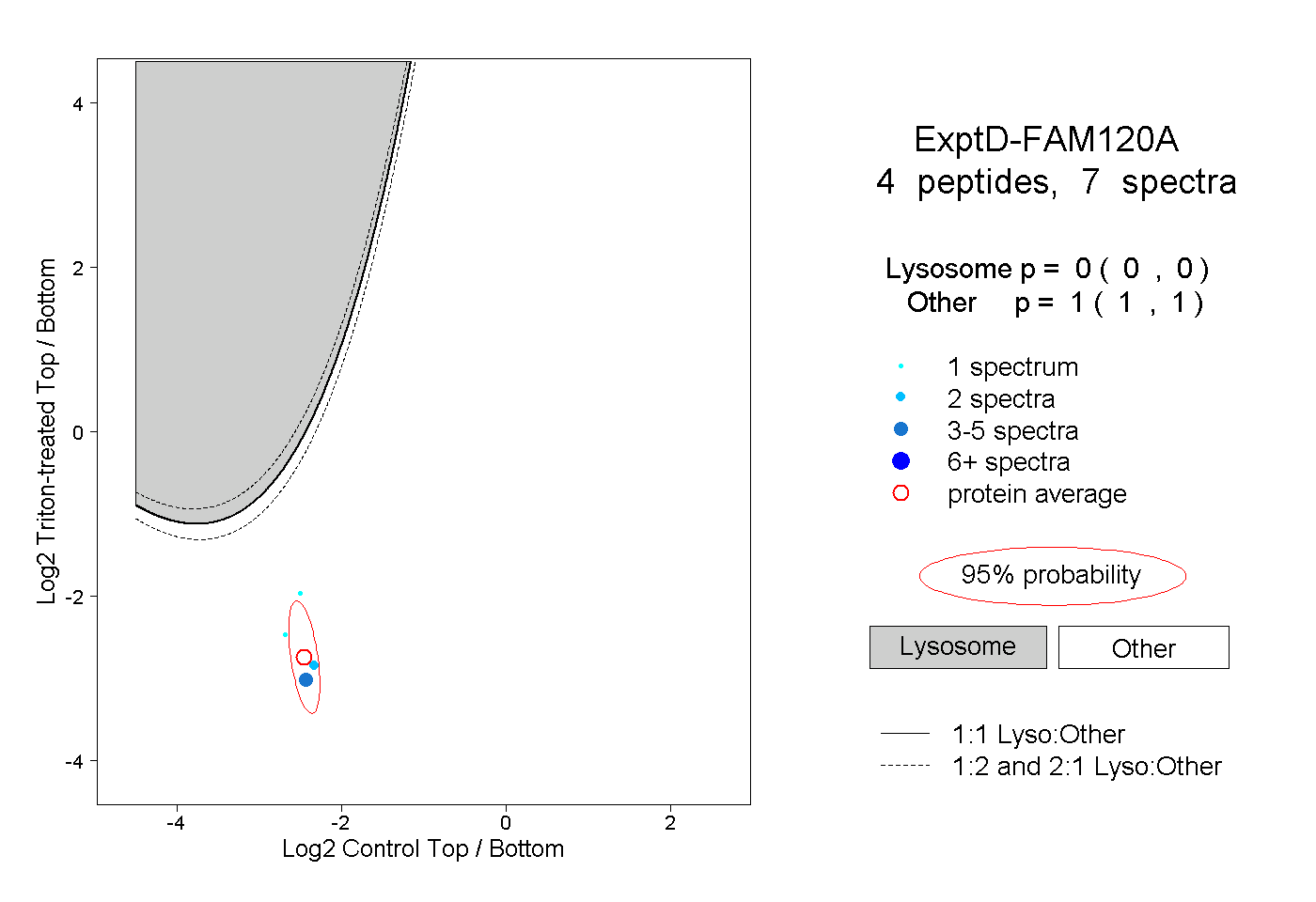
| 1 spectrum, SLTTSQYLMHEVAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, IENLDPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GSLVGGGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, EWAAYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QLDLNPNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GTPPPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, SPQTPELVEALAFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LYEPDQLQELK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AVADYVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LHEWVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SQGGVQPIPSQGGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QRPPQTPLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EWTCPNLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LLVDADNCLHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QSILEGLNFSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, GDPGDQVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QTAQQIVSHVQNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, AFLACMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GVISTPVIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VAQSIEDHHQEVIGFCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GLMYPYIFHVLTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, HTPLYER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LPPEFSPLIIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |