peptides
spectra
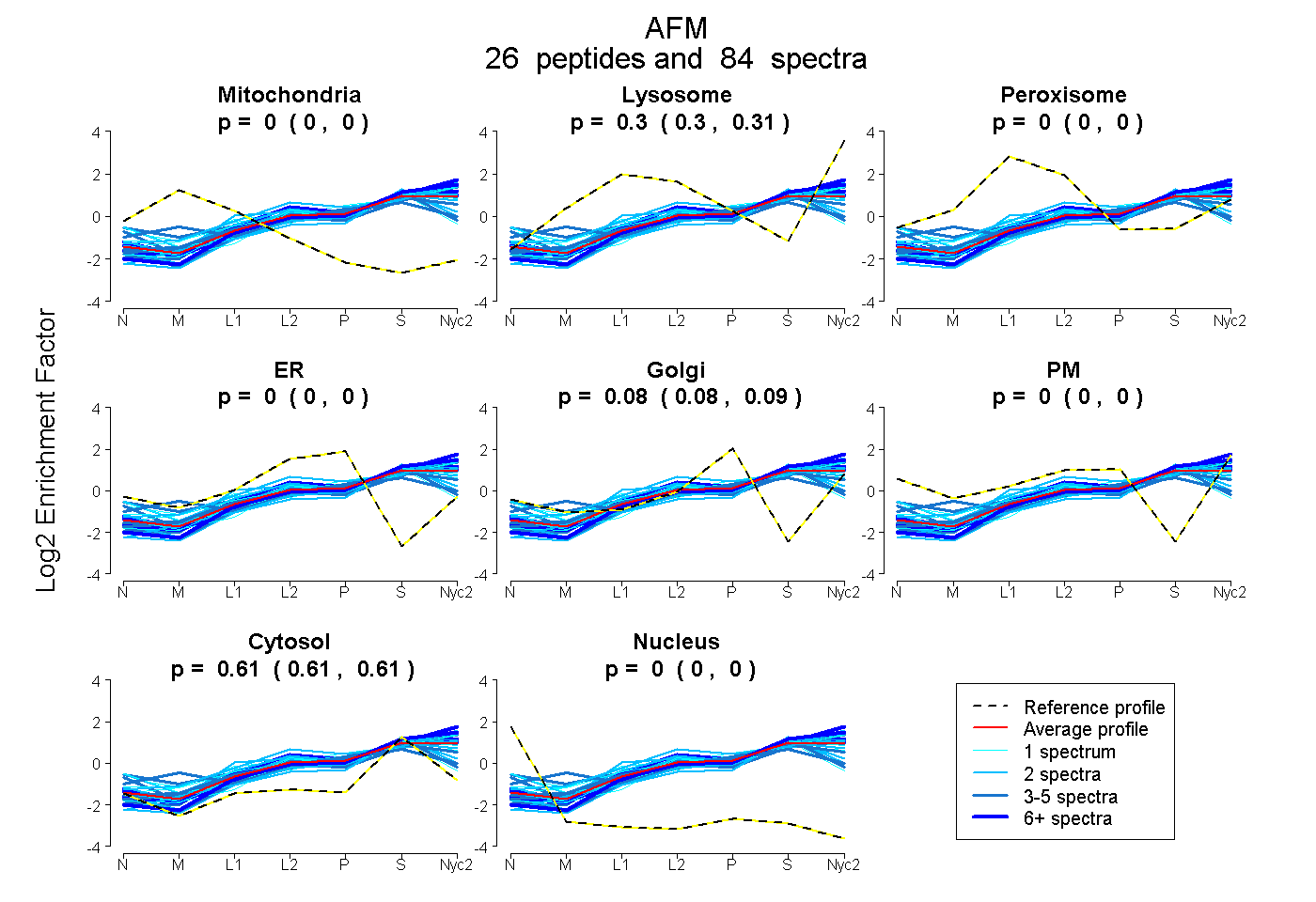
0.000 | 0.000
0.301 | 0.307
0.000 | 0.000
0.000 | 0.000
0.081 | 0.086
0.000 | 0.000
0.609 | 0.613
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
84 spectra |
 |
0.000 0.000 | 0.000 |
0.305 0.301 | 0.307 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.084 0.081 | 0.086 |
0.000 0.000 | 0.000 |
0.611 0.609 | 0.613 |
0.000 0.000 | 0.000 |
| 4 spectra, ATCFQDK | 0.000 | 0.311 | 0.000 | 0.000 | 0.000 | 0.156 | 0.533 | 0.000 | ||
| 4 spectra, ADFAFR | 0.000 | 0.324 | 0.000 | 0.000 | 0.034 | 0.000 | 0.642 | 0.000 | ||
| 2 spectra, VMLDYK | 0.000 | 0.307 | 0.000 | 0.000 | 0.011 | 0.000 | 0.682 | 0.000 | ||
| 1 spectrum, CLADSTLPECSK | 0.000 | 0.321 | 0.000 | 0.093 | 0.044 | 0.000 | 0.543 | 0.000 | ||
| 1 spectrum, NVCGALLK | 0.000 | 0.084 | 0.000 | 0.194 | 0.000 | 0.000 | 0.722 | 0.000 | ||
| 1 spectrum, NPLSCYR | 0.000 | 0.373 | 0.000 | 0.000 | 0.114 | 0.000 | 0.512 | 0.000 | ||
| 2 spectra, LCLFTK | 0.000 | 0.339 | 0.013 | 0.051 | 0.000 | 0.000 | 0.597 | 0.000 | ||
| 2 spectra, DDRPEDLSLR | 0.000 | 0.298 | 0.000 | 0.000 | 0.099 | 0.000 | 0.602 | 0.000 | ||
| 1 spectrum, QFQELGK | 0.000 | 0.231 | 0.000 | 0.000 | 0.000 | 0.219 | 0.550 | 0.000 | ||
| 8 spectra, FLVNLVK | 0.000 | 0.427 | 0.000 | 0.000 | 0.014 | 0.000 | 0.559 | 0.000 | ||
| 2 spectra, QAGFQR | 0.000 | 0.372 | 0.000 | 0.000 | 0.051 | 0.000 | 0.577 | 0.000 | ||
| 3 spectra, ANVGFLPPFPTLDPEEK | 0.000 | 0.244 | 0.000 | 0.000 | 0.087 | 0.099 | 0.570 | 0.000 | ||
| 4 spectra, AAPQLPMEELVSLSK | 0.000 | 0.382 | 0.000 | 0.000 | 0.000 | 0.000 | 0.618 | 0.000 | ||
| 3 spectra, SLAMVQQECK | 0.000 | 0.266 | 0.000 | 0.004 | 0.133 | 0.000 | 0.596 | 0.000 | ||
| 2 spectra, TLNSINIAVFSK | 0.000 | 0.462 | 0.000 | 0.000 | 0.080 | 0.000 | 0.458 | 0.000 | ||
| 5 spectra, LCFFYNK | 0.000 | 0.115 | 0.000 | 0.132 | 0.000 | 0.000 | 0.753 | 0.000 | ||
| 4 spectra, TINPTVDHCCR | 0.009 | 0.089 | 0.117 | 0.000 | 0.255 | 0.000 | 0.530 | 0.000 | ||
| 4 spectra, IANDAIQDMLCDMK | 0.000 | 0.316 | 0.000 | 0.000 | 0.078 | 0.000 | 0.606 | 0.000 | ||
| 6 spectra, ALSSYQR | 0.000 | 0.325 | 0.000 | 0.000 | 0.072 | 0.000 | 0.603 | 0.000 | ||
| 1 spectrum, RPCFEHLK | 0.000 | 0.266 | 0.000 | 0.000 | 0.082 | 0.000 | 0.652 | 0.000 | ||
| 2 spectra, DLLEDCCNR | 0.000 | 0.162 | 0.000 | 0.000 | 0.016 | 0.000 | 0.822 | 0.000 | ||
| 7 spectra, FTDSENVCQER | 0.000 | 0.292 | 0.000 | 0.000 | 0.098 | 0.000 | 0.610 | 0.000 | ||
| 2 spectra, ADWCQPLK | 0.000 | 0.192 | 0.000 | 0.055 | 0.011 | 0.000 | 0.742 | 0.000 | ||
| 10 spectra, WMPEITDEER | 0.000 | 0.347 | 0.000 | 0.000 | 0.000 | 0.000 | 0.653 | 0.000 | ||
| 1 spectrum, AAPITQYLK | 0.000 | 0.319 | 0.000 | 0.000 | 0.082 | 0.091 | 0.507 | 0.000 | ||
| 2 spectra, HTELSTPELLR | 0.000 | 0.253 | 0.000 | 0.000 | 0.000 | 0.212 | 0.535 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
20 spectra |
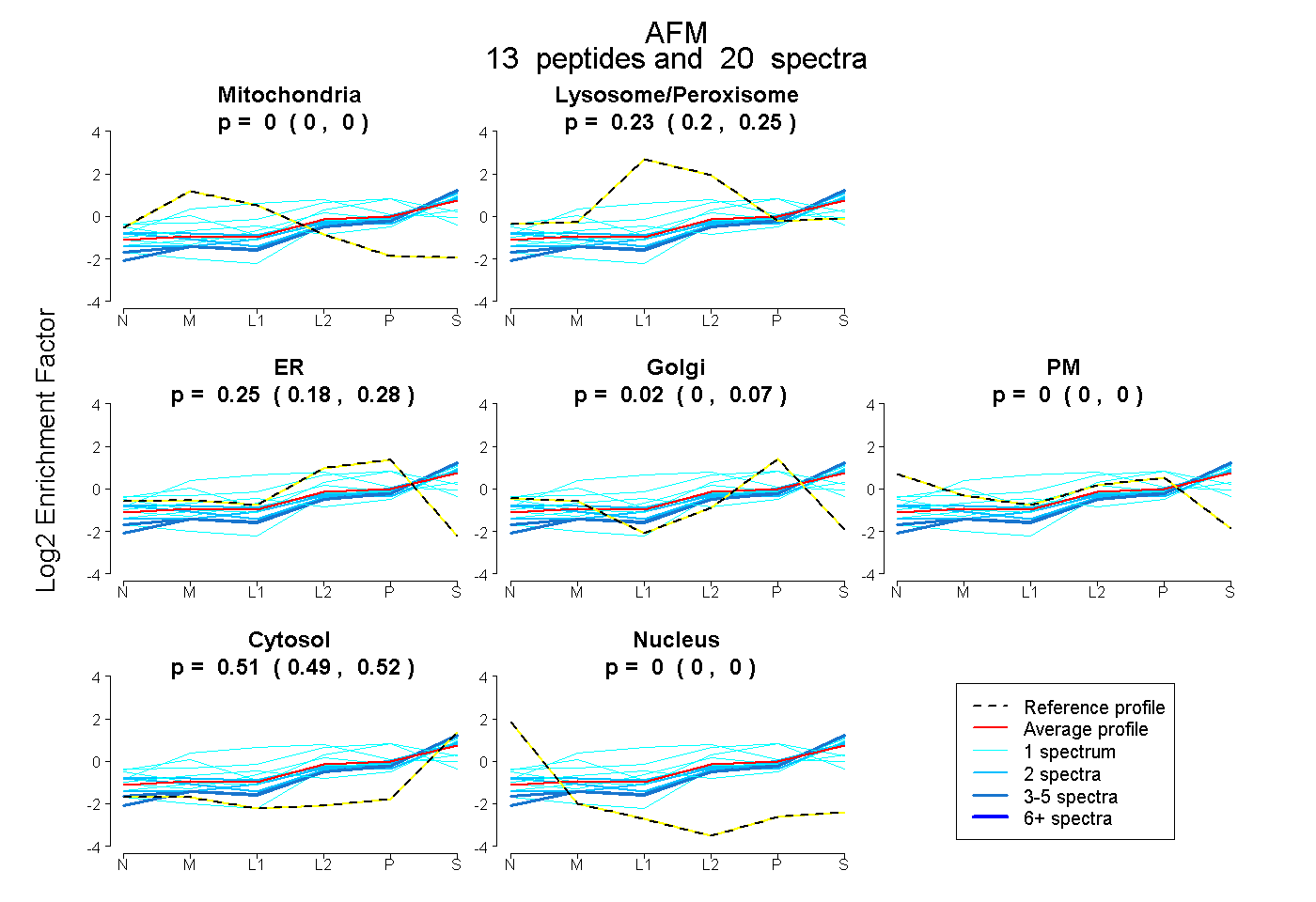 |
0.000 0.000 | 0.000 |
0.225 0.204 | 0.251 |
0.247 0.175 | 0.277 |
0.019 0.000 | 0.072 |
0.000 0.000 | 0.000 |
0.509 0.488 | 0.521 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
111 spectra |
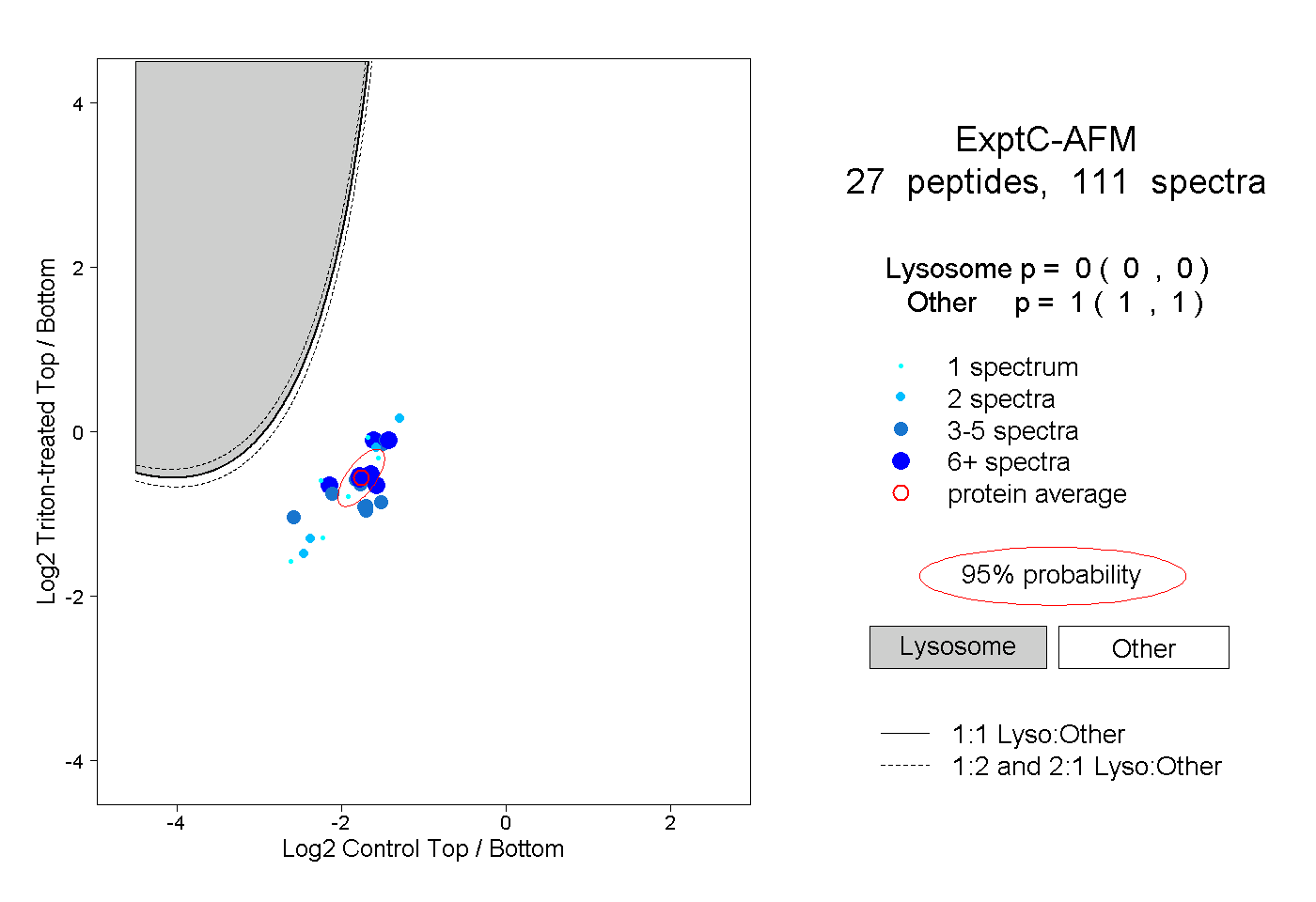 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
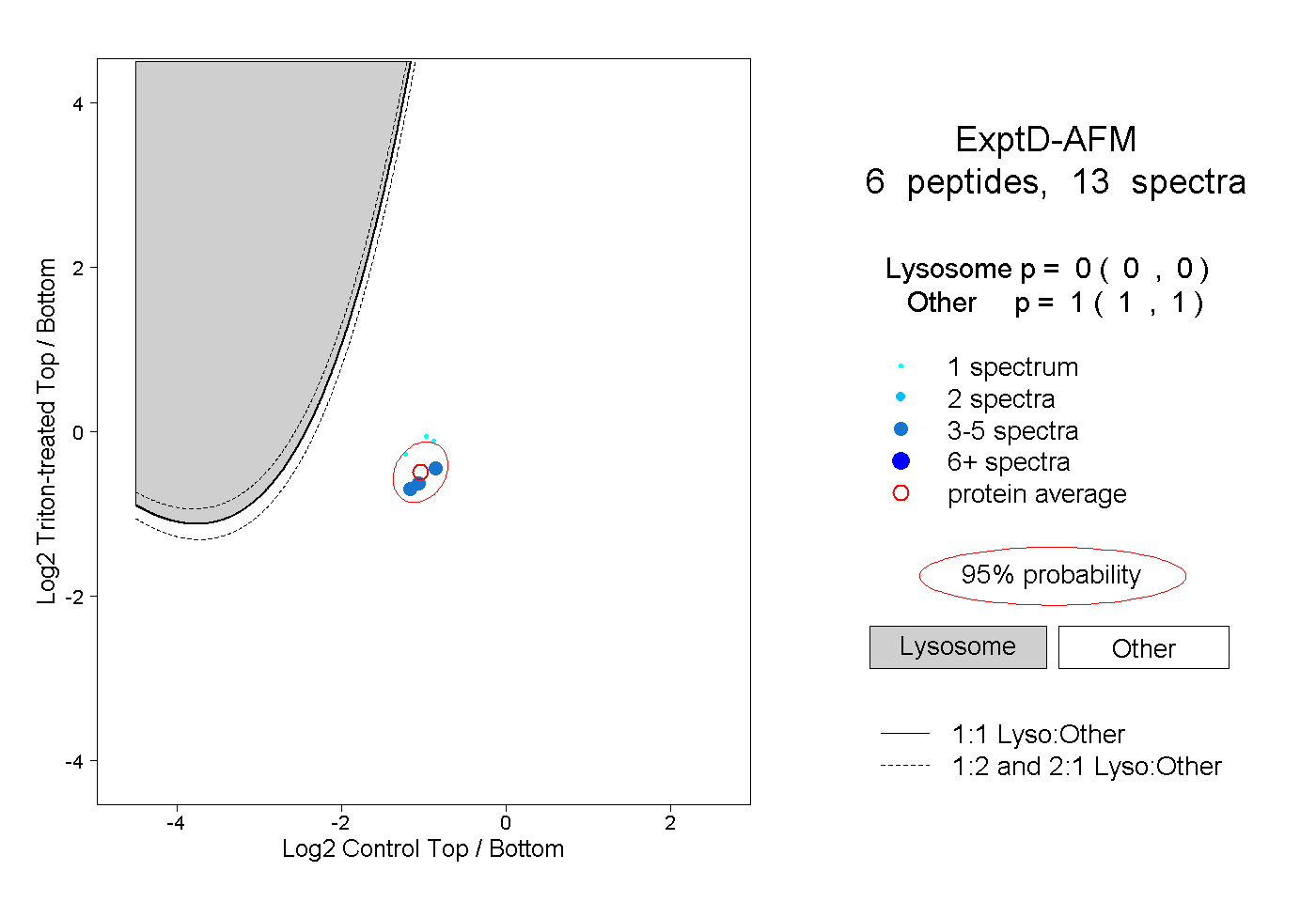 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |