peptides
spectra
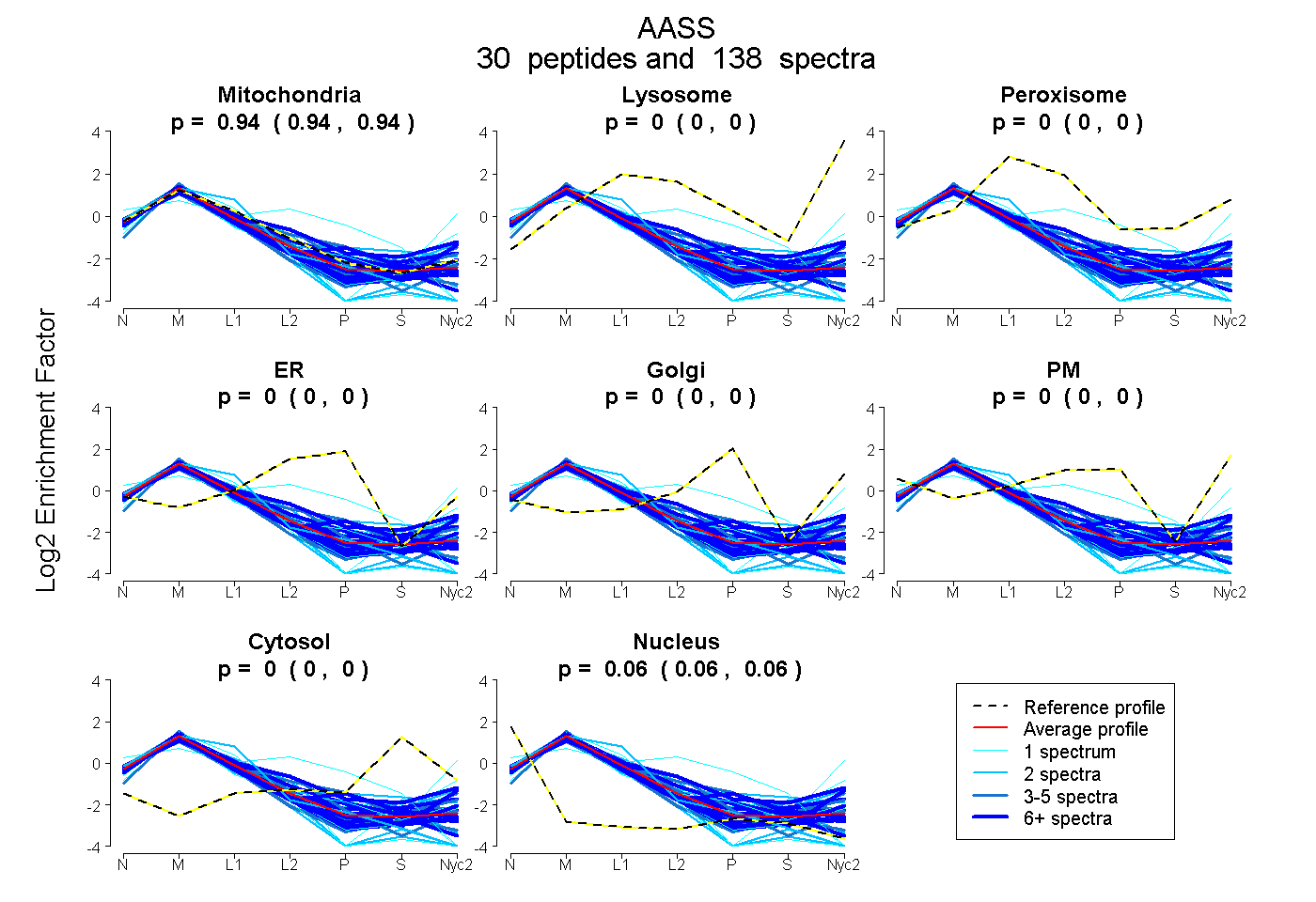
0.936 | 0.939
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.061 | 0.064
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
138 spectra |
 |
0.937 0.936 | 0.939 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.063 0.061 | 0.064 |
| 1 spectrum, AEGIVFNTQSTIK | 0.780 | 0.217 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.003 | ||
| 2 spectra, ETYPALRPEANPLTWK | 0.811 | 0.016 | 0.000 | 0.000 | 0.133 | 0.000 | 0.039 | 0.000 | ||
| 2 spectra, DLGATIESYVSYCGGLPAPEHSDNPLR | 0.835 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.165 | ||
| 12 spectra, VLIQPSNR | 0.913 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.087 | ||
| 9 spectra, LSYGPEEK | 0.912 | 0.042 | 0.000 | 0.000 | 0.046 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, NSSQAVQAVR | 0.936 | 0.000 | 0.000 | 0.012 | 0.000 | 0.000 | 0.000 | 0.053 | ||
| 2 spectra, YAEIYGISSAHTLLR | 0.921 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.079 | ||
| 1 spectrum, GAQEVFNELPCEYVEPHELK | 0.917 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.083 | ||
| 1 spectrum, LIDYEK | 0.916 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.084 | ||
| 1 spectrum, ACIDSK | 0.790 | 0.158 | 0.000 | 0.000 | 0.003 | 0.000 | 0.000 | 0.049 | ||
| 4 spectra, GNNIEITLGSDMTNQMQQLSK | 0.964 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.014 | 0.022 | ||
| 1 spectrum, SIGPLTFVFTGTGNVSK | 0.847 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.153 | ||
| 7 spectra, MLLDGEIETK | 0.889 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.111 | ||
| 5 spectra, IQFLSMSTK | 0.809 | 0.000 | 0.000 | 0.118 | 0.000 | 0.000 | 0.000 | 0.073 | ||
| 1 spectrum, TIDLVVYGDFNGFSAMAK | 0.635 | 0.000 | 0.000 | 0.274 | 0.000 | 0.000 | 0.005 | 0.086 | ||
| 4 spectra, DSFGIR | 0.851 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.149 | ||
| 2 spectra, ALNGFVK | 0.796 | 0.000 | 0.000 | 0.000 | 0.047 | 0.000 | 0.150 | 0.008 | ||
| 1 spectrum, TDGVYDPVEYEK | 0.915 | 0.000 | 0.000 | 0.000 | 0.041 | 0.000 | 0.000 | 0.044 | ||
| 2 spectra, AGGILQEDITEACLILGVK | 0.823 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.177 | ||
| 6 spectra, QLLCDLVGISR | 0.873 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.127 | ||
| 3 spectra, AQEANMSLLDEVLK | 0.951 | 0.003 | 0.000 | 0.000 | 0.000 | 0.000 | 0.031 | 0.014 | ||
| 9 spectra, TYAFFSHTIK | 0.955 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.045 | ||
| 3 spectra, DMIVMR | 0.936 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.064 | ||
| 3 spectra, EIYGPILER | 0.895 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.052 | 0.053 | ||
| 8 spectra, VYGTVLSR | 0.864 | 0.000 | 0.000 | 0.000 | 0.034 | 0.000 | 0.004 | 0.098 | ||
| 2 spectra, DAGYEISLGLMPK | 0.933 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.067 | ||
| 11 spectra, VNMVTASYITPAMK | 0.773 | 0.085 | 0.000 | 0.000 | 0.000 | 0.059 | 0.084 | 0.000 | ||
| 12 spectra, LGLLGGR | 0.892 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.108 | ||
| 11 spectra, EDVNAWER | 0.928 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.028 | 0.043 | ||
| 8 spectra, GLMGPFSK | 0.919 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.081 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
59 spectra |
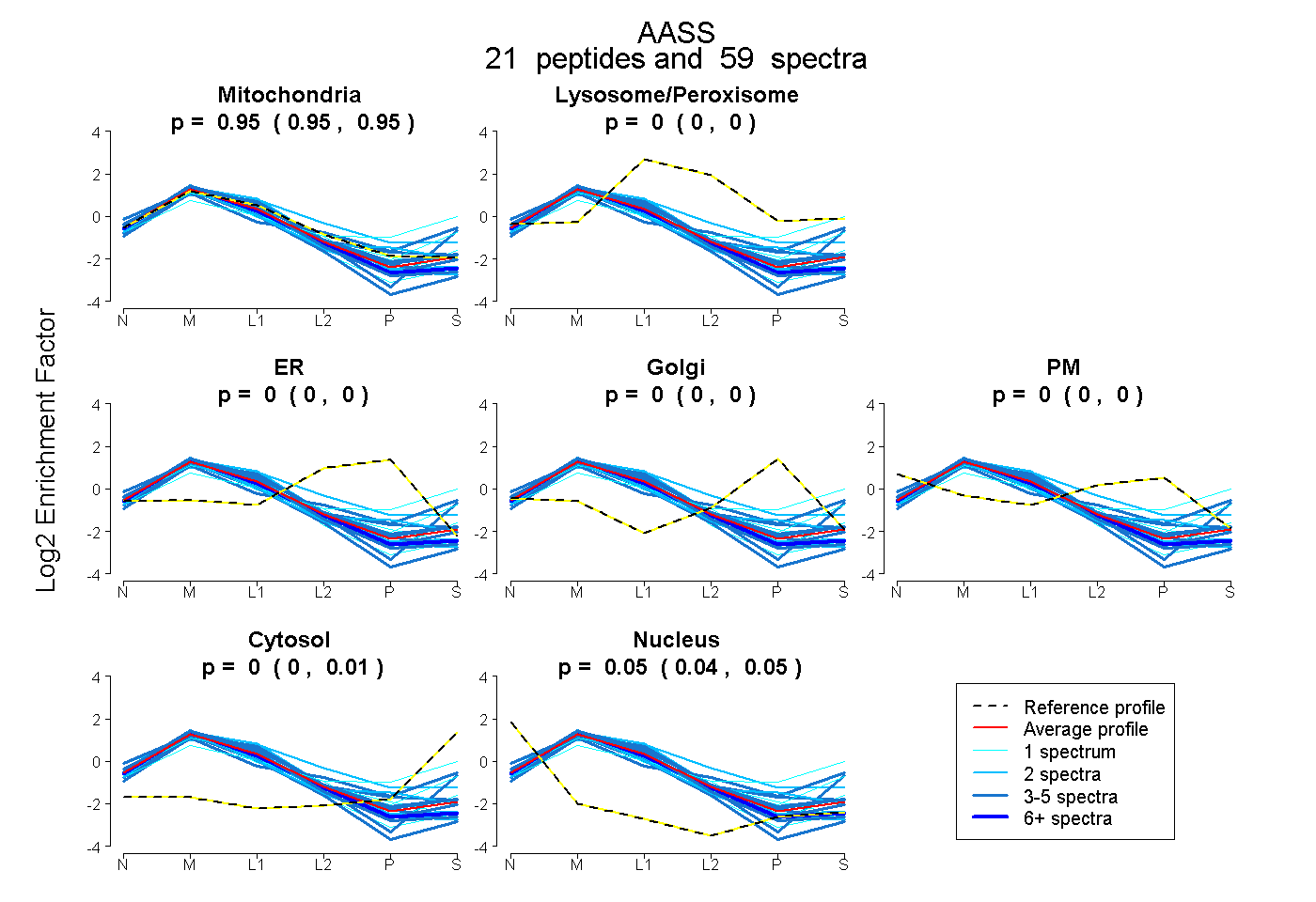 |
0.951 0.947 | 0.953 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.001 0.000 | 0.007 |
0.048 0.043 | 0.050 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
600 spectra |
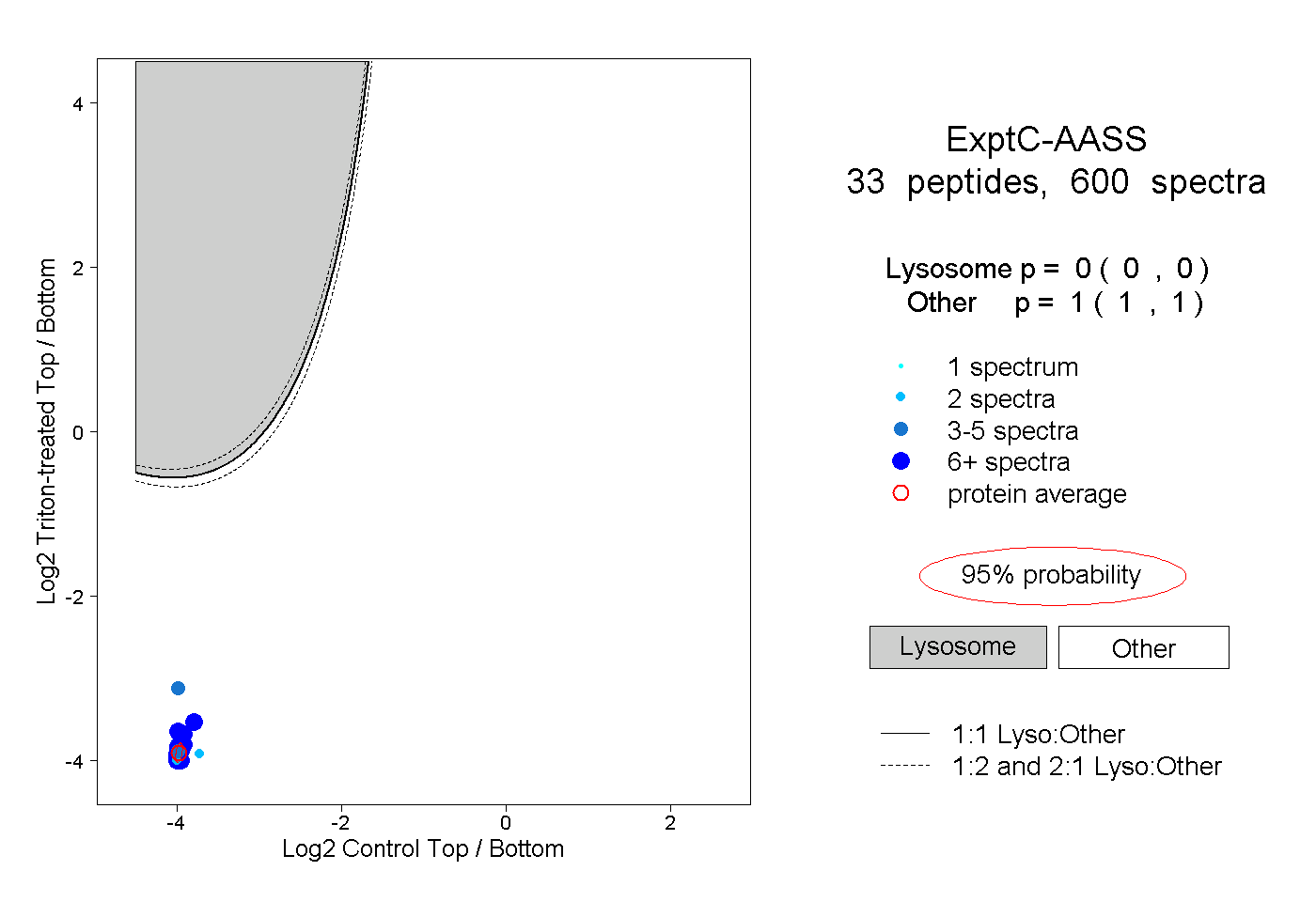 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
52 spectra |
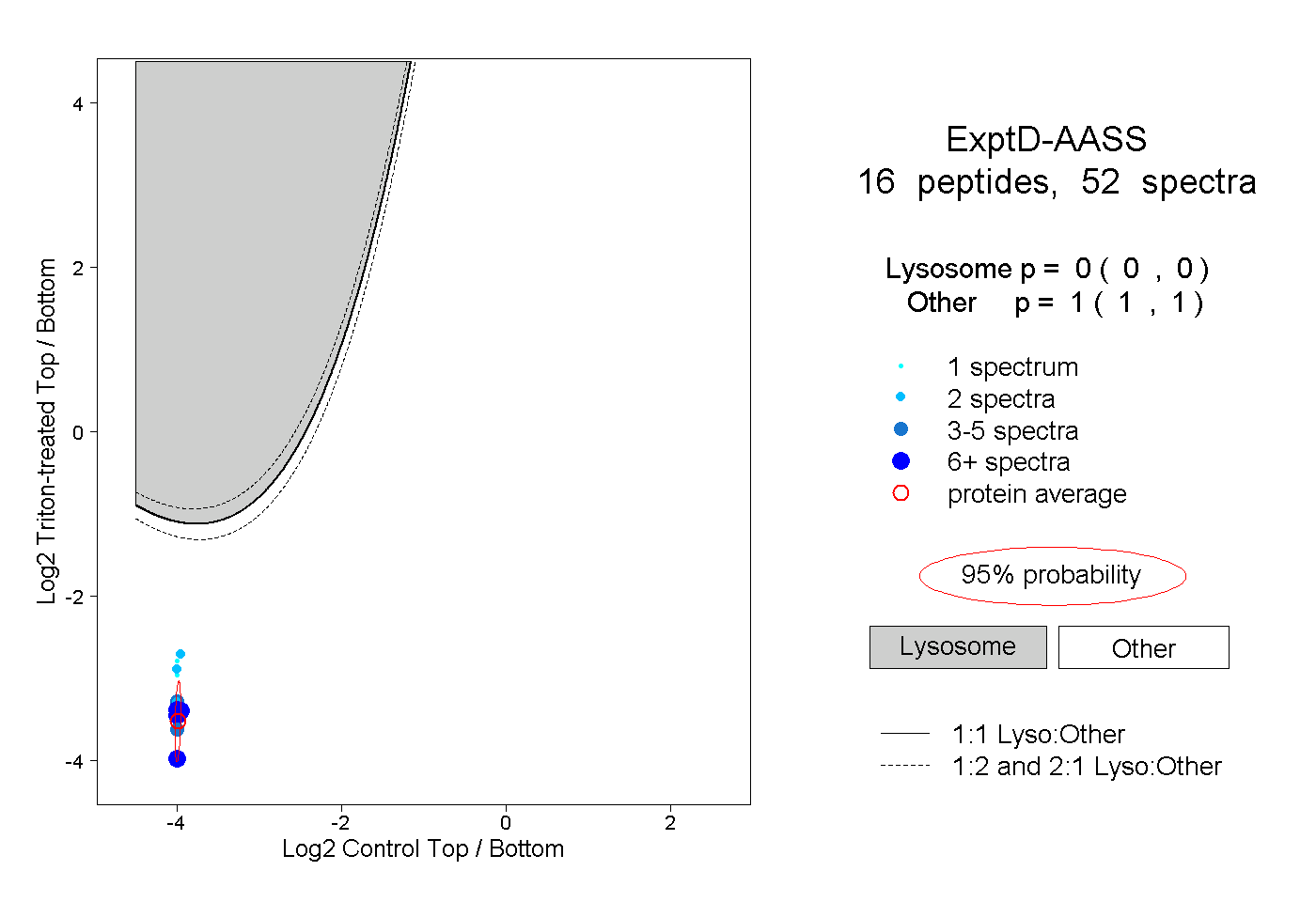 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |