peptides
spectra
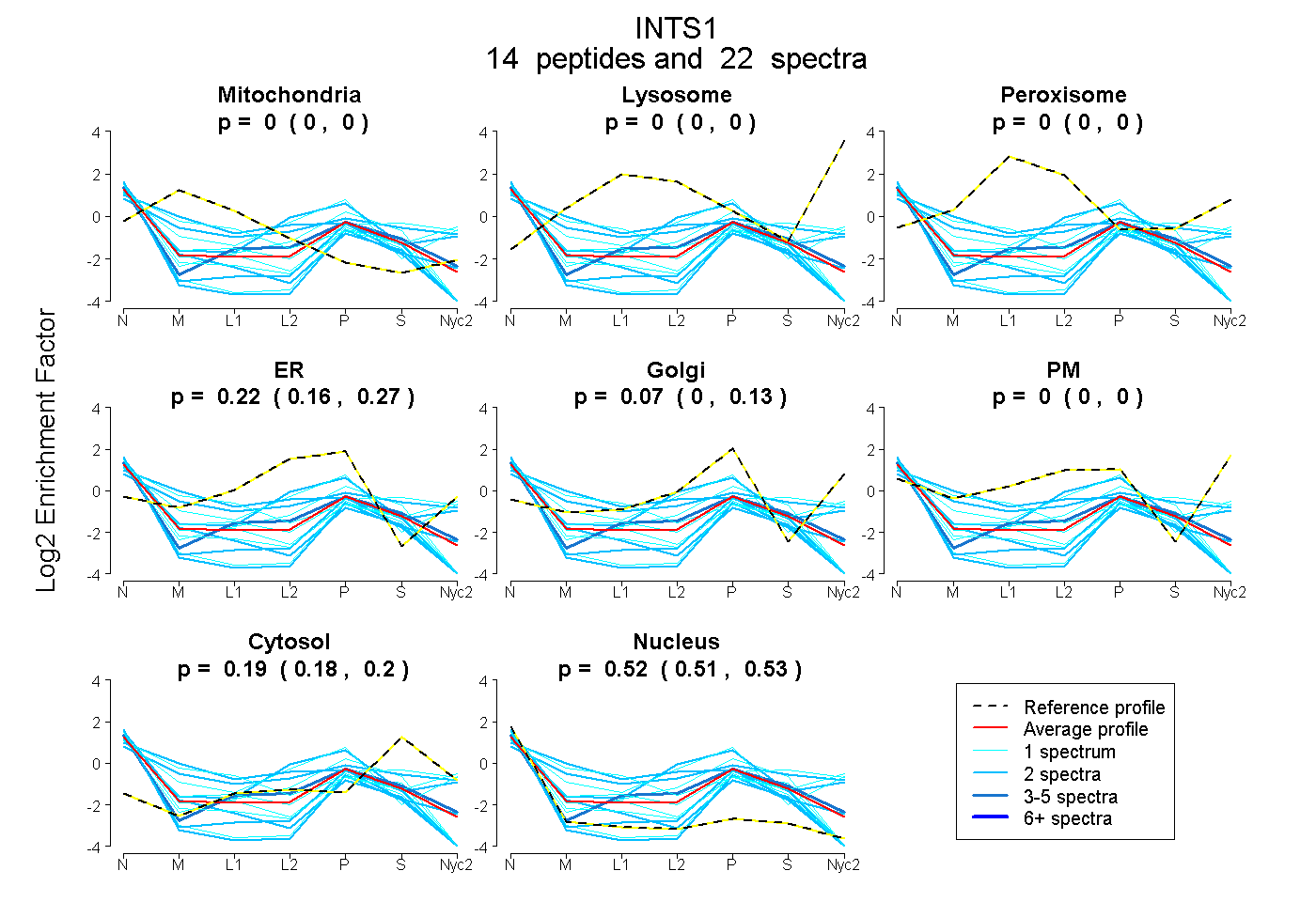
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.159 | 0.275
0.000 | 0.129
0.000 | 0.000
0.177 | 0.198
0.505 | 0.534
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.224 0.159 | 0.275 |
0.065 0.000 | 0.129 |
0.000 0.000 | 0.000 |
0.189 0.177 | 0.198 |
0.522 0.505 | 0.534 |
| 1 spectrum, NPDFLLHIIQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.047 | 0.260 | 0.398 | 0.295 | ||
| 1 spectrum, AVIATLR | 0.000 | 0.000 | 0.000 | 0.273 | 0.000 | 0.000 | 0.223 | 0.505 | ||
| 2 spectra, LPLLLSCCR | 0.000 | 0.000 | 0.000 | 0.066 | 0.017 | 0.000 | 0.162 | 0.755 | ||
| 2 spectra, RPPPHILDQVK | 0.354 | 0.000 | 0.014 | 0.359 | 0.000 | 0.000 | 0.024 | 0.249 | ||
| 1 spectrum, ILVIGLSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.045 | 0.000 | 0.115 | 0.839 | ||
| 1 spectrum, TLIQTR | 0.000 | 0.000 | 0.000 | 0.118 | 0.000 | 0.000 | 0.167 | 0.715 | ||
| 1 spectrum, NLAFSLALR | 0.000 | 0.000 | 0.000 | 0.188 | 0.257 | 0.263 | 0.013 | 0.279 | ||
| 2 spectra, LDGLIHR | 0.140 | 0.000 | 0.000 | 0.026 | 0.000 | 0.372 | 0.317 | 0.145 | ||
| 1 spectrum, FVQFIHK | 0.019 | 0.000 | 0.000 | 0.130 | 0.000 | 0.000 | 0.204 | 0.647 | ||
| 2 spectra, SLLAGLSLPSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.037 | 0.000 | 0.076 | 0.887 | ||
| 2 spectra, DYVHCLHK | 0.000 | 0.000 | 0.000 | 0.319 | 0.112 | 0.151 | 0.153 | 0.264 | ||
| 1 spectrum, VYIEDSLGER | 0.260 | 0.000 | 0.000 | 0.000 | 0.000 | 0.373 | 0.173 | 0.194 | ||
| 3 spectra, LGHLLCR | 0.000 | 0.000 | 0.000 | 0.276 | 0.000 | 0.000 | 0.252 | 0.472 | ||
| 2 spectra, DFEVVQTALR | 0.032 | 0.000 | 0.000 | 0.081 | 0.023 | 0.000 | 0.096 | 0.767 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
1 spectrum |
 |
0.000 NA | NA |
1.000 NA | NA |