peptides
spectra
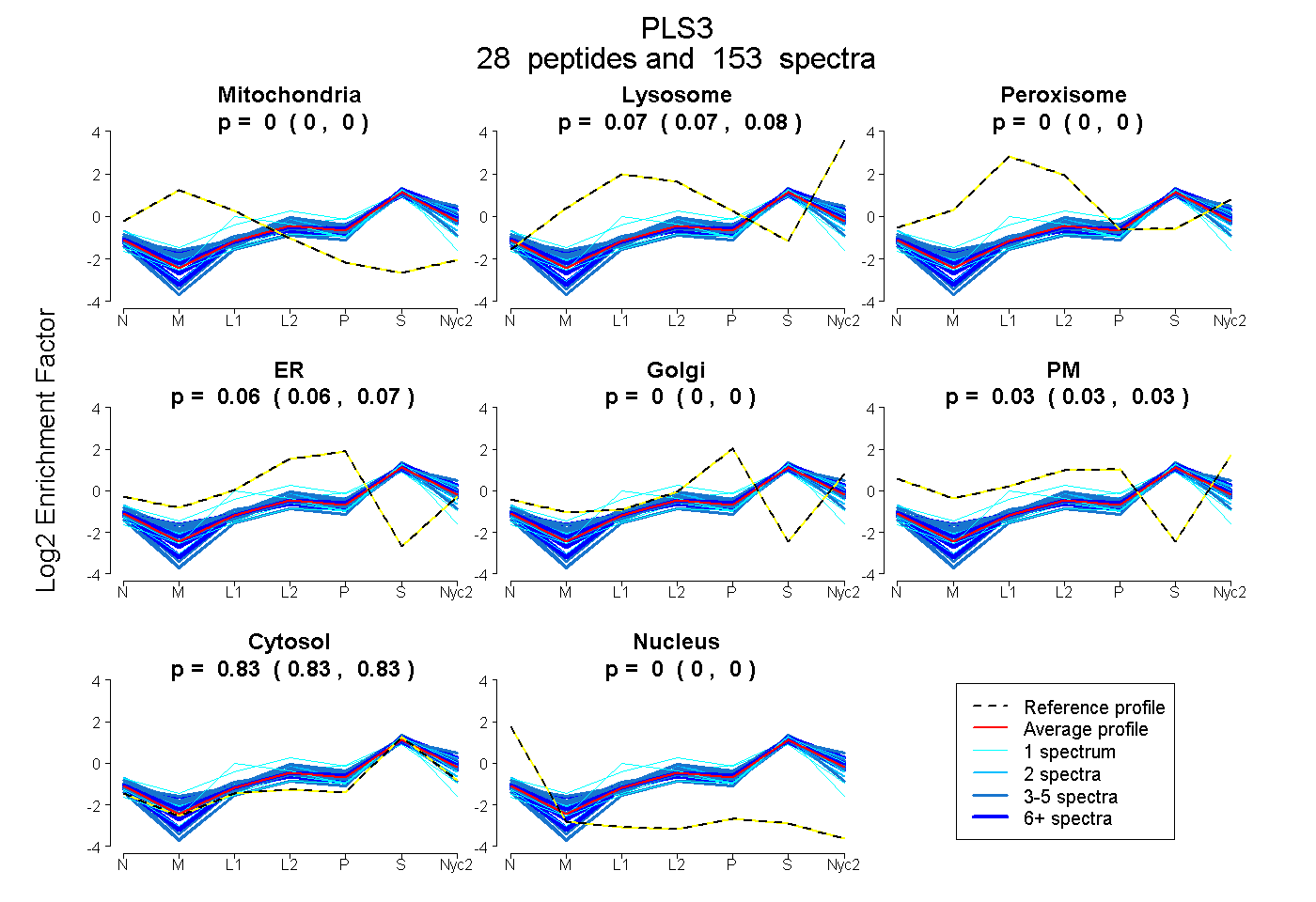
0.000 | 0.000
0.073 | 0.076
0.000 | 0.000
0.062 | 0.068
0.000 | 0.000
0.026 | 0.032
0.830 | 0.832
0.000 | 0.000
peptides
spectra
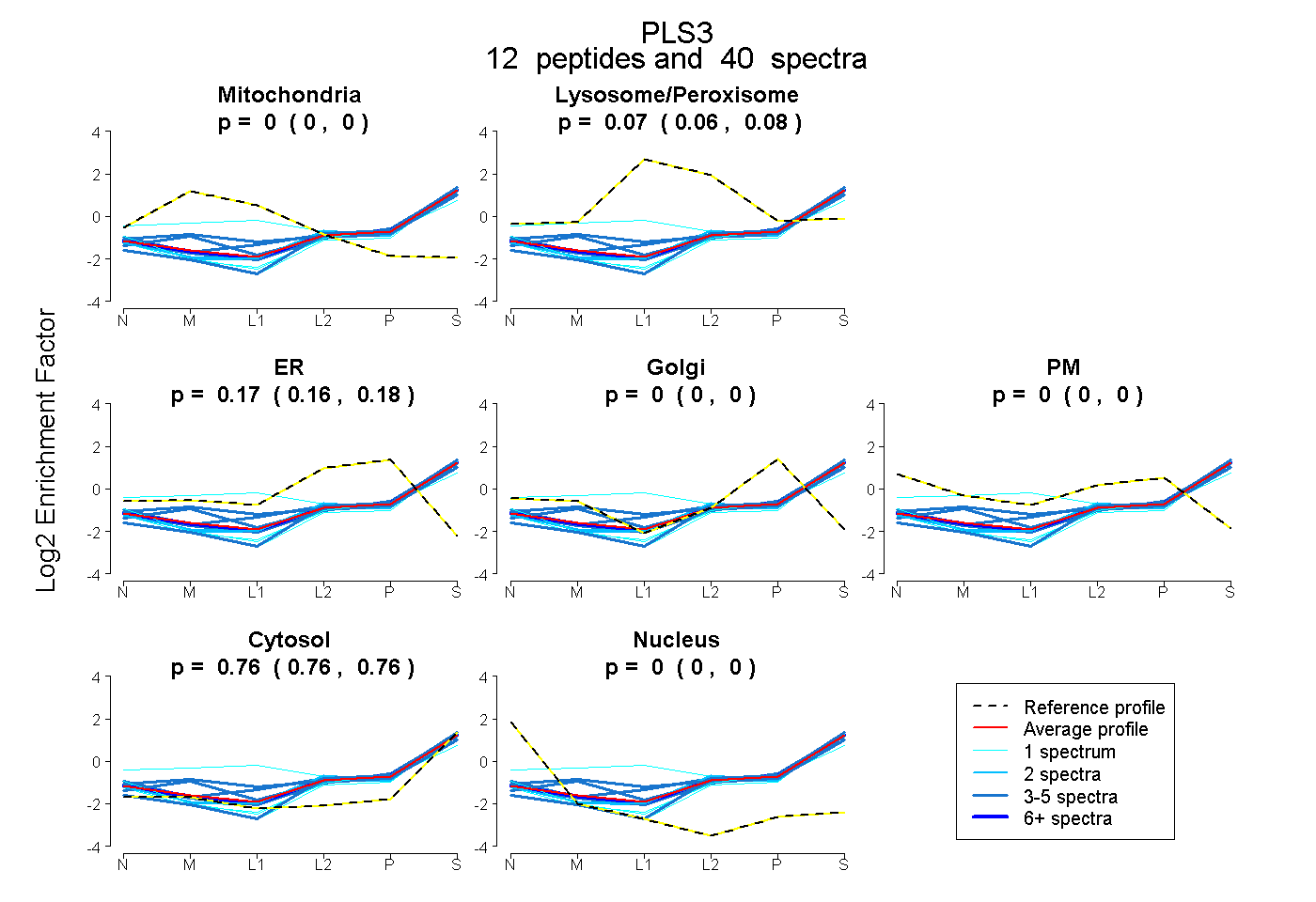
0.000 | 0.000
0.058 | 0.078
0.164 | 0.178
0.000 | 0.000
0.000 | 0.000
0.756 | 0.764
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
153 spectra |
 |
0.000 0.000 | 0.000 |
0.075 0.073 | 0.076 |
0.000 0.000 | 0.000 |
0.065 0.062 | 0.068 |
0.000 0.000 | 0.000 |
0.029 0.026 | 0.032 |
0.831 0.830 | 0.832 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
40 spectra |
 |
0.000 0.000 | 0.000 |
0.069 0.058 | 0.078 |
0.171 0.164 | 0.178 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.760 0.756 | 0.764 |
0.000 0.000 | 0.000 |
| 2 spectra, NEALAALLR | 0.000 | 0.079 | 0.143 | 0.000 | 0.000 | 0.778 | 0.000 | |||
| 4 spectra, LNLAFVANLFNK | 0.000 | 0.024 | 0.196 | 0.000 | 0.000 | 0.779 | 0.000 | |||
| 4 spectra, QFVTPADVVSGNPK | 0.000 | 0.232 | 0.000 | 0.120 | 0.004 | 0.644 | 0.000 | |||
| 1 spectrum, DGETLEELMK | 0.000 | 0.000 | 0.109 | 0.000 | 0.000 | 0.891 | 0.000 | |||
| 1 spectrum, LMLDGDR | 0.000 | 0.000 | 0.179 | 0.005 | 0.000 | 0.816 | 0.000 | |||
| 1 spectrum, IENCNYAVELGK | 0.070 | 0.316 | 0.000 | 0.000 | 0.138 | 0.476 | 0.000 | |||
| 2 spectra, ALENDPDCR | 0.000 | 0.056 | 0.128 | 0.000 | 0.019 | 0.796 | 0.000 | |||
| 3 spectra, AYFHLLNQIAPK | 0.000 | 0.200 | 0.043 | 0.056 | 0.000 | 0.701 | 0.000 | |||
| 3 spectra, MINLSVPDTIDER | 0.000 | 0.108 | 0.113 | 0.039 | 0.000 | 0.739 | 0.000 | |||
| 13 spectra, LSPEELLLR | 0.000 | 0.055 | 0.184 | 0.000 | 0.000 | 0.761 | 0.000 | |||
| 1 spectrum, VDLNSNGFICDYELHELFK | 0.000 | 0.000 | 0.157 | 0.056 | 0.000 | 0.787 | 0.000 | |||
| 5 spectra, YAVSMAR | 0.000 | 0.000 | 0.173 | 0.000 | 0.000 | 0.827 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
167 spectra |
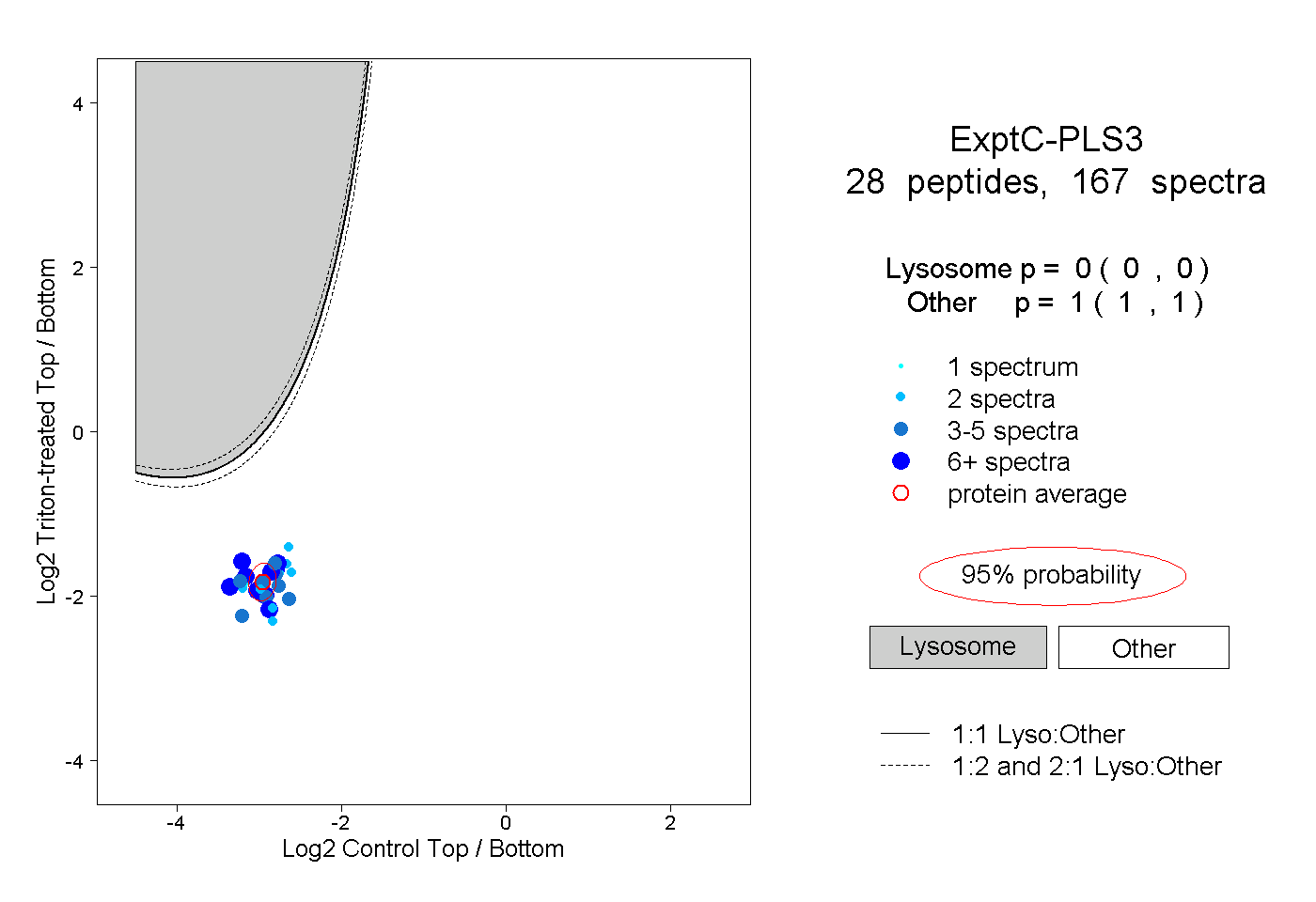 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
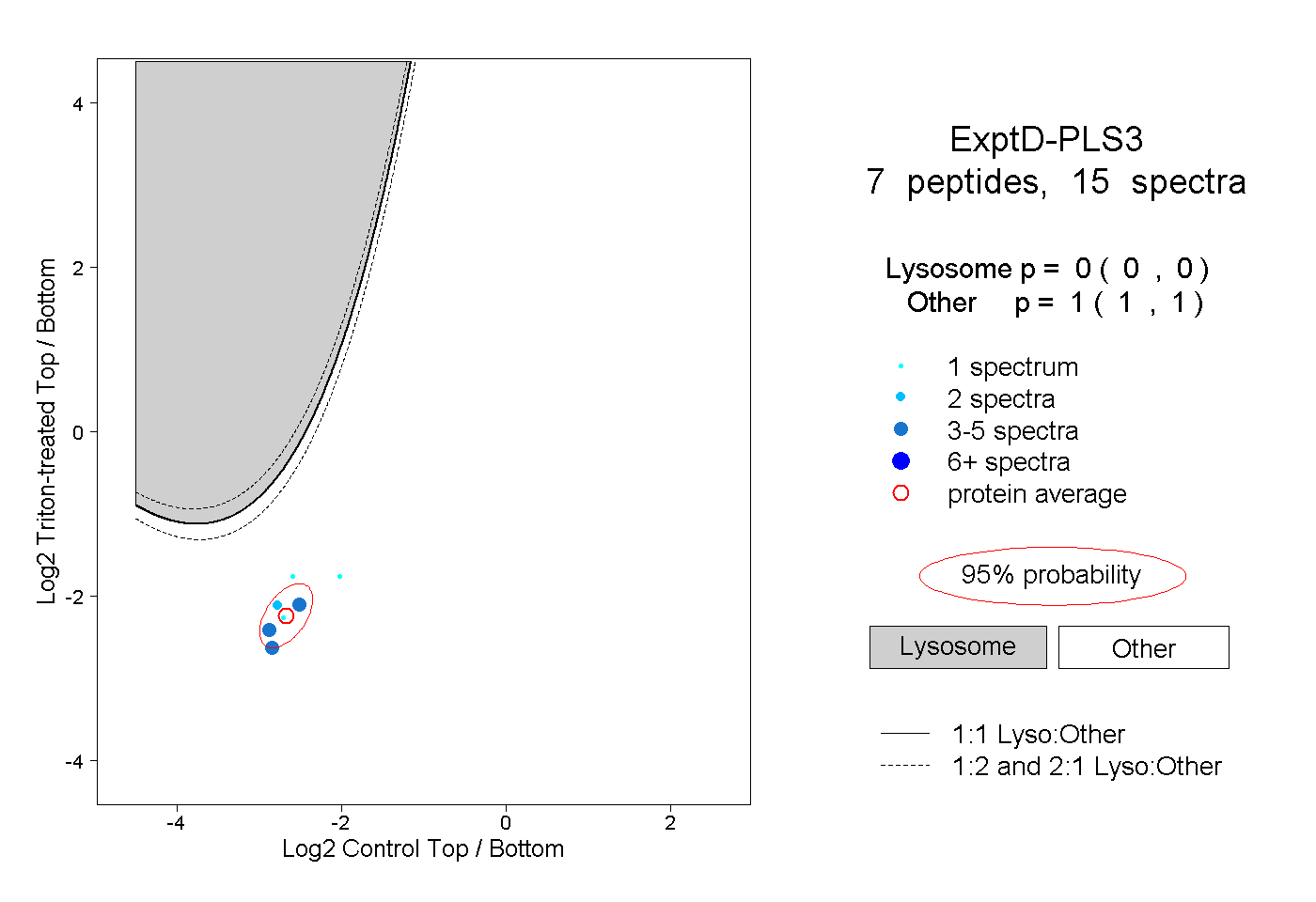 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |