peptides
spectra
0.000 | 0.000
0.000 | 0.015
0.004 | 0.048
0.000 | 0.035
0.072 | 0.123
0.000 | 0.010
0.832 | 0.857
0.000 | 0.000
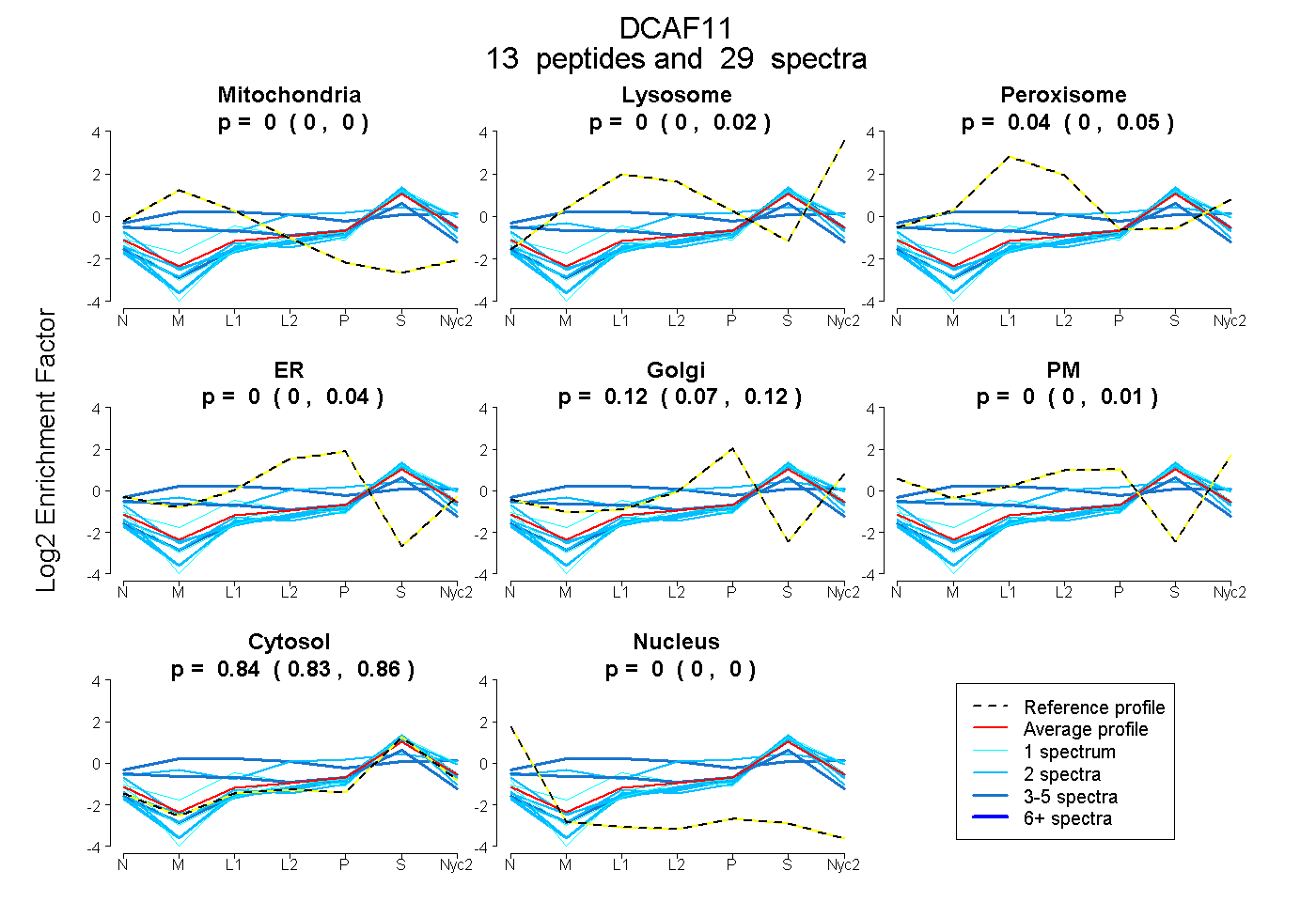
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
29 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.015 |
0.038 0.004 | 0.048 |
0.000 0.000 | 0.035 |
0.118 0.072 | 0.123 |
0.000 0.000 | 0.010 |
0.844 0.832 | 0.857 |
0.000 0.000 | 0.000 |
| 2 spectra, GHGVLHTLIR | 0.005 | 0.021 | 0.212 | 0.000 | 0.229 | 0.078 | 0.454 | 0.000 | ||
| 1 spectrum, YLISNSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.075 | 0.000 | 0.925 | 0.000 | ||
| 1 spectrum, QAEYFQDDMTESDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.045 | 0.955 | 0.000 | ||
| 2 spectra, LPGDSSLMTYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, GSFSLGEQSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, IVSSSWDGSLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.084 | 0.000 | 0.916 | 0.000 | ||
| 2 spectra, VELATGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.035 | 0.000 | 0.965 | 0.000 | ||
| 5 spectra, ELEYNEIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.058 | 0.000 | 0.942 | 0.000 | ||
| 1 spectrum, DVSWHPFEEK | 0.040 | 0.000 | 0.163 | 0.000 | 0.000 | 0.000 | 0.797 | 0.000 | ||
| 3 spectra, DGQIFMSACQDQTIR | 0.134 | 0.034 | 0.313 | 0.000 | 0.071 | 0.130 | 0.319 | 0.000 | ||
| 2 spectra, LAATQQNWDYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.069 | 0.077 | 0.854 | 0.000 | ||
| 4 spectra, TAQEHSFPR | 0.226 | 0.000 | 0.090 | 0.050 | 0.028 | 0.000 | 0.605 | 0.000 | ||
| 2 spectra, EGMEASR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
9 spectra |
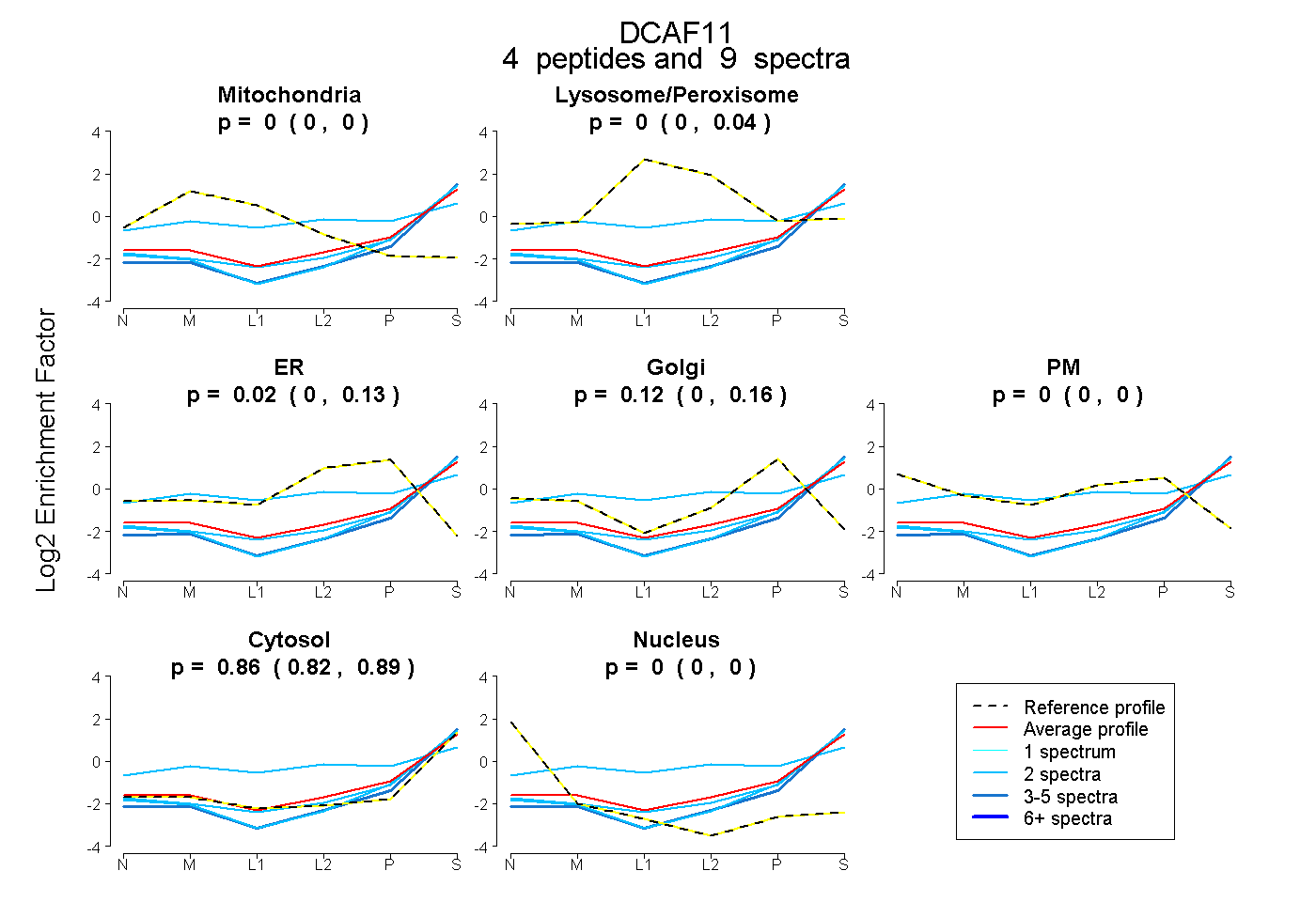 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.036 |
0.021 0.000 | 0.130 |
0.118 0.000 | 0.160 |
0.000 0.000 | 0.000 |
0.861 0.822 | 0.889 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
27 spectra |
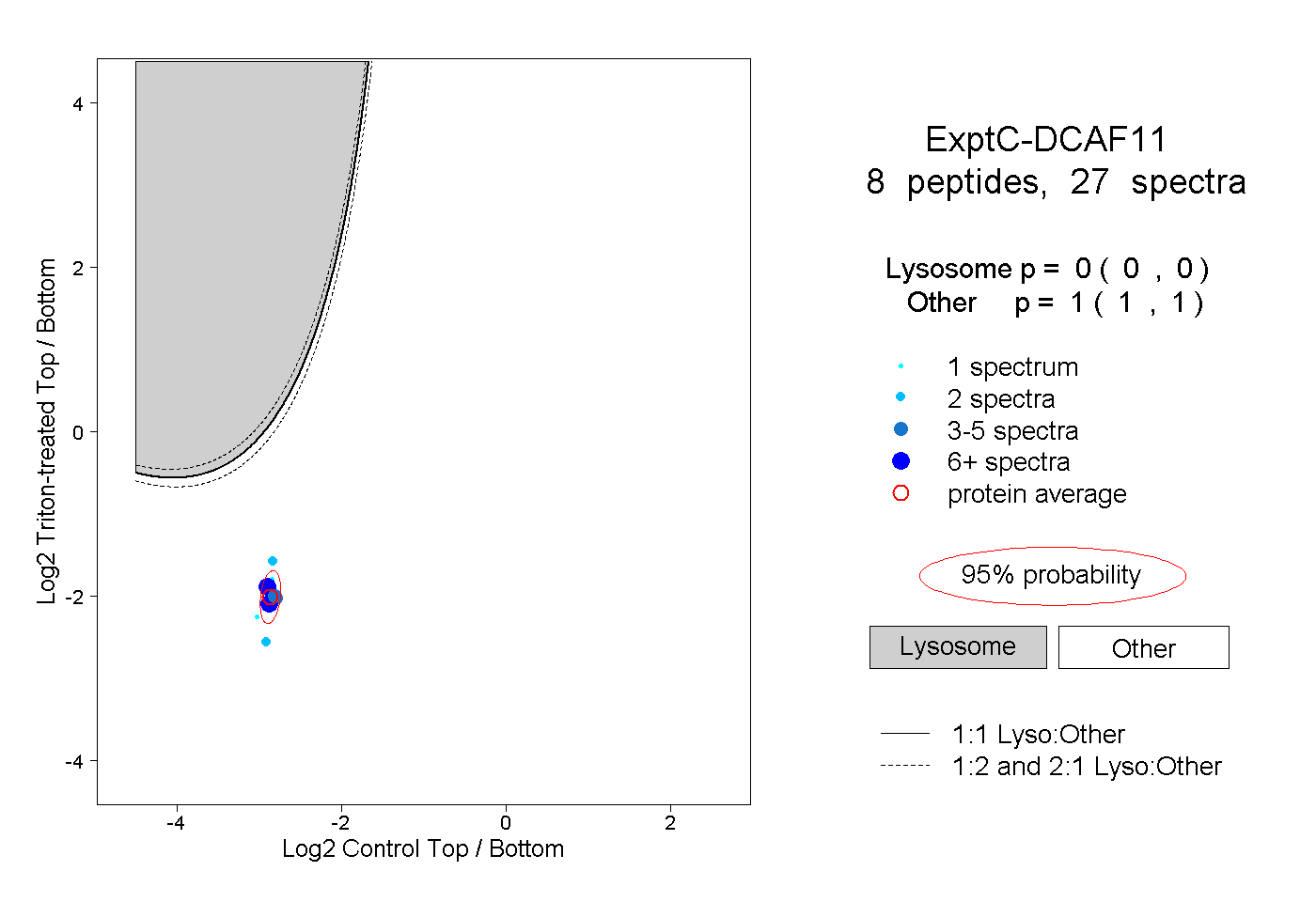 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
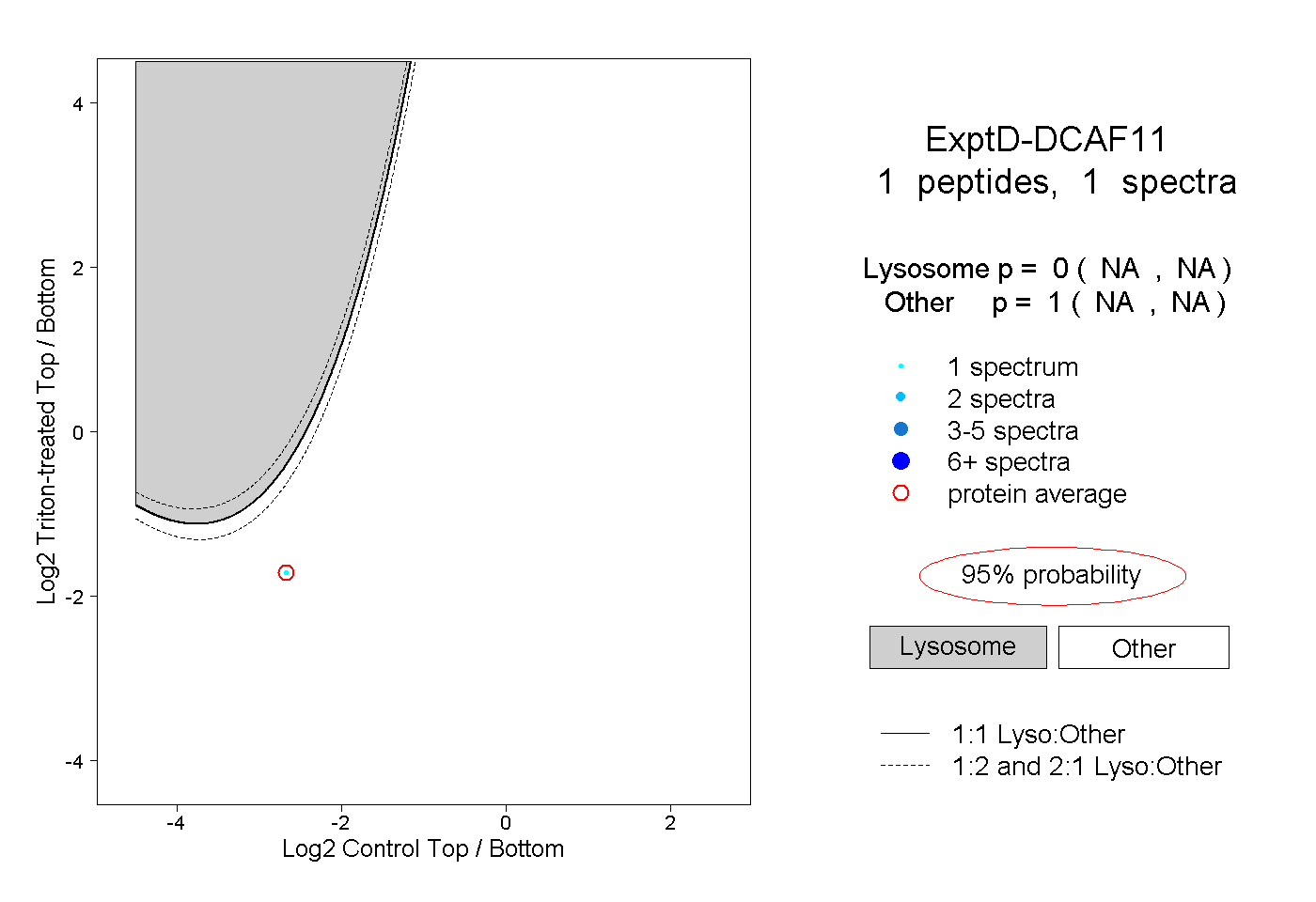 |
0.000 NA | NA |
1.000 NA | NA |