GIMAP1
[ENSRNOP00000055930]
Main page
| | | Plot |
Mito |
Lyso |
|
Perox |
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt A |
 2
2
peptides |
5
spectra |
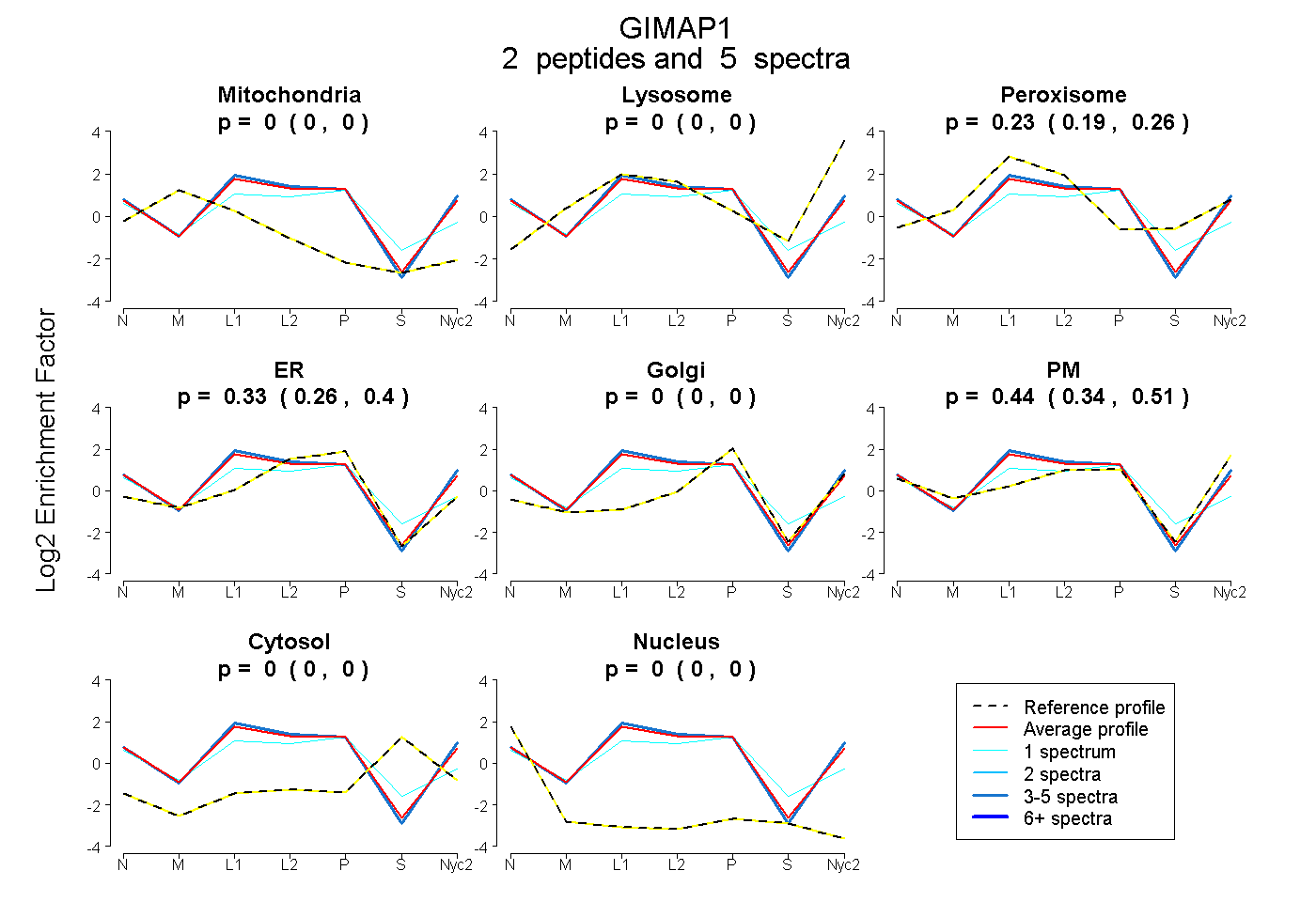 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
|
0.229
0.192 | 0.261 |
0.334
0.262 | 0.399 |
0.000
0.000 | 0.000 |
0.436
0.343 | 0.506 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
|
| | | Plot |
Mito |
|
Lyso or Perox |
|
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt B |
 2
2
peptides |
2
spectra |
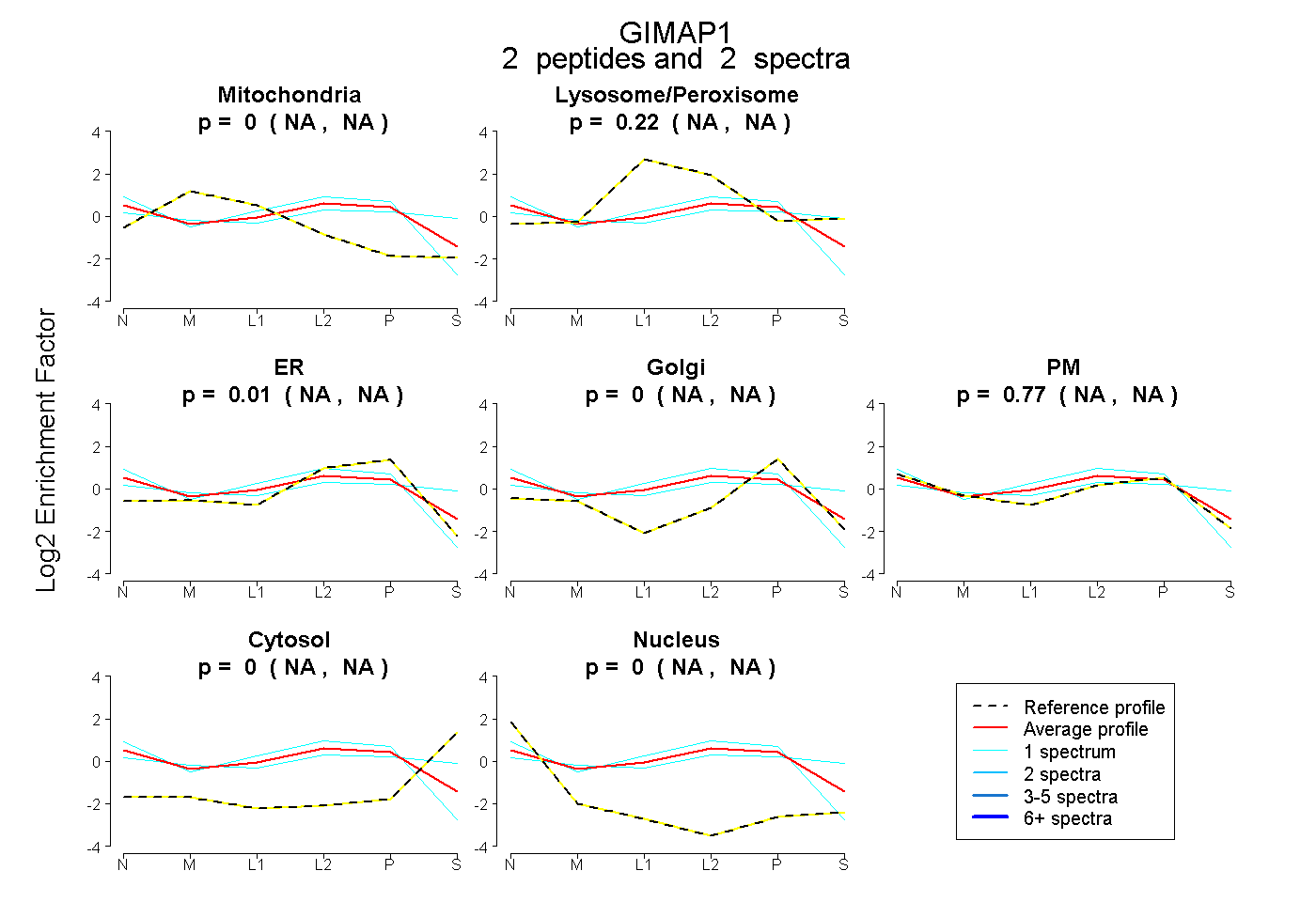 |
0.000
NA | NA |
|
0.220
NA | NA |
|
0.010
NA | NA |
0.000
NA | NA |
0.771
NA | NA |
0.000
NA | NA |
0.000
NA | NA |
|
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt C |
 11
11
peptides |
34
spectra |
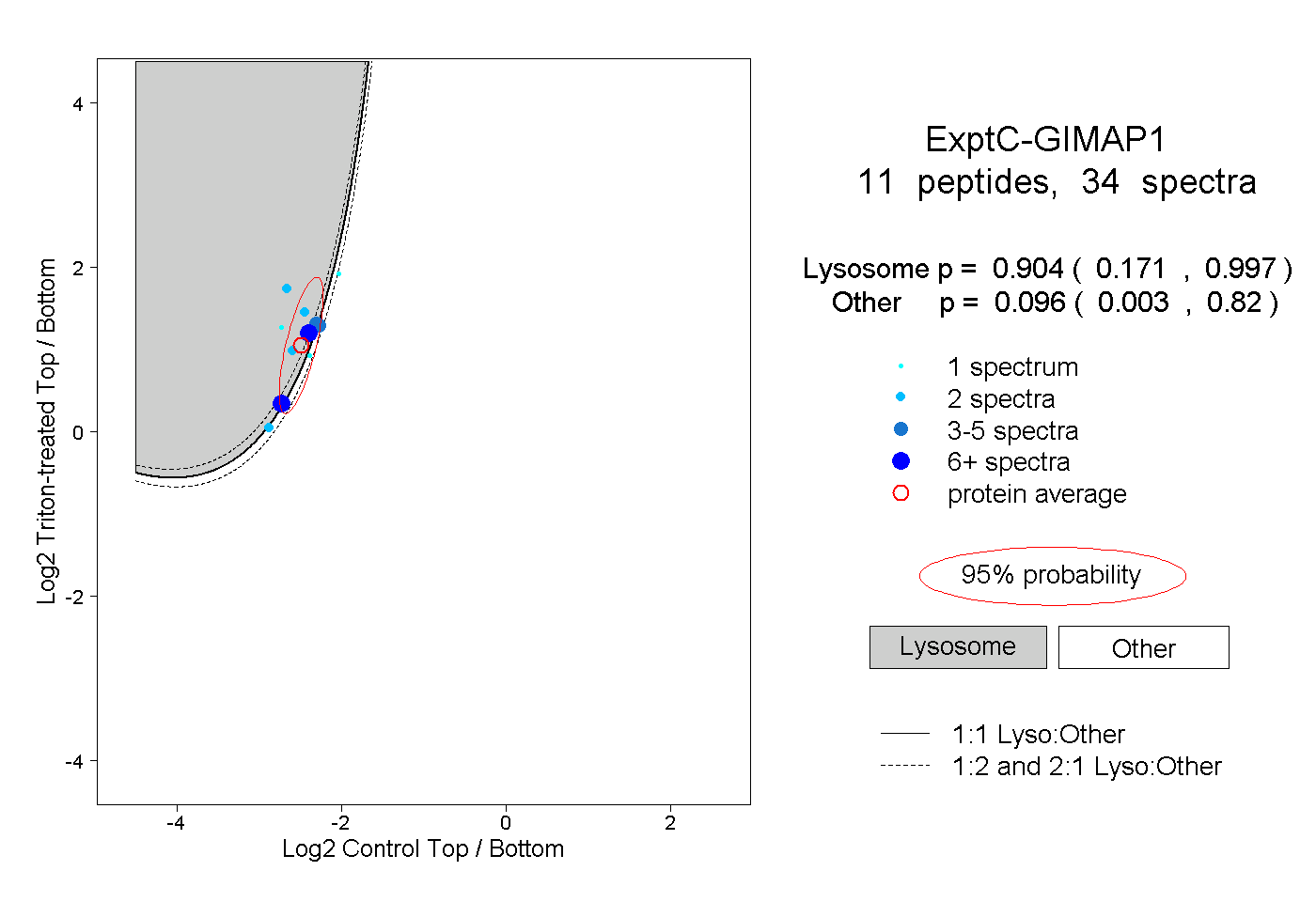 |
|
0.904
0.171 | 0.997 |
|
|
|
|
|
|
|
0.096
0.003 | 0.820 |
| 4 spectra, ELVAECGDR |
|
0.458 |
|
|
|
|
|
|
|
0.542 |
| 3 spectra, APQEPHLR |
|
0.624 |
|
|
|
|
|
|
|
0.376 |
| 10 spectra, SDPGCVEAAR |
|
0.827 |
|
|
|
|
|
|
|
0.173 |
| 1 spectrum, CADPQDQLTK |
|
0.346 |
|
|
|
|
|
|
|
0.654 |
| 1 spectrum, LGAVPVTR |
|
0.162 |
|
|
|
|
|
|
|
0.838 |
| 1 spectrum, VAEMVVAR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 6 spectra, LILVGR |
|
0.602 |
|
|
|
|
|
|
|
0.398 |
| 2 spectra, SATGNSILGQK |
|
0.969 |
|
|
|
|
|
|
|
0.031 |
| 2 spectra, VCALNNR |
|
0.988 |
|
|
|
|
|
|
|
0.012 |
| 2 spectra, SCTLASR |
|
0.429 |
|
|
|
|
|
|
|
0.571 |
| 2 spectra, TVVVFTR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt D |
 2
2
peptides |
2
spectra |
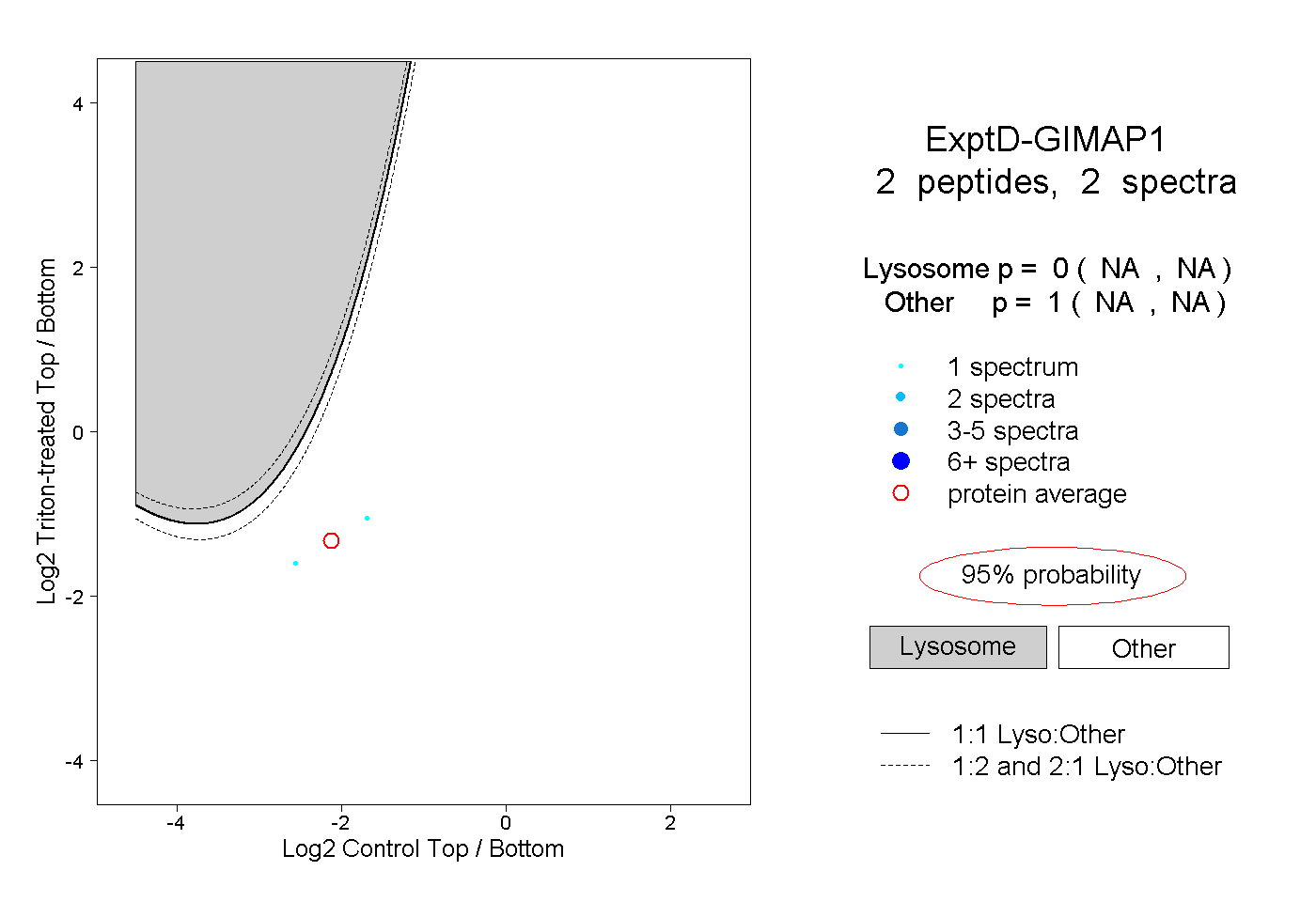 |
|
0.000
NA | NA |
|
|
|
|
|
|
|
1.000
NA | NA |



