peptides
spectra
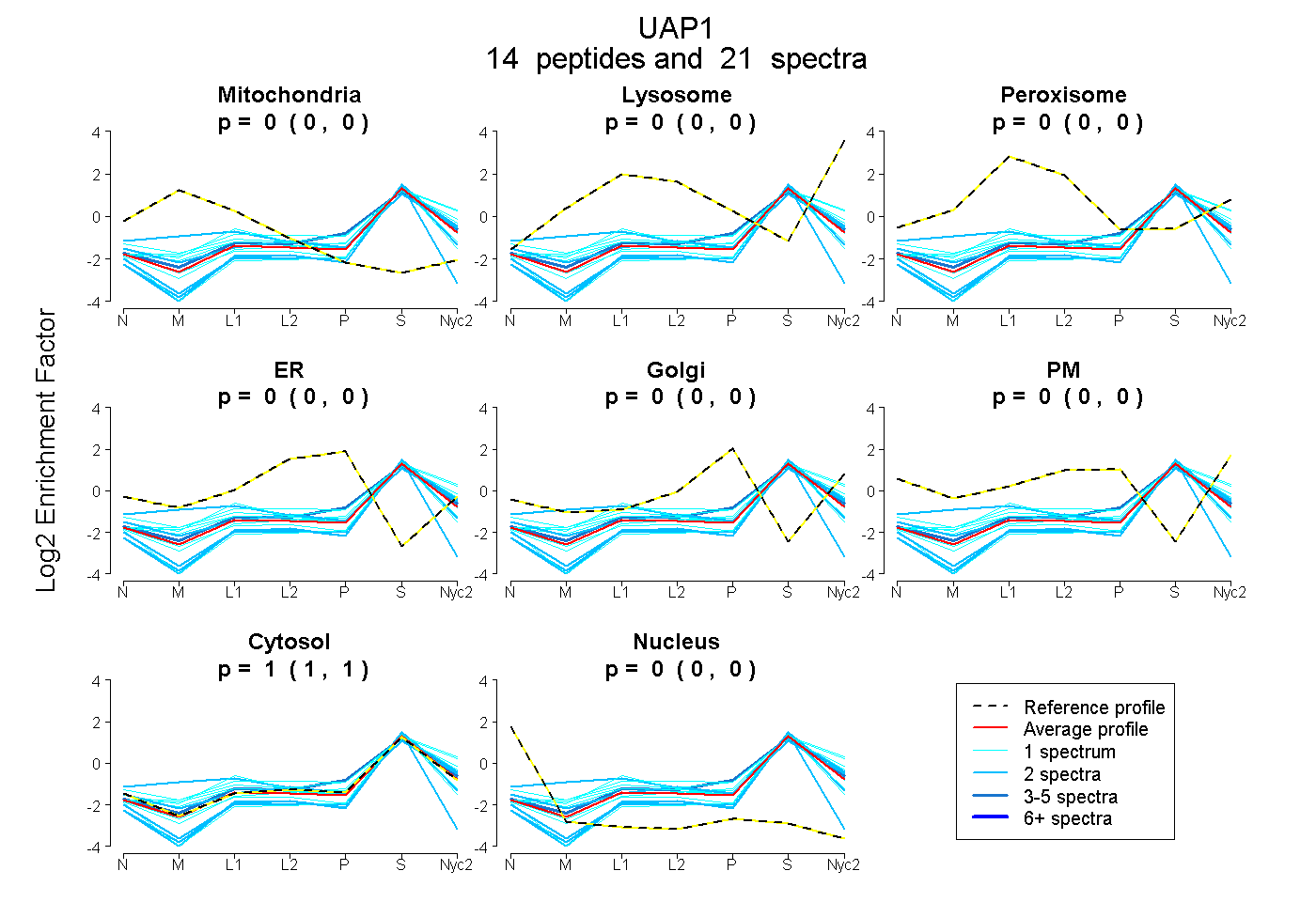
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
21 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, QVLGSATR | 0.000 | 0.167 | 0.000 | 0.000 | 0.000 | 0.000 | 0.833 | 0.000 | ||
| 1 spectrum, LPAIPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.928 | 0.072 | ||
| 1 spectrum, TMESTK | 0.000 | 0.128 | 0.000 | 0.000 | 0.023 | 0.000 | 0.849 | 0.000 | ||
| 2 spectra, ALAAQNIVEDMEQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, GMYDVGLPSHK | 0.152 | 0.062 | 0.057 | 0.000 | 0.000 | 0.000 | 0.730 | 0.000 | ||
| 2 spectra, TLFQIQAER | 0.000 | 0.053 | 0.000 | 0.000 | 0.000 | 0.000 | 0.947 | 0.000 | ||
| 3 spectra, DVVNVYEPQLQHHVAQK | 0.000 | 0.031 | 0.000 | 0.000 | 0.048 | 0.000 | 0.921 | 0.000 | ||
| 2 spectra, TNPTEPVGVVCR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.836 | 0.164 | ||
| 1 spectrum, GADCGAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, CTIPWYIMTSGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.973 | 0.027 | ||
| 1 spectrum, MEPVPR | 0.000 | 0.194 | 0.000 | 0.000 | 0.000 | 0.000 | 0.806 | 0.000 | ||
| 1 spectrum, AVGEFDR | 0.030 | 0.048 | 0.000 | 0.000 | 0.000 | 0.000 | 0.922 | 0.000 | ||
| 1 spectrum, FVFDIFQFAK | 0.000 | 0.079 | 0.000 | 0.000 | 0.000 | 0.000 | 0.921 | 0.000 | ||
| 1 spectrum, VILEEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
3 spectra |
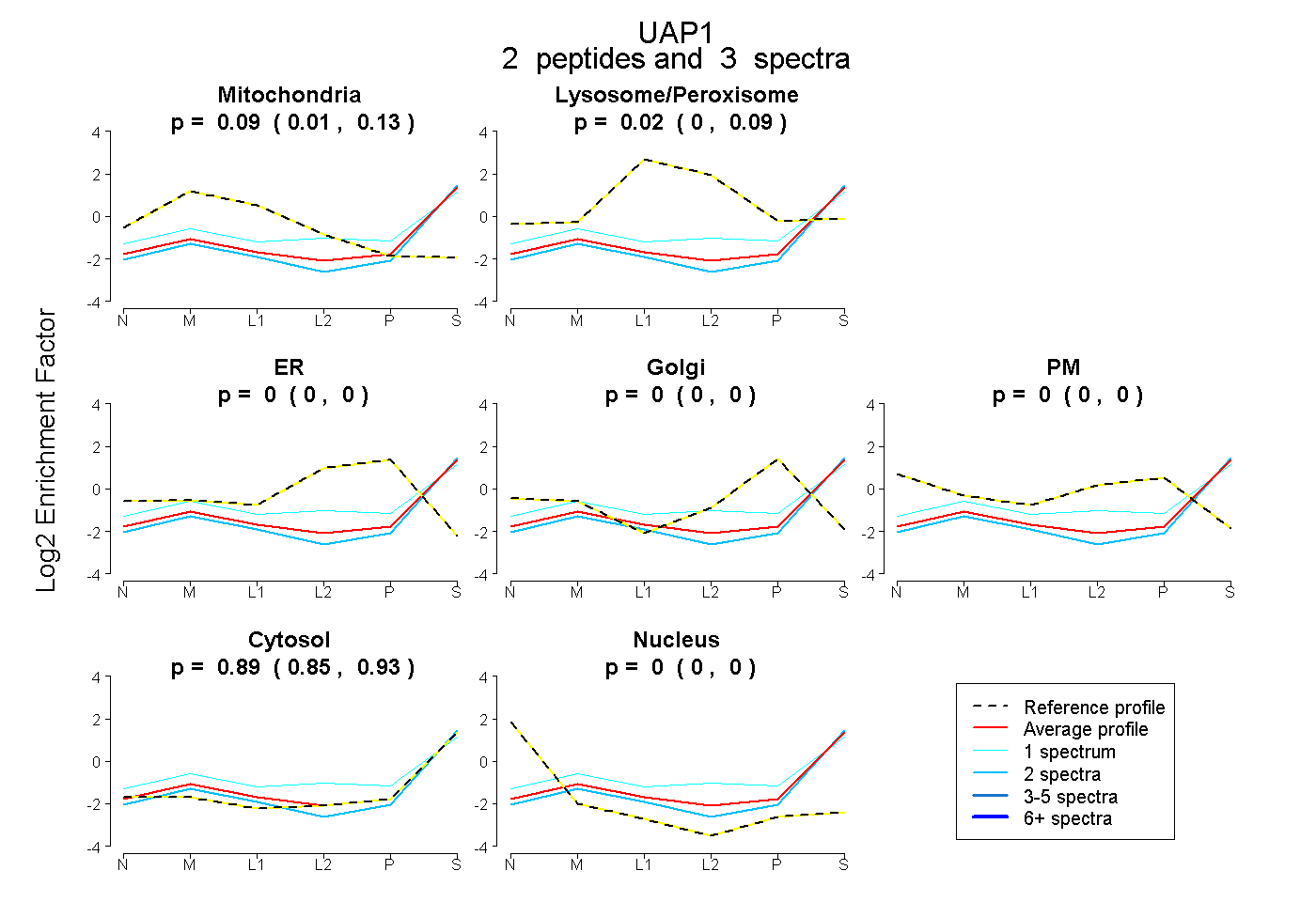 |
0.093 0.009 | 0.127 |
0.015 0.000 | 0.092 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.891 0.845 | 0.930 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
20 spectra |
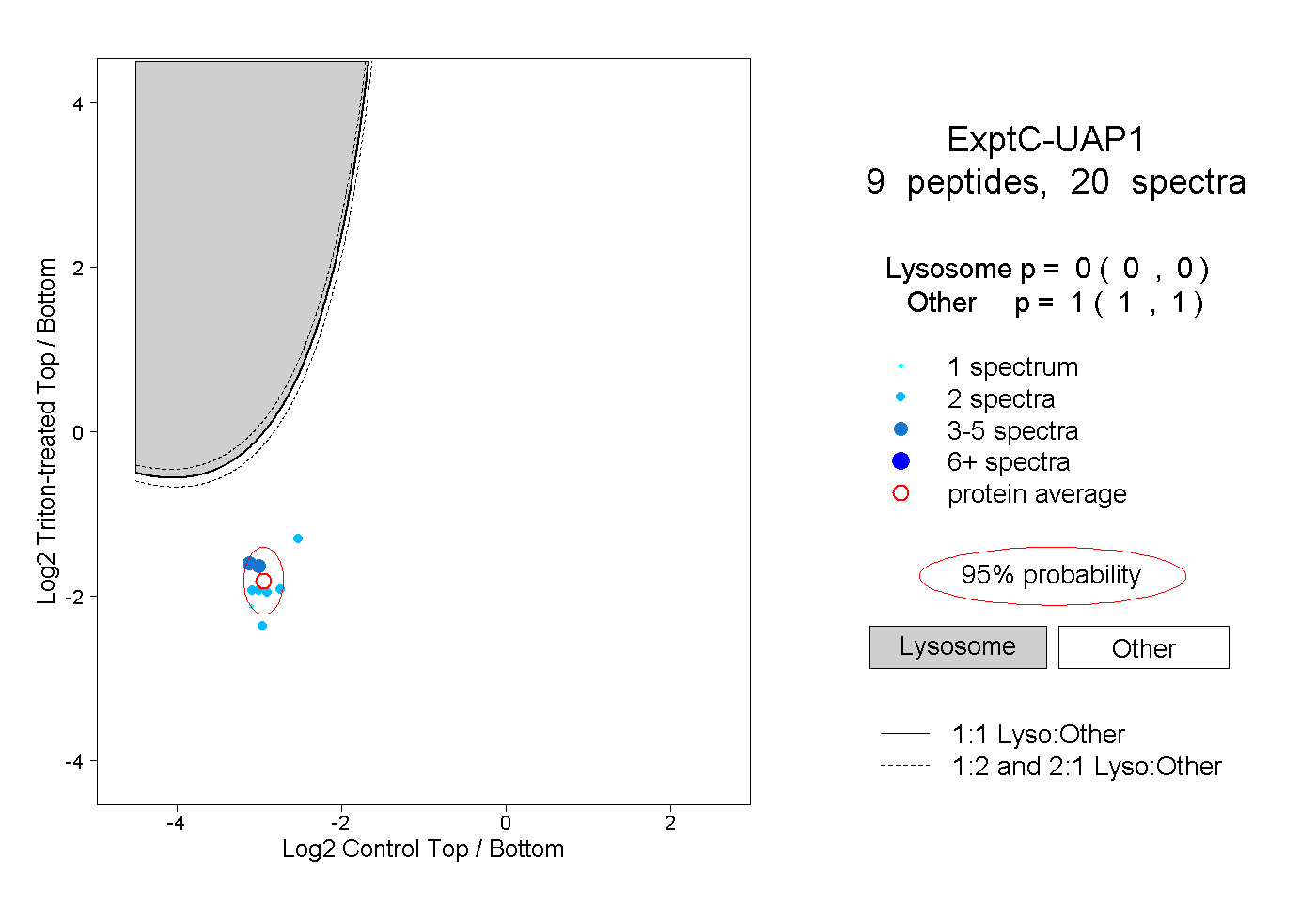 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |