peptides
spectra
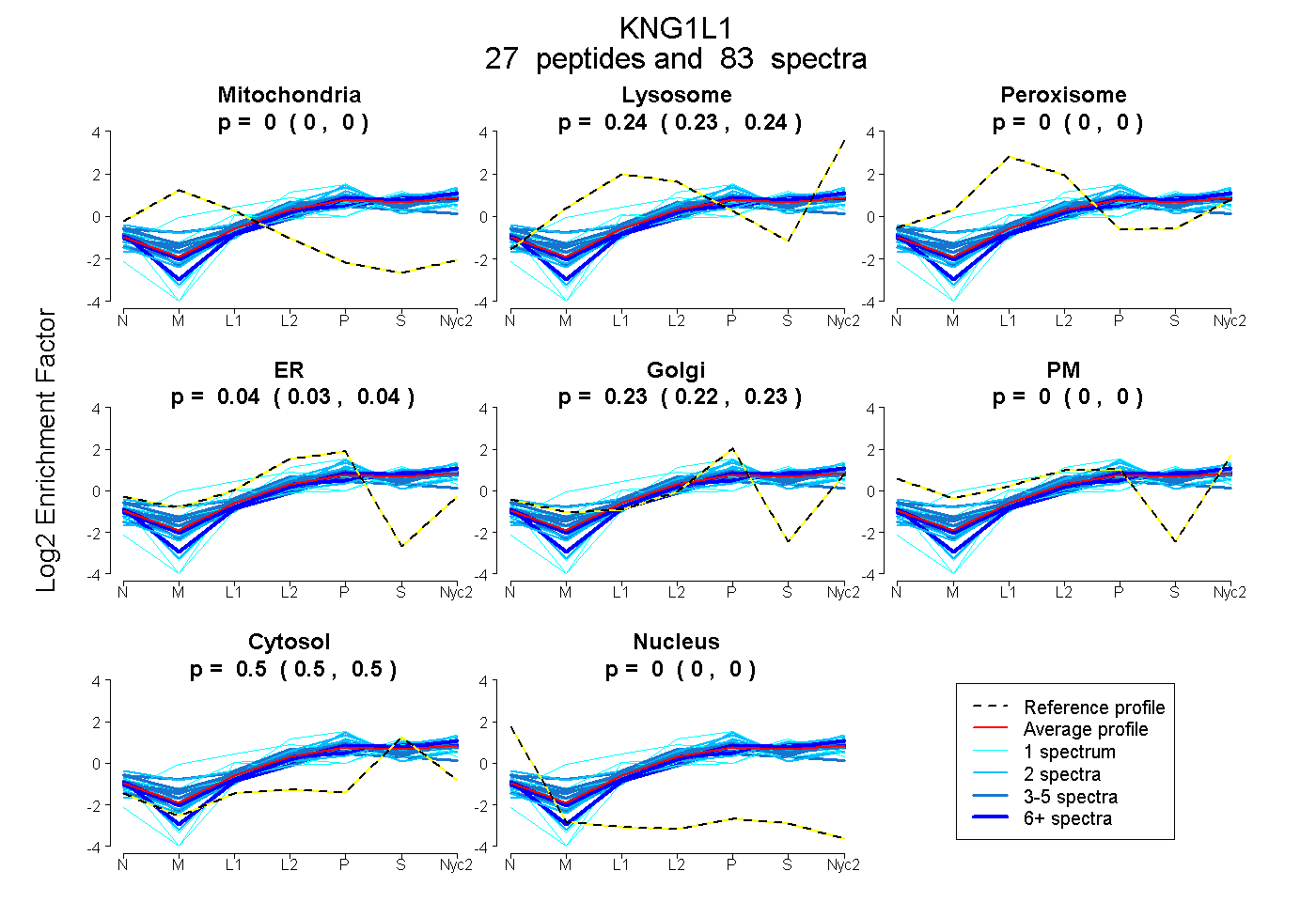
0.000 | 0.000
0.233 | 0.239
0.000 | 0.000
0.030 | 0.040
0.223 | 0.234
0.000 | 0.000
0.497 | 0.502
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
83 spectra |
 |
0.000 0.000 | 0.000 |
0.236 0.233 | 0.239 |
0.000 0.000 | 0.000 |
0.035 0.030 | 0.040 |
0.229 0.223 | 0.234 |
0.000 0.000 | 0.000 |
0.500 0.497 | 0.502 |
0.000 0.000 | 0.000 |
| 10 spectra, VVPTVR | 0.000 | 0.245 | 0.000 | 0.033 | 0.168 | 0.000 | 0.554 | 0.000 | ||
| 2 spectra, GNAFVDIHK | 0.000 | 0.250 | 0.000 | 0.000 | 0.249 | 0.000 | 0.501 | 0.000 | ||
| 1 spectrum, HTHLFALTEVK | 0.000 | 0.184 | 0.000 | 0.076 | 0.000 | 0.031 | 0.709 | 0.000 | ||
| 2 spectra, LVQVQETK | 0.000 | 0.282 | 0.000 | 0.066 | 0.105 | 0.000 | 0.546 | 0.000 | ||
| 2 spectra, NHQGHK | 0.000 | 0.135 | 0.000 | 0.089 | 0.322 | 0.000 | 0.454 | 0.000 | ||
| 1 spectrum, SAHSQVVAGMNYK | 0.000 | 0.358 | 0.000 | 0.000 | 0.131 | 0.000 | 0.510 | 0.000 | ||
| 4 spectra, LLNSCEYK | 0.000 | 0.322 | 0.000 | 0.132 | 0.005 | 0.000 | 0.541 | 0.000 | ||
| 4 spectra, VLDMTSVIR | 0.000 | 0.226 | 0.000 | 0.000 | 0.300 | 0.000 | 0.473 | 0.000 | ||
| 3 spectra, YNAGLK | 0.000 | 0.253 | 0.000 | 0.026 | 0.277 | 0.048 | 0.397 | 0.000 | ||
| 1 spectrum, VVVPTR | 0.000 | 0.181 | 0.012 | 0.000 | 0.051 | 0.144 | 0.612 | 0.000 | ||
| 2 spectra, HTHLFALGEVK | 0.000 | 0.095 | 0.159 | 0.080 | 0.330 | 0.030 | 0.307 | 0.000 | ||
| 5 spectra, EDCVPLPYGDHGECR | 0.000 | 0.026 | 0.230 | 0.071 | 0.248 | 0.016 | 0.409 | 0.000 | ||
| 2 spectra, YNAELESGNQFLLYR | 0.000 | 0.255 | 0.000 | 0.000 | 0.119 | 0.000 | 0.626 | 0.000 | ||
| 2 spectra, ISRPPGFSPFR | 0.000 | 0.307 | 0.000 | 0.000 | 0.176 | 0.000 | 0.516 | 0.000 | ||
| 12 spectra, RPPGFSPFR | 0.000 | 0.114 | 0.000 | 0.000 | 0.303 | 0.000 | 0.583 | 0.000 | ||
| 3 spectra, ATSQVVAGTK | 0.000 | 0.205 | 0.000 | 0.007 | 0.199 | 0.130 | 0.459 | 0.000 | ||
| 6 spectra, YVIEFIAR | 0.000 | 0.231 | 0.000 | 0.000 | 0.268 | 0.000 | 0.502 | 0.000 | ||
| 2 spectra, NIPVDSPELK | 0.000 | 0.301 | 0.000 | 0.000 | 0.288 | 0.000 | 0.411 | 0.000 | ||
| 2 spectra, FSVATQICNITPGK | 0.000 | 0.246 | 0.000 | 0.165 | 0.009 | 0.000 | 0.581 | 0.000 | ||
| 3 spectra, EIPVDSPELK | 0.000 | 0.199 | 0.000 | 0.000 | 0.317 | 0.000 | 0.484 | 0.000 | ||
| 3 spectra, VVPTVK | 0.000 | 0.252 | 0.000 | 0.000 | 0.300 | 0.000 | 0.448 | 0.000 | ||
| 2 spectra, CPGRPWKPVSR | 0.000 | 0.147 | 0.000 | 0.073 | 0.383 | 0.000 | 0.397 | 0.000 | ||
| 4 spectra, DGAETLYSFK | 0.000 | 0.265 | 0.000 | 0.041 | 0.199 | 0.000 | 0.495 | 0.000 | ||
| 2 spectra, LISDFPEATSHK | 0.000 | 0.143 | 0.000 | 0.000 | 0.397 | 0.000 | 0.460 | 0.000 | ||
| 1 spectrum, SGNQFVLYQVTEGTK | 0.000 | 0.500 | 0.049 | 0.137 | 0.000 | 0.000 | 0.313 | 0.000 | ||
| 1 spectrum, EDGYDHR | 0.000 | 0.066 | 0.000 | 0.347 | 0.152 | 0.000 | 0.435 | 0.000 | ||
| 1 spectrum, DAEEAATGECTTTLGK | 0.000 | 0.098 | 0.000 | 0.027 | 0.099 | 0.000 | 0.777 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
36 spectra |
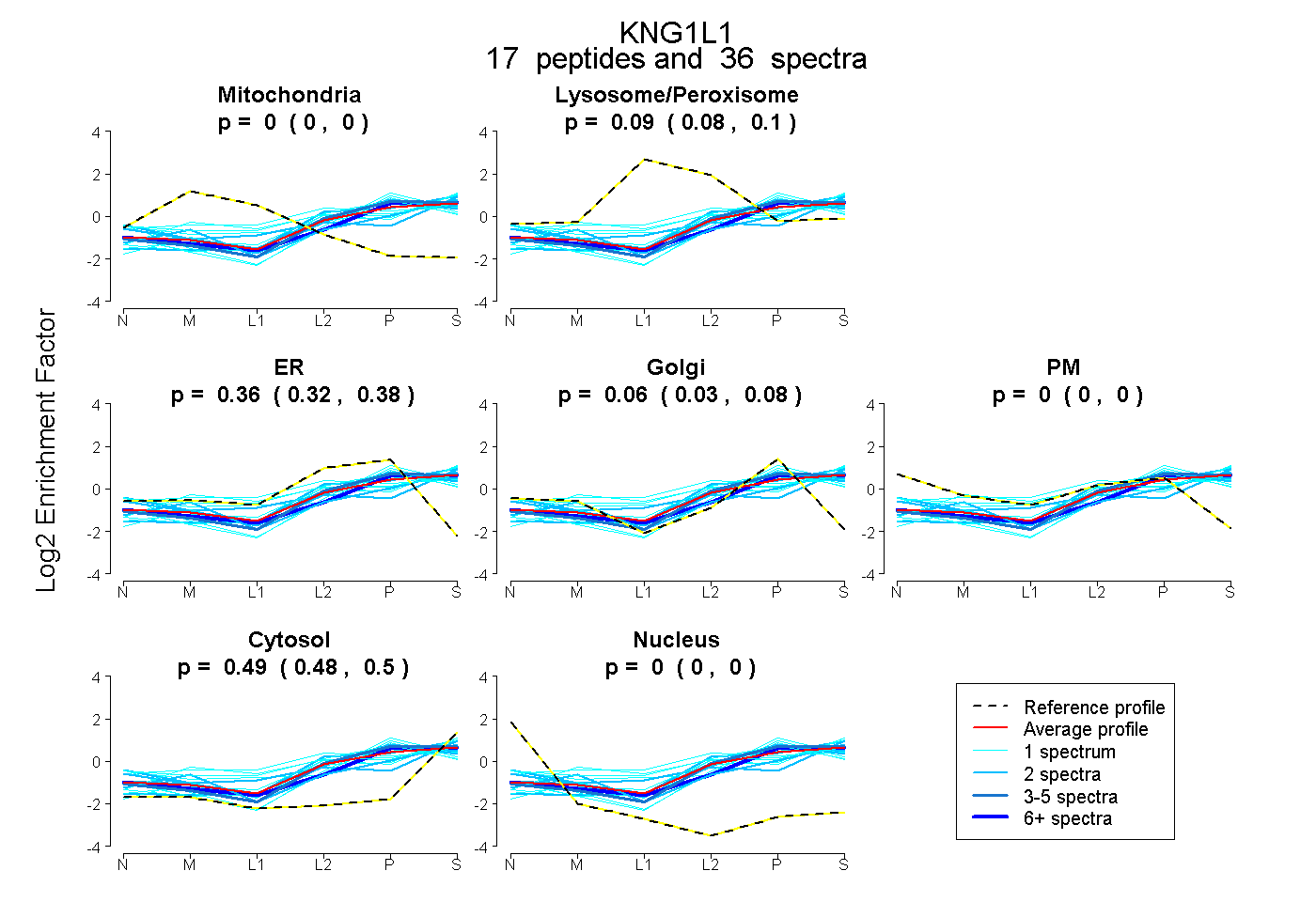 |
0.000 0.000 | 0.000 |
0.094 0.083 | 0.104 |
0.357 0.324 | 0.383 |
0.059 0.031 | 0.083 |
0.000 0.000 | 0.000 |
0.490 0.480 | 0.498 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
310 spectra |
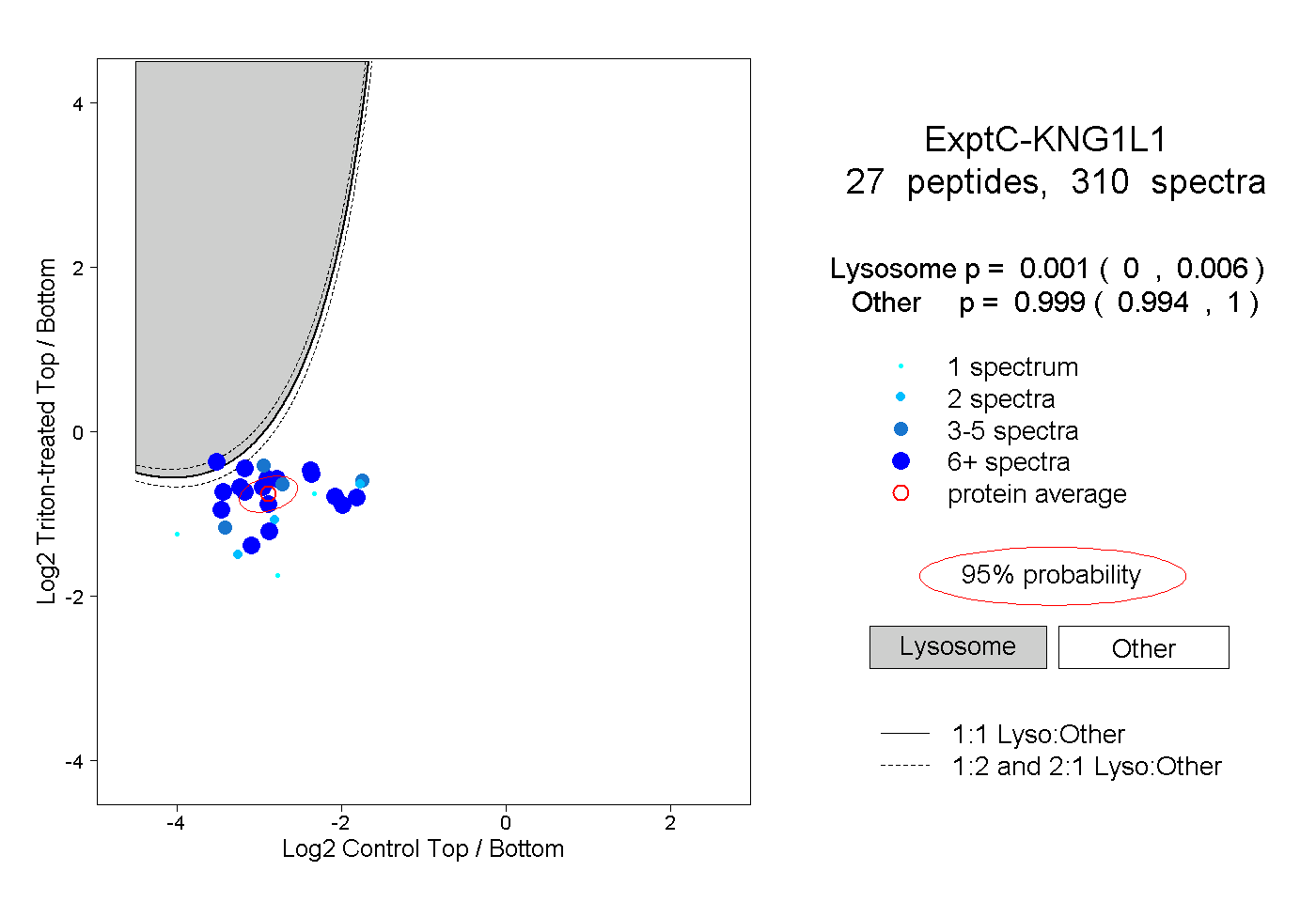 |
0.001 0.000 | 0.006 |
0.999 0.994 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
30 spectra |
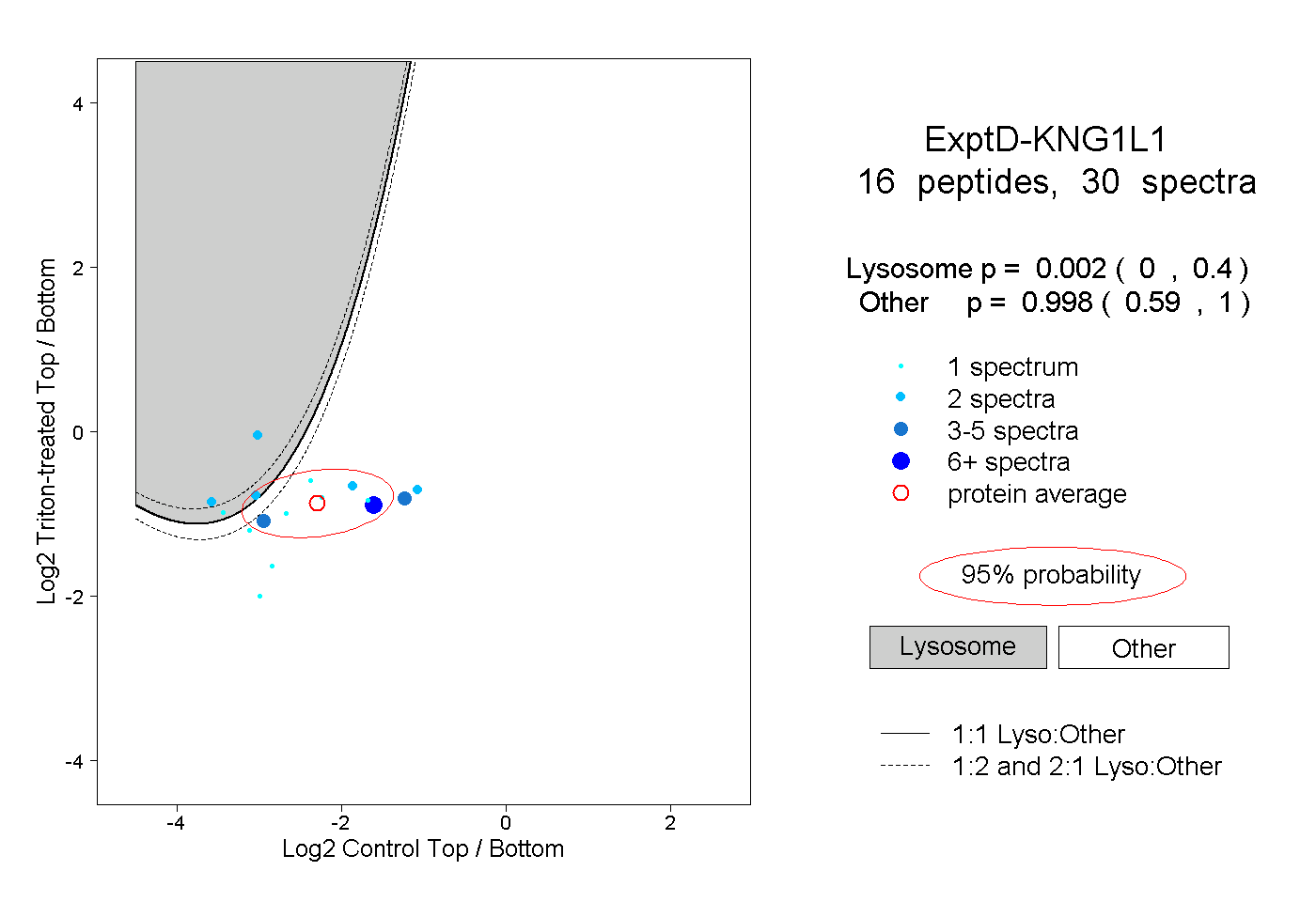 |
0.002 0.000 | 0.400 |
0.998 0.590 | 1.000 |