peptides
spectra
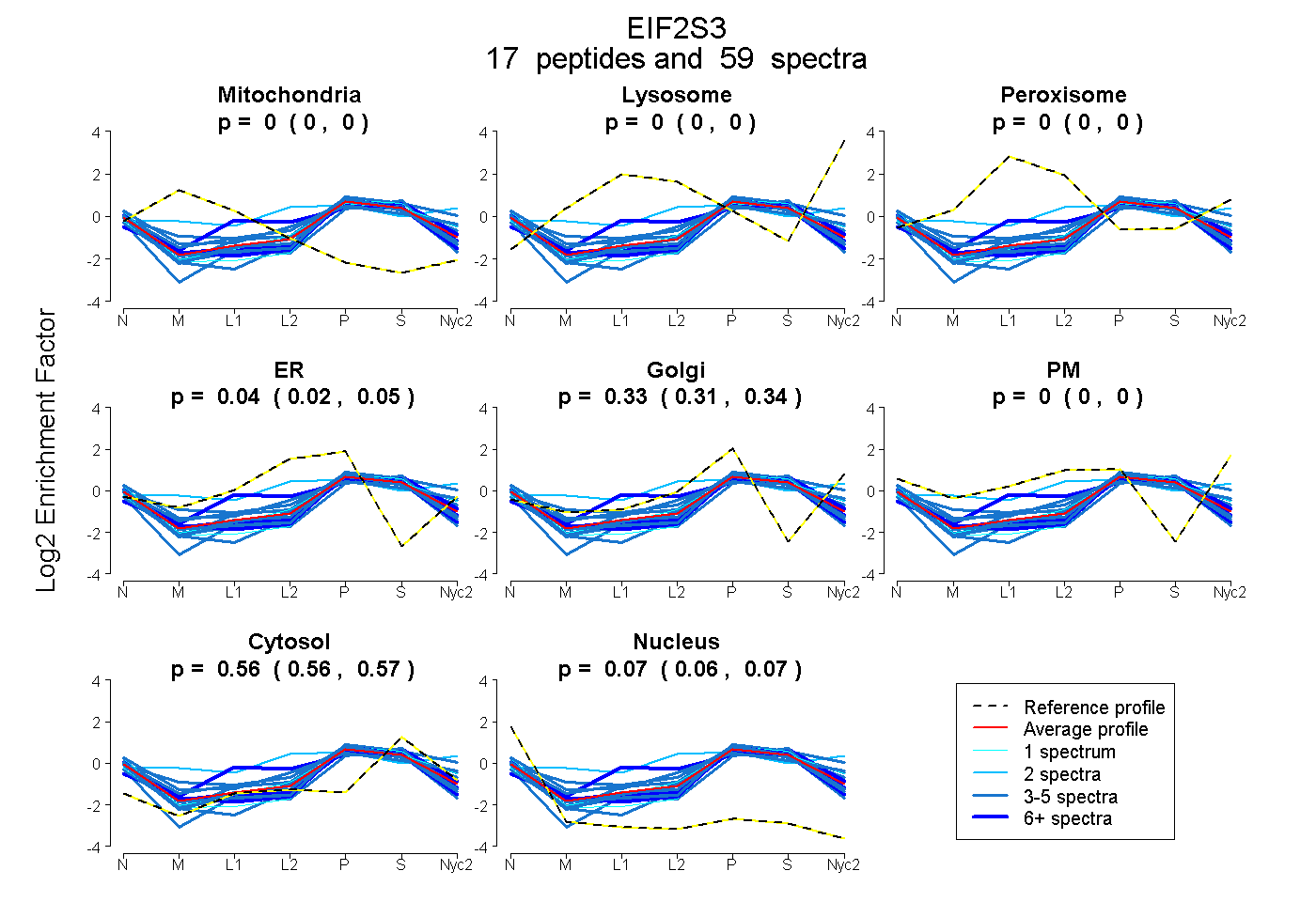
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.024 | 0.053
0.312 | 0.344
0.000 | 0.000
0.560 | 0.565
0.063 | 0.070
peptides
spectra
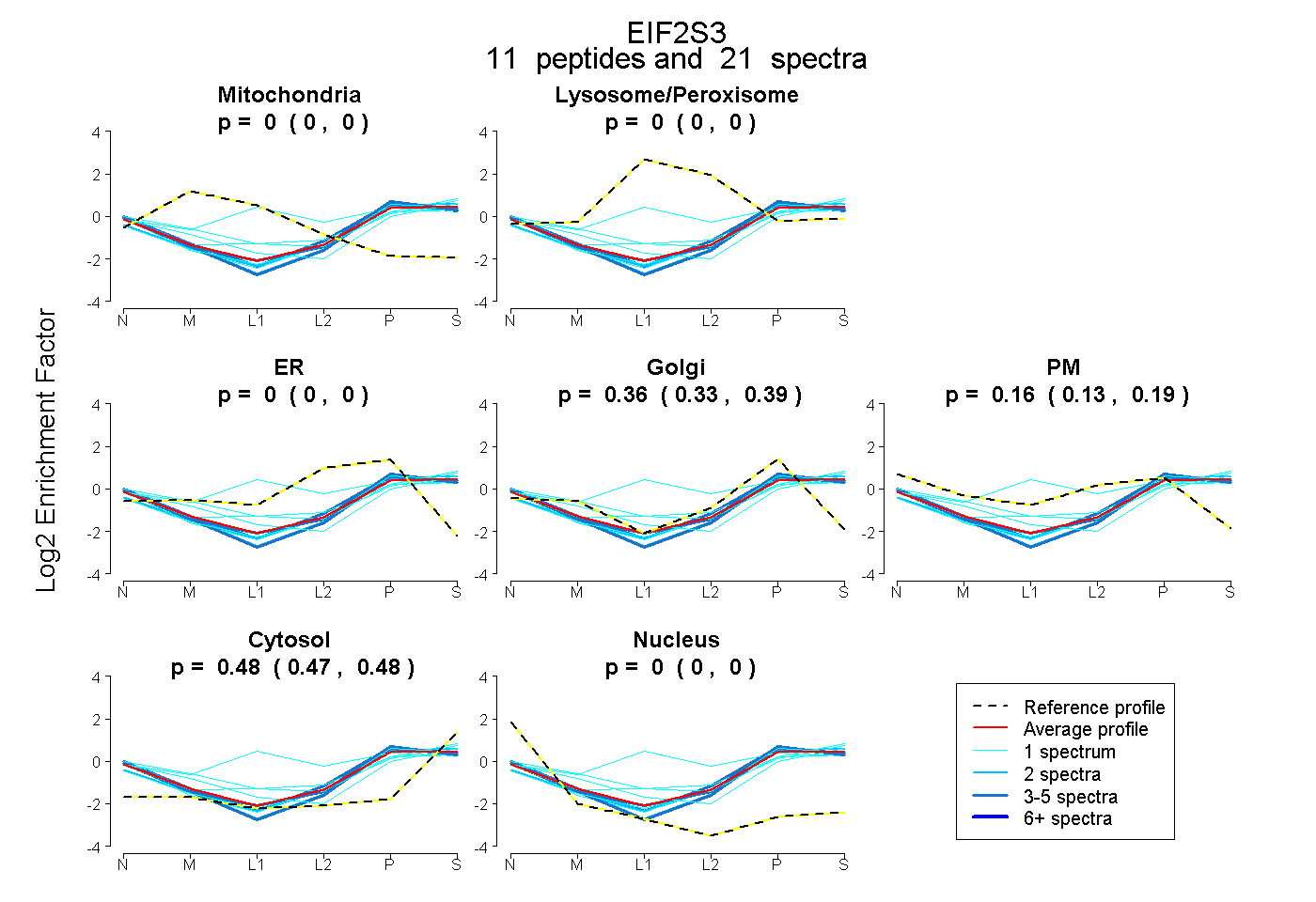
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.333 | 0.386
0.134 | 0.187
0.471 | 0.482
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
59 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.041 0.024 | 0.053 |
0.329 0.312 | 0.344 |
0.000 0.000 | 0.000 |
0.563 0.560 | 0.565 |
0.067 0.063 | 0.070 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
21 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.360 0.333 | 0.386 |
0.163 0.134 | 0.187 |
0.477 0.471 | 0.482 |
0.000 0.000 | 0.000 |
| 1 spectrum, VGQEIEVRPGIVSK | 0.000 | 0.000 | 0.000 | 0.214 | 0.220 | 0.549 | 0.016 | |||
| 1 spectrum, LMCKPIFSK | 0.000 | 0.000 | 0.000 | 0.356 | 0.061 | 0.583 | 0.000 | |||
| 2 spectra, HILILQNK | 0.000 | 0.000 | 0.000 | 0.484 | 0.004 | 0.512 | 0.000 | |||
| 1 spectrum, QATINIGTIGHVAHGK | 0.000 | 0.070 | 0.000 | 0.154 | 0.366 | 0.410 | 0.000 | |||
| 1 spectrum, YNIEVVCEYIVK | 0.000 | 0.125 | 0.000 | 0.422 | 0.034 | 0.419 | 0.000 | |||
| 1 spectrum, LTPLSHEVISR | 0.000 | 0.481 | 0.000 | 0.270 | 0.023 | 0.225 | 0.000 | |||
| 4 spectra, LIGWGQIR | 0.000 | 0.000 | 0.000 | 0.529 | 0.000 | 0.446 | 0.025 | |||
| 4 spectra, QDLATLDVTK | 0.000 | 0.000 | 0.000 | 0.487 | 0.087 | 0.425 | 0.000 | |||
| 2 spectra, IDPTLCR | 0.000 | 0.000 | 0.000 | 0.522 | 0.000 | 0.449 | 0.028 | |||
| 3 spectra, DFTSEPR | 0.000 | 0.000 | 0.000 | 0.468 | 0.122 | 0.410 | 0.000 | |||
| 1 spectrum, LDDPSCPRPECYR | 0.000 | 0.000 | 0.000 | 0.306 | 0.133 | 0.561 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
54 spectra |
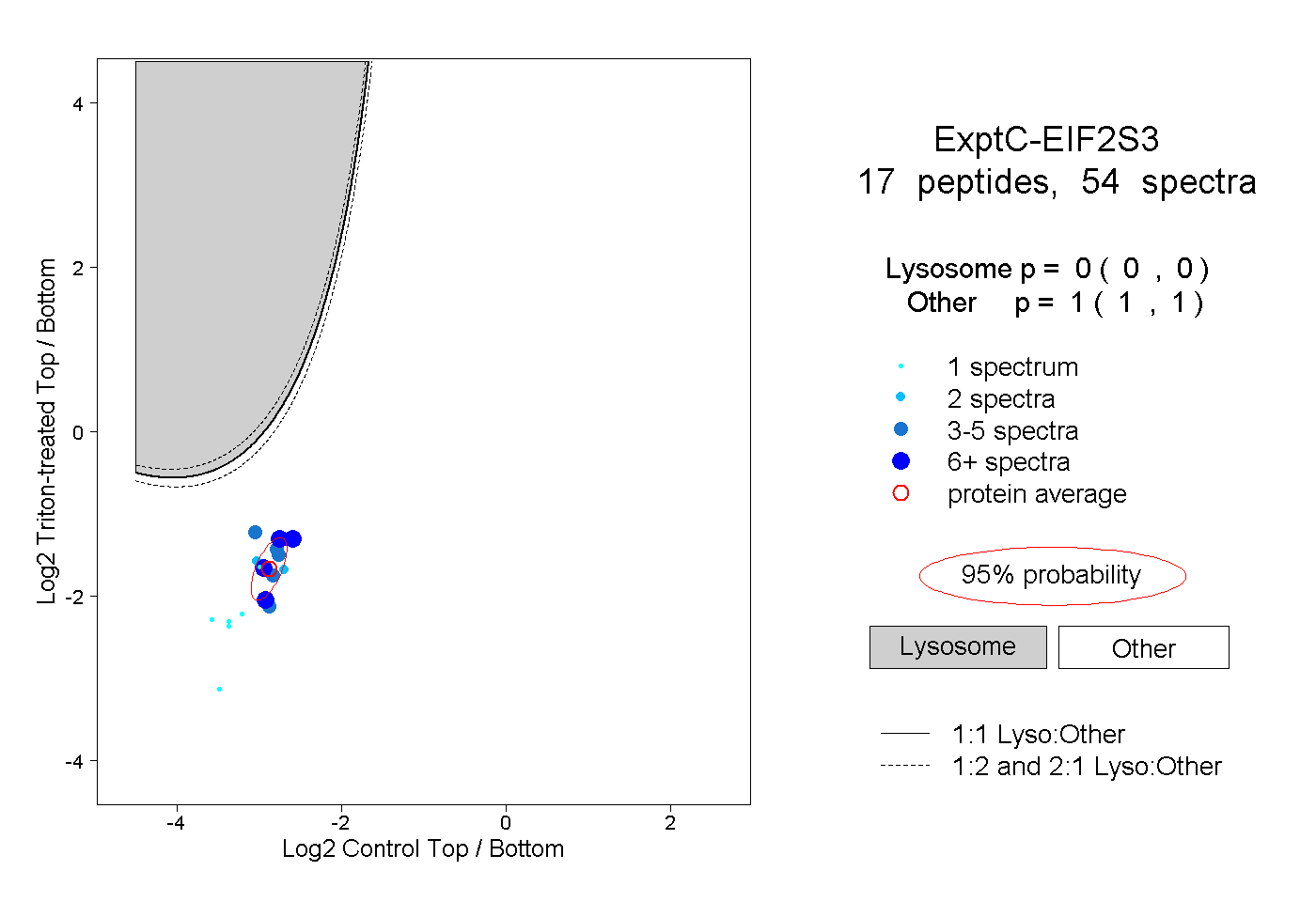 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
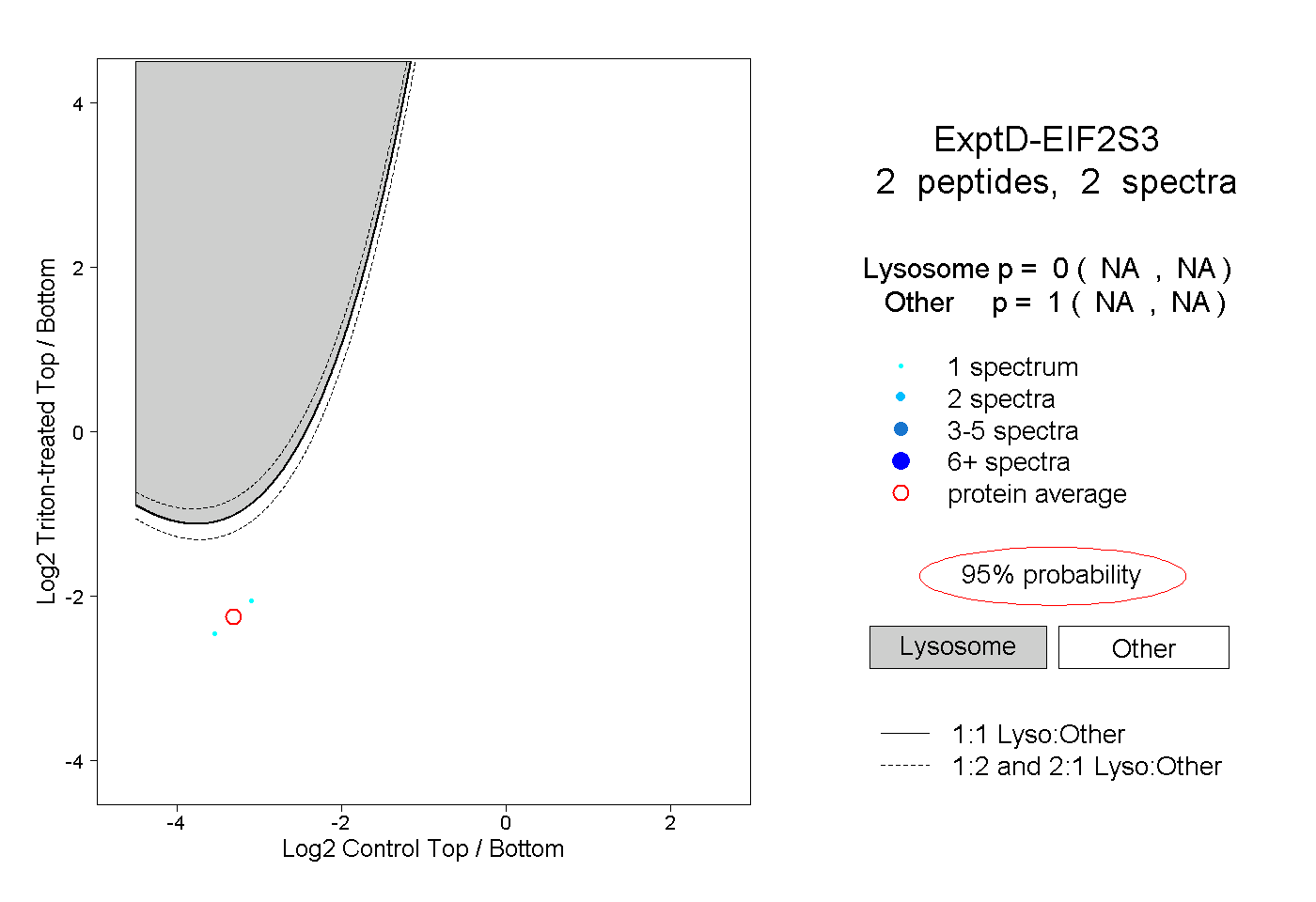 |
0.000 NA | NA |
1.000 NA | NA |