peptides
spectra
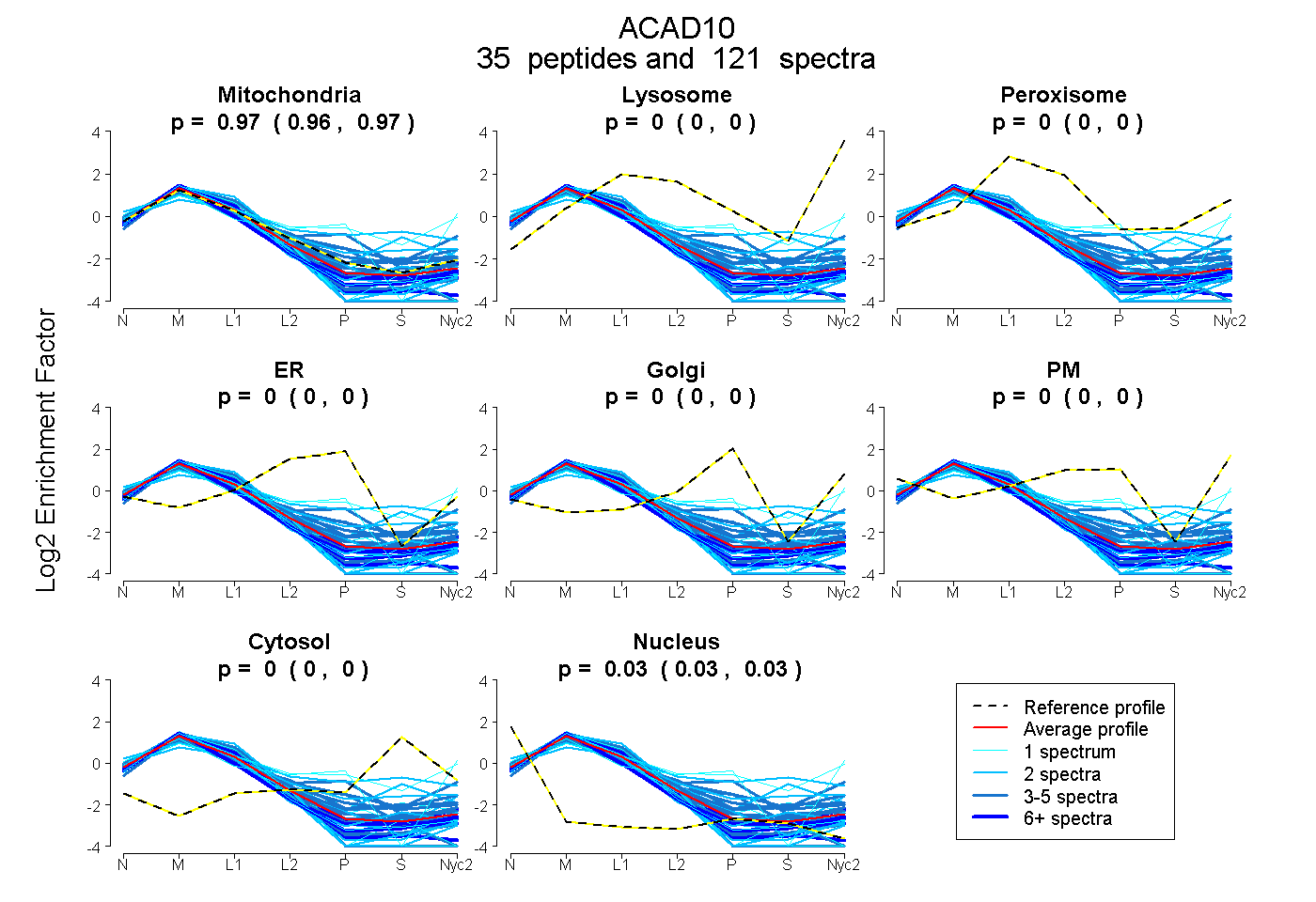
0.965 | 0.968
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.032 | 0.035
peptides
spectra
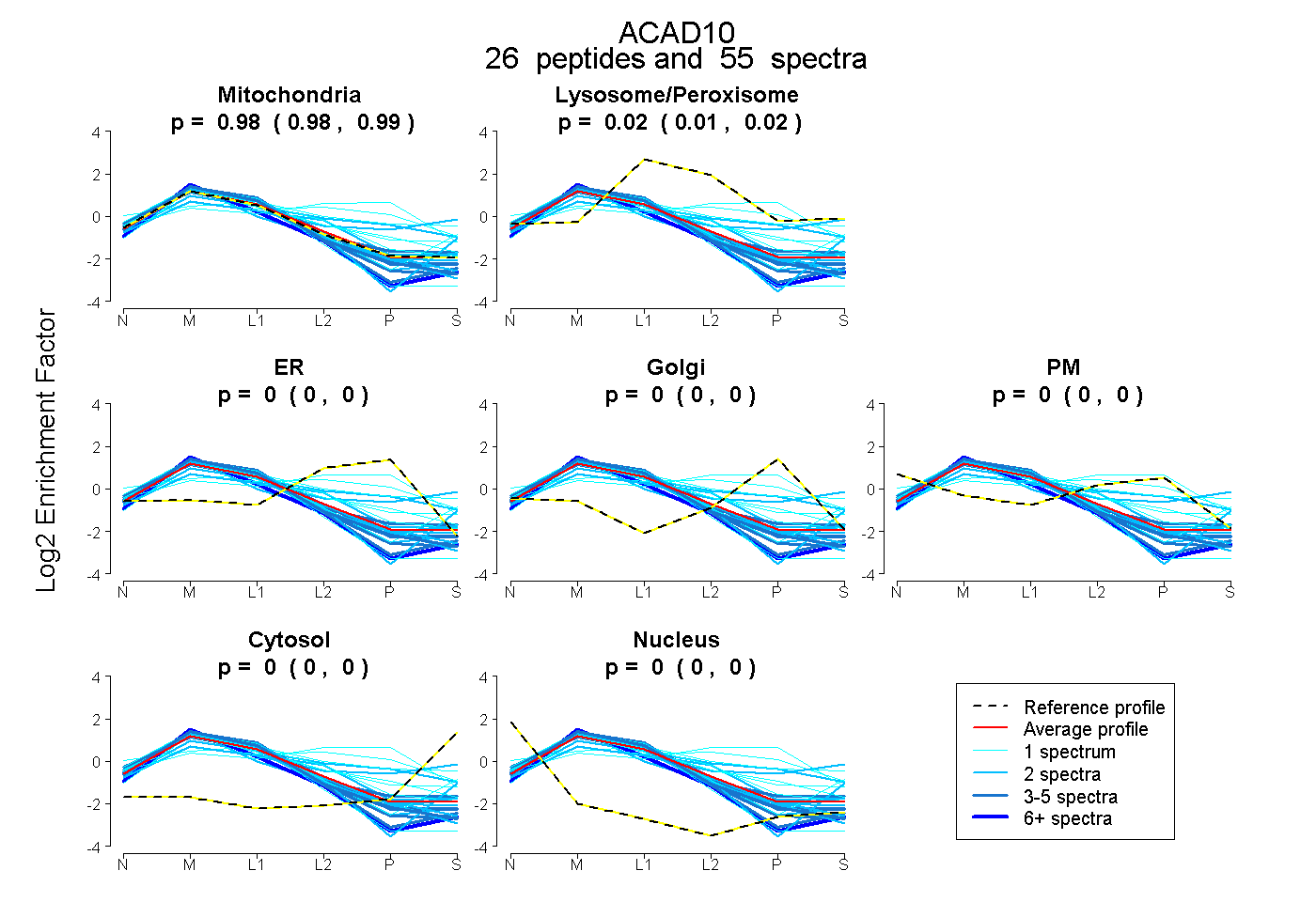
0.975 | 0.988
0.011 | 0.023
0.000 | 0.002
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
121 spectra |
 |
0.966 0.965 | 0.968 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.034 0.032 | 0.035 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
55 spectra |
 |
0.983 0.975 | 0.988 |
0.017 0.011 | 0.023 |
0.000 0.000 | 0.002 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, ELEDLLGFPLHGGVPNTRPVR | 0.381 | 0.295 | 0.000 | 0.115 | 0.000 | 0.210 | 0.000 | |||
| 2 spectra, VAAILQGVYK | 0.933 | 0.000 | 0.000 | 0.000 | 0.000 | 0.067 | 0.000 | |||
| 4 spectra, FLEEFGR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VDNPETAVK | 0.841 | 0.049 | 0.000 | 0.000 | 0.000 | 0.110 | 0.000 | |||
| 1 spectrum, GGLIISPEGLSPR | 0.142 | 0.324 | 0.275 | 0.259 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VAASLGIR | 0.941 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.059 | |||
| 2 spectra, ALELMK | 0.895 | 0.049 | 0.056 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VASALVAR | 0.726 | 0.112 | 0.062 | 0.057 | 0.042 | 0.000 | 0.000 | |||
| 3 spectra, LQEPAAPR | 0.906 | 0.034 | 0.000 | 0.000 | 0.030 | 0.014 | 0.017 | |||
| 2 spectra, LLQFDHGQSNPTYYIR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, WLAPLLEGR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EAIYTAMNQVLCR | 0.263 | 0.383 | 0.000 | 0.289 | 0.065 | 0.000 | 0.000 | |||
| 2 spectra, AAETSSIPAMER | 0.965 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.035 | |||
| 2 spectra, TDPQAPR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, QFPVMTQAVSQIR | 0.717 | 0.137 | 0.049 | 0.032 | 0.000 | 0.065 | 0.000 | |||
| 2 spectra, AAHLMDVAGNK | 0.480 | 0.283 | 0.000 | 0.221 | 0.000 | 0.016 | 0.000 | |||
| 2 spectra, AAALEIAMIK | 0.959 | 0.000 | 0.000 | 0.000 | 0.000 | 0.041 | 0.000 | |||
| 1 spectrum, AEGLQTAVLTNNFLLSNGK | 0.274 | 0.354 | 0.000 | 0.000 | 0.263 | 0.108 | 0.000 | |||
| 2 spectra, VIRPLSVFGLEDPPGGHGEVQFK | 0.976 | 0.024 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, ENILLGPGR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LIGYSER | 0.969 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.031 | |||
| 6 spectra, AMPATTTLTR | 0.961 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.039 | |||
| 3 spectra, GFEIAQGR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TTVVHGDFR | 0.852 | 0.095 | 0.053 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, IFQLCLQR | 0.954 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.046 | |||
| 2 spectra, SFLPLDR | 0.998 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.002 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
537 spectra |
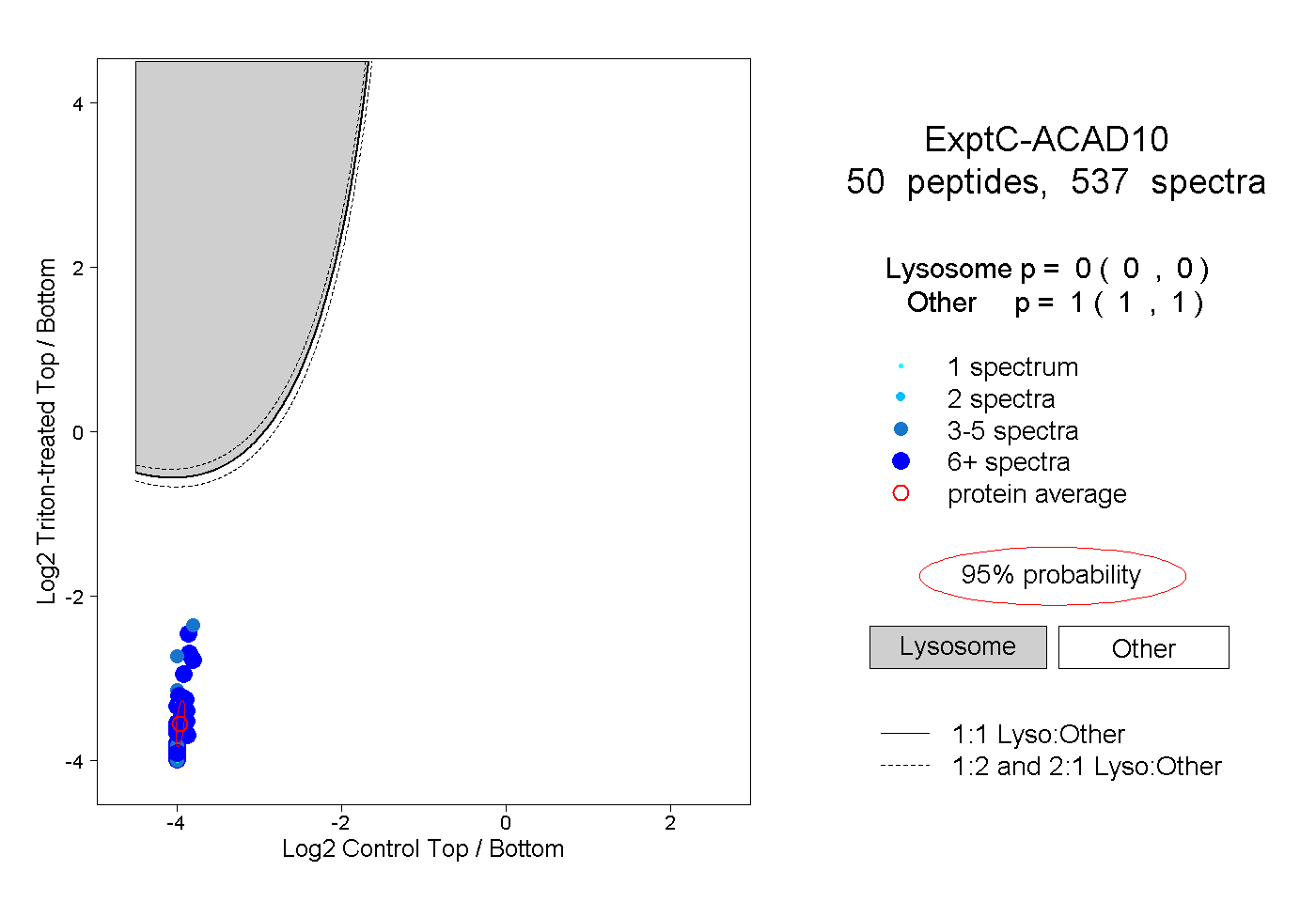 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
42 spectra |
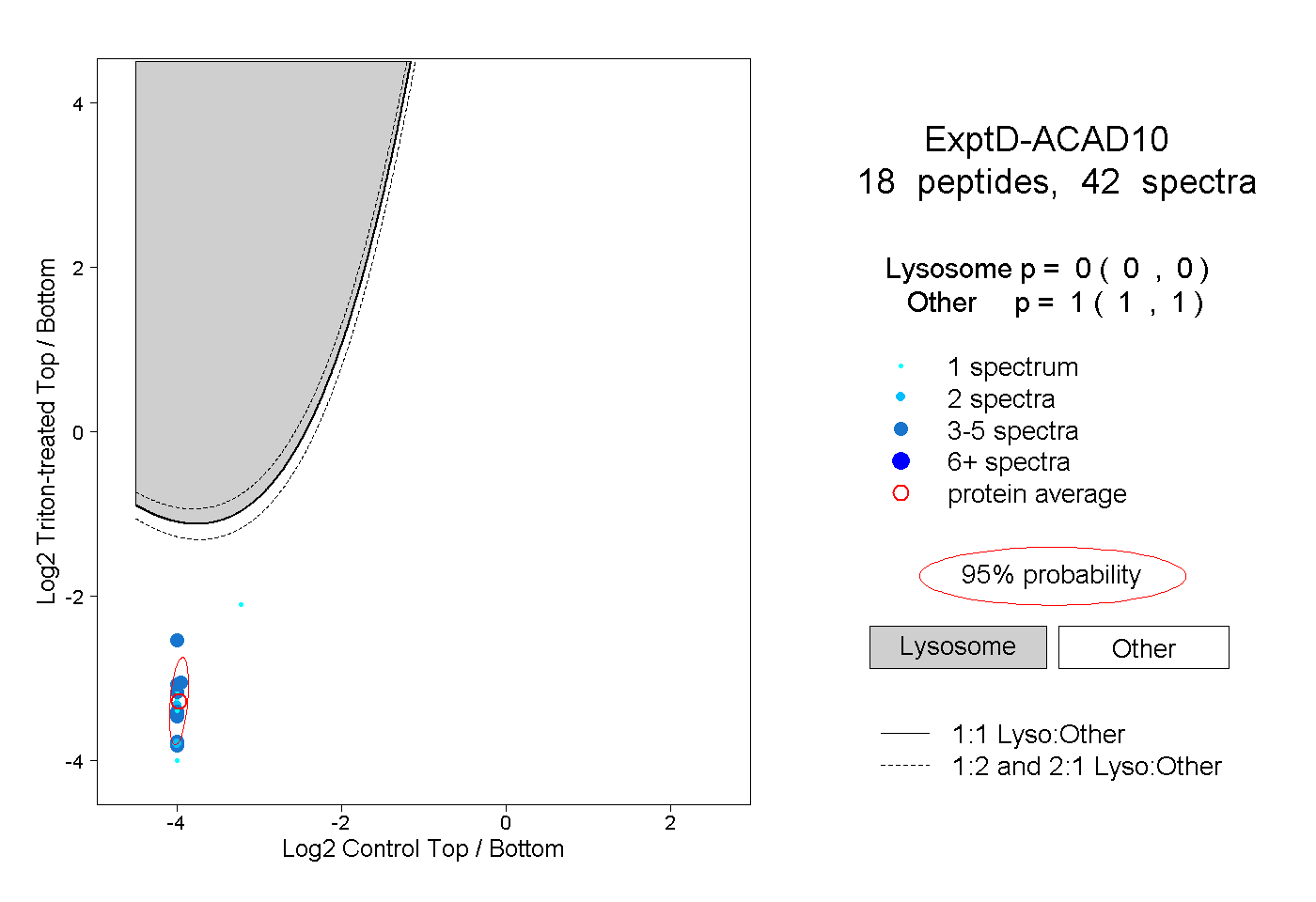 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |