peptides
spectra
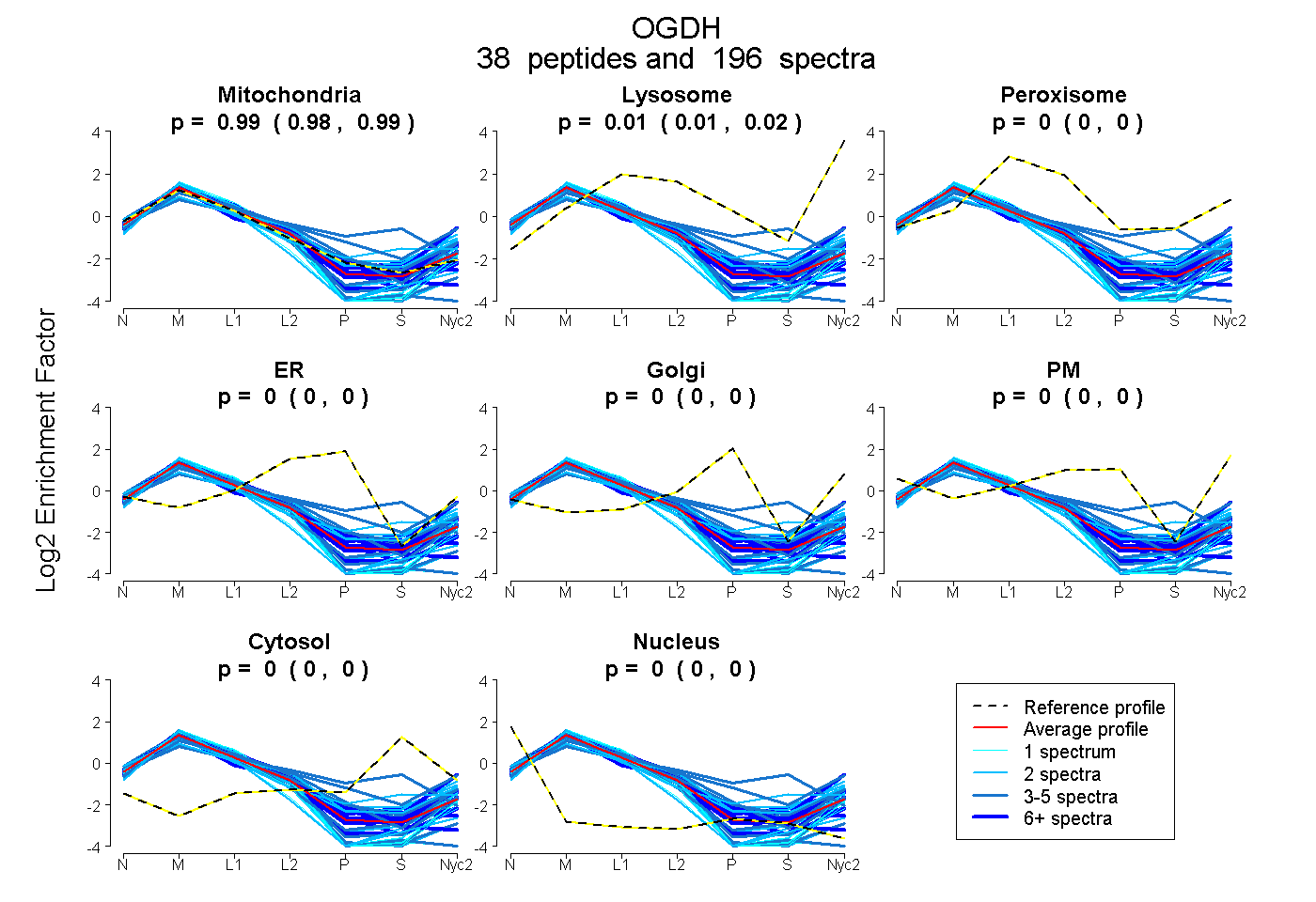
0.983 | 0.987
0.012 | 0.016
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
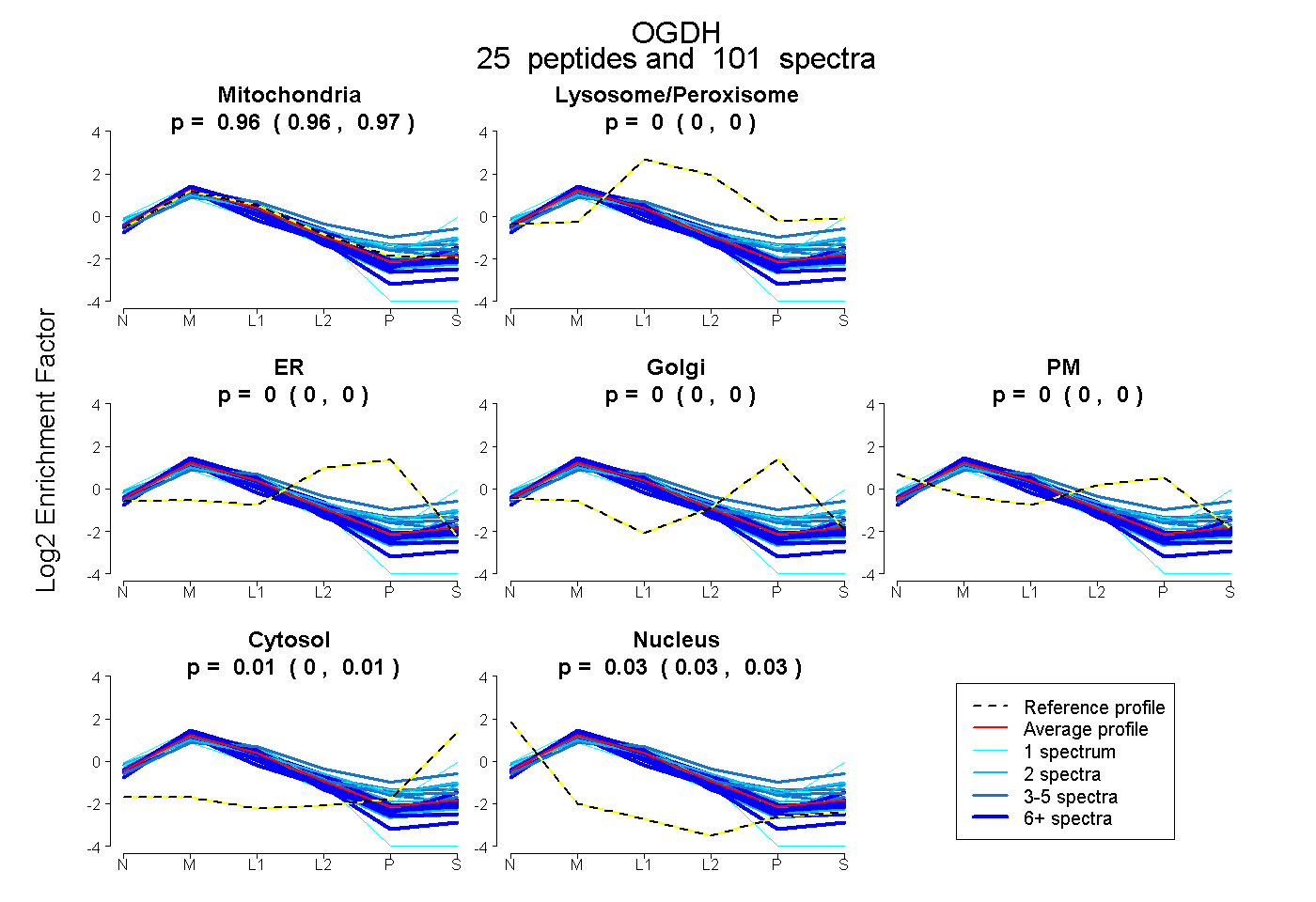
0.962 | 0.966
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.004 | 0.012
0.025 | 0.030
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
196 spectra |
 |
0.985 0.983 | 0.987 |
0.015 0.012 | 0.016 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
101 spectra |
 |
0.964 0.962 | 0.966 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.008 0.004 | 0.012 |
0.028 0.025 | 0.030 |
| 8 spectra, SWDIFFR | 0.937 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.063 | |||
| 2 spectra, FLDTAFDLDAFK | 0.997 | 0.000 | 0.003 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, KPLIVFTPK | 0.877 | 0.013 | 0.000 | 0.000 | 0.110 | 0.000 | 0.000 | |||
| 3 spectra, IEQLSPFPFDLLLK | 0.808 | 0.047 | 0.000 | 0.000 | 0.018 | 0.127 | 0.000 | |||
| 6 spectra, QILLPFR | 0.950 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.050 | |||
| 2 spectra, ICEEAFTR | 0.791 | 0.080 | 0.000 | 0.000 | 0.000 | 0.130 | 0.000 | |||
| 3 spectra, ELVTNR | 0.986 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.014 | |||
| 3 spectra, TSFDEMLPGTHFQR | 0.553 | 0.282 | 0.000 | 0.040 | 0.000 | 0.124 | 0.000 | |||
| 4 spectra, LIFCTGK | 0.961 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.039 | |||
| 1 spectrum, DVVVDLVCYR | 0.888 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.112 | |||
| 3 spectra, VAAEWR | 0.872 | 0.000 | 0.000 | 0.000 | 0.076 | 0.052 | 0.000 | |||
| 2 spectra, LNVLANVIR | 0.994 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.006 | |||
| 9 spectra, FEEFLQR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VIPEDGPAAQNPDK | 0.727 | 0.117 | 0.000 | 0.000 | 0.045 | 0.111 | 0.000 | |||
| 7 spectra, LSGQDVER | 0.937 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.063 | |||
| 4 spectra, AKPVWYAGR | 0.754 | 0.094 | 0.000 | 0.000 | 0.099 | 0.054 | 0.000 | |||
| 1 spectrum, HWLDSPWPGFFTLDGQPR | 0.648 | 0.023 | 0.000 | 0.000 | 0.000 | 0.329 | 0.000 | |||
| 9 spectra, DMAEEVAITR | 0.923 | 0.000 | 0.000 | 0.000 | 0.000 | 0.055 | 0.023 | |||
| 4 spectra, EGIHVR | 0.940 | 0.000 | 0.035 | 0.025 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, FGLEGCEVLIPALK | 0.846 | 0.000 | 0.000 | 0.000 | 0.000 | 0.093 | 0.061 | |||
| 6 spectra, VYYDLTR | 0.936 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.064 | |||
| 1 spectrum, QKPVLQK | 0.835 | 0.061 | 0.000 | 0.011 | 0.074 | 0.007 | 0.012 | |||
| 8 spectra, LVEDHLAVQSLIR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, SSPYPTDVAR | 0.847 | 0.000 | 0.000 | 0.000 | 0.000 | 0.101 | 0.052 | |||
| 3 spectra, ELEQIFCQFDSK | 0.971 | 0.000 | 0.000 | 0.000 | 0.000 | 0.029 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
777 spectra |
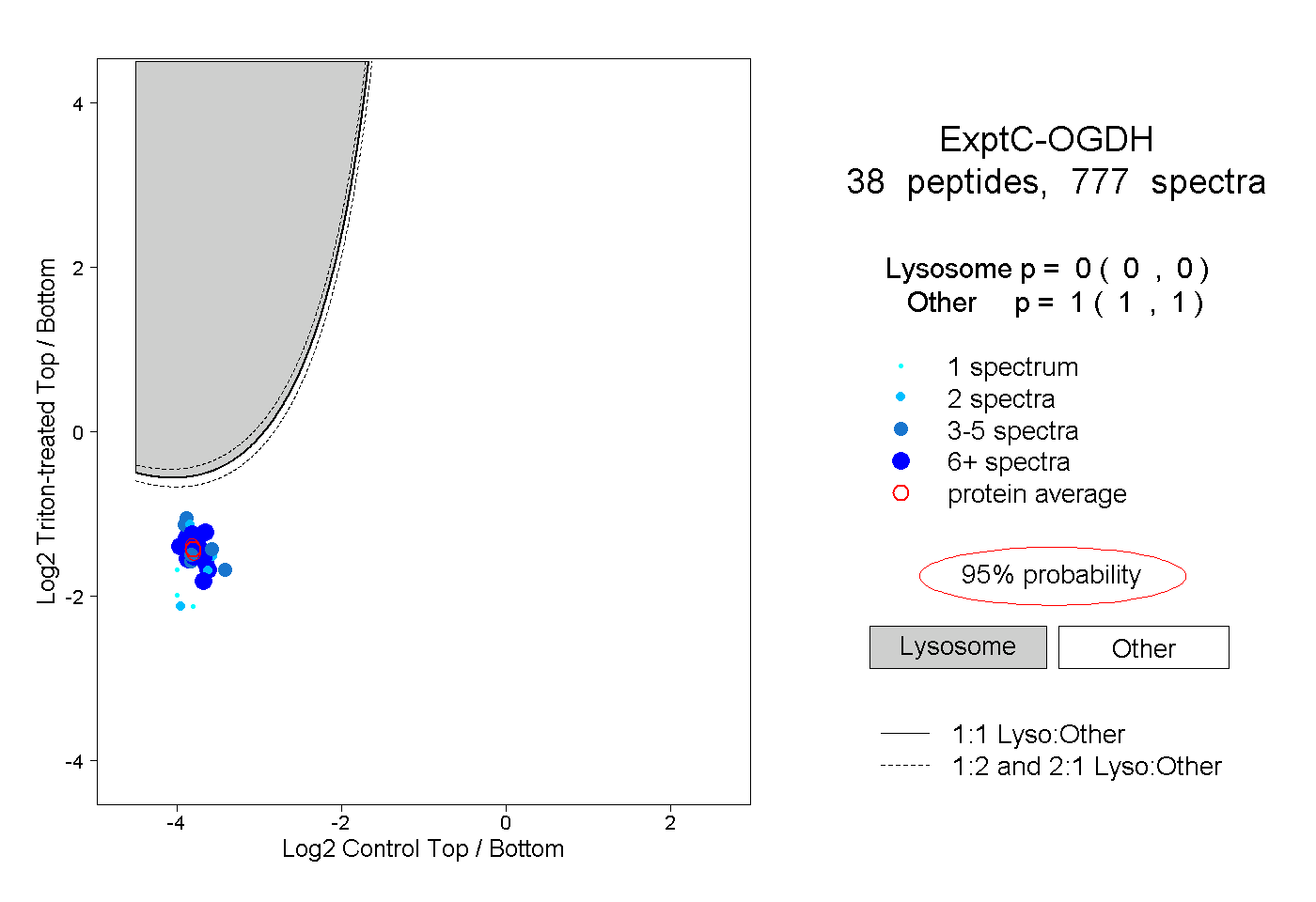 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
70 spectra |
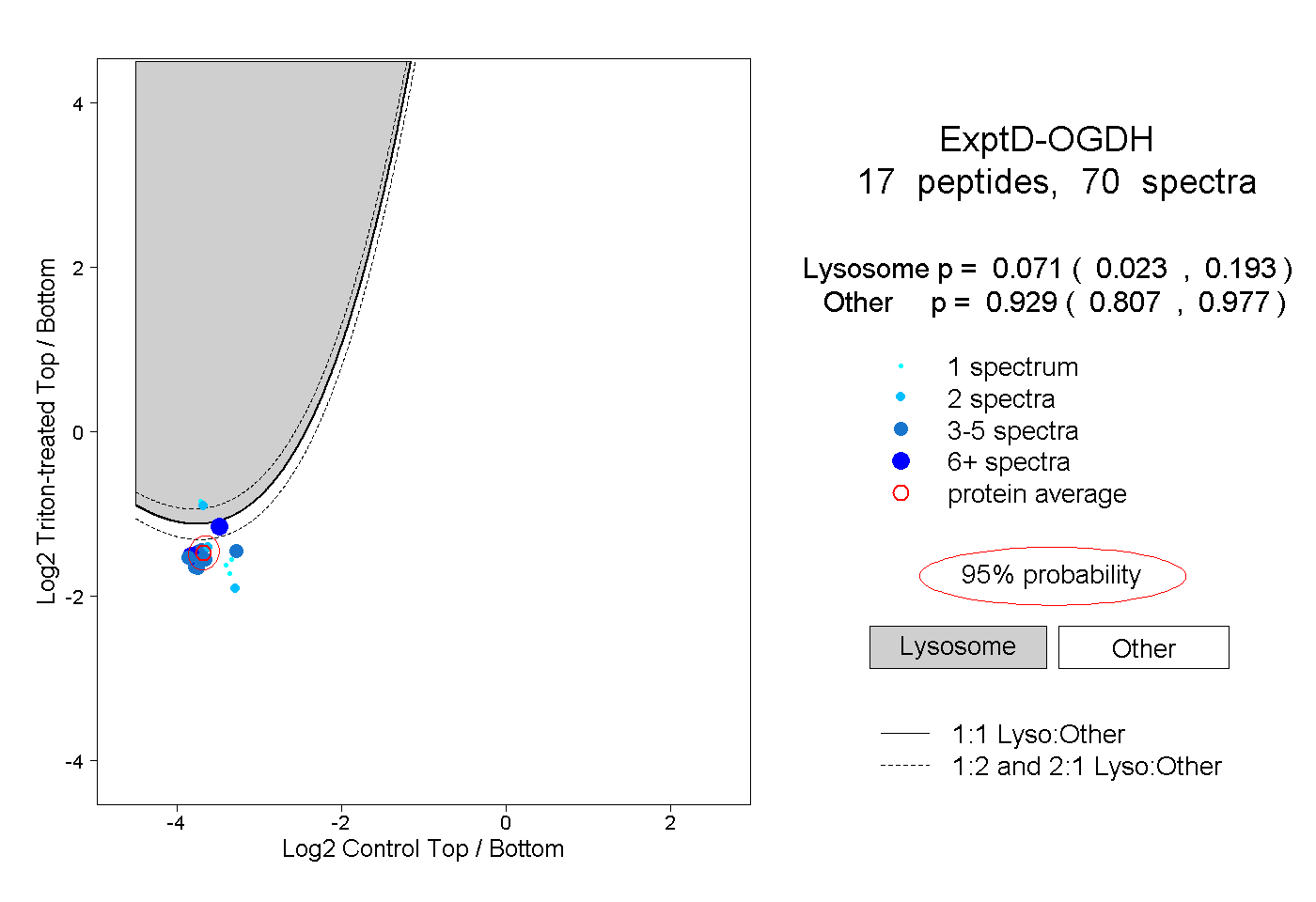 |
0.071 0.023 | 0.193 |
0.929 0.807 | 0.977 |